Упражнение 1
|
|
|
| DNA and protein in ribbons model | DNA in wireframe model |
|
|
|
| All ribose oxygenes (set1) | All phosphate oxygenes (set2) |
|
|
| ALl nitrogenes (set3) |
Упражнение 2
Контакты атомов белка с |
Полярные |
Неполярные |
Всего |
остатками 2'-дезоксирибозы |
17 |
93 |
110 |
остатками фосфорной кислоты |
21 |
80 |
101 |
остатками азотистых оснований со стороны большой бороздки |
1 |
5 |
6 |
остатками азотистых оснований со стороны малой бороздки |
9 |
25 |
34 |
Неполярных контактов больше. Наиболее часто атомы белка контактируют с остатками 2'- дезоксирибозы
Скрипт
Упражнение 3. Получение популярной схему ДНК-белковых контактов с помощью программы nuclplot
nucplot 1i3j_old.pdb Файл получается в формате ps.
Упражнение 4.
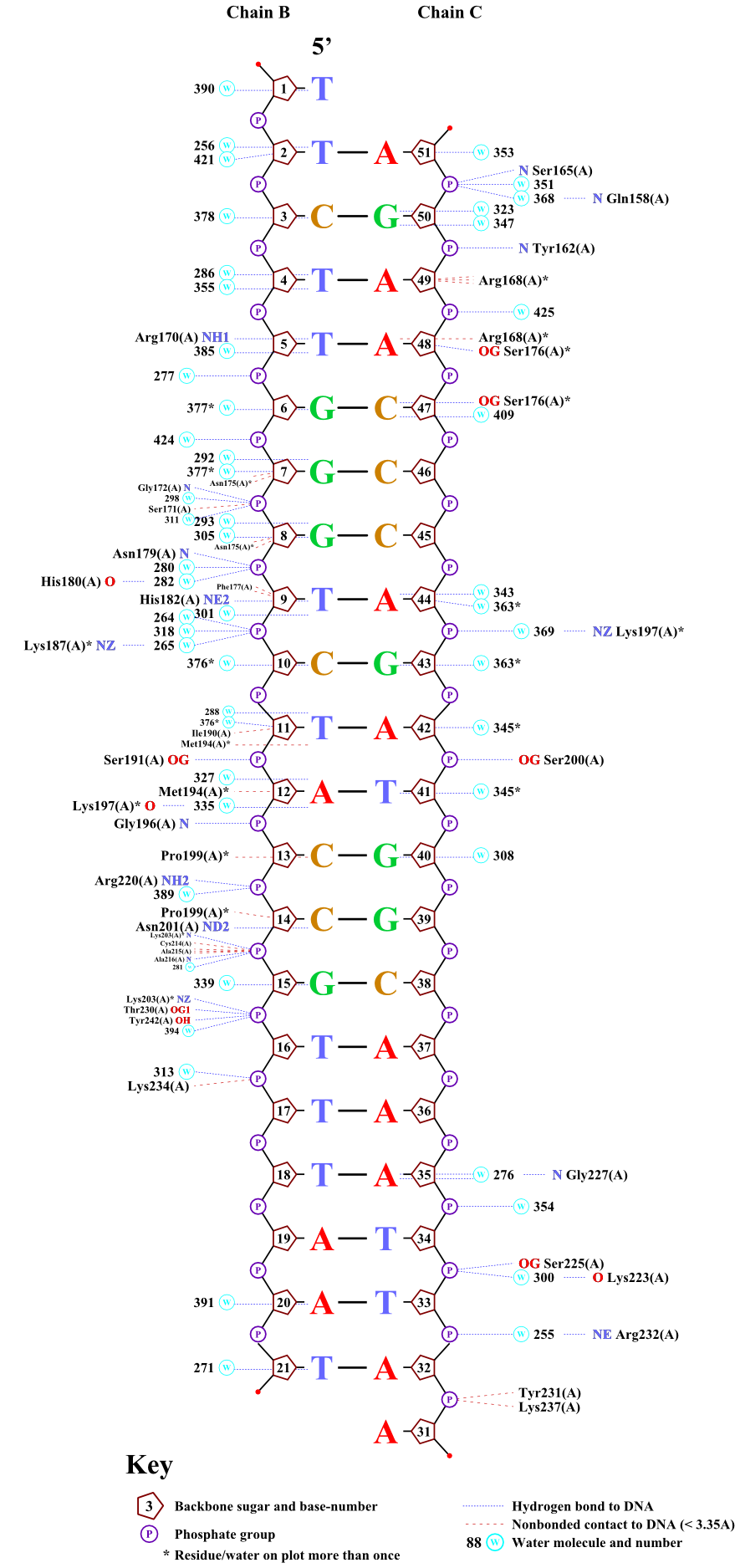
1)Выделить аминокислотный остаток с наибольшим числом указанных на схеме контактов с ДНК невозможно, так как одновременно 6 аминокислотных остатка образуют наибольшее число контактов - 2. (это остатки Lys203, Lys197, Ser176, Met194, Arg168, Asn175)
2) На мой взгляд, наиболее важный остаток для распознования последовательности ДНК - Lys197, так как он, в отличии от других остатков из пункта 1), взаимодействует с обеими цепями ДНК
На первом изображении показано взаимодействие Lys197 с ДНК через молекулы воды. При этом аминокислота сама находится практически внутри малой бороздки ДНК, и своими связями, возможно, стабилизирует пространственную структуру ДНК.
На втором изображении показано взаимодействие наиболее "контактных" с ДНК аминокислотных остатков.
Также еще в белке можно увидеть ион цинка, который взаимодействует с четырьма цистеинами (164, 151, 153, 167). Эти аминокислотные остатки непосредственно не взаимодействуют с ДНК, но при этом структура (цинковый палец) может стабилизировать комплекс ДНК-белок.
Задание 2.
Упражнение 1.
При параметрах по умолчанию получаются пустые файлы. Если изменить threshold на 15, то находится акцепторный стебль (правда, по сравнению с find_pair, со смещением в два нуклеотида.
Если изменить gap на 5, threshold на 10, match на 10, а mismatch на -1, получается выравнивание 1-28 с 31-55 нуклеотидами. Это точно не акцепторный стебль и не T-стебль. Возможно, там присутствует часть D-стебля, и часть аникодонового стебля, но, так как выравнивание с 11 гэпами, я бы таким результатам не доверяла
Если изменить gap - 5, threshold - 5, match - 5, mismatch - -1, то находится часть антикодонового стебля, но, опять-таки, выравнивание сомнительное.
Вывод - при разных параметрах хорошо находится акцепторный стебль, частично - D-стебль и антикодоновый стебль, T-петля не находится никак.
Упражнение 2
Пользовалась web-версией. Параметры не меняла ( и так получилась точная структура)
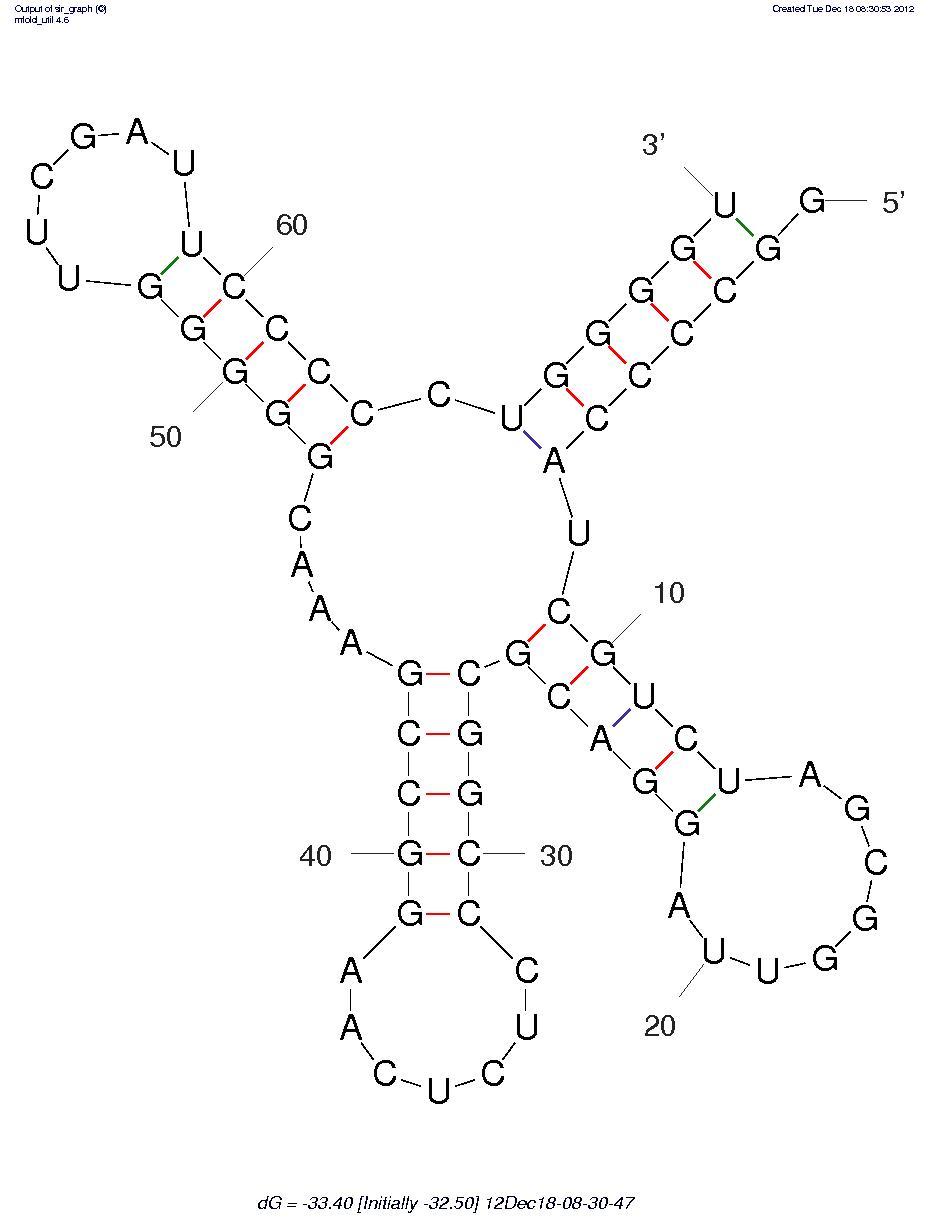
Видно, что нуклеотиды стеблей совпадают с полученными через find_pair, но нумерация почему-то смещена на 1.
| Участок структуры | Позиции в структуре (по результатам find_pair) | Результаты предсказания с помощью einverted |
Результаты предсказания по алгоритму Зукера |
| Акцепторный стебель |
5'-1-6-3' 5'-67-72-3' Всего 6 пар (5 канонических и 1 неканоническая) |
5'-3-7-3' 5'-65-69-3' 5 пар (все канонические) |
5'-2-7-3' 5'-65-70-3' 6 пар (5 канонических и 1 неканоническая) |
| D-стебель |
5'-10-13-3' 5'-22-25-3' Всего 4 пары |
3 5'-10-13-3' нашлась лишь часть, 3 канонических нуклеотида | 5'-9-13-3' 5'-22-26-3' Всего 5 пар (4 канонических и 1 неканоническая) |
| T-стебель |
5'-49-53-3' 5'-61-65-3' Всего 5 пар |
0 |
5'-48-52-3' 5'-59-63-3' Всего 5 пар |
| Антикодоновый стебель |
5'-26-32-3' 5'-38-44-3' Всего 7 пар (2 из них неканонические) |
лишь часть, 2 нуклеотида |
5'-48-52-3' 5'-59-63-3' Всего 5 пар |
| Общее число канонических пар нуклеотидов | 22 | 10 | 19 |