Учебный сайт Смирновой Виктории
Введение в PyMOL
-
Зона контакта лиганда с белком (запись 1LMP банка PDB):
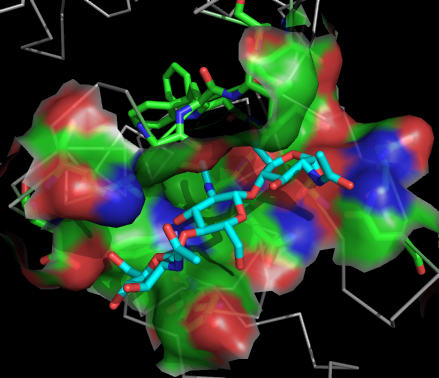
Углероды лиганда окрашены в cyan, контактирующие остатки изображены в виде sticks, показана их
поверхность.
Средствами Tcl/Tk интерфейса была проведена мутация в белке из структуры 1LMP, которая может
привести к потере связывания с лигандом - замена Glu35, с которым было возможно электростатическое
взаимодействие лиганда NDG, на Gly:
| Без мутации: |
С мутацией: |
 |
 |
Структура с заменой:
1LMP_mut.pdb
- Скрипт для анимационного ролика, где происходит совмещение белков и показывается место мутации: movie.pml
Необходимы файлы ala_valentine.pdb и 1LMP_mut.pdb.
- Поли-аланиновая последовательность в форме валентинки
(1LMP.pdb),
созданная через меню "build" PyMOL и изменение торсионных углов в режиме Editing:

- Cкрипт для построения поли-аланиновой альфа спирали длиной 100 аминкислот:
polyala.pml
© Smirnova Victoriya, 2011



