Визуализация деревьев с паралогичными и ортологичными белками
Протеомы выбранных бактерий сложила в один файл, проиндексировала его, и затем запустила blastp.
Фрагмент выдачи blastp
CLPX_MOOTA Q2RL30 ATP-dependent Clp protease ATP-binding subuni... 533 0.0
CLPX_CLOBH A5I6W0 ATP-dependent Clp protease ATP-binding subuni... 530 0.0
CLPX_BACSU P50866 ATP-dependent Clp protease ATP-binding subuni... 516 0.0
CLPX_LISMO Q8Y7K9 ATP-dependent Clp protease ATP-binding subuni... 511 1e-179
CLPX_STAA8 Q2FXQ7 ATP-dependent Clp protease ATP-binding subuni... 498 1e-174
CLPX_STRPN P63791 ATP-dependent Clp protease ATP-binding subuni... 486 4e-170
Q5FKR6_LACAC Q5FKR6 ATP-dependent Clp protease ATP-binding subu... 484 3e-169
CLPY_BACSU P39778 ATP-dependent protease ATPase subunit ClpY OS... 106 2e-25
HSLU_LACAC Q5FKD8 ATP-dependent protease ATPase subunit HslU OS... 101 1e-23
Q2RJP5_MOOTA Q2RJP5 ATP-dependent protease ATPase subunit HslU ... 100 4e-23
HSLU_LISMO Q8Y7J8 ATP-dependent protease ATPase subunit HslU OS... 99.8 5e-23
HSLU_STAA8 Q2FZ28 ATP-dependent protease ATPase subunit HslU OS... 98.2 2e-22
Q8Y8B1_LISMO Q8Y8B1 UVR domain-containing protein OS=Listeria m... 60.5 4e-10
CLPL_STAA8 Q2FV74 ATP-dependent Clp protease ATP-binding subuni... 57.8 3e-09
Методом Maximum Likelyhood с бутстрепом построила дерево (.nwk) в программе MEGA.
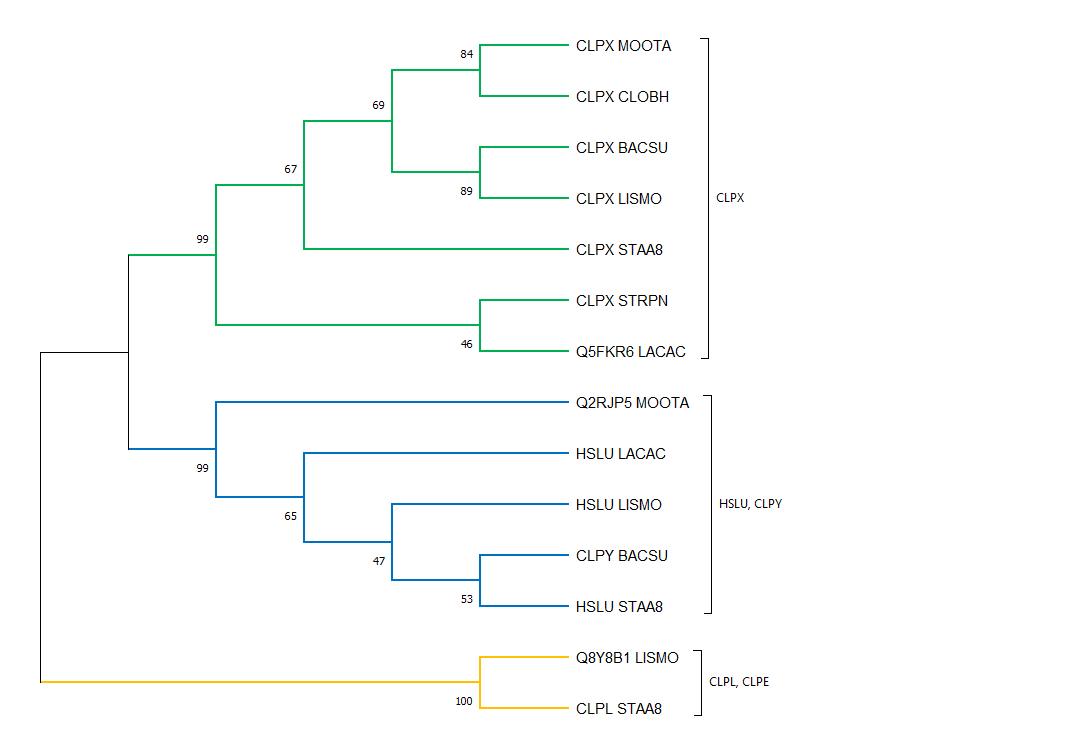
Три пары ортологов: CLPX_MOOTA & CLPX_CLOBH, HSLU_LACAC & CLPY_BACSU, CLPL_STAA8 & Q8Y8B1_LISMO;
три пары паралогов: CLPX_LISMO & HSLU_LISMO, CLPX_MOOTA & Q2RJP5_MOOTA, HSLU_STAA8 & CLPL_STAA8.
Белки с АС'шниками вместо мнемоник функции просто не аннотированы, но я проверила, что они действительно имеют отношение к этой протеазе.
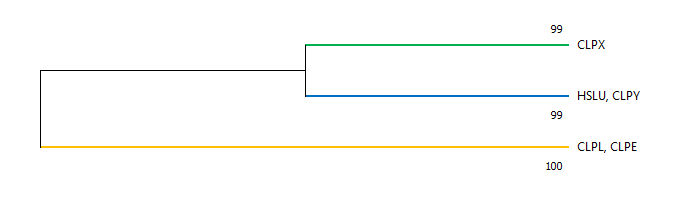
В группе CLPX по белку из каждой бактерии; с деревом из 1 практикума совпадают только самые поздние дихотомии. Группа HSLU, CLPY представлена 5 видами; ветви, отделяющие MOOTA и LACAC, совпадают с исходным деревом. В группе CLPL, CLPE всего два вида.