На главную страницу четвертого семестра
Исследование филогенетического дерева белков семейства глобинов из Crocodylidae, Xenopus и Homo sapiens.
Составление выборки аминокислотных последовательностей.
С помощью SRS в БД UniProt были найдены следующие АК последовательности:
- Белки семейства глобинов из таксонов Crocodylidae, Xenopus.Поиск проводился по названию таксона (поле Taxonomy) и идентификатору PF00042 из БД Pfam (поле DBxref_ ).
- Заданные глобины человека.
- Заданные белки внешней группы - миоглобины.
В первой части выборки не оказалось фрагментов (менее 90 а.о.) и белков из 2-х подвидов одного вида.
Всего врезультате поиска было найдено 67 последовательностей.
Затем с помощью SRS была построена матрица попарных расстояний (ClustalW в поле Launch --->DistmatP) и рассмотрены
нулевые значения. Их оказалось 6. Из каждой пары была отброшена одна из последовательностей:
| 1-я последовательность |
2-я последовательность |
Была оставлена |
| Q3B895_XENLA |
HBB1_XENLA 14 |
HBB1_XENLA 14 |
| Q5D090_XENLA |
HBA5_XENLA 8 |
HBA5_XENLA 8 |
| Q5D089_XENLA |
HBA4_XENLA 7 |
HBA4_XENLA 7 |
| Q5D093_XENLA |
HBBL_XENLA 19 |
HBBL_XENLA 19 |
| Q66KT5_XENLA |
HBB2_XENLA 17 |
HBB2_XENLA 17 |
| Q6GP50_XENLA |
HBA1_XENLA 2 |
HBA1_XENLA 2 |
Построение филогенетического дерева.
Построение дерева осуществлялось следующим образом:
- Модифицированная выборка была выравнена с помощью программы ClustalW.
- С помощью программы eprotdist была построена квадратная матрица попарных расстояний.
- По полученной матрице с помощью программы eneighbor по алгоритму ближайших
соседей (Neighbour-Joining)было получено дерево в скобочном виде.
- Редактирование дерева производилось в программе GeneMaster.
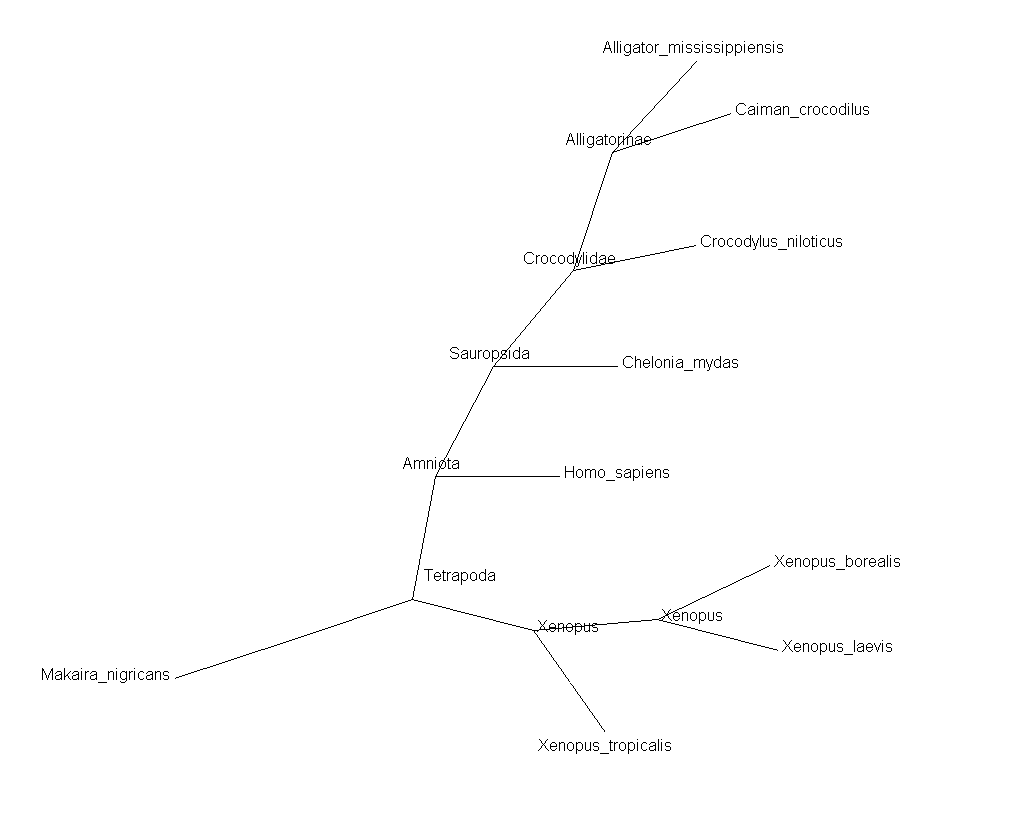
Построение таксономического дерева.
Построение дерева осуществлялось следующим образом:
- На сайте NCBI был задан список организмов
, белки которых составляли выборку.
- Полученное дерево было сохранено в формате phylip и немного отредактировано вручную.
- Визуализация дерева производилась программой GeneMaster.
Анализ дерева.
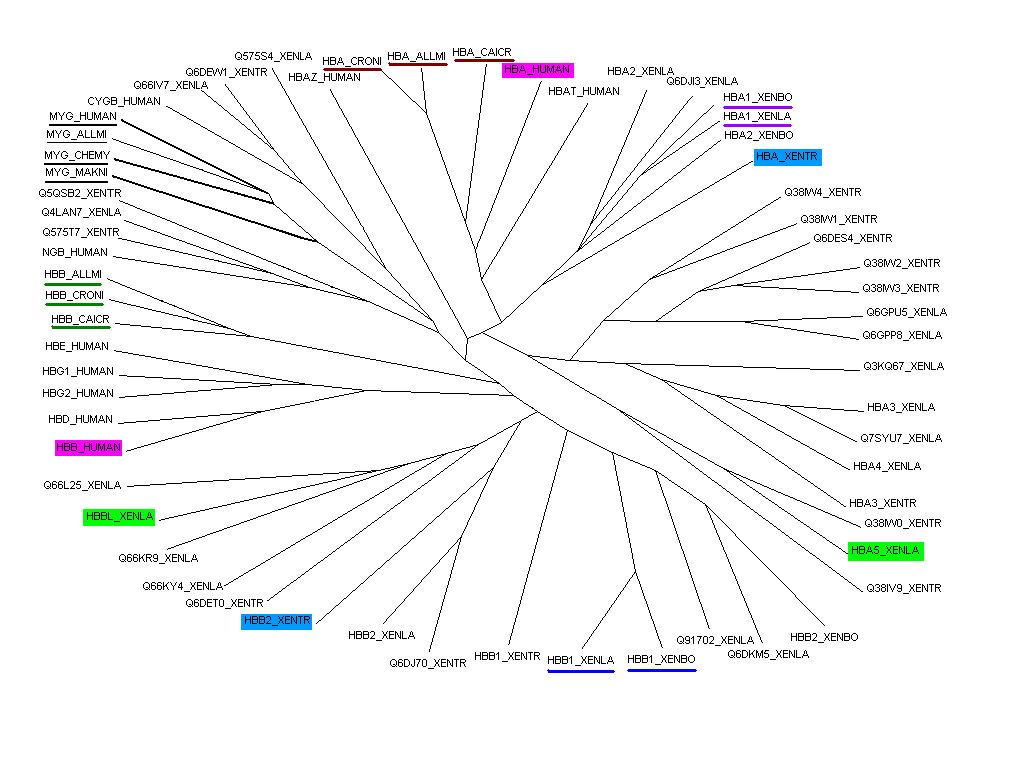
По определению ортологи - последовательности, возникшие из одного общего предшественника в процессе
видообразования.Ортологи, как правило, имеют одну и ту же функцию.
По таксономическому дереву видна близость трех представителей CROCODYLIDAE:ALLIGATOR MISSISSIPPIENSIS,
CAIMAN CROCODILUS и CROCODYLUS NILOTICUS.Данное видообразование обуславливает наличие 2-х троек ортологов (альфа и бета цепи гемоглобина),
которые подчеркнуты коричневым и зеленым цветом.Причем филогенетическое дерево свидетельствует о том,что
общий предок АLLIGATOR MISSISSIPPIENSIS и CAIMAN CROCODILUS был ближе к АLLIGATOR MISSISSIPPIENSIS.
Похожим образом дело обстоит с XENOPUS LAEVIS и XENOPUS BOREALIS.Опять видны две пары ортологов,которые подчеркнуты
синим и фиолетовым цветом.Ортологами также являются белки внешней группы,к ним,как видно,относится и
миоглобин аллигатора.
Паралоги - последовательности, возникшие из одного общего предшественника в результате дупликации одного гена в одном организме. Паралоги, как правило, имеют разные функции.
Из определения следует,что паралогами можно назвать белки из разных клад дерева,принадлежащих одному организму.
Пары паралогов на дереве заштрихованы зеленым,голубым и фиолетовым цветом.
На главную страницу четвертого семестра.