| Результат выполнения - Задание 8.
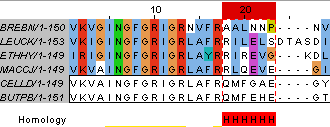
Задание 1. Используя расскраску BLOSUM62 с порогом консервативности 30 и ClustalX, и отсортировав последовательности по сходству получаем выравнивание, изображенное на Рисунок 1(а) и Рисунок 1(b).  Рисунок 1(а).Выравнивание раскраской BLOSUM62 с порогом консервативности 30.
|
||||||||||||||||||||||||
| Задание 2.
В данном выравнивании надо найти участки, где можно ожидать гомологию аминокислотных остатков этих последовательностей.
Вертикальные блоки отмечены символом В. Участки между блоками отмечены символом C, если они могут быть объединены в кластеры. Самый длинный участок, не входящих в
состав блока и кластера - Х (18-29).
Рисунок 2. Выравнивание с вертикальными блоками и кластерами. |
||||||||||||||||||||||||
Рассмотрим в блоке 1 - 17 абсолютно консервативные позиции, абсолютно функционально консервативные позиции, консервативные и функционально консервативные на 70 %.
Данные представлены в таблице ниже.
|
||||||||||||||||||||||||
По заданию добавляем в выравнивание дополнительную последовательность.После добавления получается :
 Рисунок 3. Выравнивание с дополнительной последовательностью. |
||||||||||||||||||||||||
Добавляем негомологичную последовательность LmbE family protein YP_004659637
Результат:  Рисунок 4. Выравнивание с последовательностью белка.
Совпадение консервативных позиций составляет 35% |
||||||||||||||||||||||||
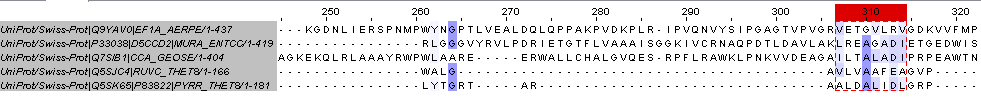
| Строим выравнивание, используя белки, с которыми работали мои однокурсники. Через идентификаторы базы данных UniProt находим последовательности и делаем выравниванием через muscle with default.
Рисунок 5. Множественное выравнивание.По этому выравниванию можно сказать, что выделить отдельные вертикальные блоки сложно, но реально. Явно заданных блоков найти нельзя, из чего следует вывод, что эти последовательности вероятно не гомологичны. |
||||||||||||||||||||||||