Практикум №11
1. Выбор семейства доменов из Pfam для анализа
Выбор домена осуществлялся случайным образом так, чтобы все удовлетворяло заданным условиям.
2. Описание семейства доменов
3. Построение карты локального сходствадвух белков с доменом семейства, но с разной доменной архитектурой
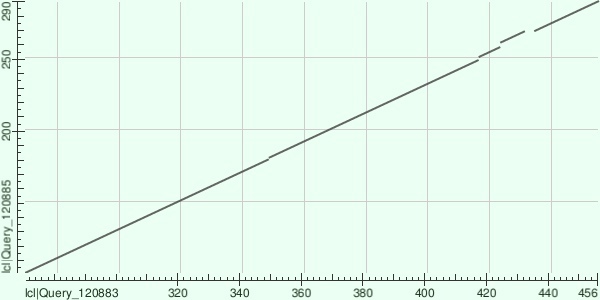
В парном локальном выравнивании использованы белки A0A2Z3JH74_9DEIO (аминокислотные остатки отложены по вертикали) и V4Y4N4_9ARCH (аминокислотные остатки отложены по горизонтали).
На карте выравниваний можно заметить, что произошло несколько делеций или вставок, самая масштабная из которых составляет 4 остатка.
Мне стало интересно, что произойдет при увеличении значения E-value. Я увеличила его до 10. Молучила такой результат:
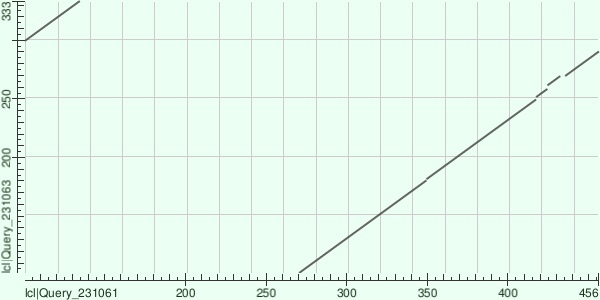
На второй карте локального сходства можно заметить дупликацию начального фрагмента участка.
4. Выделение на основании сходста двух подгрупп доменов Pfam
Выравнивание full. Для определения доменов подгруппы я использовала метод построения филогенетического дерева. Я решила поработать с двумя крупными группам, которые в проекте Jalview обозначены темно-зеленым (первая) и синим (вторая).
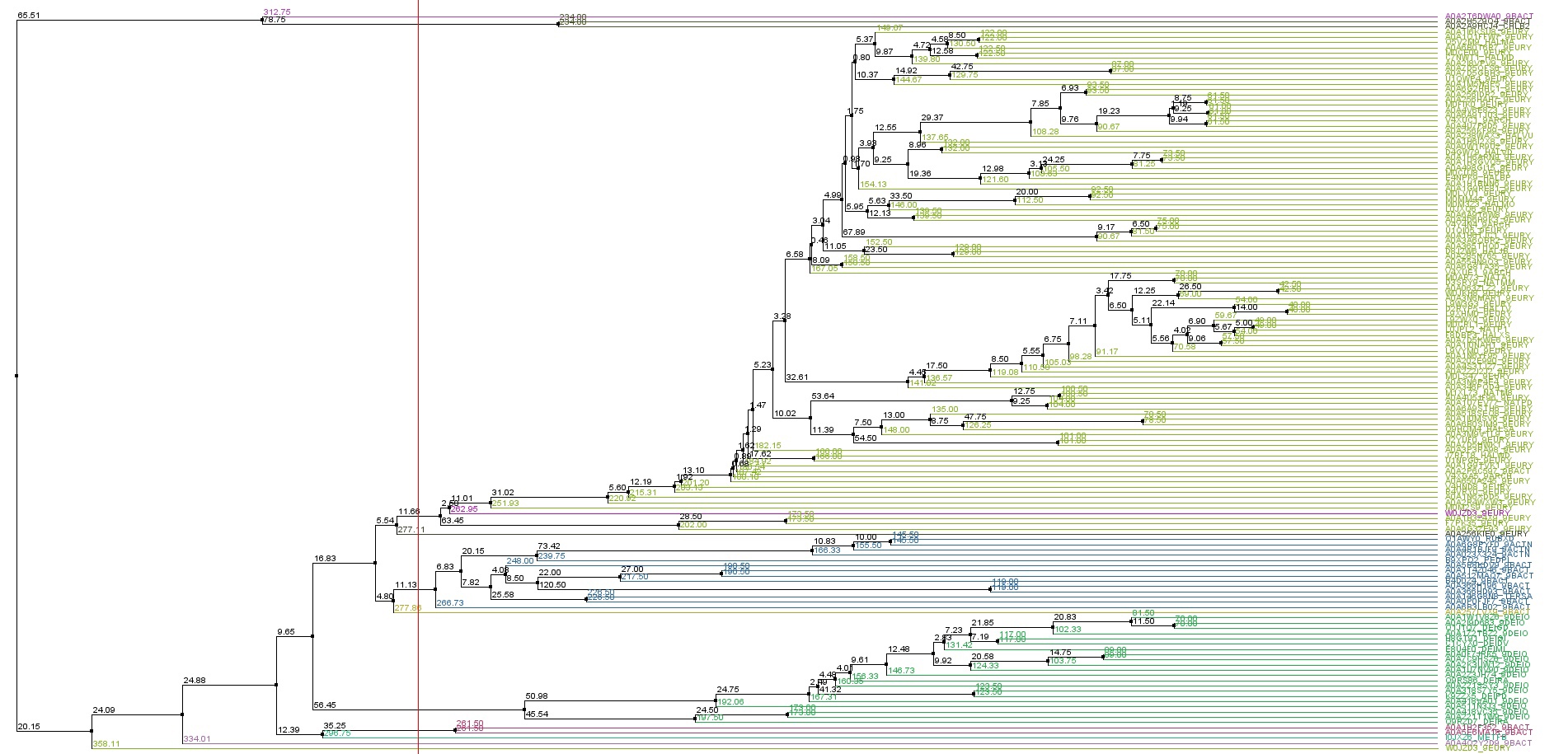
Различия выбранных мною групп я отразила в Таблице 1.
| Колонка | 21 | 62 | 68 | 93 | 103 | 107 | 110 | 113 | 132 | 140 |
| Группа №1 | Q | Много L, V, M | Много A | D | Много H | Много H, R | R | P | H | E |
| Группа №2 | E | Много G | Много V, L | E | Много Y, F | K | P | R | Много D | G |
Таблицу со всеми белками из Uniprot с доменом семейства Pfam можно скачать здесь