Практикум №8
Введение
Данный мне идентификатор соответсвует белку флоретингидролаза бактерии Mycobacteroides abscessus. В условиях структурных состояний легких, таких как муковисцидоз, бронхоэктазы и ХОБЛ, Mycobacteroides abscessus может вызывать хроническую легочную инфекцию[1].
Информация о белке
Флоретингидролаза по современной классификации является ферментом EC:3.7.1.4. Гидролизует следующую реакцию: H2O + phloretin = 1,3,5-trihydroxybenzene + H+ + phloretate [2].
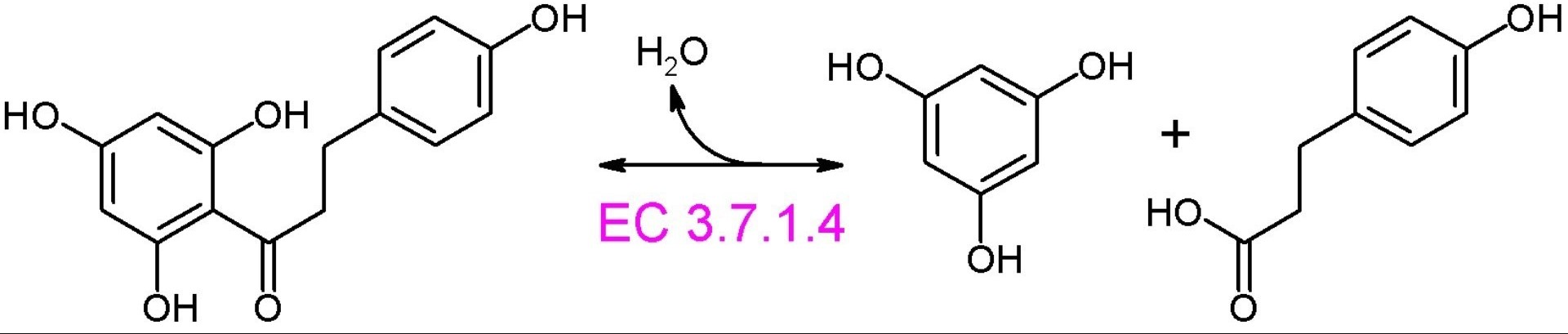
Также гидролизует другие C-ацилированные фенолы. В качестве кофактора присутсвует цинк.
Информация о 3D-структуре белка записана в PDB с индентификатором "5XE5". Мне удалось выяснить, что белок состоит из двух цепей - A и B. Общий вес структуры: 64,05 кДа. Белок имеет следующие микромолекулы: 1,2-этандиол и ион магния.
Информация о кластерах
Кластеры UniRef100_B1MK49, UniRef90_B1MK49 и UniRef50_B1MK49 имеют по 5, 27 и 51 белок соотвественно.
Информация о запросах
Из своих запросов я поняла, что флоретингидролаза - белок который встречается только у бактерий (прокариот) и не встречается у эукариот. Также мне удалось понять, что исследуемый белок встречается у не только у Mycobacteroides abscessus, но и еще у нескольких видов семейства Mycobacteriaceae.
1. Выбор и скачивание протеомов
Я выбрала для сравнения протеомы бактерий Mycobacteroides abscessus (strain ATCC 19977 / DSM 44196 / CIP 104536 / JCM 13569 / NCTC 13031 / TMC 1543) и Mycobacteroides franklinii. Протеом первой бактерии является нереференсным протеомом данного мне организма, а протеом второй бактерии - контрольный - референсный протеом сравнительно близкого организма. Я решила взять организм с нереференсным протеомом, т.к он достаточно хорошо изучен, состоит из белков, часть которых входит в Swiss-Prot. Обширная характеристика с помощью фенотипического анализа, биохимических тестов, тестов на чувствительность к лекарственным средствам, ПЦР-анализ рестрикционных ферментов гена hsp65 и ITS, секвенирование ДНК генов домашнего хозяйства и ДНК-ДНК-гибридизация продемонстрировали, что M. franklinii принадлежит виду, который отделен от M.abscessus[3].
Информация о протеоме Mycobacteroides abscessus (strain ATCC 19977 / DSM 44196 / CIP 104536 / JCM 13569 / NCTC 13031 / TMC 1543)
Информация о протеоме Mycobacteroides franklinii
Наиболее изучен протеом первой бактерии, тк количество его белков, входящих в Swiss-Prot составляе 237. в то время как у второго оранизма их вовсе 0.
2. Сравнение протеомов по представленности определенных групп белков
Для сравнения долей, которые составляют белки некоторой функциональной группы в протеоме моей бактерии и в контрольном протеоме, я буду использовать поисковые запросы.
Трансмембранные белки
Запросы:
keyword:"Transmembrane [KW-0812]" AND organism:"Mycobacteroides abscessus (strain ATCC 19977 / DSM 44196 / CIP 104536 / JCM 13569 / NCTC 13031 / TMC 1543) (Mycobacterium abscessus) [561007]" AND proteome:up000007137.
keyword:"Transmembrane [KW-0812]" AND organism:"Mycobacteroides franklinii [948102]" AND proteome:up000295165.
Запрос выдал для M.abscessus 980 белков, что составляет 19,8% от общего количества, а для M.franllinii выдал 986 белков, что составляет 20,3% от общего количества.
Можно сделать вывод о том, что доля трансмембранных белков в обоих организмах практически одинаковая.
Ферменты
Запроcы:
annotation:(type:"catalytic activity") AND organism:"Mycobacteroides abscessus (strain ATCC 19977 / DSM 44196 / CIP 104536 / JCM 13569 / NCTC 13031 / TMC 1543) (Mycobacterium abscessus) [561007]" AND proteome:up000007137.
annotation:(type:"catalytic activity") AND organism:"Mycobacteroides franklinii [948102]" AND proteome:up000295165.
Запрос выдал 627 белков для M.abscessus, из них в Swiss-Prot 124 белка. А для M.franklinii выдал 618 белков.
Гидролазы
Я решила сравнить наличие в протеомах бактерий ферментов класса гидролазы, тк отличительные параметры исследуемых мной бактерии могут быть связаны именно с этим ферментом.
Запросы:
keyword:"Hydrolase [KW-0378]" AND organism:"Mycobacteroides abscessus (strain ATCC 19977 / DSM 44196 / CIP 104536 / JCM 13569 / NCTC 13031 / TMC 1543) (Mycobacterium abscessus) [561007]" AND proteome:up000007137.
keyword:"Hydrolase [KW-0378]" AND organism:"Mycobacteroides franklinii [948102]" AND proteome:up000295165.
Запрос выдал 294 белка для M.abscessus , а для M.franklinii запрос выдал 514 белков , что почти в 2 раза больше, чем у предыдущей бактерии. Эта находка как раз и подтверждает то, что различия в свойствах организмов обучловлены наличием гидролаз
Месторасположение белков в клетке
Я решила посмотреть, как белки распределились в клетке. Однако, изначально изучая протеом, я поняла, что не для всех белков известно их расположение в клетке. несмотря на это, я все же решила провести анализ и сравнениие протеомов двух организмов.
Для реализации данной идеи я использовала Bash. Команды:
zcat term2/pr8/UP000007137.swiss.gz | cut -d '{' -f1 | grep 'CC -!- SUBCELLULAR LOCATION' |sort| uniq -c| less
zcat term2/pr8/UP0002*.swiss.gz | cut -d '{' -f1 | grep 'CC -!- SIMILARITY' |sort| uniq -c| less
| Mycobacteroides abscessus | Mycobacteroides franklinii | |
|---|---|---|
| Cell inner membrane | 4 | 6 |
| Cell membrane | 142 | 137 |
| Cell surface | 2 | 2 |
| Cytoplasm | 230 | 231 |
| Cytoplasm, nucleoid | 2 | 2 |
| Endosome membrane | 1 | 1 |
| Membrane | 240 | 236 |
| Secreted | 3 | 1 |
| Secreted, cell wall | 4 | 4 |
Из таблицы видно, что месторасположение белков в клетке у обеих бактерии схоже. Это и логично, ведь организмы - довольно близкие родственники.
Источники информации
[1] Maggioncalda, EC, Story-Roller, E., Mylius, J. et al. Мышиная модель легочной инфекции Mycobacteroides abscessus . Научный представитель 10, 3690 (2020). https://doi.org/10.1038/s41598-020-60452-1 Ссылка на статью
[2] Han, Jian-Ting; Zhang, Si-Ping; Jia, Wen-Juan; Zhang, Zhang; Wang, Yong; He, Yong-Xing (2019). Discovery and structural analysis of a phloretin hydrolase from the opportunistic human pathogen Mycobacterium abscessus. The FEBS Journal, (), –. doi:10.1111/febs.14792
[3]Cnockaert, Margo; Simmon, Keith E.; Vandamme, Peter; Lourenço Nogueira, Christiane; Carlos Palomino, Juan; Chimara, Erica; Brown-Elliott, Barbara A.; Wallace, Richard J.; Martin, Anandi; Cardoso Leão, Sylvia (2015). Mycobacterium franklinii sp. nov., a species closely related to members of the Mycobacterium chelonae–Mycobacterium abscessus group. International Journal of Systematic and Evolutionary Microbiology, 65(7), 2148–2153. doi:10.1099/ijs.0.000234