Практикум 11
Практикум по множественному эволюционному выравниванию белковых доменов
Для проведения выравнивания было выбрано семейство белковых доменов из базы данных Pfam с AC PF01585 (G-patch domain). Результаты анализа множественного выравнивания приведены в таблице 1.
| Название | Информация | Комментарии |
|---|---|---|
| Выравнивание seed | sequences: 45 columns: 59 | Количество последовательностей в этом семействе белковых доменов равно 45, количество колонок в выравнивании равно 59 |
| All | 52k | Число всех белков с доменом семейства равно 52 |
| Swissprot | 184 | Число белков с доменом Swissprot равно 184 |
| architectures | 1018 | Число разных доменных архитектур равно 1018 |
| 3D | 17 | Число доменов с известной 3D структурой. |
| Taxonomy | eukaryota: 51945 archaea: 0 bacteria: 0 viruses: 54 | Число всех белков с доменом семейства по супер-царствам. Делки с данным доменом известны только среди эукариот и вирусов. |
Описание выравнивания белковых доменов
Данные приведены в таблице 2.
| Название | Информация | Комментарии |
|---|---|---|
| Выравнивание seed | sequences: 45 columns: 59 | Количество последовательностей в этом семействе белковых доменов равно 45, количество колонок в выравнивании равно 59 |
| Максимальный достоверный блок, включающие все последовательности (МДБ-all) | columns: 3-14 | Максимальный достоверный блок данного выравнивания выделяется между 3-14 колонками. |
| 100% консервативные колонки в МДБ-all | 13:G, 24:G | 13-ая и 24-ая колонки выравнивания являются абсолютно (100%) консервативными и состоят только из гилцина. |
| Максимальный достоверный блок, включающий не все последовательности (МДБ-notAll) | columns: 5-13 sequences: 1-32 | Максимальный достоверный блок, включающий не все последовательности, состоит из колонок 5-13 включительно, а также из последовательностей 1-32 включительно |
| 100% консервативные колонки в МДБ-notAll | 5:[G], 13:[G], 24:[G] | В МДБ-notAll указаны только 100%-консервативные колонки, в скобках указана соответствующая единственная аминокислота, из которой состоит колонка выравнивания |
| Участок выравнивания, в котором нет никаких достоверных подблоков, и потому маловероятно, что выравнивание на этом участке отражает ход эволюции. | columns: 25-54 | Такой блок состоит, например, из колонок с 25 по 54 включительно. По результатам сортировки по группам в нём не было выявлено ни одной группы, состоящей более чем из одной последовательности, следовательно, данный блок является недостоверным |
Карта локального сходства (dotplot)
Данные приведены в таблице 3.
| Название | Информация | Комментарии |
|---|---|---|
| Доменная архитпектура 1 | PF01585 - PF13821 | Последовательность AC доменов, входящих в состав доменной архитектуры. |
| Белок с архитектурой 1 | DUF4187 | AC белка для данной доменной архитектуры |
| Доменная архитпектура 2 | PF12457 - PF01585 - PF07842 | Последовательность AC доменов, входящих в состав доменной архитектуры. |
| Белок с архитектурой 2 | Q9Y103 | AC белка для данной доменной архитектуры |
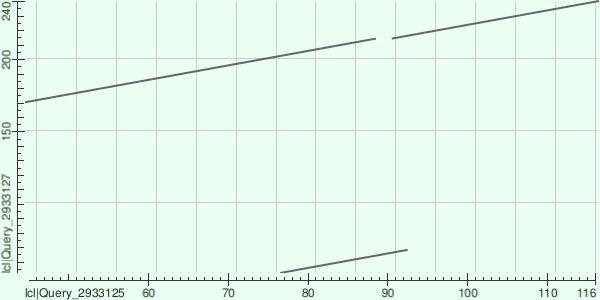
Представленный график Dot Plot подтверждает гомологию исследуемых белков по ключевому домену, что отражено в виде основной длинной диагонали. Наличие небольшого разрыва в этой линии свидетельствует о локальной инсерции или делеции в одной из последовательностей. При этом наличие второй короткой параллельной линии в нижней части графика прямо указывает на различия в доменной архитектуре: данный участок свидетельствует о повторе мотива или наличии дополнительного сходного фрагмента, который отсутствует в том же месте у второй последовательности. Значительная разница в масштабах осей подтверждает, что один из белков обладает большей длиной и, вероятно, содержит дополнительные структурные элементы, что полностью соответствует условию задачи о сравнении белков с разной архитектурой при наличии общего домена.