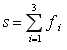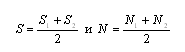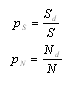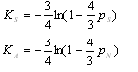|
AC: P24223 Дополнительный геном: SALTY. |
| 1.Сравнение аминокислотного и нуклеотидного выравниваний |
|
|||||||||
|
|||||||||
|
|||||||||
|
|||||||||
Выравнивание аминокислотной последовательности: |
|||||||||
|
|||||||||
|
Выравнивание нуклеотидной последовательности: |
|||||||||
|
|||||||||
|
|||||||||
Значение Identity аминокислотного выравнивания: 227/242 (93.8%)Значение Identity нуклеотидного выравнивания: 605/732 (82.7%) Значение Identity нуклеотидного выравнивания ниже потому, что в нуклеотидных последовательностях происходили синонимичные замены, не влияющие на аминокислотный состав кодируемых белков, но влияющие на идентичность нуклеотидных последовательностей. |
|||||||||
|
|