Определение таксономии и функции нуклеотидной последовательности
Ход работы
- В качестве нуклеотидной последовательности бралась последовательность из практикума 6
- Для поиска использовался blastn с параметрами по умолчанию (megablast), потому что изначально не известно является ли наша последовательность кодирующей
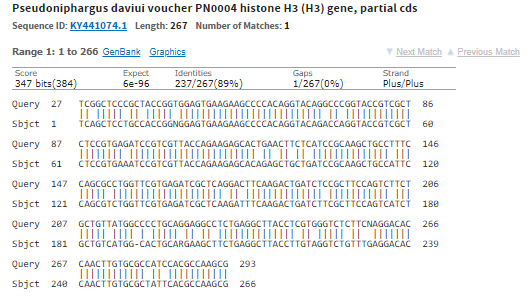
- При просмотре GenBank записи первой находки оказалось, что это partial CDS гистона-3
- При этом с помощью GenBank было поттверждено, что нуклеотидная последовательность действительно
именно кодирующая последовательность гистона-3 (рис.1)
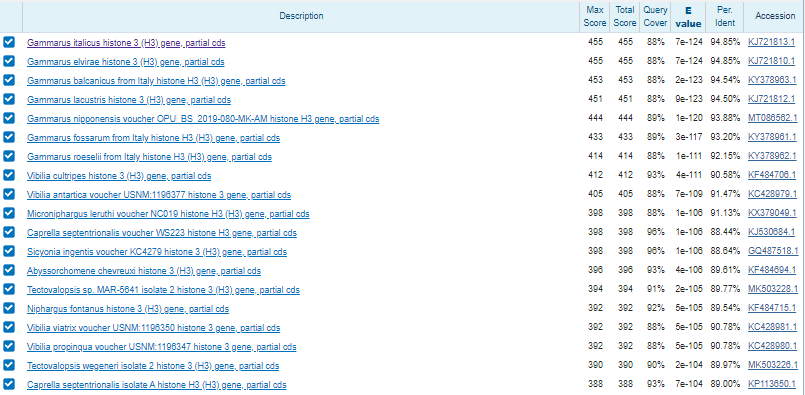
Рис 1. Выдача blastn megablast - Помимо этого был сделан blastx с параметрами по умолчанию (megablast), который ищет находки среди
белков, используя нуклеотидную
последовательность, это было сделано, чтобы проверить единственность функции этого белка (
т.к. E-value очень маленькое, а Identity, больше 95% у всех лучших находок blastx, можно быть уверенным, что этот
ген кодирует высококонсервативную аминокислотную последовательность. Это значит, что очень вероятно моя
последовательность выполняет схожую с находками функцию. (рис.2)
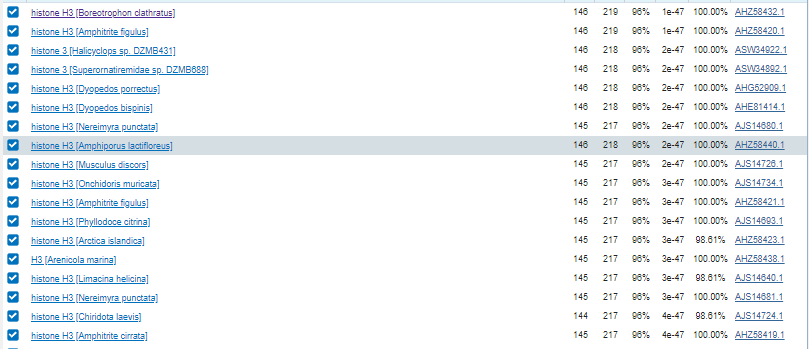
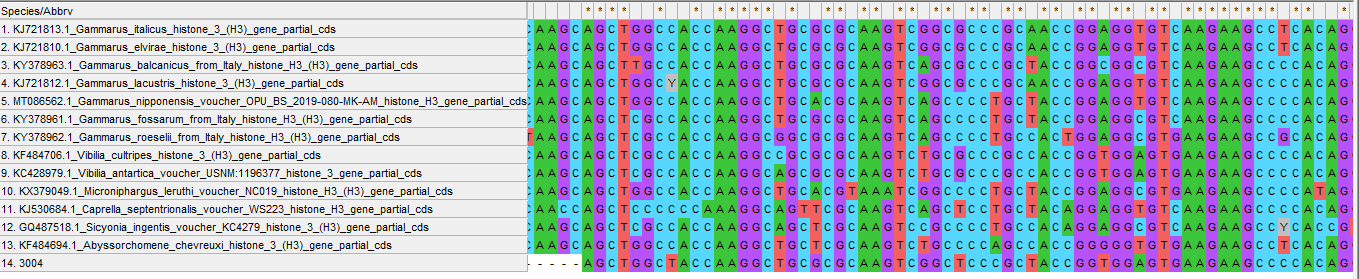
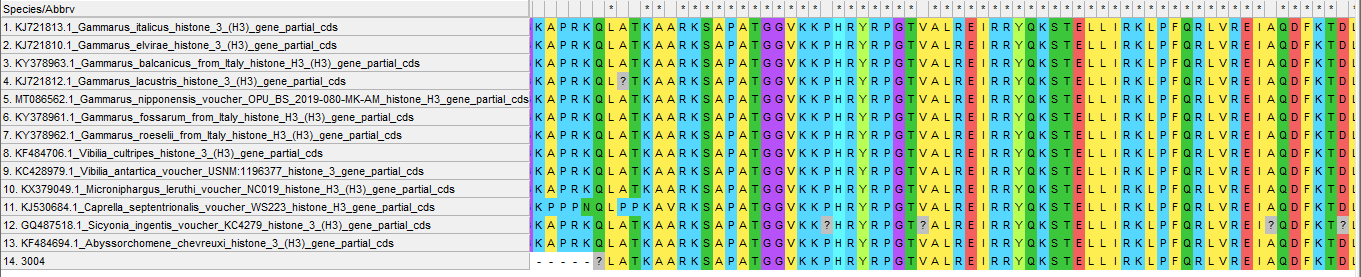
Рис 2. Выдача blastx megablast - Для определения близкородственной филогении лучше всего использовать нуклеотидные последовательности, поэтому я взял из лучших находок blastn (рис. 1) разных организмов и построил дл них выравнивание (рис. 3). Хотя подозрительно, что первые 7 лучших находок это гамарусы, но могло так получиться, что из-за меньшего покрытия, чем ,например, у Vibilia, идентичность выше (можно, конечно, попробовать построить дерево и проверить его бутстрепом, но мы этого на тот момент еще не знали. Итого решил взять организмы с E-value < e^-105, потому что с этой степени их значения уменьшались постепенно, а здесь за 13 находок скачок аж на 20 степеней (на следующие 13 находок степень уменьшилась лишь на 4).
- По голому выравниванию сложно что-то сказать вразумительное, видно что в целом последовательность консервативна, а если посмотреть на выравнивание их оттранслированных последовательностей, то видно, что если замены и есть в нуклеотидной последовательности, то большинство из них все же синонимичные (рис. 4)
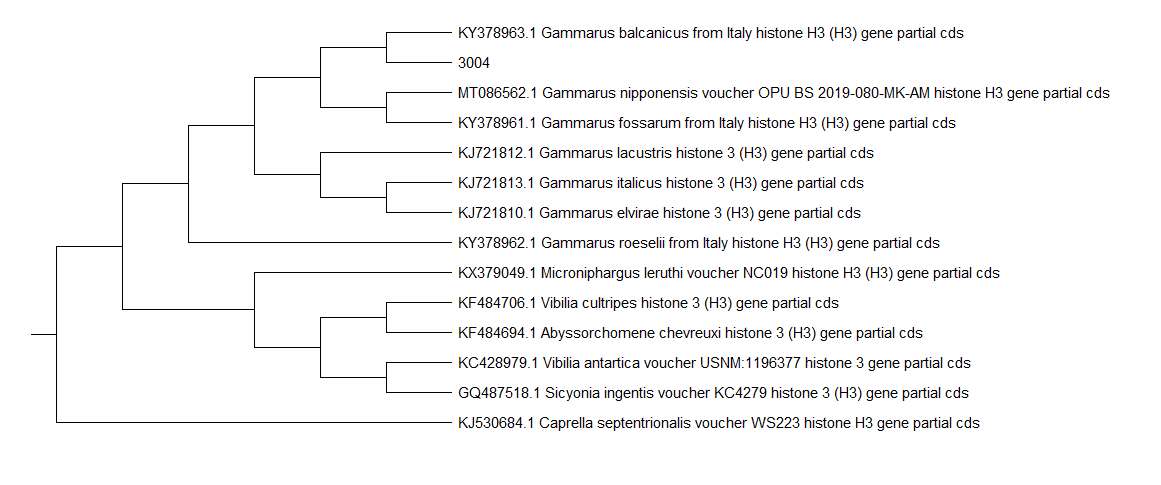
- Поэтому решил построить дерево (рис. 5)
- На дереве видно, что последовательность хорошо легла рядом с родом Gammarus (за вид наверное ручаться не могу, хотя и можно предположить, что это Gammarus balcanicus)
Сравнение выдачи разных вариантов запуска blast
- Сначала провел разные бласты для моей последовательности megablast, blastn, sensetive blastn
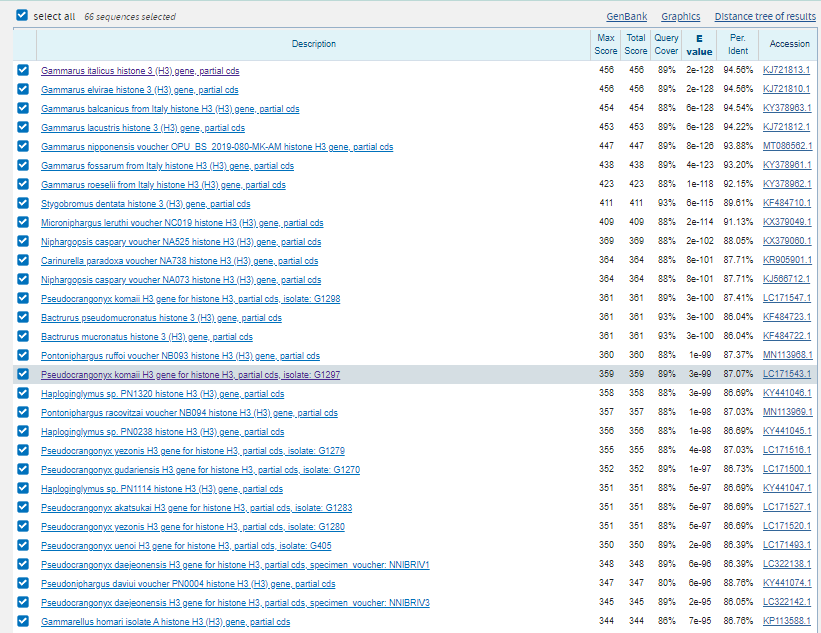
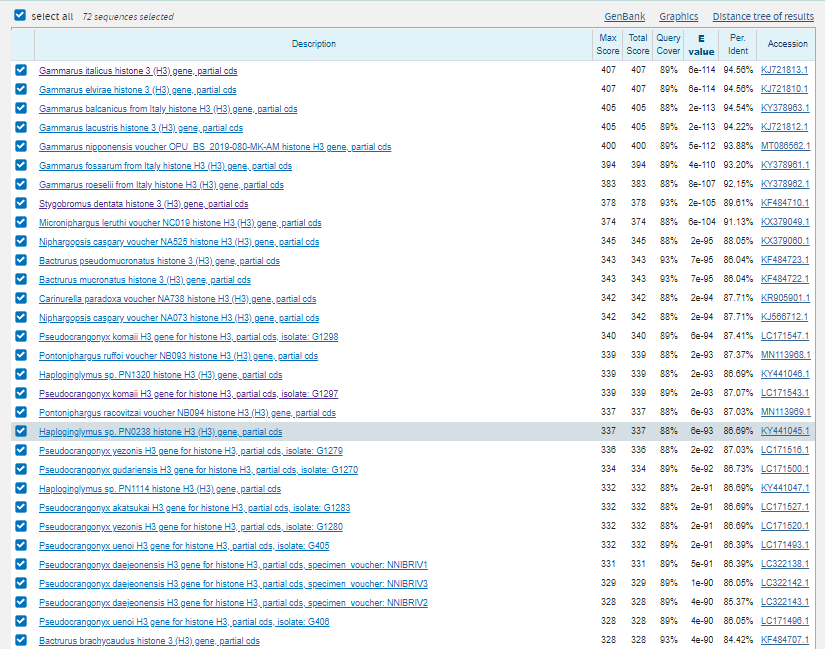
- blastn: максимум 1000 находок убрал большой род Niphargus и искал в семействе Gammarida. На выдаче получилось 66 последовательностей (рис. 6)
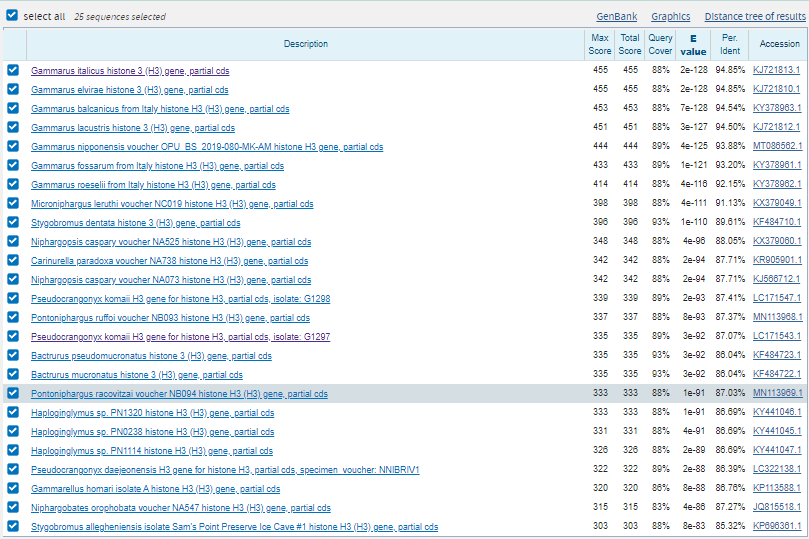
- megablast: максимум 1000 находок убрал большой род Niphargus и искал в семействе Gammarida. На выдаче 25 последовательностей. Что логично, т.к. у blastn длина минимального совпадения 11, а у megablast 28. Yfghbvth megablast не нашел Pseudoniphargus daviui voucher PN0004 histone H3 (H3) gene, partial cds, потому что в нем нету совпадений длинной 28. Так же можно заметить, что порядок последовательностей меняется. Это связано с тем, что уменьшение штрафа за мисматч дает больший вес выравнивания.
- sensetive blastn: максимум 1000 находок убрал большой род Niphargus и искал в семействе Gammarida при этом длину слова сделал минимальной 7 и мисматч 1, -1. По хорошему должны ждать находок больше, чем у blastn. Как видно на рис. 9 предсказание сбылось. Однако, теперь к нам попал и мусор с большим E-value, как раз из-за маленькой длины слова и более мягкого мисматча. На рис. 10 продемонстрировано одно из таких выравниваний.
- Теперь перейдем к вирусу. Для него выбрал protein=HicA-like toxin gene.
- blastn: аналогично, только теперь выкинул всех cellular organisms. На выдаче 132 последовательности.
- megablast: как для вирусного blastn. На выдаче 122 последовательности.
- sensetive blastn: аналогично для моей последовательности, только выкинул всех cellular organisms. На выходе 139 последовательности, но в них затесались 10 с очень большими E-value. Поэтому можно считать, что их 129.
- Общее наблюдение, что выдавались находки исключительно для вирусов Pahexavirus, возможно, это какой-то специфичный для них ген. Судя из названия можно предположить, что это какой-то их токсин.
Поиск белков в геноме
- Сначала посмотрим на Amoeboaphelidium protococcarum. В NCBI есть про него пара GenBank записей, из которых берем transl_table=6 для дальнейшего выравнивания.
- Искал я белки: ДНК-полимераза дельта - основная полимераза эукариот, гистон H4, и Na+/K+-АТФазу.
- Запросы NCBI protein: (gallus gallus[Organism]) AND dna polymerase (здесь взял subunit 3) ; (gallus gallus[Organism]) AND histone h4[Protein Name] ; (Gallus gallus[Organism]) AND ATPase[Protein Name]
- В итоге 3 файла и сборка. Далее запускаем сеанс tblastn на кодомо.
makeblastdb -in X5.fasta -dbtype nucl tblastn -query gallus_dna_pol_d.fasta -db_gencode 6 -db X5.fasta -out dna_pol_d.out tblastn -query gallus_histone_h4.fasta -db_gencode 6 -db X5.fasta -out histone_h4.out tblastn -query gallus_atpase.fasta -db_gencode 6 -db X5.fasta -out atpase.out
- На выходе имеем для Полимеразы 2 находки. Из них лучшая с весом 31,6 и E-value 1,1 и идентичностью 33%.
> scaffold-17 Length=2125590 Score = 31.6 bits (70), Expect = 1.1, Method: Compositional matrix adjust. Identities = 14/44 (32%), Positives = 27/44 (61%), Gaps = 2/44 (5%) Frame = +3 Query 404 CTDSEDD--FAKTKPPAVPKQPALPVKKEPKEERKNQKKGAATA 445 CT+S+D + KT+P A+ +QP+ P + P ++ N + A++ Sbjct 1537893 CTESQDQCTWCKTQPSALEQQPSTPQHRHPLDQIHNSHQICASS 1538024 Score = 30.8 bits (68), Expect = 1.8, Method: Compositional matrix adjust. Identities = 22/66 (33%), Positives = 35/66 (53%), Gaps = 12/66 (18%) Frame = -3 Query 51 ENSGAQLHVTYLV-----------AGNLIQNGHTCHKVAVVREDKLEAMKSKLATVTS-V 98 +NSG LH+ YL+ + L + HT ++++V L+ +S LATV + + Sbjct 231532 QNSGQTLHIEYLIQRVKTIDSNDFSKRLNNSLHTLNQISVSIWFGLQEQQSTLATVLNLI 231353 Query 99 HVYSIQ 104 VYSIQ Sbjct 231352 IVYSIQ 231335 > scaffold-105 Length=655906 Score = 30.4 bits (67), Expect = 2.2, Method: Compositional matrix adjust. Identities = 13/44 (30%), Positives = 28/44 (64%), Gaps = 2/44 (5%) Frame = -3 Query 404 CTDSEDD--FAKTKPPAVPKQPALPVKKEPKEERKNQKKGAATA 445 CT+++D + KT+P A+ +QP+ P + P ++ N ++ A++ Sbjct 469775 CTENQDQCTWCKTQPTALEQQPSTPRHRHPLDQIHNSRQICASS 469644 - Думаю, что этому не нужно доверять, потому что на мой взгляд уж что-что а субъединица основной полимеразы должна быть очень консервативна. Хотя и второе выравнивание возможно отвечает за 451..458 region_name="PIP-box".
- Для АТФазы 33 находки, что возможно было бы не странно, потому что этот белок большой 1000 а.к. Лучшая находка с весом 580, E-value 1e^-177, идентичность 35%
-
Score = 580 bits (1495), Expect = 1e-177, Method: Compositional matrix adjust. Identities = 403/1159 (35%), Positives = 594/1159 (51%), Gaps = 171/1159 (15%) Frame = +2 Query 8 DKYEPTATSEHGTKKKKAKERDMDELKKEISMDDHKLSLDELHRKY-GTDL-------SR 59 D+ E + + K+ K D + KK + + +H LS +EL +KY G S+ Sbjct 103883 DRVEDSKINTSAVKEPVVKGHDKE--KKSVHITEHMLSPEELSQKYYGVKFDAEKPTQSQ 104056 Query 60 GLTTARAAEILARDGpntltpppttpEWVKFCRQLFGGFSLLLWIGSLLCFLAYGITSVM 119 GL+ + A E LA GPN ++PP +TP ++KF LF F+ LL +L F+ YGI Sbjct 104057 GLSESLAEEKLAEHGPNMMSPPKSTPAYLKFLHCLFNQFNQLLIFAGILSFILYGI---- 104224 Query 120 EGEPNSDNLYLGVVLAAVVIITGCFSYYQEAKSSKIMESFKNMVPQQALVVRNGEKMSIN 179 + + +LY+G +L V +I + Q KS I++SF +VP+ +R+G+ S+ Sbjct 104225 DPQNGISSLYVGAILILVALINSTIEFVQIQKSEAILKSFLGLVPRNCTTIRDGKLKSMG 104404 Query 180 AEGVVVGDLVEVKGGDRIPADLRIISAHGCKVDNSSLTGESEPQTRSPDFSNENPLETRN 239 AE +V GD++ V+ GD++PAD+ I A KVDNSSLTGE++PQ R P + ENPLE N Sbjct 104405 AESLVPGDVIHVRMGDKLPADIYIFWAAEFKVDNSSLTGEADPQERGPGNTQENPLEAHN 104584 Query 240 IAFFSTNCVEGTAVGIVISTGDRTVMGRIASLASGLEGGKTPIAMEIEHFIHLITGVAVF 299 +AF + V G A G+VI TGD TV+G+IA++ASG + ++P+ +EI++F+ +I VA Sbjct 104585 LAFSGSLAVNGEAYGVVIRTGDFTVLGQIANMASGEKKRQSPMTVEIDNFVKMIALVAAL 104764 Query 300 LGVSFFILSLIL---EYTWLEAVI-----FLIGIIVANVPEGllatvtvcltltaKRMAR 351 GV FFI+ + ++ + +I F IG+ ++ VPE L A VT+ L+ A+RM++ Sbjct 104765 TGVVFFIIGITTLGGQFPDSKQLIAFNFTFAIGVFISWVPEALPAIVTLLLSFAAQRMSK 104944 Query 352 KNCLVKNLEAVGTLGSTSTICSDKTGTLTQNRMTVAHMWFDNQIHEADTTENQSGASFD- 410 +N LVK+L V TLGS + + +DKTGTLT+N+MTV + W ++++ +E++S A+ D Sbjct 104945 RNVLVKDLRGVETLGSITLLATDKTGTLTRNQMTVTNFWSSGEMYQVGKSEHKSSANLDG 105124 Query 411 -------------------KSSATWLALSR---------------------------IAG 424 + + L L+R I Sbjct 105125 QPKSAGDENMPPVINGKDGEQAIGMLPLNRVPTVQMAPADDFKQFSLDVKSLNDLSMICY 105304 Query 425 LCNRAVFQANQENVPILKRAVAGDASESALLKCIELCCGSVKEMRERYPKVVEIPFNSTN 484 LC++A F A +VP+ +R+V GDA+ES L + E+YPKV EIPFNSTN Sbjct 105305 LCSKARFDAT--DVPLKQRSVIGDATESGLFLFAANTLPDSDTLAEQYPKVFEIPFNSTN 105478 Query 485 KYQLSIHKNANAGESRHLLVMKGAPERILDRCDSILIH-GKVQPLDEEIKDAFQNAYlel 543 K+ LSIHK + LL+ KGAPERI C I G + + E+K FQ +Y L Sbjct 105479 KWHLSIHKMKHDNGDLTLLI-KGAPERIFRLCSKIYSQSGDEKEITAEMKQDFQKSYEAL 105655 Query 544 gglgervlgFCHLALPDDQFPEGFQFDTDEVN--------------FPVEKLCFVGLMSM 589 G RV+G LP +P F F D+ + +P F GL+S+ Sbjct 105656 AAKGHRVIGTAKFNLPAADYPADFTFRKDDQDKKELGEDKPGILGTYPKGGYTFCGLVSL 105835 Query 590 IDPPRAAVPDAVGKCRSAGIKVIMVTGDHPITAKAIAKGVGIISDGNETVEDIAARLNIP 649 DPP+ V +A+GKCR AG+KV+MVTGDHP+TA+AIA+ + ++ ET E +A R N Sbjct 105836 EDPPKHGVREAIGKCRQAGVKVMMVTGDHPLTAEAIARKINLML--QETKEMVAKRTNRA 106009 Query 650 VSQVNPRDAKACVVHGSDLKDMTSEQLDDILLHHTEIVFARTSPQQKLIIVEGCQRQGAI 709 +S + + + V+HG + +T + + IL + EI+FARTSP+ KL IV+ CQ +G I Sbjct 106010 LSSIQEHEYNSIVIHGEKVDSLTEDDWERIL-NKDEIIFARTSPKHKLQIVKHCQERGHI 106186 Query 710 VAVTGDGVNDSPALKKADIGVAMGIAGSDVSKQAADMILLDDNFASIVTGVEEGRLIFDN 769 V VTGDGVNDSPALKKAD+G++M I+GSDVSK+AA MILLDDNFAS V G+ EGRLIF N Sbjct 106187 VGVTGDGVNDSPALKKADLGISMNISGSDVSKEAAAMILLDDNFASTVHGISEGRLIFQN 106366 Query 770 LKKSIAYTLTSNIPEITPFLIFIIANIPLPLGTCTILCIDLGTDMVPAISLAY---EQAE 826 LKK + YTL +PE+ L+F++ IPLPL I+ IDLG + +S A+ E E Sbjct 106367 LKKCVRYTLCHILPEVIANLLFVVVPIPLPLYALQIILIDLGFEFFNGLSYAWEVPEHGE 106546 Query 827 SDIMKRQPRNPKTDKLVN-------------ERLISMAYGQIGMIQALGGFFTYFVIMAE 873 I+ PR P + + ++ +++ M YG A V +E Sbjct 106547 EGILMALPRKPVSLRSIDLLRRNNAYKAKQQNQVMQMVYGNNRPAAAAENSLVQDVDTSE 106726 Query 874 NGFLPSGLVGIRLQWDDRWINDVEDSYGQQWTFEQRK--------IVEFT---------- 915 + S + + W + D G Q +E R+ I+ + Sbjct 106727 MNW--STYLKYKTAATRVWFRSLFDKEGWQLYWEPRQEETLVDADILSYAYLEVGVLETI 106900 Query 916 -CHTAFF-VSIVVVQWADLIICKT----RRNSVFQQGMKNKIL--------------IFG 955 C AFF V V + W ++ + + Q +K + IF Sbjct 106901 GCLLAFFHVFYVELGWTPAVVAQNAAQFSNTNALPQNLKEALFKAQSAYYFALLIMQIFN 107080 Query 956 LF-------------------------EETALAAFLSYCPGMDVALRMYPLKPTWWFCAF 990 +F A + F+ Y P M + L P +W F Sbjct 107081 MFCCKVTTSYPFGWRVLKNKVTWISLAVSVAFSCFVIYPPFMHDVFQTNYLSPQYWLFPF 107260 Query 991 PYSLLIFLYDEIRKLIIRR 1009 +I +Y R RR Sbjct 107261 VMGFVILMYVSARVAYRRR 107317 - Опять же я бы не поверил, что АТФ-аза может так различаться, хот и E-value многообещающий и при этом последовательность целиком легла на скэффолд, что тоже подозрительно.
- Для гистона H4 все получше потому что лучшая выборка имеет массу 159, E-value 6e^-49 и при этом 94% идентичность.
Score = 159 bits (403), Expect = 6e-49, Method: Compositional matrix adjust. Identities = 77/82 (94%), Positives = 81/82 (99%), Gaps = 0/82 (0%) Frame = -2 Query 22 VLRDNIQGITKPAIRRLARRGGVKRISGLIYEETRGVLKVFLENVIRDAVTYTEHAKRKT 81 +LRDNIQGITKPAIRRLARRGGVKRISGLIYEETRGVLK FLENV+RD+VTYTEHAKRKT Sbjct 331 ILRDNIQGITKPAIRRLARRGGVKRISGLIYEETRGVLKSFLENVVRDSVTYTEHAKRKT 152 Query 82 VTAMDVVYALKRQGRTLYGFGG 103 VTA+DVVYALKRQGRTLYGFGG Sbjct 151 VTALDVVYALKRQGRTLYGFGG 86- Вот здесь впринципе можно быть уверенным, что нашлось совпадение.
Поиск гена в контиге
- Контиг взял из сборки с AC: GCA_000767325.1 для Danio rerio. Длина 22667 н.о.
- Далее провожу blastx, который ищет находки среди белков по нуклеотидной последовательности. Для меньшего количества ненужных находок будем искать только у эукариот и только по проверенным reference белкам (соответствующая бд выбрана: refseq_protein)
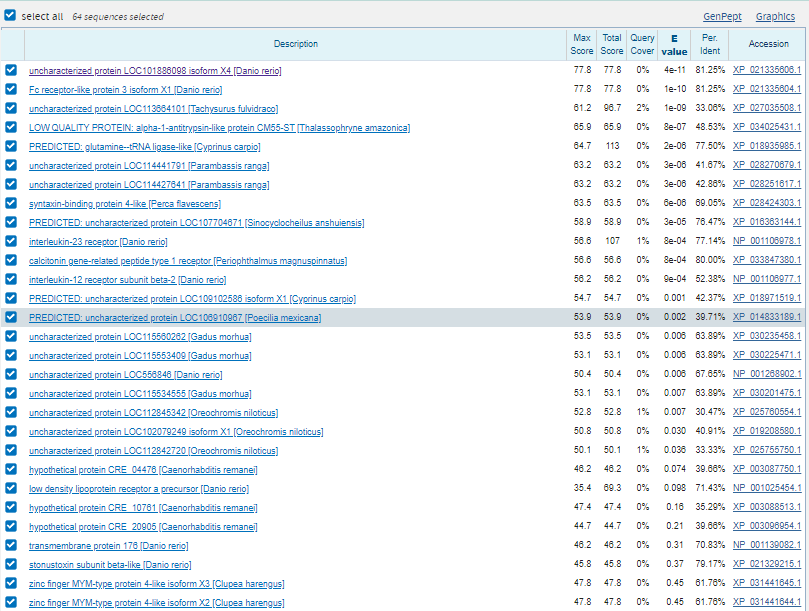
- Итого на выдаче 64 последовательности рис. 11
- Теперь отбросим все находки с E-value >= 0,01 и среди них обратим внимание на находки с Ident, хотя бы больше 70%, то вероятно можем предположить, что эти гены этих белков расположены на выбранном контиге