Часть 1 – GO Enrichment Analysis
- Название моего файла: list46.txt, в котором указано 10 ID
- 10 из 10 ID, т.к. все ID нашлись в БД
- Всего находок - 41. Столько, потому что их p-value < 0,05 (т.е. значимые находки)
- 10 самых значимых находок:
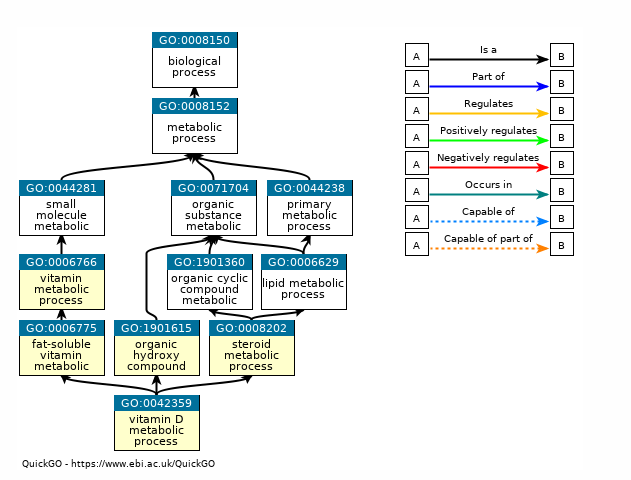
vitamin D metabolic process (GO:0042359) 15 7 .01 + > 100 1.65E-19 2.63E-15 fat-soluble vitamin metabolic process (GO:0006775) 41 7 .02 + > 100 7.08E-17 5.65E-13 steroid metabolic process (GO:0008202) 260 9 .14 + 65.62 4.64E-16 2.47E-12 organic hydroxy compound metabolic process (GO:1901615) 469 9 .25 + 36.38 8.53E-14 3.40E-10 vitamin metabolic process (GO:0006766) 128 7 .07 + > 100 1.31E-13 4.19E-10 small molecule metabolic process (GO:0044281) 1718 10 .91 + 11.03 1.51E-10 4.02E-07 lipid metabolic process (GO:0006629) 1201 9 .63 + 14.20 3.57E-10 8.14E-07 calcitriol biosynthetic process from calciol (GO:0036378) 4 3 .00 + > 100 3.81E-09 7.61E-06 vitamin D biosynthetic process (GO:0042368) 4 3 .00 + > 100 3.81E-09 6.76E-06 vitamin D3 metabolic process (GO:0070640) 5 3 .00 + > 100 6.10E-09 9.73E-06
Часть 2 – String
- Получившийся граф:
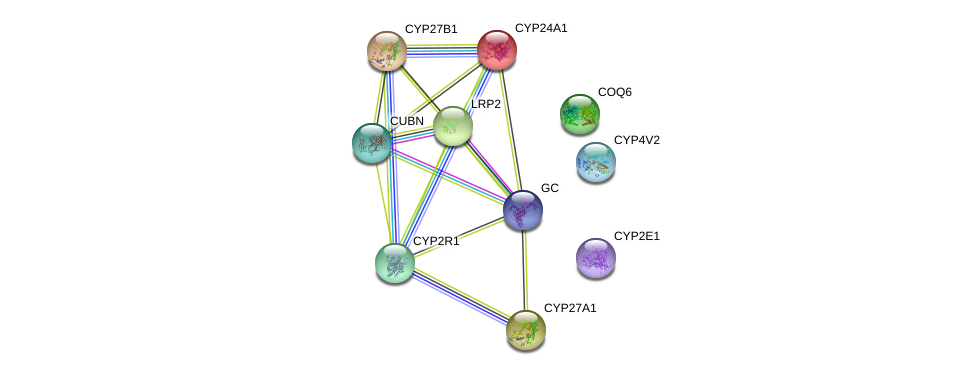
Рис 2. String граф с 10 ID - Для каждого из узлов есть 3D структура
- В моем графе присутствуют from curated databases, experimentally determined, gene co-occurrence, textmining, co-expression, protein homology взаимодействия
- Т.к. в моем графе не все узлы соединены пришлось дополнять его (при этом со 2 попытки очень долго остовался
изолированным белок CYP4V2 и лишь примерно через 7 увеличений количества узлов он наконец включился в общий граф).
Также теперь на этом графе есть все виды взаимодействия. Также выделился зеленый кластер сверху, что говорит о том,
что эти гены соседи и что они хорошо описаны в литературе (их взаимодействие).
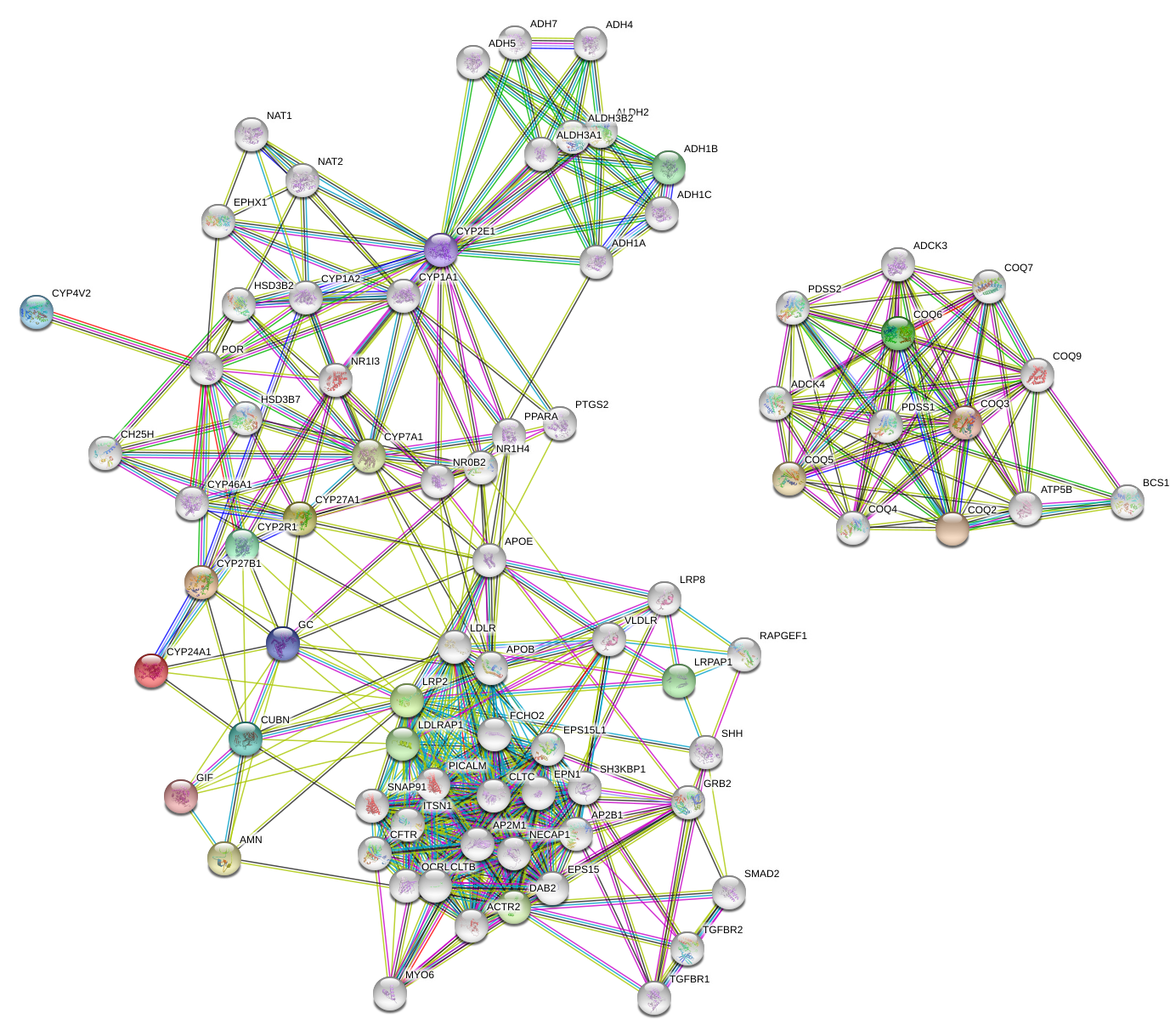
Рис 3. String граф с 10 ID, все соединены - Консервативность: видно, что эти белки высоко консервативны у хордовых организмов, особенно у приматов (что не
странно). Видно, что некоторые из белков отсутствуют (либо в БД, либо вообще) у бактерий и даже у некоторых хордовых (или квадратики настолько
белые, что их не видно, а это говорит об их сильном различии - такое встретилось у некоторых бактерий: Planctomycetes 4 столбик).
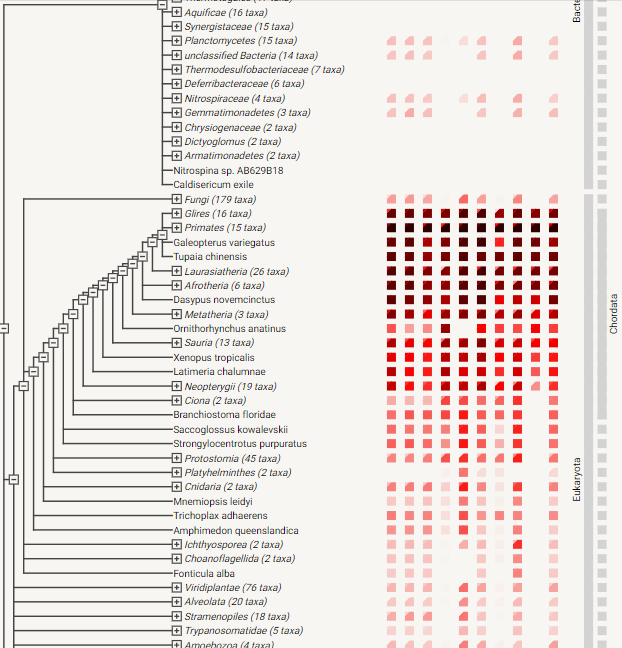
Рис 4. Cooccrurrence - Коэкспрессия: у человека видно только один факт коэкспрессии GC и CYP2E1 и то довольна слабая. У других организмов
коэкспрессия замечена чаще (это может значить, что коэкспрессия у человека либо еще не до конца изучена, либо не наблюдалась).
Хотя видно, что коэкспрессии GC и CYP2E1 также наблюдается у других организмов.
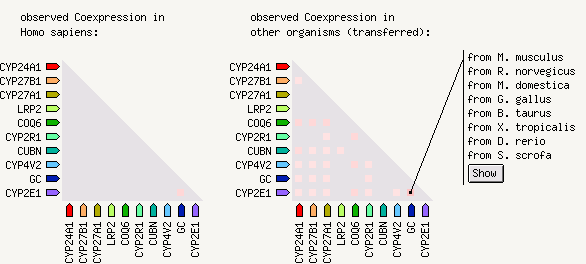
Рис 5. Коэкспрессия