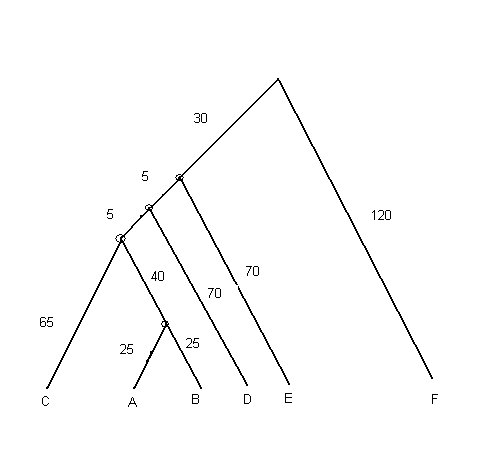
По заданной скобочной формуле с помощью программы Paint было построено дерево:
На данном рисунке представлено укорененное бинарное дерево.
Описание дерева, как разбиения множества листьев
A B C D E F . . * * * * . . . * * * . . . . * *На данной схеме показана топология исcледуемого дерева. Три строки соответствуют внутренним ветвям, от которых отходят внешние ветви с листьями (точками обозначены листья, отходящие от узла внутренней ветви, а звездочками - все остальное).
Получение искусcтвенных мутантных последовательностей
Для получения искусственных мутантных последовательностей была использована программа msbar пакета EMBOSS. Длина гена PYRG_ECOLI - 1638 н.п.. Формула для пересчета расстояний (D) в число мутаций (N):
N=1638*D/100Мутантные последовательности получены с помощью следующего скрипта.
Результат записан в файле mut.fasta.
Используя полученные мутантные последовательности, соответствующие листьям, тремя различными алгоритмами были реконструированы деревья.
Метод максимального правдоподобия
fdnaml mut.fasta -ttratio 1 -auto
+---------C +--1 | +-----------D +------2 | | +----------------------------------F | +----3 | +------E | 4---B | +----AАлгоритм UPGMA
fdnadist mut.fasta -ttratio 1 -auto
fneighbor mut.fdnadist -treetype u -auto+-----A +---------1 +-2 +-----B ! ! +-3 +---------------C ! ! +--------------------4 +-----------------E ! ! --5 +-----------------D ! +--------------------------------------FАлгоритм Neighbor-joining
fdnadist mut.fasta -ttratio 1 -auto
fneighbor mut.fdnadist -auto+--B ! ! +--------------D 2----3 ! ! +--------C ! +-4 ! ! +-----E ! +-----1 ! +------------------------------------F ! +----AСравнение топологий