В базе даннвых ОРМ был найден белок с ID 6x9z, являющийся дизайнерским β-баррелем. Относится найденный белок к надсемейству OmpA-OmpF porin family, к классу Beta-barrel transmembrane и типу Transmembrane белков.
Классификация белков на сайте устроена следующим образом: тип -> класс -> суперсемейство -> семейство -> вид -> локализация -> белок. Причем на сайте всего три типа: Трансмембранные (содержат 3 класса), Пептидные (соедржат 4 класса) и монотопические/периферические белки (содержат 4 класса).
При описании белка OPM ссылается на такие базы данных, как: Uniprot, PDB, Pfam, MSD (Macromolecular Structure Database), PDBsum.
В рамках задания мною был выбран белок, выданный мне преподавателем, кальциевая АТФаза в состоянии E2-фосфат. Английское название белка: Calcium ATPase E2-Pi state. Идентификатор PDB: 3n5k. Индентификатор UniProt: P04191.
Белок был выделен из кролика (Oryctolagus cuniculus), и располагается в мембране эндоплазматического ретикулума. Является ключевым регулятором работоспособности поперечно-полосатых мышц, действующий, в основном, как Ca2+ АТФаза, отвечающая за обратный захват цитозольного кальция в саркоплазматический ретикулум. Кроме того, катализирует гидролиз АТФ, сопряженный с переносом ионов кальция из цитозоля в просвет саркоплазматического ретикулума.
Координаты трасмембранных участков белка, приведенные в OPM:
A - Tilt: 22 - TM segments: 1( 59- 78), 2( 85- 104), 3( 256- 280), 4( 291- 314), 5( 759- 781), 6( 789- 807), 7( 832- 853), 8( 896- 916), 9( 933- 950),10( 967- 987)

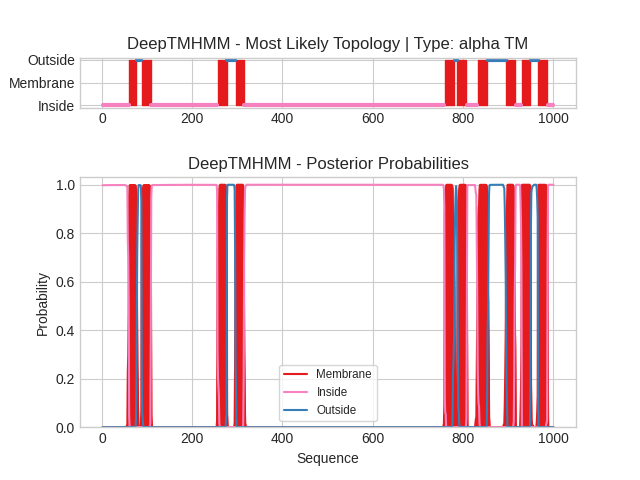
Текстовый вывод программы DeepTMHMM
Оба метода выявили 10 трансмембранных сегментов. То есть отсутствуют "не замеченные" участки. Кроме того, оба метода определили, что оба конца, и N- и C- находятся внутри мембранны и что между некоторыми сегменатми, такими как ТМ2-ТМ3 и Тм4-ТМ5 находятся петли, значительное превышающие по длине остальные.
Полностью совпадают покрытия ТМ8 (896-916) и ТМ10 (967-987), почти идеално сходи границы ТМ5 в обоих метода: (759-781 в OPM против 760-781 у DeepTMHMM). Еще очень близки границы у ТМ7 (832-853 в OPM и 833-854 у DeepTMHMM). Остальные участки отличаются на 4-6 сегментов, но все равно очень близки по покрытию. Такие различия могут быть связаны с тем, что на OPM четко указано состояние белка (E2-фосфат), в то время как DeepTMHMM может предсказывать как бы усредненное состояние.