Практикум №3
Реконструкция дерева по нуклеотидным последовательностям (12S rRNA)
Для каждого вида были найдены полные митохондриальные геномы в базе ENA. Далее по координатам, указанным в аннотации, был вырезан ген 12S рРНК.
Для Drosophila simulans последовательность 12S рРНК не была обнаружена, поэтому взяли последовательность близкородственного вида Drosophila willistoni.
| Вид | Мнемоника | Accession номер (митохондриальный геном) | Координаты 12S rRNA |
|---|---|---|---|
| Artemia franciscana | ARTSF | X69067 | complement(13289..14000) |
| Tetrodontophora bielanensis | TETBI | AY653001 | [1..274] |
| Apis ligustica | APILI | MH341407 | [14763..15547] |
| Samia ricini | SAMRI | JN215366 | complement(14245..15023) |
| Anopheles gambiae | ANOGA | MG753662 | complement(14045..14844) |
| Aedes aegypti | AEDAE | OR413794 | complement(14366..15155) |
| Anopheles quadrimaculatus | ANOQU | PQ613902 | complement(5709..6503) |
| Cochliomyia hominivorax | COLHO | FM867729 | [1..644] |
| Drosophila melanogaster | DROME | X97155 | [1..688] |
| Drosophila willistoni | SPAST | X97154 | [1..665] |
| Drosophila subobscura | DROSU | MG421014 | complement(14157..14938) |
Все полученные файлы с последовательностями были объединены в один файл:
cat *_12S.fasta > all_12S.fastaДалее необходимо выровнять эти последовательности, воспользуемся следующей командой:
muscle -align all_12S_rRNA.fasta -output 12S_all_aligment.fastaНеобходимо перевести выравнивания в единственный формат, который воспринимается программой FastME ("phylip-relaxed").
Была написана программа, берущая на вход выравнивание в формате fasta и выдающая выравнивание в формате phylip-relaxed.
Будем использовать программу IQ-TREE. Эта программа использует метод максимального правдоподобия, то есть сама ищет наиболее вероятную модель эволюции, которая больше подходит под наши последовательности, также она сама определяет тип данных, поэтому воспользуемся командой:
iqtree -s 12S.phyПрограмма создает несколько файлов, нужный нам - файл со скобочной формулой дерева

Алгоритм: максимальное правдоподобие
Программа: IQ-TREE
Модель: выбрана автоматически
Укоренение: midpoint

Алгоритм: максимальное правдоподобие
Программа: IQ-TREE
Модель: выбрана автоматически
Укоренение: midpoint
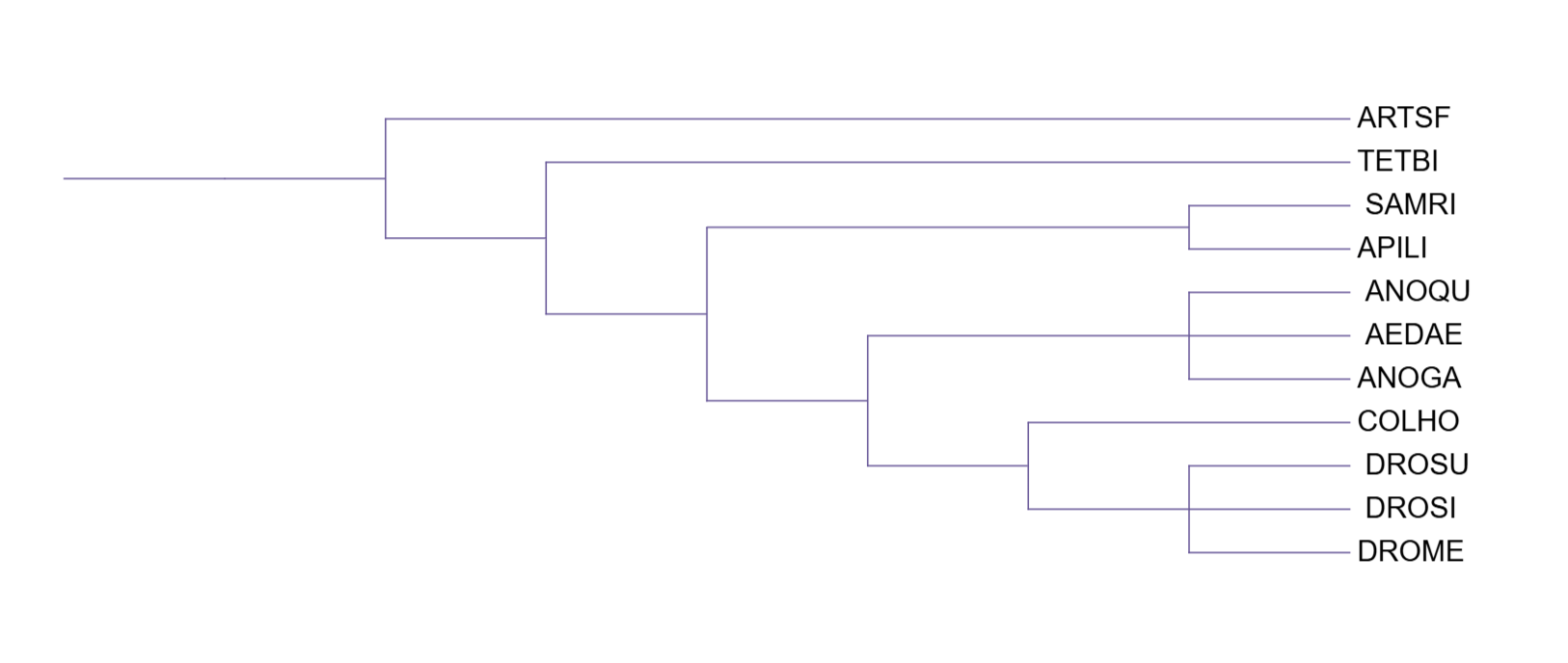
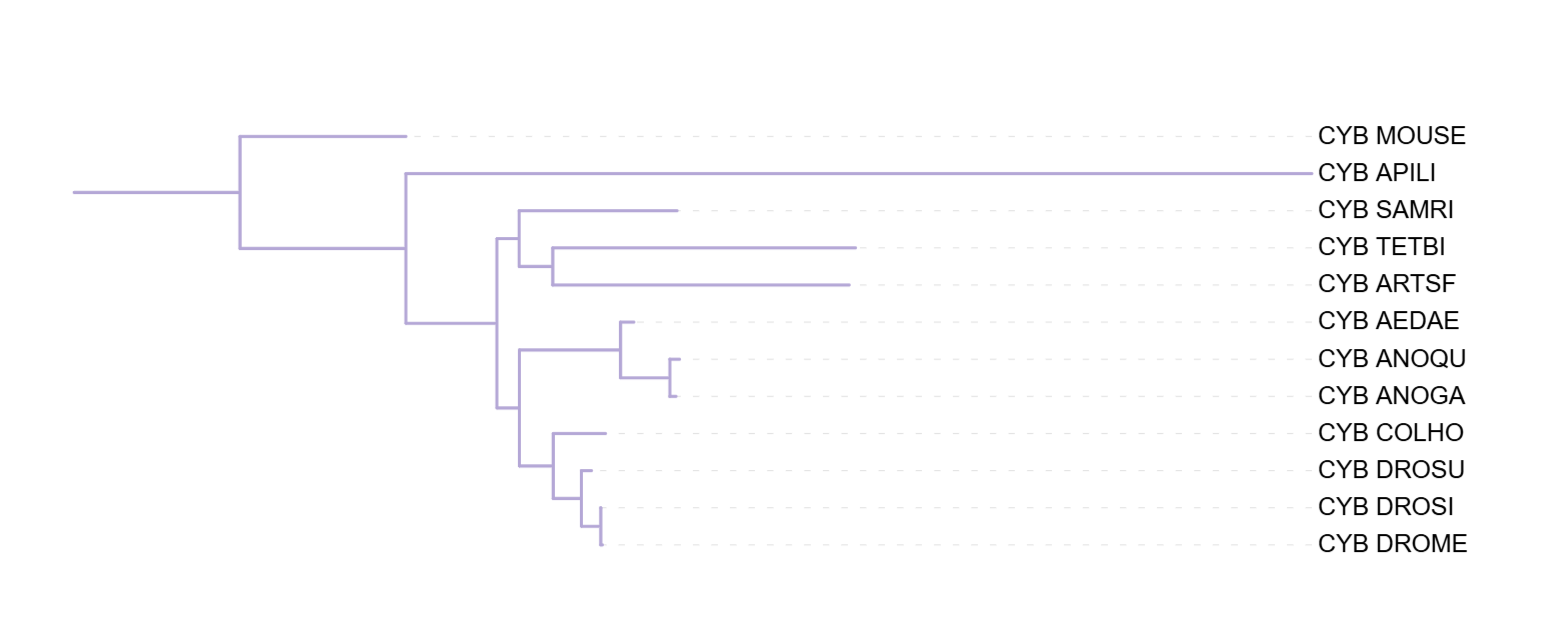
Сравнение таксономического дерева (рис. 2), дерева по цитохрому B (рис. 1) и дерева по 12S рРНК (рис. 3) показывает:
- Во всех реконструированных деревьях ракообразные (ARTSF) отделяются от остальных организмов, что подтверждает правильность укоренения.
- Ни один метод не поместил TETBI (паукообразных) отдельно от насекомых.
- В дереве по 12S рРНК (рис. 3) AEDAE отделился от других комаров и образовал кладу с APILI и COLHO, а TETBI объединился с SAMRI.
- Дерево по цитохрому B (рис. 1) показало лучший результат среди реконструированных деревьев: комары и дрозофилы собраны правильно, хотя TETBI по-прежнему внутри насекомых.
Таким образом, цитохром B восстанавливает филогению точнее, чем 12S rRNA (но никто все равно не всправился с правильным размещением паукообразных).
Укоренение во внешнюю группу
Все исследуемые в работе виды относятся к типу Членистоногие, поэтому в качестве внешней группы была выбрана мышь Mus musculus.
| Вид | Таксономия | Мнемоника |
|---|---|---|
| Mus musculus | Eumetazoa; Bilateria; Deuterostomia; Chordata; Craniata; Vertebrata; Gnathostomata; Teleostomi; Euteleostomi; Sarcopterygii; Dipnotetrapodomorpha; Tetrapoda; Amniota; Mammalia; Theria; Eutheria; Rodentia; Muridae; Mus | MOUSE |
Для построения дерева по цитохрому использовались те же шаги, что и в практикуме 2, но к старым группам была добавлена последовательность цитохрома В мыши. Для выполнения этой части практикума тоже использовалась программа iqtree.
Алгоритм: максимальное правдоподобие
Программа: IQ-TREE
Модель: выбрана автоматически
Укоренение: на ветви, ведущей к внешней группе
Как видно на рис. 4, дерево укоренено на ветви, ведущей к внешней группе (Mus musculus). Внешняя группа отделилась от всех членистоногих, что соответствует ожиданиям, однако добавление внешней группы немного изменило внутреннюю топологию: на рис.1 видно, что TETBI образует кладу с APILI, а отдельно от всех выступает ARTSF; на рис.4 мы видим, что TETBI уже объединился с ARTSF, в то время как APILI отделилась. Остальные клады остались как прежде.
Бутстреп
Для оценки достоверности отдельных ветвей дерева был выполнен бутстреп-анализ с использованием программы FastME. Было задано 100 бутстреп-реплик, и использовалось выравнивание по цитохрому B.
fastme -i ../../cyb.phy -pM -o cyb_bootstrep_trev.tre -b 100-i ../../cyb.phy— входной файл-b 100— количество бутстреп реплик-o cyb_bootstrep_trev.tre— выходной файл с деревом и поддержками

Алгоритм: минимальная эволюция
Программа: FastME
Модель: MtREV
Бутстреп: 100 реплик
Укоренение: midpoint
Проанализировав поддержки на рис.5, можно следать следующие выводы:
Клада дрозофил (DROME, DROWI, DROSU) имеет поддержку 69% - среднее значение, есть сомнения в надежности клады.
Клада комаров (ANOGA, AEDAE, ANOQU) имеет поддержку 100% - очень высокая поддержка, значит клада надежна.
Ошибочное положение TETBI внутри насекомых имеет поддержку 48%, что свидетельствует о невысокой достоверности данных в этом месте.