Филогенетические деревья
| Название | Мнемоника |
| Bacillus anthracis | BACAN |
| Clostridium botulinum | CLOBA |
| Geobacillus kaustophilus | GEOKA |
| Lactobacillus acidophilus | LACAC |
| Listeria monocytogenes serovar 1/2a | LISMO |
| Moorella thermoacetica | MOOTA |
| Staphylococcus aureus | STAAR |
| Staphylococcus epidermidis | STAES |
Скобочная формула: ((LACAC,((STAAR,STAES),(LISMO,(GEOKA,BACAN)))),(MOOTA,CLOBA));
Ветви дерева
У дерева есть пять нетривиальных ветвей:
1){GEOKA,BACAN} vs {LISMO,STAAR,STAES,LACAC,MOOTA,CLOBA}
2){STAAR,STAES} vs {GEOKA,BACAN,LISMO,LACAC, MOOTA,CLOBA}
3){GEOKA,BACAN,LISMO} vs {STAAR,STAES,LACAC,MOOTA,CLOBA}
4){GEOKA,BACAN,LISMO,STAAR,STAES} vs {LACAC,MOOTA,CLOBA}
5){GEOKA,BACAN,LISMO,STAAR,STAES,LACAC} vs {MOOTA,CLOBA}
Изображение получено с помощью программы MEGA.
Изображение дерева
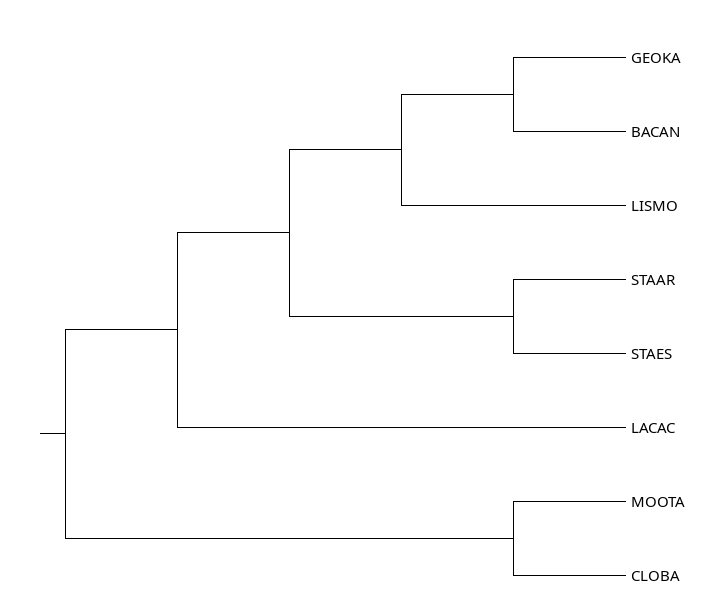
Рис.1 Филогенетическое древо выбранных бактерий
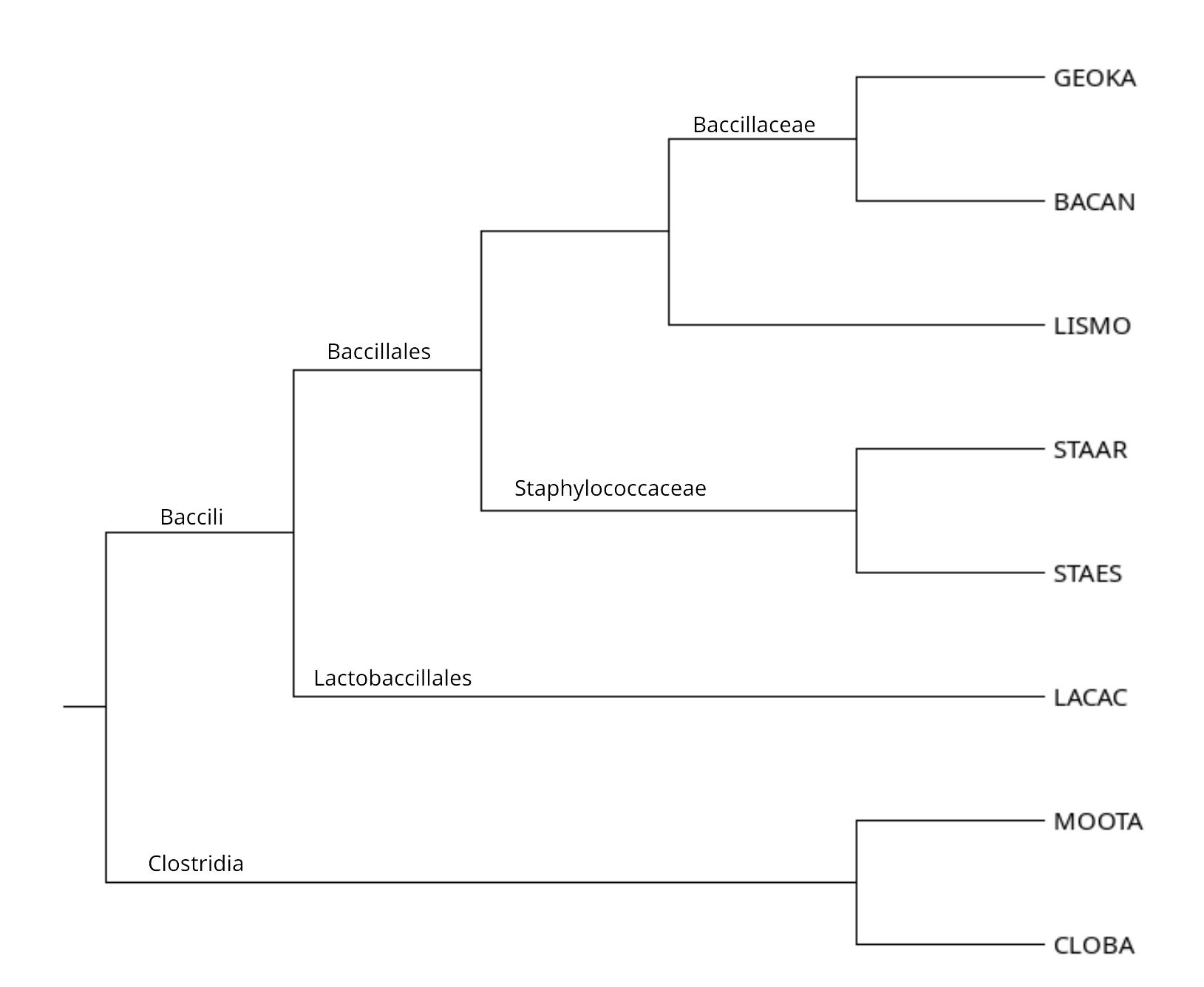
Рис.2 Соответствие таксонов нетривиальным ветвям дерева
Таксономия
С помощью таксономического браузера NCBI была получена таксономия для каждой выбранной бактерии (см. Рис. 2).
| Superkingdom | Bacteria | Bacteria | Bacteria | Bacteria | Bacteria | Bacteria | Bacteria | Bacteria |
| Bacteria group | Terrabaceria group | Terrabaceria group | Terrabaceria group | Terrabaceria group | Terrabaceria group | Terrabaceria group | Terrabaceria group | Terrabaceria group |
| Phylum | Firmicutes | Firmicutes | Firmicutes | Firmicutes | Firmicutes | Firmicutes | Firmicutes | Firmicutes |
| Сlass | Baccili | Baccili | Baccili | Bacilli | Bacilli | Bacilli | Clostridia | Clostridia |
| Order | Baccillales | Baccillales | Baccillales | Baccillales | Baccillales | Lactobacillales | Clostridiales | Thermoanaerobacterales |
| Family | Bacillaceae | Bacillaceae | Listeriaceae | Staphylococcaceae | Staphylococcaceae | Lactobacillaceae | Clostridiaceae | Thermoanaerobacteraceae |
| Genus | Bacillus | Geobacillus | Listeria | Staphylococcus | Staphylococcus | Lactobacillus | Clostridium | Morella |
| Species group | Bacillus cereus group | Geobacillus thermoleovorans group | - | - | - | - | - | Moorella group |
| Species | Bacillus anthracis | Geobacillus kaustophilus | Listeria monocytogenes | Staphylococcus aureus | Staphylococcus epidermidis | Lactobacillus acidophilus | Clostridium botulinum | Moorella thermoacetica |
FastME vs MEGA
В данном задании предлагалось сравнить работу консольной программы FastME и программы MEGA при составлении дерева по методу Минимальной эволюции.
Программа Fastme принимает на вход формат PHYLIP - в первой строке этого формата указано количество таксонов и длину последовательностей, далее идет выравнивание, по 60 символов на строку. Переконвертировать выравнивание в формат phy легче всего в Jalview - попытки проделать это с помощью seqret или в онлайн-конвертерах оканчиваются неудачей, так как все последовательности отличаются по длине. Fastme можно запускать без аргументов, но лучше сразу указать все параметры:
1) -i alignment.phy
2) -p надо указать, что на ввод подаётся выравнивание белковых последовательностей, а не матрица расстояний или нуклеотидные последовательности
3) -m BalME какая-то сбалансированная версия метода минимальной эволюции
На выходе - txt файл с формулой дерева в Newick-формате (которому лучше поменять расширение на nwk прежде чем рисовать картинку в MEGA)
Результат оказался довольно похожим, картинки, нарисованные в MEGA можно увидеть ниже (Рис. 3,4). Как можно заметить, программы в большинстве мест согласуются друг с другом - единственное различие в том, что FastME группирует вместе MOOTA и CLOBA, а MEGA - нет. Однако они довольно сильно расходятся с деревом, данным для работы в практикуме 1 и 2!
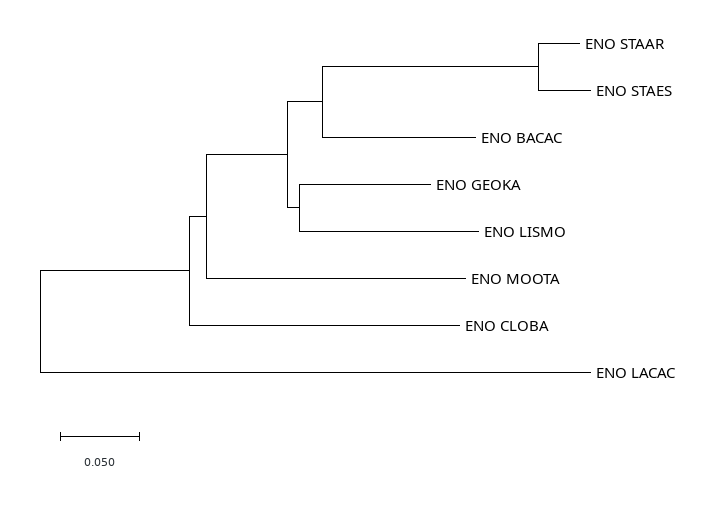
Рис.3 MEGA, метод минимальной эволюции
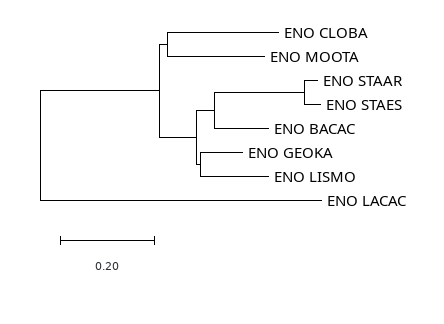
Рис.4 FastME, метод минимальной эволюции

Рис.5 "Исходное" дерево