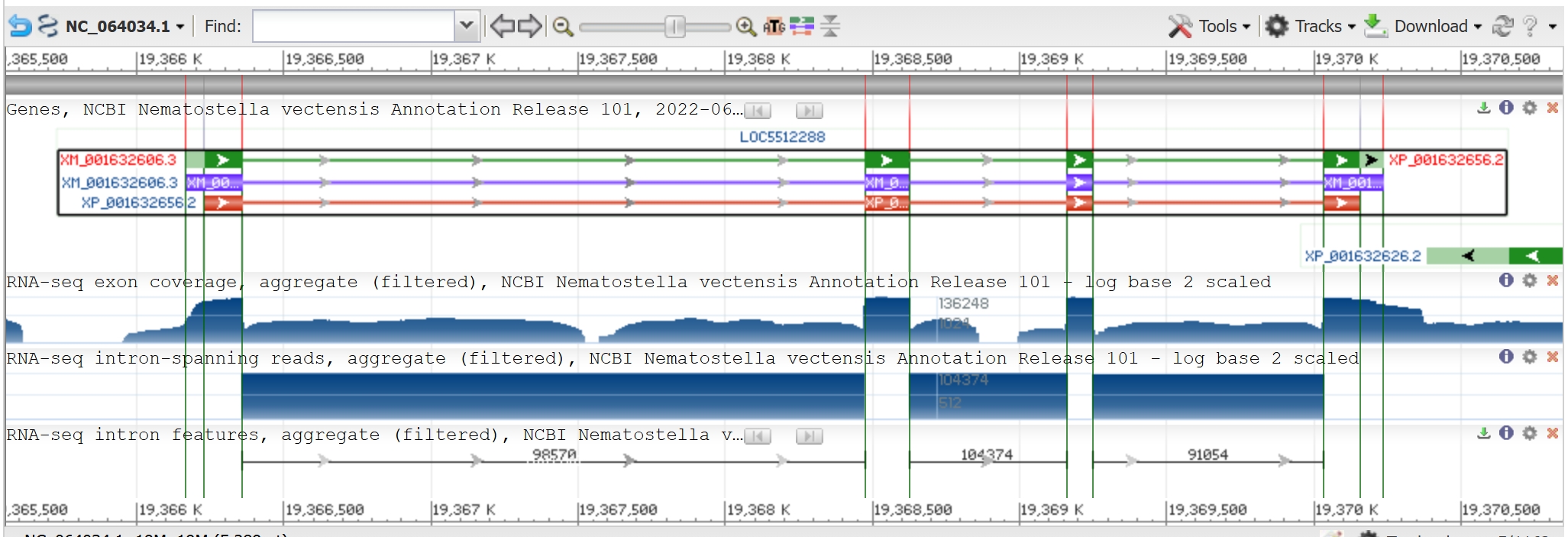
Среди белковых последовательностей Nematostella vectensis одна (XP_001632656) была идентифицирована как δ-субъединица АТФ-синтазы. Этот белок закодирован на участке NC_064034 первой хромосомы.

Nematostella vectensis (звездчатая актиния) относится к типу Стрекающие (Cnidaria). Для поиска отдалённых гомологов выбран таксон Apoidea (Пчёлы) – первичноротые, эволюционно удалённая группа; в RefSeq насчитывается 38 полностью секвенированных геномных сборок пчёл. В качестве запроса использована нуклеотидная последовательность гена δ-субъединицы АТФ-синтазы N. vectensis (XM_001632606.3). Поиск выполнен на NCBI BLAST с базой данных refseq_genomes, ограниченной таксоном Apoidea.
Для поиска отдалённых гомологов метод tblastx значительно эффективнее blastn, так как он опирается на аминокислотную консервативность.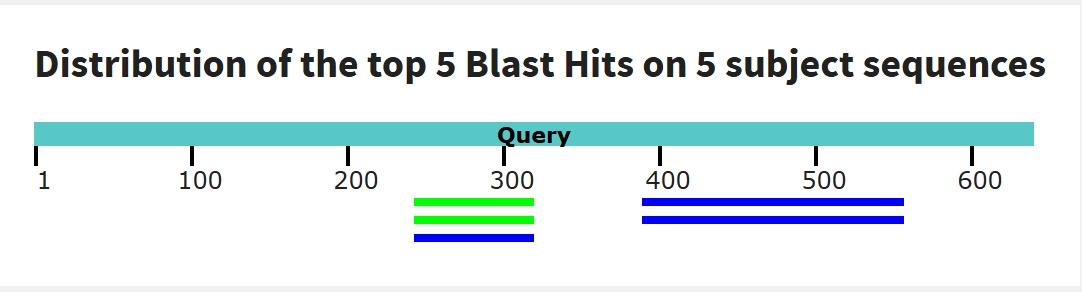
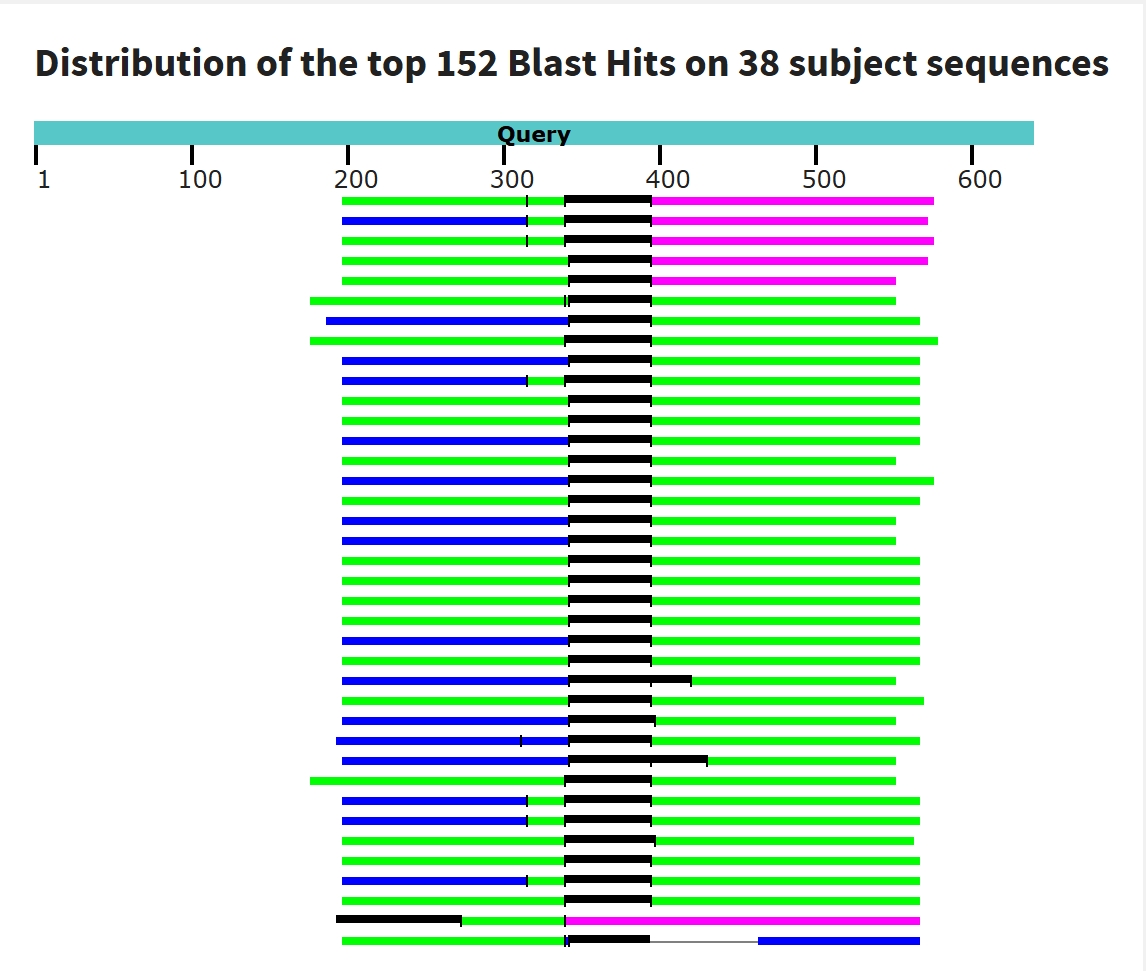
При поиске с помощью tblastx обнаружено 152 хита на 38 геномных сборок, значительно длиннее, чем при использовании blastn. Качество также заметно выше. Это объясняется тем, что tblastx сравнивает последовательности на уровне белков, где консервативность выше.
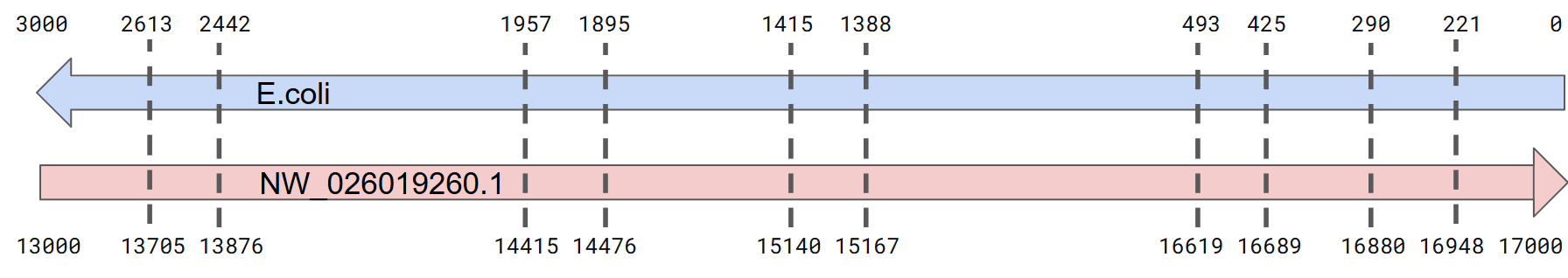
Далее нужно было найти в геномной сборке Nematostella vectensis гомологи двух рРНК E. coli — 16S и 23S. Сначала последовательности генома были проиндексированы на своем компьютере с помощью команды:
makeblastdb -in GCF_932526225.1_jaNemVect1.1_genomic.fna -dbtype nucl -out Nematostella
Получив локальную базу данных, был проведен поиск с использованием алгоритма blastn для 16S и 23S рРНК. Для повышения чувствительности использовался параметр -word_size 7.Команды:
blastn -query e.coli_16S.txt -db Nematostella -word_size 7 -outfmt 7 -out 16S.txt blastn -query e.coli_23S.txt -db Nematostella -word_size 7 -outfmt 7 -out 23S.txt
Результаты для 16S рРНК(16S.txt):: обнаружено 383 хита в 10 гомологах
Результаты для 23S рРНК(23S.txt): обнаружено 372 хита в 15 гомологах
Для построения карт локального сходства были выбраны два полностью секвенированных генома бактерий рода Mycoplasmoides: Mycoplasmoides pneumoniae (NZ_CP010546.1) и Mycoplasmoides genitalium (NZ_CP159789.1). Эти организмы являются близкими родственниками, но имеют существенные различия в размере генома и наборе генов. Карты построены на сайте NCBI BLAST с помощью инструмента «Align two sequences».
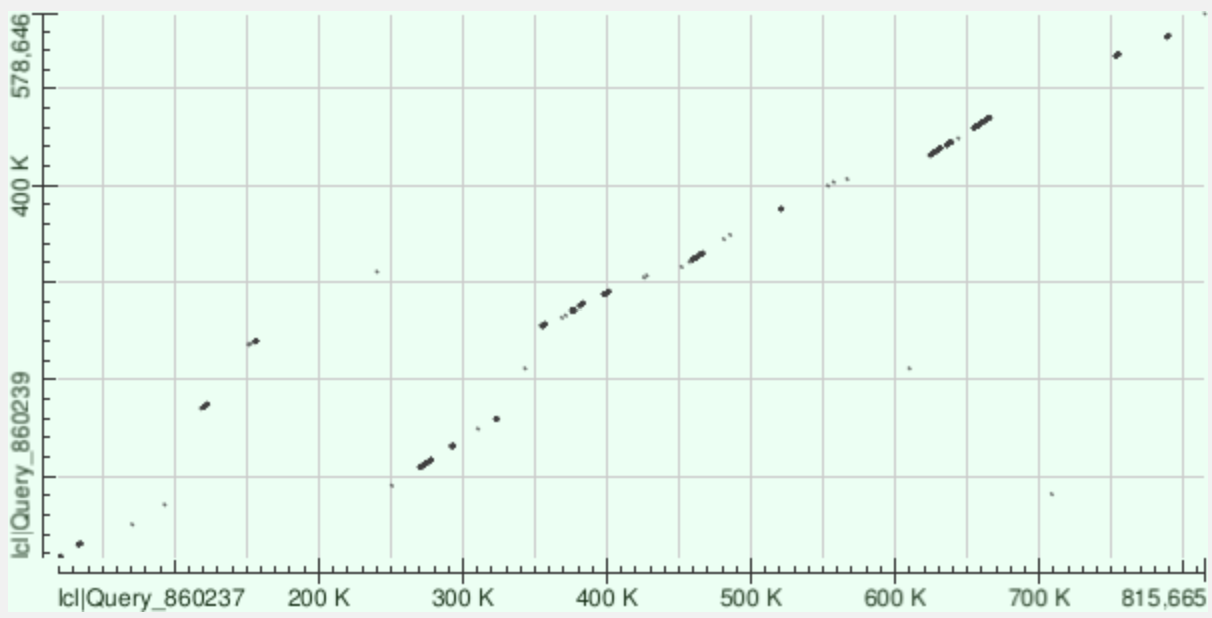
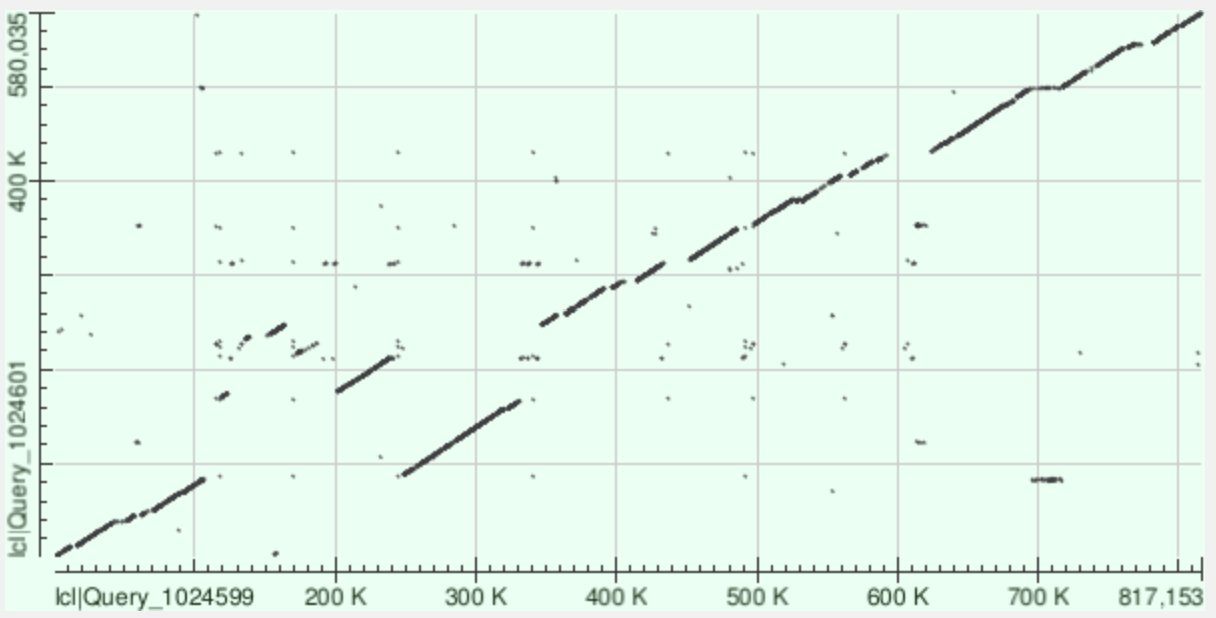
Основные геномные перестройки, выявленные на карте blastn:
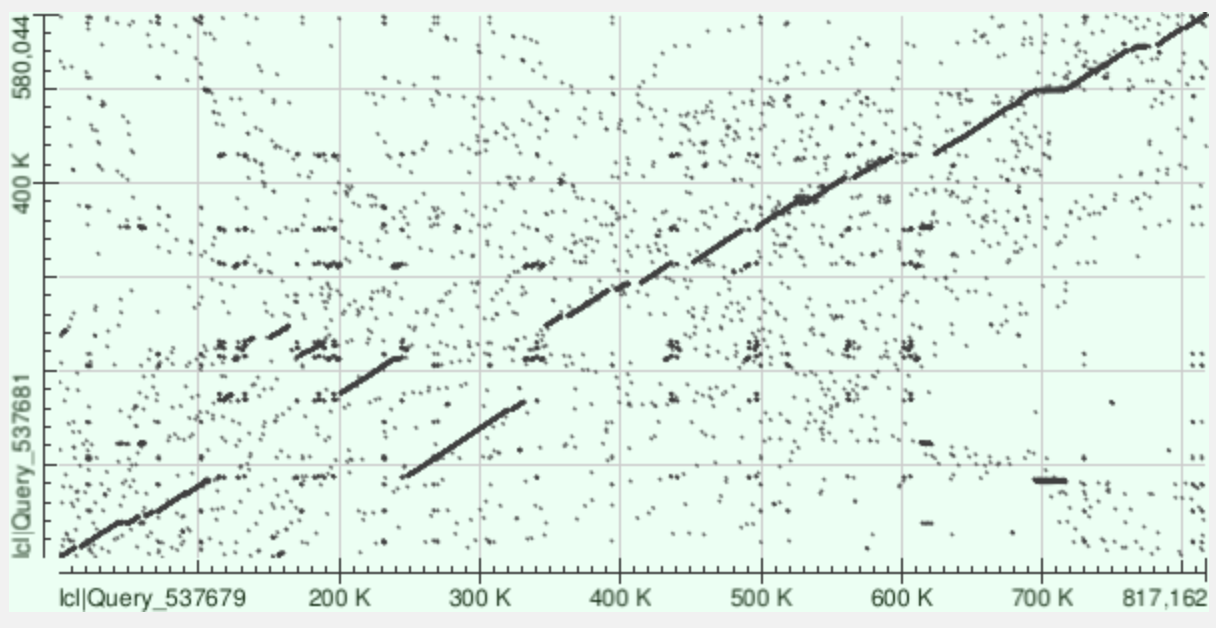
В карте blastn наблюдаются две основные перестройки: делеция в районе 600 т.п.н. (разрыв диагонали, указывающий на утрату этого участка у M. pneumoniae) и транслокация в районе 250-350 т.п.н.