Практикум 4.
Составление списка гомологичных белков, включающих паралоги
Из директории /P/y22/term4/Proteomes на кодомо я скопировала к себе в рабочую диреткорию файлы с протеомами 7 бактерий:
Затем в протеомах данных бактерий были найдены гомологи белка CLPX_ECOLI с помощью программы blastp с порогом E-value 0.0001
cat *.fasta > all_sequences.fasta #объединила все протеомы в один файл
makeblastdb -in all_sequences.fasta -dbtype prot -out proteomes #создание базы данных из протеомов бактерий
blastp -query ECOLI.fasta -db proteomes -outfmt 6 -evalue 0.0001 -out res.txt #запуск blastp с табличным форматом выдачи и порогом E-value 0.0001
В результате выполнения приведенных выше команд получила список найденных последовательностей: находки из выдачи blastp
Реконструкция и визуализация
Затем из файла all_sequences.fasta были получены найденные последовательнсоти с помощью скрипта и осуществленно выравнивание программой muscle. Затем на kodomo программой FastME (алгоритм которой основан на принципе минимальной эволюции (Minimum evolution)) было реконструированно дерево найденных гомологов.
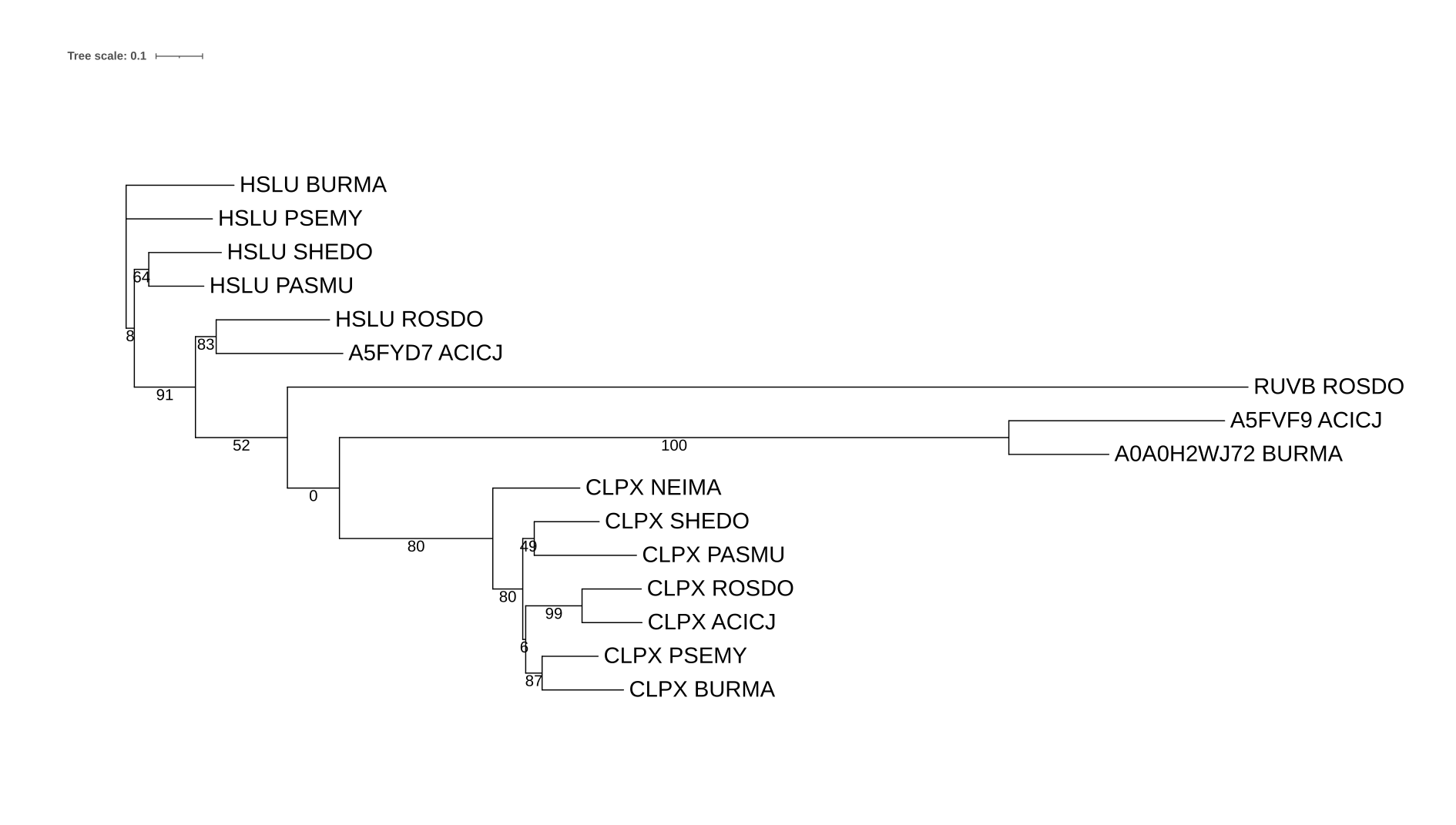
Для дерева на рисунке 1 была составлена формула Newick
Затем дерево было укоренено в среднюю точку.
Если считать это дерево верно реконструированным, примерами ортологов (гомолочиные белки из разных организмов, разделение произошло в результате видообразования) являются: HSLU BURMA и HSLU PSEMY, CLPX SHEDO и CLPX ROSDO, CLPX NEIMA и CLPX SHEDO.
Примерами паралогов (два гомологичных белка из одного организма) являются: HSLU ROSDO и CLPX ROSDO, HSLU BURMA и CLPX BURMA, HSLU SHEDO и CLPX SHEDO.

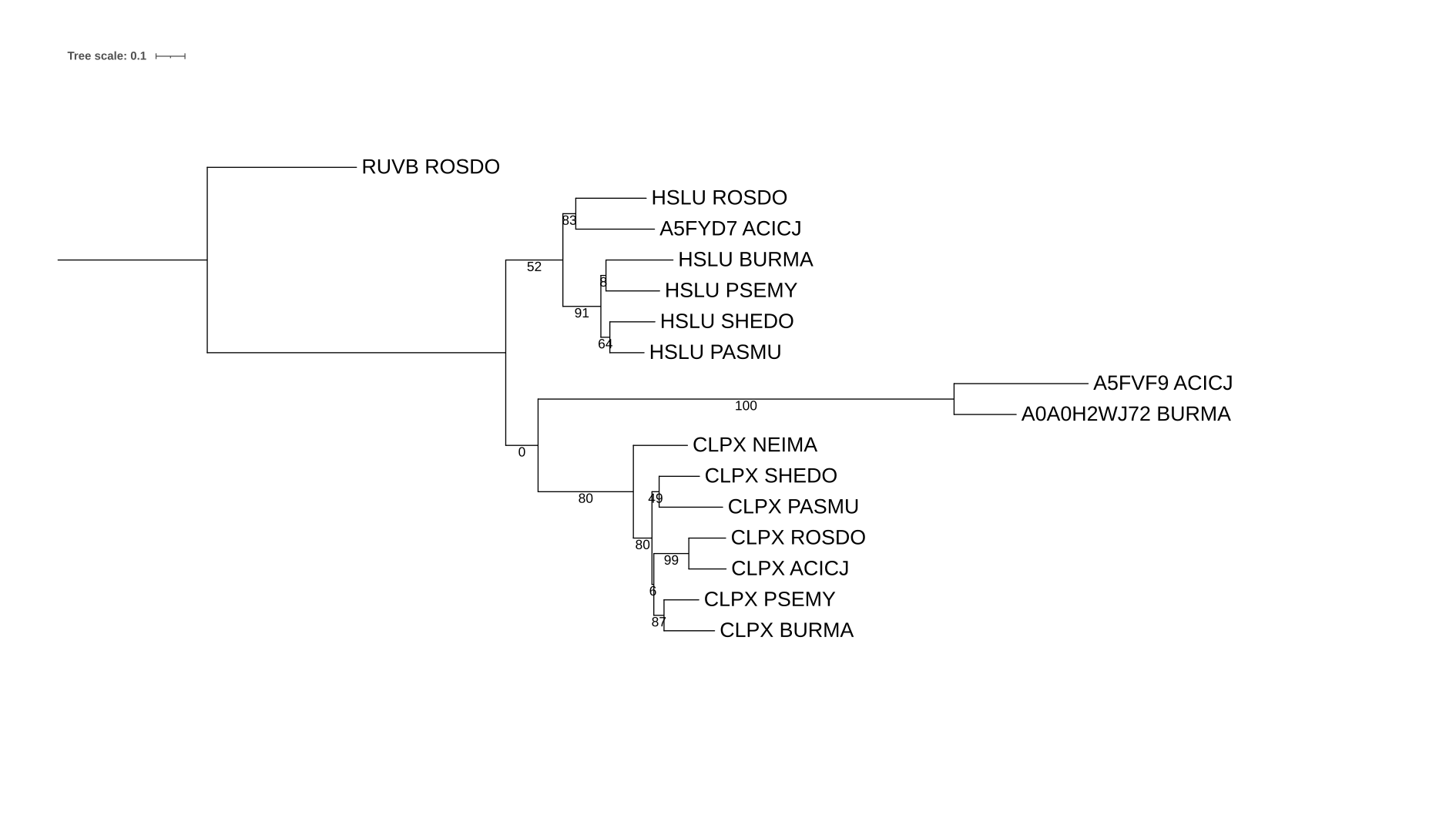
На рисунке 3 представлены две ортологические группы (то есть наборы попарно ортологичных белков), которые раскрашены фиолетовым (белки HSLU) и голубым (белки CLPX).

На рисунке 4 схлопнуты выбранные ранее ортологические группы.
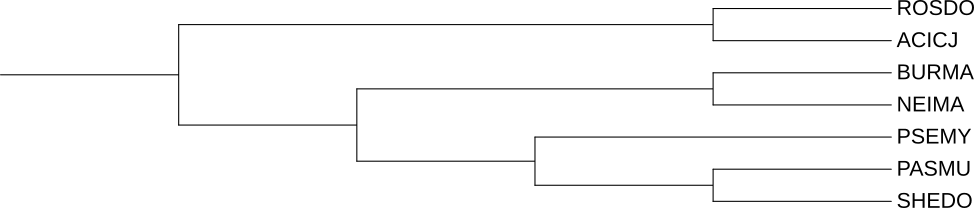
На рисунке 5 представлено дерево, отражающее верную филогению выбранных бактерий. Сравнивая рисунок 3 и рисунок 5, можно заметить, что в группе HSLU представлены белки 6 бактерий. Филогения белков почти точно отражает филогению бактерий, за исключением клады (HSLU BURMA, HSLU PSEMY). На филогенетическом дереве бактерий от общего предка сначала отходит BURMA, потом PSEMY, а на дереве белков HSLU BURMA и HSLU PSEMY являются сестринскими группами. В группе CLPX представлены все 7 исследуемых бактерий, но филогения белков сильно отличается от правильной филогении бактерий. Проще написать то, что совпало: CLPX SHEDO и CLPX PASMU, а также CLPX ROSDO и CLPX ACICJ объединены в сестринские группы.