Практикум 7. Трансмембранные белки.
Трансмембранный белок с β-листом (β-баррельный белок)
В рамках данного практикума было необходимо познакомиться с OPM (Orientations of Proteins in Membranes) - базой данных, предоставляющей пространственную ориентацию мембранных белков в липидном бислое.
Система классификации белков в OPM построена по иерархическому типу, включая следующие ступени: "Type" (тип), "Class" (класс), "Superfamily" (надсемейство) и "Family" (семейство). Все мембранные белки по способу взаимодействия с липидным бислоем делятся на три основных типа: трансмембранные, монотопические/периферические (постоянно связаны с только одним слоем липидов мембраны/временно связанные с мембраной) и мембрано-активные пептиды (короткие молекулы, которые приобретают трехмерную структуру при контакте с мембраной). Класс определяется общей архитектурой трансмембранного домена (α-спираль или β-лист), надсемейство объединяет белки с общим эволюционным происхождением, а семейство - более узкую группу со сходной последовательностью и функцией.
OPM ссылается на следующие базы данных: PDB, PDB Sum, MSD (Macromolecular Structure Database), MMDB (Molecular Modeling Database), EncoMPASS (Encyclopedia of Membrane Proteins Analyzed by Structure and Symmetry), Uniprot, TCDB (Transporter Classification Database), Pfam / InterPro, а также NCBI.
Информация о выбранном белке:
- Белок: Attachment invasion locus protein
- PDB ID: 3qra
- UniProt: Q8D0Z7_YERPE
- Type: Transmembrane
- Class: Beta-barrel transmembrane
- Superfamily: OmpA-OmpF porin family
- Family: Enterobacterial Ail/Lom protein
- Организм: Yersinia pestis
- Локализация: наружная мембрана грамм-отрицательной бактерии
Трансмембранный α-спиральный белок.
В рамках данного задания было необходимо сравнить результаты предсказаний трансмембранных участков по последовательности (с помощью DeepTMHMM) и по трехмерной структуре (база данных OPM) в α-спиральном белке.
Информация о выбранном белке:
- Белок: Глицеринпроводящий канальный белок (Glycerol uptake facilitator, GlpF)
- PDB ID: 1ldf
- UniProt: GLPF_ECOLI
- Type: Transmembrane
- Class: Alpha-helical polytopic
- Superfamily: Major Intrinsic Protein (MIP)/FNT superfamily
- Family: Major intrinsic protein (MIP) family
- Класс: Alpha-helical polytopic
- Организм: Escherichia coli
- Локализация: внутренняя мембрана грамм-отрицательной бактерии
- Функция: Транспорт глицерина через цитоплазматическую мембрану, имеет ограниченную проницаемость для воды и малых незаряженных молекул.
| № спирали | Координаты (OPM) |
|---|---|
| 1 | 11–32 |
| 2 | 41–59 |
| 3 | 86–107 |
| 4 | 145–166 |
| 5 | 179–195 |
| 6 | 233–251 |
Для запуска DeepTMHMM была скачана последовательность данного белка из Uniprot.
Результаты выдачи DeepTMHMM представлены здесь.
| № спирали | Координаты (DeepTMHMM) |
|---|---|
| 1 | 15–32 |
| 2 | 46–62 |
| 3 | 90–107 |
| 4 | 146–166 |
| 5 | 177–197 |
| 6 | 230–250 |
На рисунке 1 в верхней части представлена наиболее вероятная топология, по оси х указаны координаты последовательности, а по оси у - локализация (синяя линия - внеклеточная локализация, розовая - внутриклеточная, красные столбцы - трансмембранная). В нижней части представлена вероятность расположения (внеклеточного, трансмембранного и внутриклеточного) каждой позиции последовательности белка.
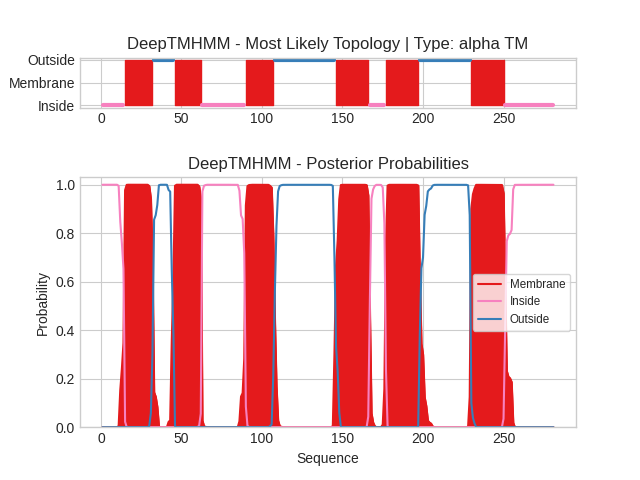
Сравнивая координаты в таблице 1 и в таблице 2, можем сделать вывод, что DeepTMHMM и OPM идентифицировали одинаковое количество трансмембранных спиралей (6). Расхождения в границах составляют 1-5 аминокислот, что объясняется различиями в методах (предсказание по последовательности и по трехмерной структуре). Несмотря на небольшие отклонения, координаты всех 6 трансмембранных α-спиралей предсказанны DeepTMHMM корректно и совпадают с данными OPM.