Краткий обзор генома и протеома бактерии Rummeliibacillus stabekisii
Введение
Rummeliibacillus stabekisii — это грамположительная, спорообразующая бактерия из класса Bacillus, типа Firmicutes, принадлежащая к новому роду Rummeliibacillus, выделенному на основании значительных различий в последовательности 16S рРНК и геномном анализе. Этот микроорганизм впервые был выделен из различных географических источников, включая чистое помещение в Payload Hazardous Servicing Facility Космического центра Кеннеди (штаммы KSC-SF6g^T, M32 и NBRC 12622)[1], а позднее — из антарктических почв (штамм РР9)[2].
Геном R. stabekisii содержит многочисленные адаптивные гены, обеспечивающие устойчивость к окислительному стрессу, ультрафиолетовому излучению, засухе и другим неблагоприятным факторам. Он также кодирует ферменты, способствующие синтезу экзополисахаридов для формирования биопленок, повышающих защиту бактерии в суровых условиях. Эти геномные особенности тесно связаны с метаболической гибкостью бактерии и её экологической универсальностью[2][3].
Систематическое положение R. stabekisii[4]:
- Домен: Bacteria
- Отдел: Firmicutes
- Класс: Bacillus
- Порядок: Bacillus
- Семейство: Caryophanaceae
- Род: Rummeliibacillus
- Вид: Rummeliibacillus stabekisii
Методы и материалы
Данные о геноме и протеоме R. stabekisii были взяты с сайта Национального Центра Биотехнологической информации (NCBI)[5]. Анализ последовательностей и визуализация результатов выполнены с использованием Google Sheets.
- Для исследования общей характеристики генома R. stabekisii использовалась таблица S1 (листы: gene_localization, per-replicones, gene_distribution_strand_chromosome, gene_distribution_strand_plasmid).
- Для исследования длины белков R. stabekisii использовалась таблица S2 (листы: prot_lengths, prot_lengths_hist).
- Для анализа промежутков между генами на хромосоме использовалась таблица S1 (листы: strand_plus_chromosome, strand_minus_chromosome, inter_cds(+)_intervals-hist, intersecting_cds(+)-hist, inter_cds(-)_intervals-hist, intersecting_cds(-)-hist). Для более детального анализа больших пересечений был составлен рейтинг самых больших пересечений среди двух цепей, далее начиная с самого большого пересечения искались пары генов, не содержащие в своем составе гипотетический белок. Таким образом были отобраны топ-3 самых больших пересечения, о которых подробнее описано в соответствующем подразделе результатов.
Все вышеперечисленные материалы можно найти в разделе "Сопроводительных материалов".
Результаты и обсуждение
1. Общая характеристика генома Rummeliibacillus stabekisii
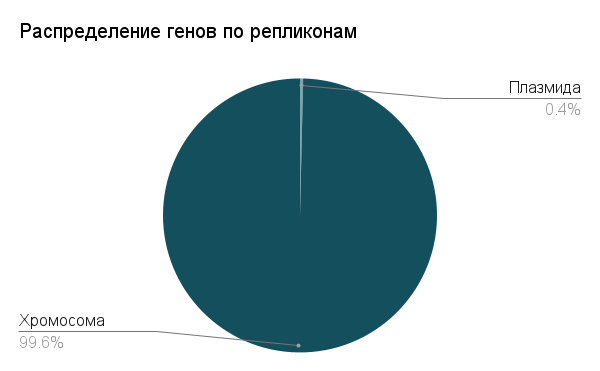
Геном R. stabekisii содержит 1 кольцевую хромосому и плазмиду pPP9.
На хромосоме расположено в общей сложности 3529 гена из которых можно выделить четыре основные категории кодирующих элементов: белок-кодирующие гены (protein), гены транспортных РНК (тРНК), рибосомных РНК (рРНК) и псевдогены. Также были выявлены некоторые другие последовательности, не относящиеся к данным категориям. А именно, ген SRP RNA (1 шт.), некодирующая РНК, составляющая ядро сигнального распознающего частицы (SRP), которая обеспечивает котрансляционную транспортировку белков с сигнальными пептидами к мембранам[6]. Также был выявлен ген tmRNA (транспортно-матричная РНК, участвующая в механизме транс-трансляции[7], (1 шт.). Также были выявлены гены ncRNA (3 шт.) — класс РНК-молекул, не подвергающихся трансляции в белки, выполняющих регуляторные, каталитические и структурные функции в клетке[8]. И, в конце концов, обнаружена RNase P (1 шт.) (эндорибонуклеаза Р, рибозим, функция — расщепление РНК)[9].
Таблица 1. Распределение генов различных классов по плазмиде и хромосоме, а также численное соотношение генов данных классов в геноме, выраженное в процентах.
| protein | tRNA | rRNA | tmRNA | ncRNA | RNase P RNA | SRP RNA | pseudogene | |
|---|---|---|---|---|---|---|---|---|
| chromosome | 3335 | 101 | 36 | 1 | 3 | 1 | 1 | 51 |
| plasmid (pPP9) | 13 | 0 | 0 | 0 | 0 | 0 | 0 | 0 |
| % содержания в геноме | 94.5 | 2.9 | 1 | 0.03 | 0.08 | 0.03 | 0.03 | 1.4 |
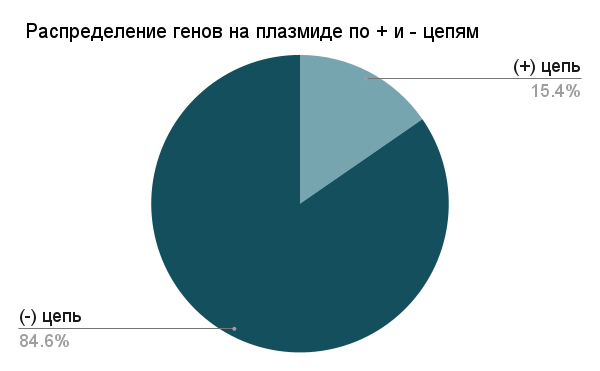
Далее было проанализировано распределение генов по прямой и обратной цепям ДНК как на хромосоме, так и на плазмиде. На хромосоме наблюдается близкое к равномерному распределение генов между цепями. На плазмиде, напротив, гены преимущественно локализованы на минус-цепи, что представляет собой статистически значимое отклонение, требующее статистической обработки для подтверждения неслучайности и дальнейшего анализа возможных причин такой асимметрии.
 и (-) цепям.png)
2. Длины белков R. stabekisii
С целью выявления общей картины о белках бактерии было проведено распределение протеинов по их длине. Результатом является гистограмма (рис. 4). Также были выявлены следующие моменты. Белок с минимальной длиной среди всех продуктов трансляции — предполагаемый холин-подобный токсин (putative holin-like toxin), длина этого белка составляет 27 аминокислотных остатков. Белок с максимальной длиной — SpaA isopeptide-forming pilin-related protein, состоящий из 1781 аминокислотных остатков. Анализируя данные, можно заключить, что пик длин пришелся на значения между 140 и 170 аминокислотными остатками. Для более полного представления были посчитаны средняя длина всех протеинов бактерии, которая составила 280 аминокислотных остатков и медиана длин белков — 241 аминокислотных остатков.
.png)
3. Анализ промежутков между генами на хромосоме
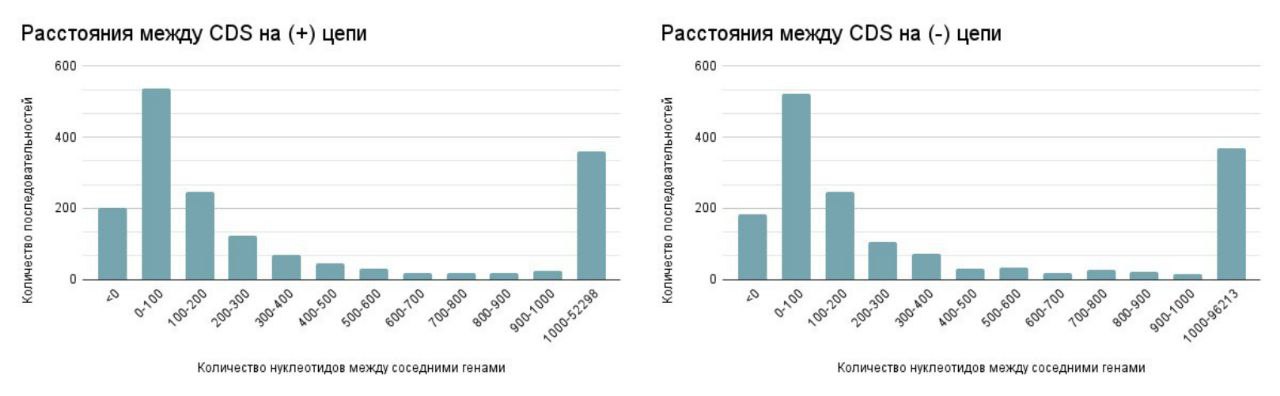
В данном разделе рассматривается статистика межгенных промежутков на + и - цепях хромосомы. Как видно на рис. 5, пики длин промежутков на обеих цепях пришелся на значения от 0 до 100 нуклеотидов. Также были выявлены отрицательные интервалы, что говорит о наличии пересекающихся генов.
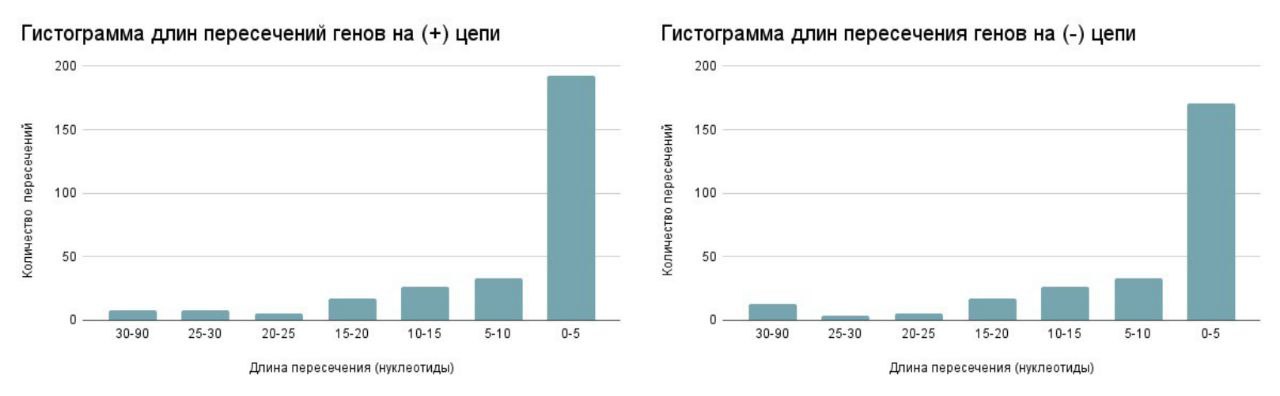
На рис. 6 данные пересечения рассмотрены детальнее. Можно заметить, что наиболее частое значение пересечения приходится на промежуток от 0-10 нуклеотидов. Но также встречаются и довольно большие перекрывания вплоть до 86 нуклеотидов. Далее был проведен более детальный анализ больших пересечений (см. раздел "Методы и материалы"). После чего было установлено, что 3 самых длинных пересечения между генами с известной функцией являются пересечениями одной пары генов, а именно replication-relaxation family protein и FtsK/SpoIIIE domain-containing protein. Что может говорить о тесной связи между этими генами и вероятном участии в неком общем механизме.
Также на первый взгляд может показаться, что значения пересечений на (+) цепи и (-) цепи схожи, но при более детальном анализе выяснилось, что это не совсем так. А именно, среднее значение длины пересечения 9,77, а медиана составила 4 нуклеотида. В то же время на (-) цепи среднее значение пересечения составило 11,05, а медиана — уже 8 нуклеотидов. Из чего можно сделать вывод о более плотной упаковке генома на (-) цепи.
Возможные дальнейшие исследования
Из предыдущих исследований R. stabekisii видно, что она обладает адаптациями для выживания в разнообразных экстремальных условиях, что обусловлено наличием множества адаптивных генов. Поэтому целесообразно проанализировать наличие специфических генных локусов, кодирующих белки для адаптации к определенным видам стресса, изучить их расположение и сравнить с аналогичными локусами в геномах других бактерий, адаптированных к тому же стрессу. Это позволит выявить общие тенденции организации таких генов и использовать их для предсказания адаптационных возможностей у новых изолятов.
Список литературы
- Vaishampayan P. et al. Description of Rummeliibacillus stabekisii gen. nov., sp. nov. and reclassification of Bacillus pycnus Nakamura et al. 2002 as Rummeliibacillus pycnus comb. nov //International journal of systematic and evolutionary microbiology. – 2009. – Т. 59. – №. 5. – С. 1094-1099.
- da Mota F. F. et al. Whole-genome sequence of Rummeliibacillus stabekisii strain PP9 isolated from Antarctic soil //Genome Announcements. – 2016. – Т. 4. – №. 3. – С. 10.1128/genomea.00416-16.
- Ильина Т. С., Романова Ю. М. Бактериальные биопленки: роль в хронических инфекционных процессах и поиск средств борьбы с ними //Молекулярная генетика, микробиология и вирусология. – 2021. – Т. 39. – №. 2. – С. 14-24.
- Таксономия R. stabekisii: https://www.ncbi.nlm.nih.gov/datasets/taxonomy/241244/names/
- Данные NCBI по геному бактерии R. stabekisii: https://ftp.ncbi.nlm.nih.gov/genomes/all/GCF/001/617/605/GCF_001617605.1_ASM161760v1
- Nagai K. et al. Structure, function and evolution of the signal recognition particle //The EMBO journal. – 2003.
- Keiler K. C. Biology of trans-translation //Annu. Rev. Microbiol. – 2008. – Т. 62. – №. 1. – С. 133-151.
- Statello L. et al. Gene regulation by long non-coding RNAs and its biological functions //Nature reviews Molecular cell biology. – 2021. – Т. 22. – №. 2. – С. 96-118.
- Wilhelm C. A. et al. Bacterial RNA-free RNase P: Structural and functional characterization of multiple oligomeric forms of a minimal protein-only ribonuclease P //Journal of Biological Chemistry. – 2023. – Т. 299. – №. 11.
Сопроводительные материалы
📊 S1. Genomic features of Rummeliibacillus stabekisii 📊 S2. CDS from genome of Rummeliibacillus stabekisii