Совмещение структур
Задание 1
В данном задании нужно было найти структурные гомологи выбранного белка и отобрать 2-3 из них с помощью сервиса PDBeFold. Я работала с цепью А алкоголь-дегидрогеназы (организм: Vanderwaltozyma polyspora) с PDB-идентификатором: 5z2x. Отобрала 3 гомолога, которые соответствуют критериям: RMSD между 0.8 и 2.5 и длина выравнивания более 70% от длины моего белка (342 остатка). Результаты представлены в таблице 1.
Таблица 1. Краткая характеристика найденных гомологов
| Название | PDB-ID | Организм | RMSD | Nres | Nalign | % (Nalign/N моего белка) |
| Methylglyoxal/ isovaleraldehyde reductase Gre2 | 4pvc:A | Saccharomyces cerevisiae S288C | 1.30 | 342 | 325 | 95% |
| Cinnamyl-Alcohol Dehydrogenase 2 | 4qtz:A | Medicago truncatula | 1.97 | 321 | 285 | 83.3% |
| Aldehyde reductase 2 | 1ujm:A | Sporidiobolus salmonicolor | 1.80 | 342 | 281 | 82.2% |
Задание 2
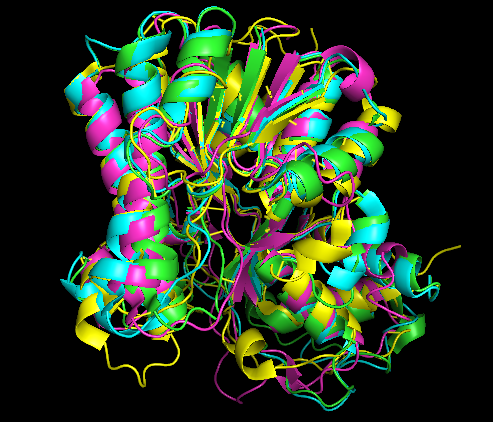
В данном задании необходимо было совместить полученные структуры и сравнить выравнивания (структурное и по последовательности). С помощью PDBeFold были получены: файл с совмещёнными структурами (ссылка) (рис. 1) и структурное выравнивание гомологов (ссылка) (рис. 2). По файлу со структурами можно сделать вывод, что большинство α-спиралей хорошо совпадают, однако, есть существенные различия в одной α-спирали: она совпадает лишь в 2 структурах (5z2x; 4pvc), в белке 4qtz в данных позициях - петля. β-тяжи неплохо совместились, в то время как петли совмещаются значительно хуже.
Рис. 1 - Совмещенные структуры (5z2x: зеленый цвет; 4pvc: синий цвет; 4qtz: розовый цвет; 1ujm: желтый цвет)
 |
С помощью JalView было получено выравнивание по последовательностям. На рисунках 2 и 3 представлены выравнивания - по структуре и по последовательности. Выравнивания очень похожи, у них немного отличий. Можно отметить то, что выравнивание Muscle содержит чуть меньше гэпов.
Рис. 2 - Структурное выравнивание белков
 |
Рис. 3 - Выравнивание белков Muscle
 |
На рисунках 4 и 5 представлены фрагменты, выбранные для подробного анализа: как можно заметить, первая колонка - абсолютно консервативная в случае структурного выравнивания, в отличие от Muscle. Я рассмотрела эти фрагменты в совмещении структур (рис. 6). В данном случае я думаю, что структурное выравнивание оказалось правильным, так как β-тяж 4qtz, чья последовательность оказалась сдвинута в выравнивании Muscle, хорошо наложился на первые 2 структуры в целом и, особенно, в том конце, который соответствует обсуждаемому аргинину.
Рис. 4 и 5 - Выбранный фрагмент выравниваний: структурное и Muscle

 |
Рис. 6 - Совмещенные фрагменты структур (5z2x: зеленый цвет; 4pvc: синий цвет; 4qtz: розовый цвет; 1ujm: желтый цвет)

 |