Рис 1. Дерево гомологичных белков бактерий отдела Pseudomonadota, реконструкция FastME, модель MtREV, бутстреп 100.
Из директории /P/y22/term4/Proteomes на kodomo были выбраны полные протеомы 8 бактрий отдела Pseudomonadota, со следующими мнемониками:
В выбранных протеомах найдем достоверные гомологи белка CLPX_ECOLI.
Объединим протеомы в один файл:
cat /P/y22/term4/Proteomes/ACICJ.fasta /P/y22/term4/Proteomes/BRUSU.fasta /P/y22/term4/Proteomes/POLAQ.fasta /P/y22/term4/Proteomes/THIDA.fasta /P/y22/term4/Proteomes/NEIMA.fasta /P/y22/term4/Proteomes/ROSDO.fasta /P/y22/term4/Proteomes/PASMU.fasta /P/y22/term4/Proteomes/PSEMY.fasta > bact.fasta
Создадим базу данных для blast:
makeblastdb -in bact.fasta -dbtype prot -out my_db
Проведем blastp:
blastp -db my_db -query CLPX_ECOLI.fasta -out results -evalue 0.0001
Список находок из выдачи BLAST
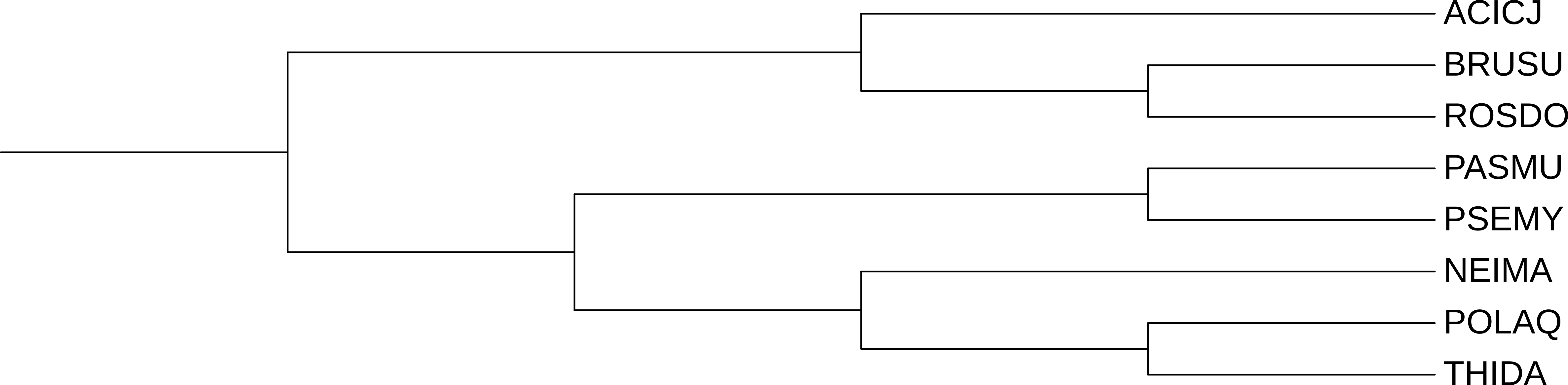
Реконструируем дерево найденных гомологов (рис 1) (скобочная формула Newick).

Укажем несколько пар ортологов (белки из разных организмов, которые разделились при видообразовании):
Несколько пар паралогов(два гомологичных белка из одного организма):
Раскрасим ортологичные группы в разные цвета (рис 2).
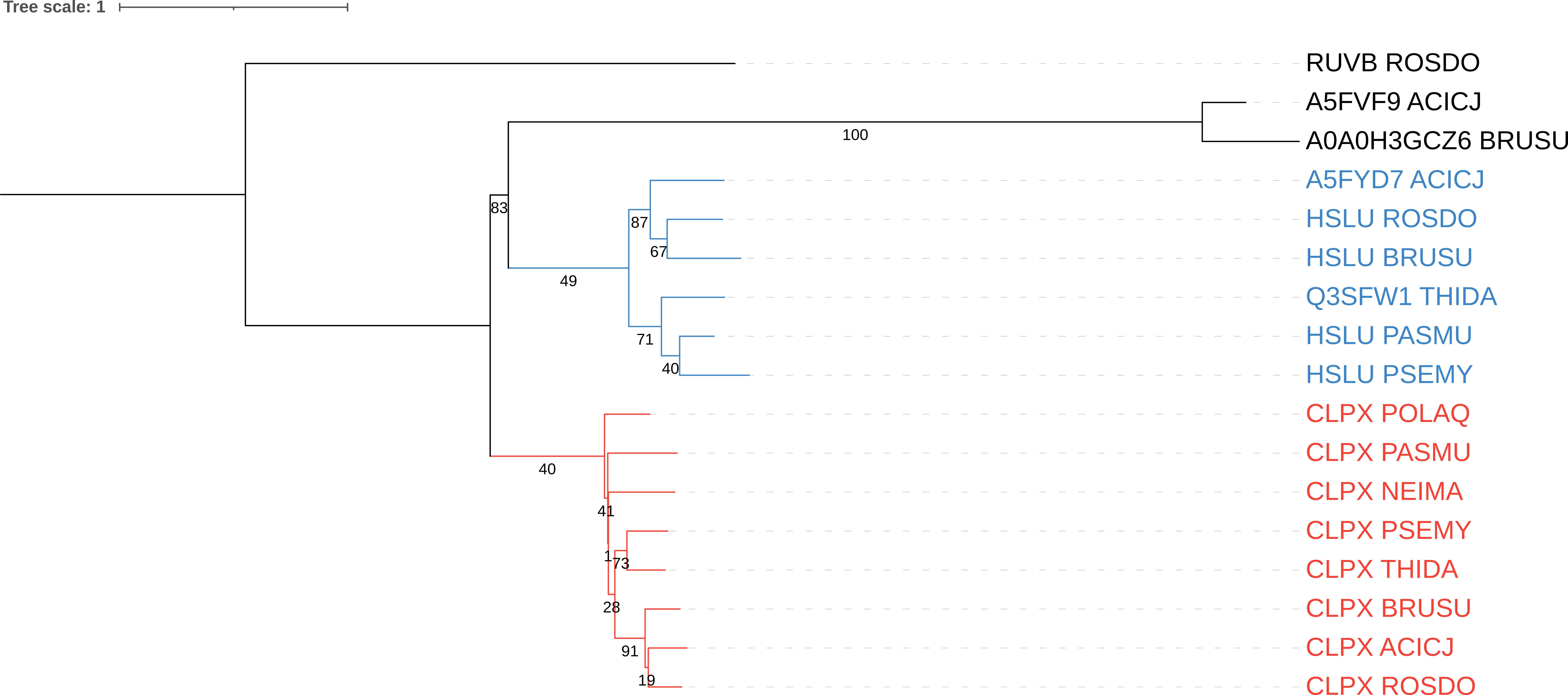
Схлопнем монофилетические группу ортологов CLPX и HSLU (A5FYD7 и Q3SFW1 также относится к HSLU) (рис 3). В группу CLPX попадают все 8 рассматриваемых бактерий. Группа ортологов HSLU содержит 6 бактерий (ACICJ, BRUSU, ROSDO, THIDA, PSEMY, PASMU).
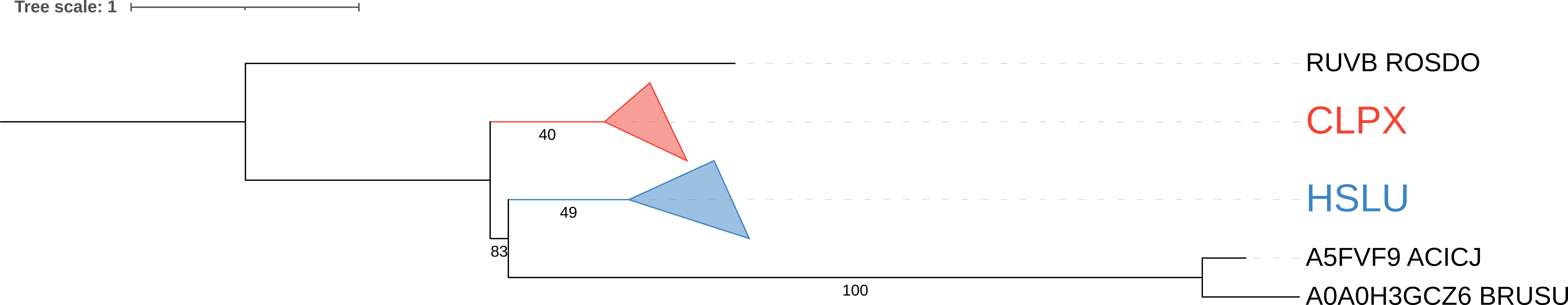
Сравним нашу реконструкцию с референсным деревом (рис 4).
Ортологическая группа HSLU, представленная шестью организмами, реконструировалась в полном соответствии дереву на рисунке 4.
С анализом ортологической группы CLPX все немного сложнее.
Нет ни одной клады, которая по топологии была бы верно реконструирована. Есть клада (BRUSU,ROSDO,ACICJ), у которой достаточно большой бутстреп, и не зря, потому что на референсном дереве она тоже присутствует. Но топологически даже эта клада реконструирована неверно. Должны BRUSU и ROSDO образовывать кладу, а у нас ROSDO и ACICJ (но бутстреп этой ветви маленький, что подтвержает возможную недостоверность). В том числе эта группа из 3х организмов должна быть базальной ко всем остальным, а у нас это не соблюдается. Реконструкция остальных ветвей получилась с совершенно другой топологией, чем должна была, и с низкими бутстсрепами (даже есть ветвь с бутстрепом 1 - совсем плохо).