Филогения паралогов и ортологов у бактерий
Выбор видов и бласт
Для поиска гомологов для белка CLPX_ECOLI были выбраны вот эти протеомы бактерий:
- AROAE (Aromatoleum aromaticum)
- NEIMA (Neisseria meningitidis)
- POLAQ (Polaromonas sp.)
- PSEAE (Pseudomonas aeruginosa)
- ROSDO (Roseobacter denitrificans)
- SHEDO (Shewanella oneidensis)
- YERPE (Yersinia pestis)
Сгрузили их вместе, сделали по ним базу данных и по ней бластовали.
cat *.fasta > all_proteomes.fasta makeblastdb -in all_proteomes.fasta -dbtype prot -out pseudomonadota_db blastp -query CLPX_ECOLI.faa -db pseudomonadota_db -outfmt 6 -evalue 0.0001 -out clpx_homologs.txt
fastme -i ali_Seqs.phy -o p_dist_Seqs.tre -pp-distanceNewick дерева
Паралоги и ортологи
В Красной (HSLU) кладе 5 белков, в зелёной (CLPX) 7.
Примеры паралогов по построенному древу:
- RUVB ROSDO/ и CLPX ROSDO. RUVB участвует в комплексе, который разрешает структуру Холлидея, возникающую во время гомологичной рекомбинации у бактерий. Второй это АТФ-зависимая регуляторная субъединица протеазы ClpXP. Она поддерживает белковый гомеостаз, расщепляя неправильно свернутые белки.
- HSLU SHEDO и CLPX SHEDO. HSLU это субъединица АТФазы протеасомного комплекса деградации, она обладает шапероновой активностью. Вторая находка это АТФ-зависимый специфический компонент протеазы Clp, в присутствии ClpB тоже может проявлять шаперонную активность.
- HSLU YERPE и A0A5P8YB42 YERPE. Первый белок описан выше, а второй это белок семейства хелатаз магния.
Примеры ортологов по построенному дереву:
- HSLU ROSDO и HSLU PSEAE
- CLPX NEIMA и A0A5P8YCE6 YERPE
- CLPX AROAE и CLPX POLAQ
.png)
.png)
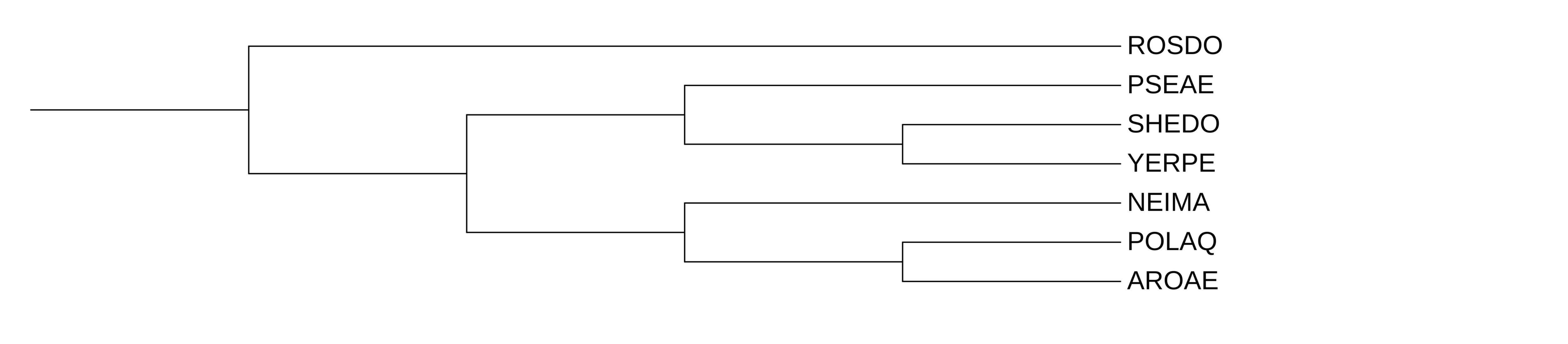
В зелёной кладе должна присутствовать ветвь, объединяющая NEIMA, POLAQ и AROAE в отдельную подкладу. Однако в построенном дереве наблюдается неверная топология: NEIMA отделяется от остальных последовательностей, включая POLAQ и AROAE. Данная ветвь имеет низкую bootstrap-поддержку (5), что указывает на её ненадёжность.
Красная клада полностью правильно восстановлена.