Работа в Pymol
from xmlrpclib import ServerProxy
import __main__
__main__.pymol_argv = [ 'pymol', '-x' ]
import pymol
pymol.finish_launching()
from pymol import cmd,stored
Для изучения возможностей Pymol как пакета для моделирования была выбрана модель лизоцима (1LMP)
cmd.reinitialize()
cmd.fetch('1lmp')
cmd.remove('solvent')
cmd.color('deepteal')
cmd.do('''
color deepsalmon, hetatm''')
cmd.zoom()
С помощью инструмента Sculpting можно изменять вручную структуру белка. Ниже представлены картинки до и после применения Wizard->Sculpting.
cmd.png(filename='pic_1.png',width='10cm',dpi=300, ray=1)
cmd.zoom()
cmd.png(filename='pic_2.png',width='10cm',dpi=300, ray=1)
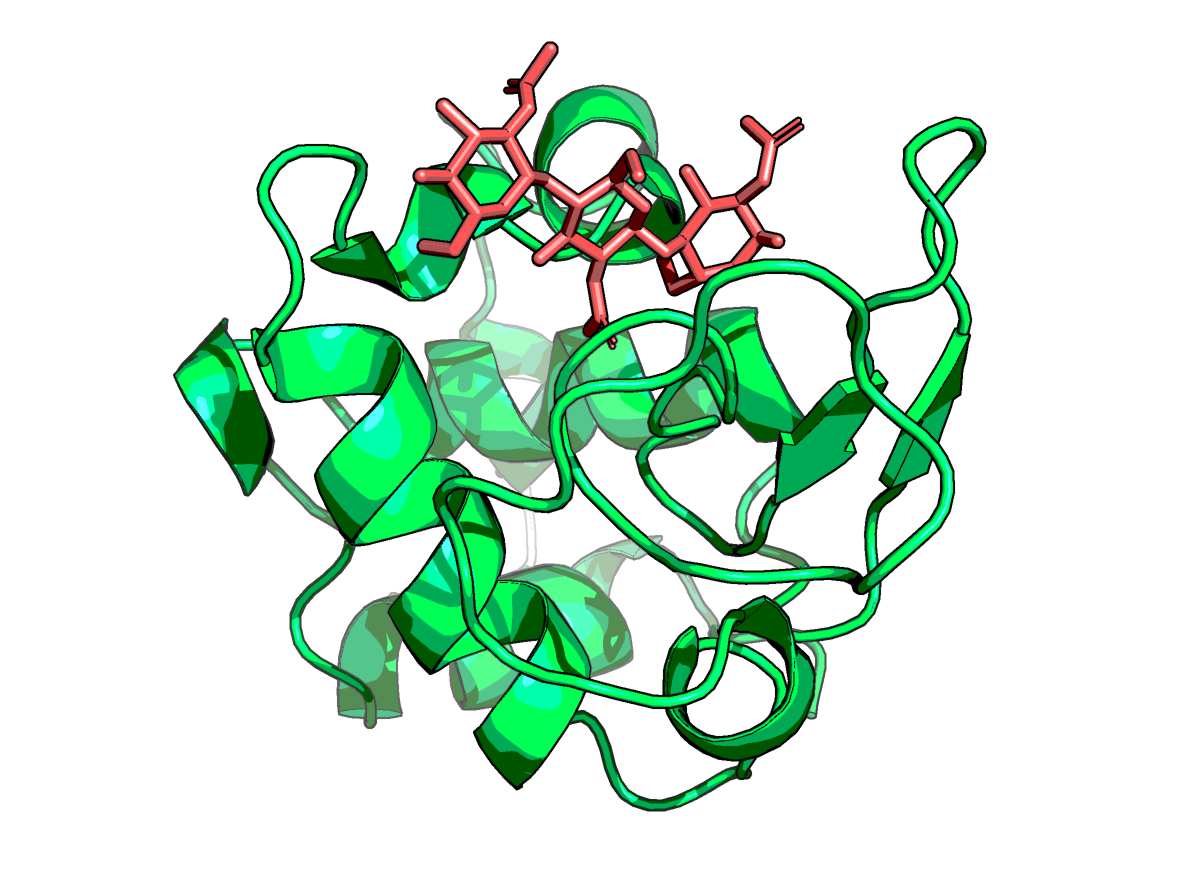 | 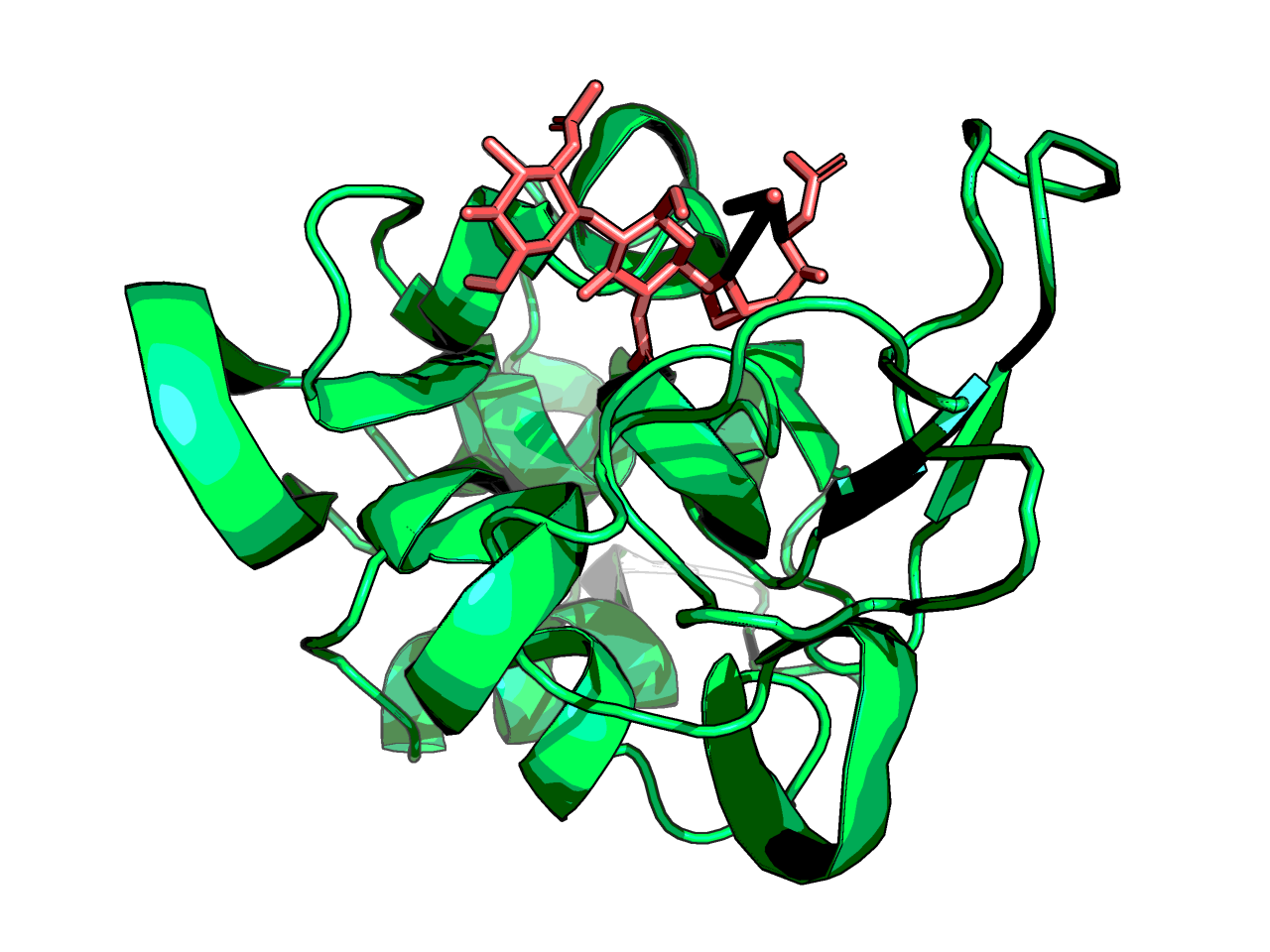 |
Хорошо видно, что с помощью данного инструмента можно как угодно (в том числе биологически необоснованно) менять структуру белка, как будто его модель пластилиновая.
Далее проведем мутагенез: выберем остаток, участвующий в связывании лиганда, и заменим его на другой таким образом, чтобы пропала водородная связь с лигандом.
cmd.reinitialize()
cmd.fetch('1lmp')
cmd.remove('solvent')
cmd.color('deepteal')
cmd.do('''
util.cbas hetatm
select pocket, byres m. 1lmp and (hetatm around 3.5)
show sticks, pocket
util.cbaw pocket
''')
cmd.orient('hetatm')
cmd.zoom('hetatm', '20')
cmd.dist('hbonds', 'm. 1lmp and (not hetatm)', 'hetatm', '3.5', '2')
cmd.do('''
label pocket and n. ca and resi 59, "%s%s" % (resn, resi)
set label_color, black
''')
cmd.zoom('hetatm', '3')
cmd.png(filename='pic_3.png',width='10cm',dpi=300, ray=1)
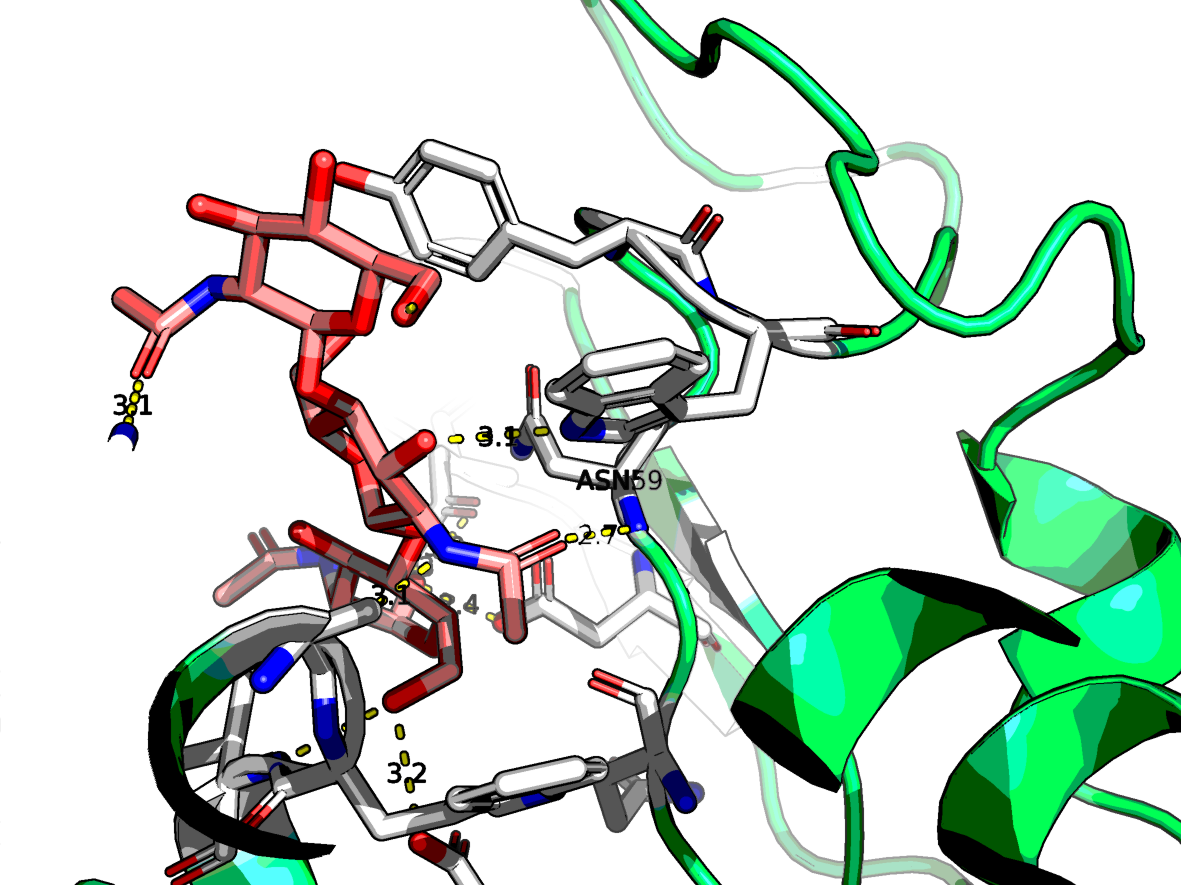
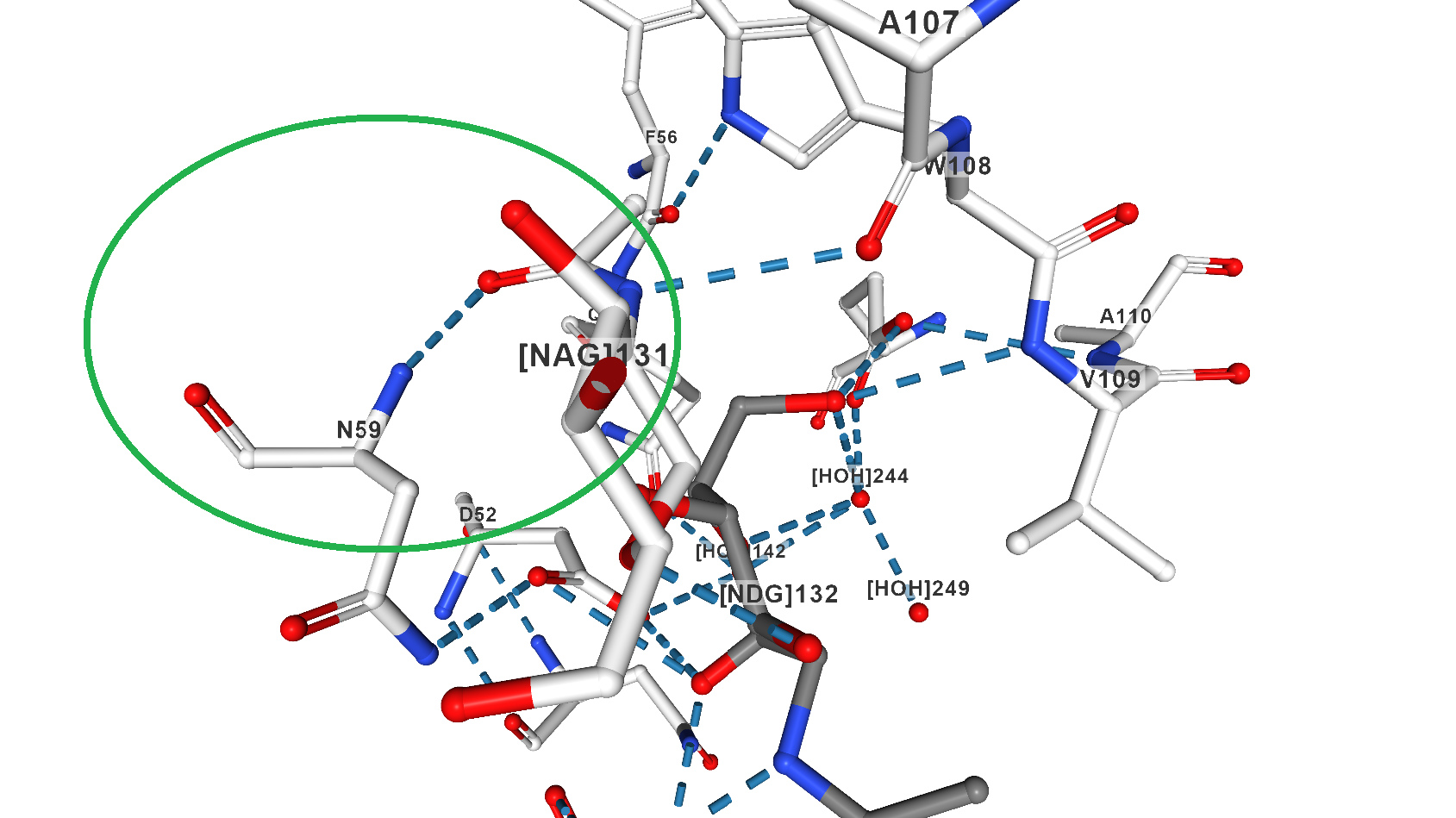
На Рис. 3 показано место связывания лигандов с лизоцимом из модели 1LMP и водородные связи, участвующие во взаимодействии. В частности, одним из остатков белка, вовлеченных в образование водородной связи с лигандом, является Asn59, что подтверждается данными с сайта PDB (Рис. 4). Он и был выбран для мутагенеза.
 |  |
cmd.png(filename='pic_5.png',width='10cm',dpi=300, ray=1)
Далее проведем мутагенез выбранного остатка Asn59, заменив его на аланин.
cmd.delete('hbonds')
cmd.hide('sticks', 'not resi 59')
from pymol import wizard