Задание 1. Реконструкция дерева по 12S rRNA
Для тех же 11 видов млекопитающих из надотрядов Euarchontoglires и Laurasiatheria
были получены последовательности гена малой субъединицы митохондриальной
рибосомной РНК (12S rRNA). Для ряда видов из предыдущего практикума
полные геномы оказались недоступны, поэтому были сделаны
замены на близкородственные виды:
Использованные последовательности:
PSAOB— Psammomys obesus (Rodentia), MG558461, 12S: 71..10219HYST— Hystrix indica (Rodentia), ON408241, 12S: 71..1028LEPYA— Lepus yarkandensis (Lagomorpha), MG279351, 12S: 69..1022SYLAU— Sylvilagus audubonii (Lagomorpha), U58928, вся запись (726 bp, partial)LEMCA— Lemur catta (Primates), AJ421451, 12S: 70..1022PONPY— Pongo pygmaeus (Primates), D38115, 12S: 72..1024TUPGL— Tupaia belangeri* (Scandentia), AF217811, 12S: 67..1014SORMN— Sorex minutissimus (Eulipotyphla), MK641805, 12S: 72..1038SORCY— Sorex cylindricauda (Eulipotyphla), KT023074, 12S: 72..1039PIPKU— Pipistrellus kuhlii (Chiroptera), KU058655, 12S: 74..1035MYOMU— Myotis muricola (Chiroptera), KT213444, 12S: 69..1032
*update: Для Tupaia glis RefSeq-запись (NC_002521) оказалась недоступна через EMBOSS на kodomo; вместо неё использована запись AF217811, которая соответствует близкому виду Tupaia belangeri.
Последовательности извлечены командой seqret (пакет EMBOSS),
переименованы мнемониками через descseq,
выровнены программой MUSCLE, конвертированы в формат phylip-relaxed
и поданы на вход FastME с флагом -d (нуклеотидные расстояния):
#извлечение seqret embl:MG558461[71:1021] PSAOB_12S.fasta #выравнивание muscle -align all_12S.fasta -output 12S_alignment.fasta #дерево fastme -i 12S.phy -d -o 12S_fastme.nwk
Полученное дерево загружено в iTOL и укоренено в ветвь между рукокрылыми и остальными таксонами.
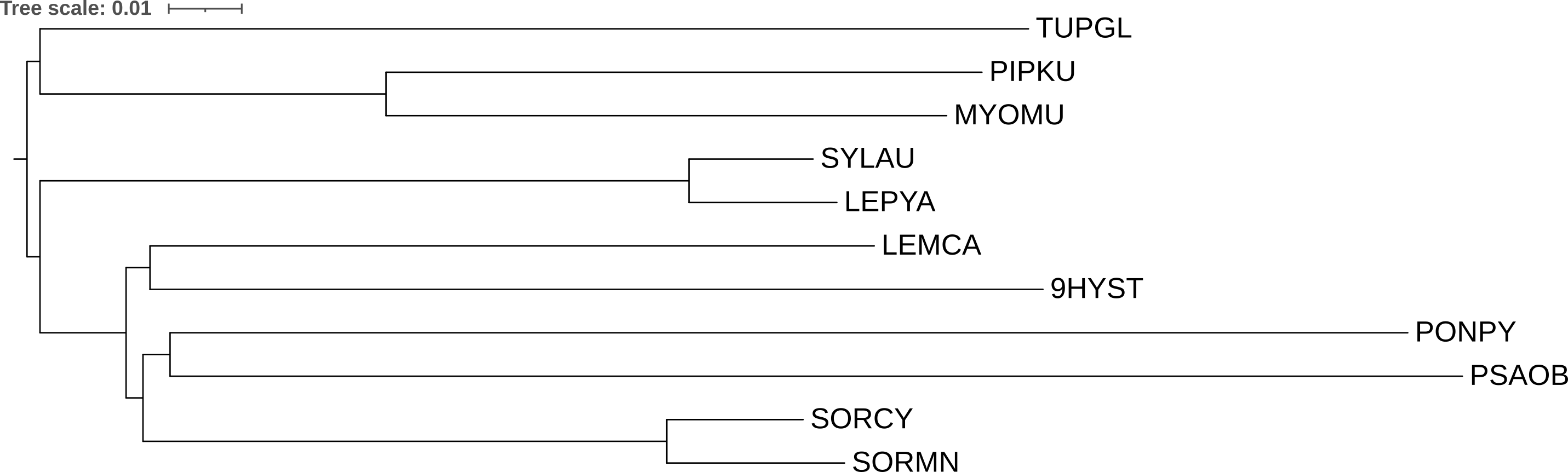
Сравнение с деревом видов Три пары близкородственных видов восстановлены правильно: (SORMN, SORCY) — землеройки, (LEPYA, SYLAU) — зайцеобразные, (MYOMU, PIPKU) — рукокрылые. При этом на уровне более дальних ветвлений дерево содержит несколько ошибок:
- Ложная клада (PONPY, PSAOB) — орангутан объединился с песчанкой, хотя они относятся к разным отрядам (Primates и Rodentia).
- Ложная клада (9HYST, LEMCA) — дикобраз попал в одну кладу с лемуром, при том что один из Rodentia, а другой из Primates.
- TUPGL оказалась сестринской к рукокрылым, хотя по таксономии тупайи ближе к Euarchontoglires.
- Деление на Euarchontoglires и Laurasiatheria не восстановлено вовсе.
Сравнение с деревьями по CytB. Характер ошибок в целом похож: пары близких видов всегда восстанавливаются правильно, а вот положение глубоких узлов «плывёт». TUPGL была проблемной и по CytB (там она уходила к землеройкам), а по 12S rRNA она оказалась рядом с рукокрылыми — ошибка другая, но природа та же. Кроме того, по 12S rRNA появилась совсем неожиданная клада (PONPY, PSAOB), которой не было ни в одном из CytB-деревьев. Всё это лишний раз показывает, что одного митохондриального гена не хватает для уверенного разрешения глубоких ветвлений при таком наборе таксонов.
Задание 2. Укоренение во внешнюю группу
Внешней группой выбран индийский слон Elephas maximus
(мнемоника ELEMA) из надотряда Afrotheria — он не входит ни в
Euarchontoglires, ни в Laurasiatheria, и поэтому гарантированно
лежит за пределами нашей выборки.
Последовательность 12S rRNA взята из записи AJ428946
(координаты 70..1031).
seqret embl:AJ428946[70:1031] ELEMA_12S.fasta #добавить к набору, перевыровнять, построить дерево cat all_12S.fasta ELEMA_12S_r.fasta > 12S_outgroup.fasta muscle -align 12S_outgroup.fasta -output 12S_outgroup_aln.fasta fastme -i 12S_outgroup.phy -d -o 12S_outgroup.nwk
Дерево укоренено в ветвь, ведущую к ELEMA.
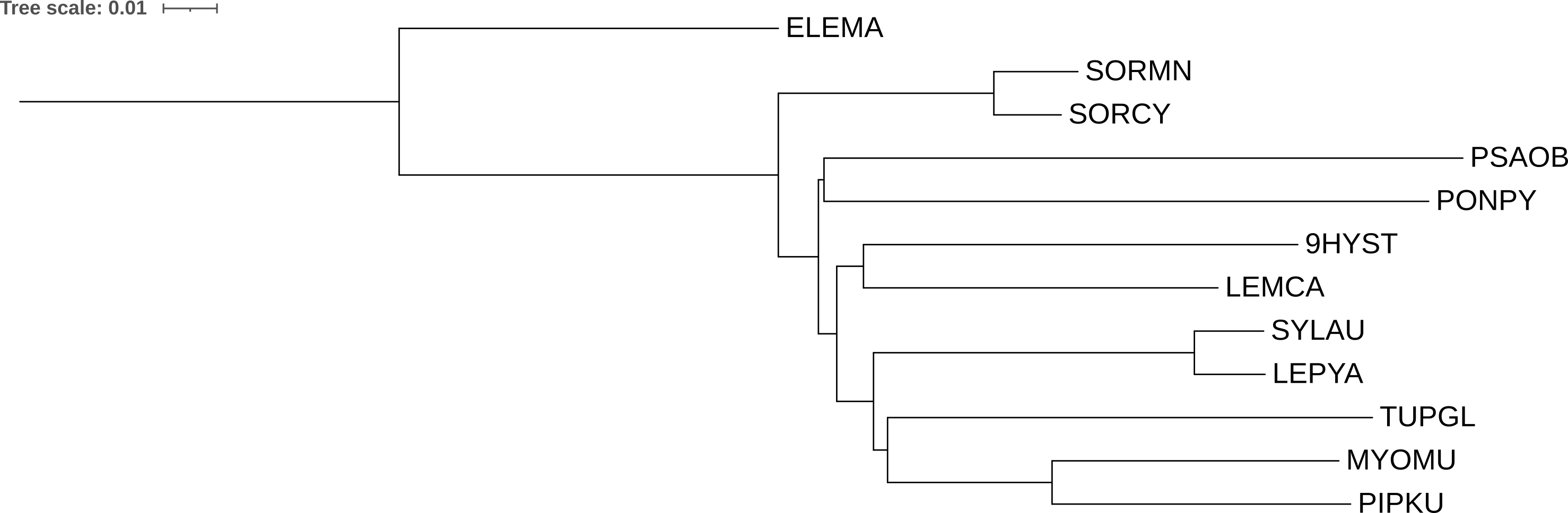
После укоренения землеройки (SORMN, SORCY) оказались самой базальной группой среди Boreoeutheria, что не совсем соответствует ожиданиям (они должны группироваться с рукокрылыми внутри Laurasiatheria). Разделения на два надотряда по-прежнему нет: TUPGL сидит рядом с летучими мышами, а ложные клады (PONPY, PSAOB) и (9HYST, LEMCA) сохраняются. Тем не менее укоренение по внешней группе даёт однозначное направление эволюции — без аутгруппы положение корня скорее всего было бы произвольным.
Задание 3. Бутстреп
Из практикума 2 была взята реконструкция по цитохрому B
(программа FastME, модель MtREV) и повторена
со 100 бутстреп-репликами:
fastme -i cyb.phy -pM -b 100 -o cyb_mtrev_bootstrap.nwk
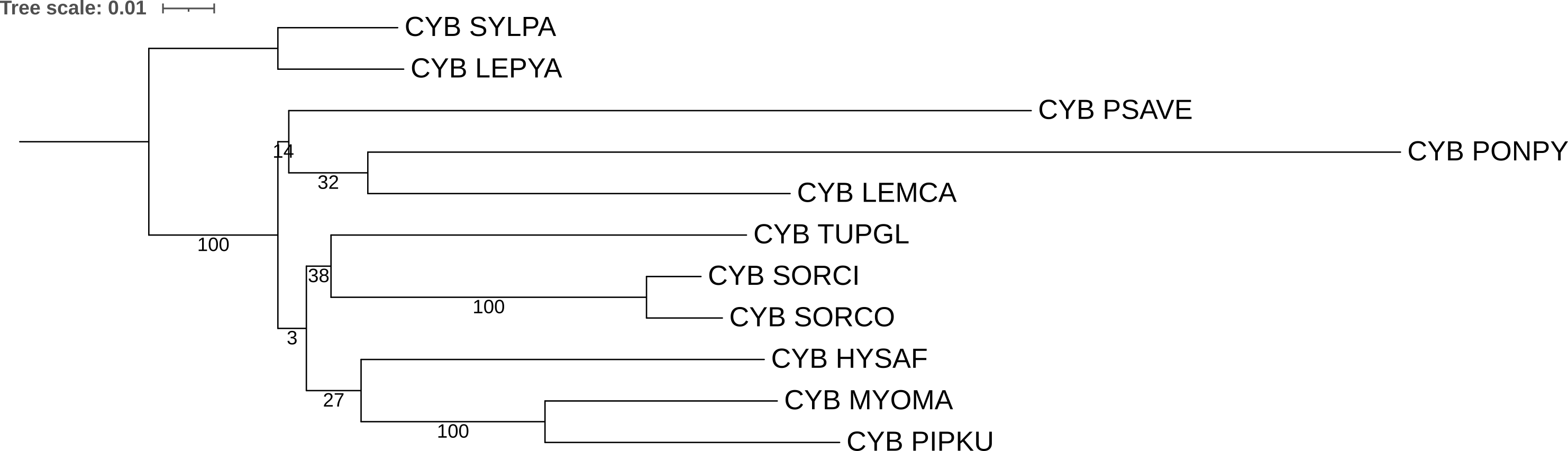
Верные клады:
- (SORCI, SORCO) — 100
- (PIPKU, MYOMA) — 100
- (LEPYA, SYLPA) — 100
- (LEMCA, PONPY) — 32 (верно, но маленькое значение)
Ошибочные клады:
- (TUPGL, (SORCI, SORCO)) — 38
- (HYSAF, (PIPKU, MYOMA)) — 27
- (PSAVE, (LEMCA, PONPY)) — 14
- большая внутренняя клада — 3
Результат получился очень наглядным. Все три «правильные» пары близкородственных видов (SORCI+SORCO, PIPKU+MYOMA, LEPYA+SYLPA) набрали 100 из 100, то есть в каждой реплике бутстрепа они оставались вместе. А вот ошибочные ветвления, которые мы отмечали ещё в практикуме 2, получили совсем низкие значения: 3, 14, 27, 38. Это значит, что при случайной перевыборке позиций выравнивания эти клады почти не воспроизводятся — филогенетического сигнала для них попросту нет.
Отдельно стоит отметить кладу (LEMCA, PONPY): она таксономически правильная (оба вида — приматы), но поддержка у неё всего 32. Скорее всего дело в очень длинной ветви PONPY — цитохром B у орангутана эволюционировал быстро, и из-за этого положение узла нестабильно.
Таким образом, бутстреп-анализ подтвердил ожидание: неправильно реконструированные ветви действительно имеют низкую поддержку, а надёжно восстановленные — высокую. Бутстреп работает как хороший индикатор того, насколько можно доверять той или иной ветви дерева.
Назад
