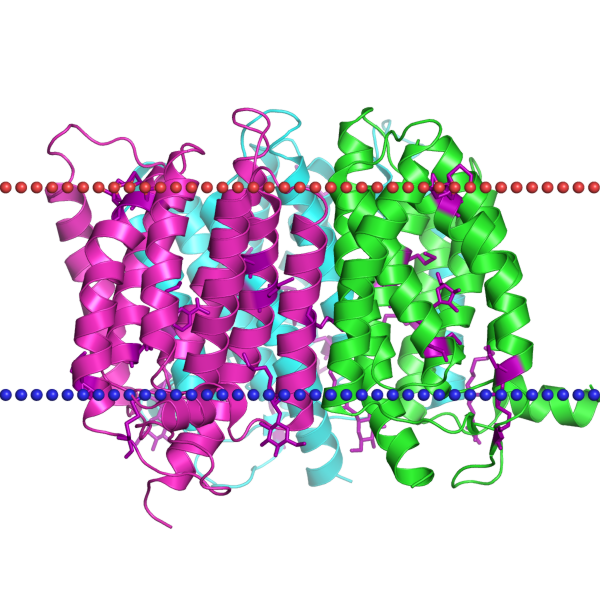
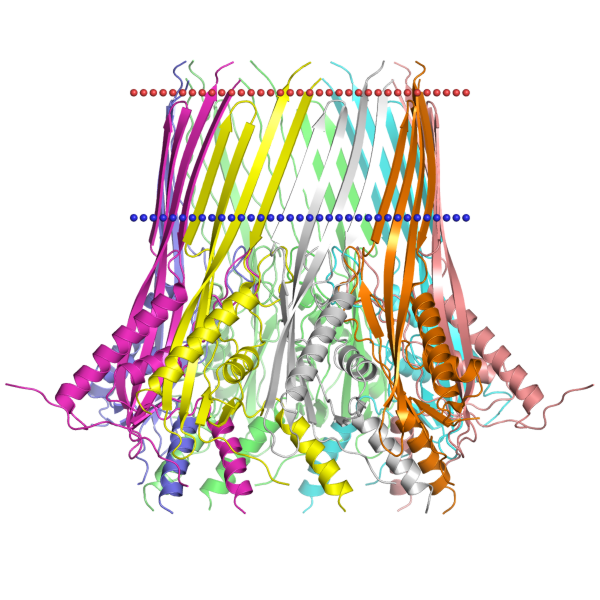
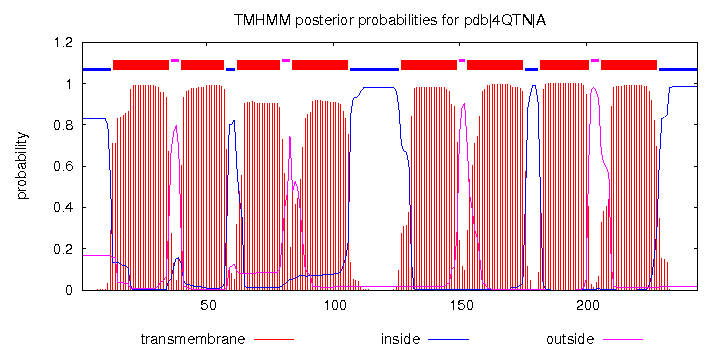
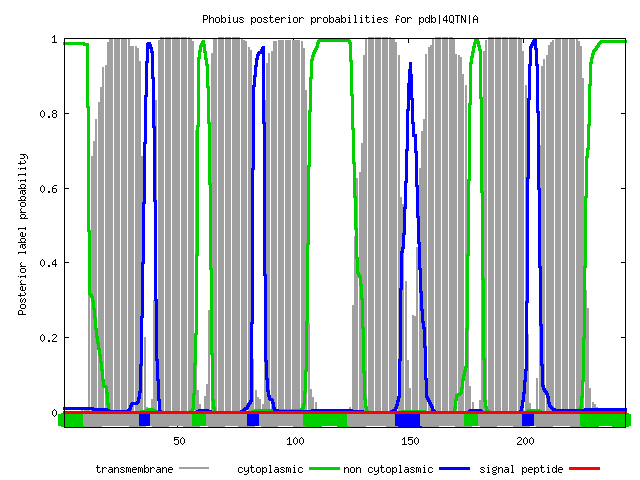
| Координаты трансмембранных бета-тяжей |
Subunits - 9
1( 152- 159), 2( 162- 167), 3( 200- 207), 4( 216- 222)
1( 152- 159), 2( 162- 167), 3( 200- 207), 4( 216- 222)
1( 152- 159), 2( 162- 167), 3( 200- 207), 4( 216- 222)
1( 152- 159), 2( 162- 167), 3( 200- 207), 4( 216- 222)
1( 152- 159), 2( 162- 167), 3( 200- 207), 4( 216- 222)
1( 152- 159), 2( 162- 167), 3( 200- 207), 4( 216- 222)
1( 152- 159), 2( 162- 167), 3( 200- 207), 4( 216- 222)
1( 152- 159), 2( 162- 167), 3( 200- 207), 4( 216- 222)
1( 152- 159), 2( 162- 167), 3( 200- 207), 4( 216- 222)
|