Практикум 8. Нуклеотидный BLAST
В прошлом практикуме мною было выбрано животное - Bufo gargarizans.
Поиск гена, кодирующего δ-субъединицу АТФ-синтазы.
Файл с последовательностью дельта субъединицы АТФ-синтазы. Идентификатор - XP_044139888.1
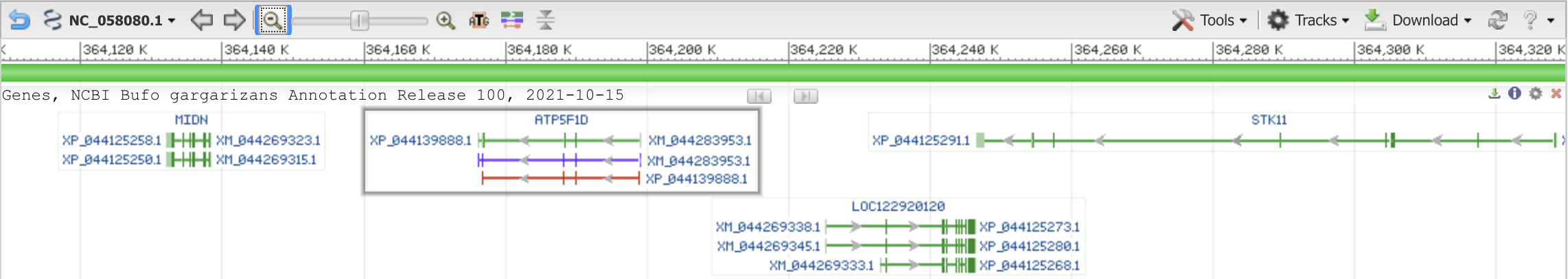
Нуклеотидная запись, содержащая дельта субъединицу - NC_058080
Файл с небольшой окрестностью гена.
Изображение окресности гена из геномного браузера:
Различные варианты BLAST для фрагмента ДНК.
АТФ-синтаза - крайне важный белок для аэробов. В связи с этим интересно посмотреть насколько он консервативен, сравнив в BLAST его последовательность и ген с удаленным семейством.
Bufo gargarizans (Дальневосточная жаба) относится к Вторичноротым (Deuterostomia), поэтому для сравнения было взято семейство Пчелы (Apoidea), так как оно относится к Первичноротым (Protostomia).
Поиск проводился по последовательностям геномов Apoidea (taxid:34735) в базе данных refseq_genomes, содержащую референсные геномы. Таких последовательностей в базе данных 38.
Для начала поиск проводился с помощью blastn, но это не дало никаких результатов даже с уменьшением длины слова и штрафов. Это можно обьяснить тем, что алгоритм сравнивает гены на уровне нуклеотидов. Я не могу назвать данный результат ожидаемым, но то, что находок будет мало я предпологала.
Далее поиск проводился с помощью tblastn, так как он уже работает в аминокислотной последовательностью, что по идее должно дать разультат. И действительно в итоге программа выдала 38 находок.

Таким образом видно, что аминокислотная последовательность дельта субъединицы - консервативна и схожа даже в таких далеких организмах, но нуклеотидная последовательность уже сильно отличается. Я думаю это связанно с мутациями не влияющими на последовательность аминокислот.
Поиск генов основных рибосомальных РНК по далекому гомологу.
16S рРНК является частью малой субъединицы рибосомы прокариот. Основная ее роль - распознавание последовательности Шайн-Дальгарно на мРНК, то есть отвечает за инициацию трансляции.
23S рРНК расположена в большой субъединице рибосомы и играет в основном структурную роль, формируя активный сайт и соответственно участвует в элонгации трансляции.
В данном задании нужно провести поиск рибосомальных РНК в геноме выбранного ранее эукариота - Bufo gargarizans. Для этого я скачала геном Дальневосточной жабы и проиндексировала его с помощью программы:
| makeblastdb -in GCF_014858855.1_ASM1485885v1_genomic.fna -dbtype nucl |
Для дальнейшего поиска был выбран blastn, так как он больше всего подходит для поиска некодирующих белки нуклеотидных последовательностей. Файлы 16SrRNA.fa и 23SrRNA.fa содержат последовательности кодирующие 16S и 23S рРНК соответственно.
| blastn -task blastn -query 16SrRNA.fa -db GCF_014858855.1_ASM1485885v1_genomic.fna -out blastn_16S.out -outfmt 7 blastn -task blastn -query 23SrRNA.fa -db GCF_014858855.1_ASM1485885v1_genomic.fna -out blastn_23S.out -outfmt 7 |
Полученные результаты: blastn_16S.out(таблица), blastn_16Stext.out(текст) и blastn_23S.out(таблица), blastn_23Stext.out(текст)
Для 16S было полученно 65 выравниваний, а для 23S - 88.
Часть выравниваний имеет довольно большой e-value, поэтому выравнивания с e-value>0.5 я не рассматривала.
Для 16S был обнаружен 15 гомологов, а для 23S - 17 гомологов.
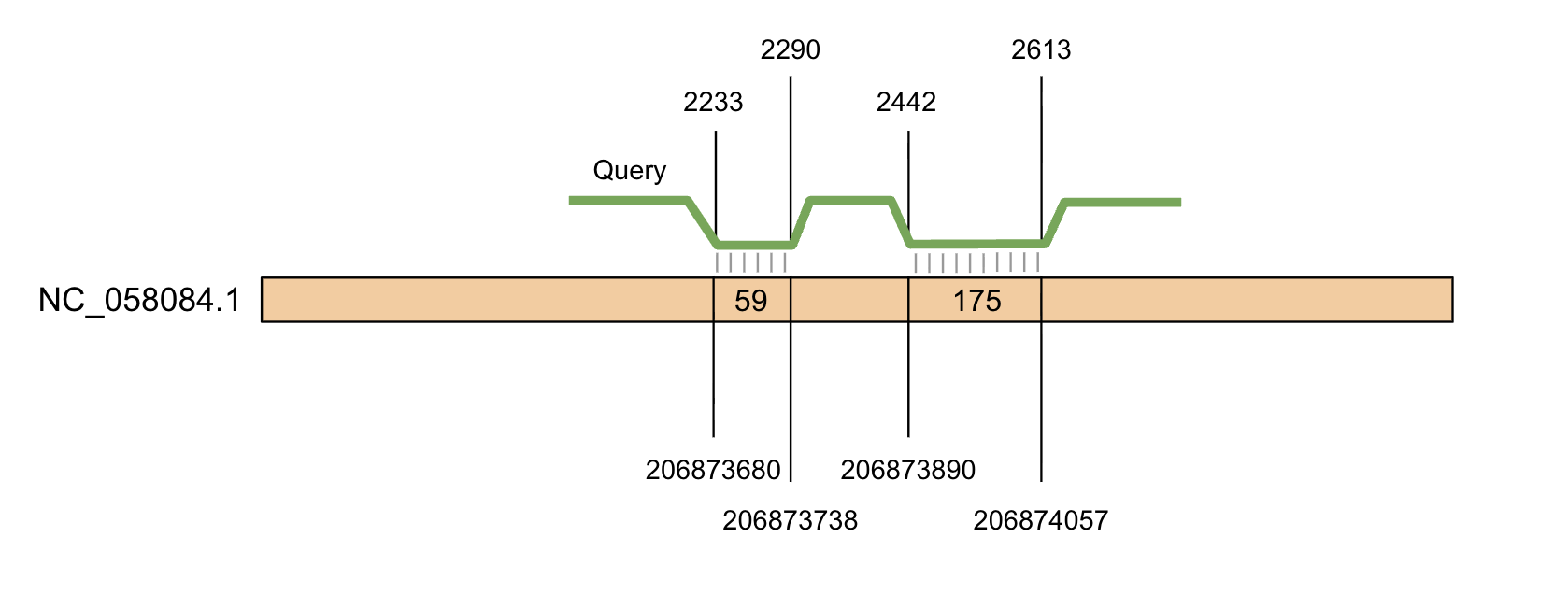
Подбор пары геномов и построенин карты их локального сходства
В качестве пары геномов мною были выбраны два генотипа Гепатита С: Hepatitis C virus genotype 1 (NC_004102.1) и Hepatitis C virus genotype 7 (NC_030791.1), которые были найдены в NCBI по запросу: ("Hepacivirus C"[Organism]) AND complete[Title] AND refseq[filter].
Далее с помощью Megablast, BLASTN и TBLASTX были построены карты их локальног осходства:
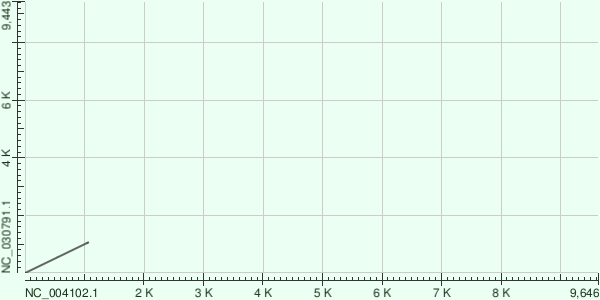
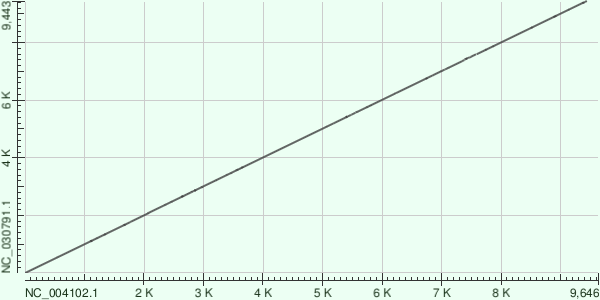
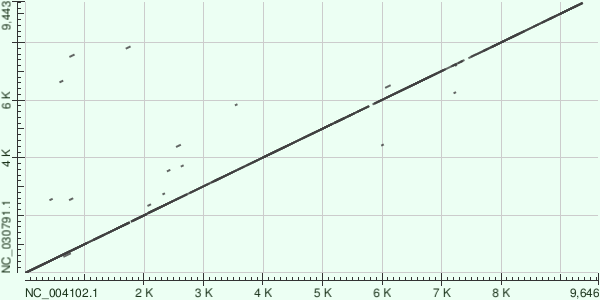
На основании Megablast говорить о родстве вирусов невозможно, но вот результаты BLASTN и TBLASTX позволяют увидеть их родство. Интересно, что TBLASTX показал делеции в то время как BLASTN нет.