Выбор геномов и построение dot polt
С помощию запросов в базе данных NCBI Genome был выбран род бактерий Listeria. В качестве геномов для сравнения были выбраны референсные геномы Listeria grayi (NZ_LR134483) и Listeria innocua (NZ_CP117229)
С помощью программ megablast и blastn было проведено выравнивание геномов. В результате были получены следующие графики
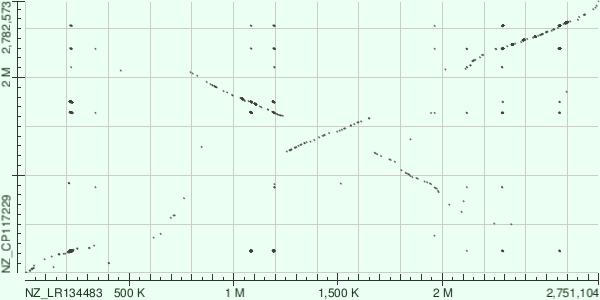
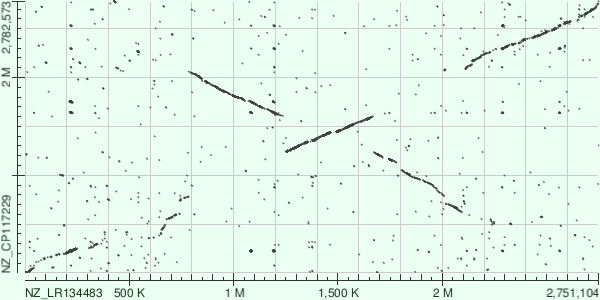
При сравнении видно, что выдача программы blastn содержит больше находок схожих участков, что немного "загрязняет" график, но содержит ценную информацию. Выдача megablast поймала только участки абсолютного сходства. Она показывает картиу геномных перестроек в целом, но интересные области пропускает. Поэтому далее будет рассматриваться dot plot построенный blastn.
Геномные перестройки
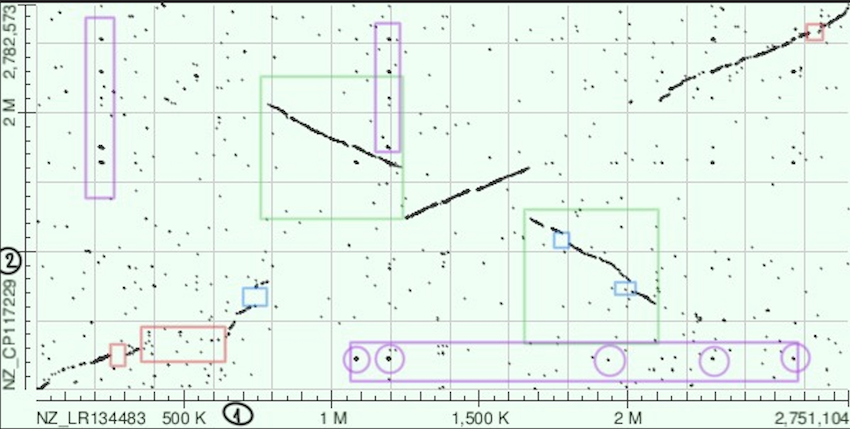
Красным выделены делеции в последовательности 1 (нижняя)
Синим выделены делеции в последовательности 2 (верхняя)
Зеленым выделены инверсии с транслокацией
Фиолетовым выделены некторые дупликации (вертикально - в последовательности 2, горизонтально - в последовательности 1), которые так же отразились в результатх megablast.
megablast обнаружил основные области перестроек и дупликаций, но по его результатм не могла быть обнаружена область делеций в нижней последовательности (выделено красным).