Филогенетическая реконструкция эволюции видов может основываться на консервативных нуклеотидных последовательностях. В данном случае будут использоваться последовательности цитохрома B (митохондриальный переносчик электронов в ЭТЦ). Для построения деревьем было проведено выравнивание последовательностей с помощью программы muscle. Затем при помощи программы FastME были оценины эволюционные расстояния двумя способами: p-distance и модель MtREV (митохондриальная модель)
Было получено 2 дерева которые были визуализированы при помощи сервиса iTOL.
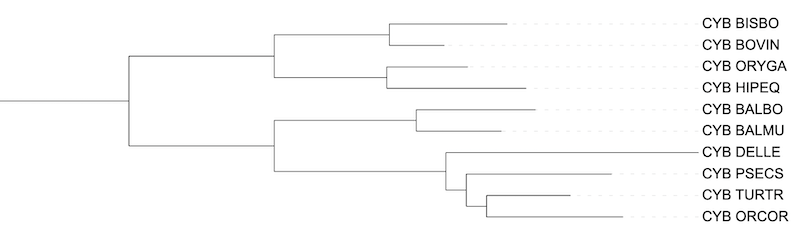
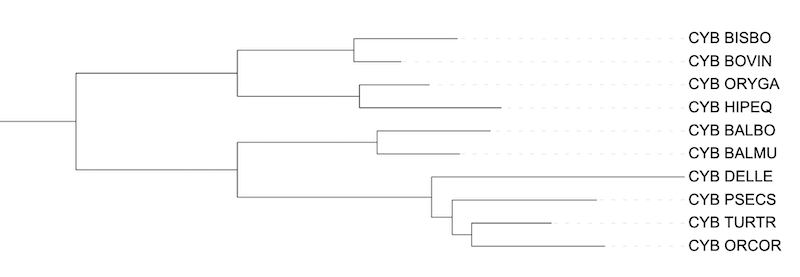
Филогенетическая реконструкция эволюции Китопарнокопытных на основе последовательности цитохрома В
Укоренение деревьев проводилось по узлу между парнокопытными и китообразными. Реконструкции деревьев программой FastME выглядят почти одинаково (в скобочной формуле есть небольшие отличия в длинах ветвей). Данные деревья похожи на результат прошлого практикума, где дерево строилось на основе известной систематики. Так же можно заметить что узел из трех видов относящихся к Delphinidae (морские дельфины) был разрешен по последовательностям цитохромов В.
При ближайшем рассмотрении деревьев бросается длина ветви DELLE (белуга). Вероятно это просто артефакт, но выглядит такая ситуация очень интересно.
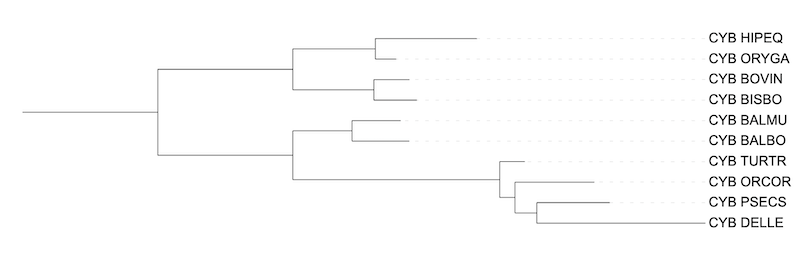
Дерево 3 отличается от предыдущих длинами ветвей. Программа IQ-Tree пердположила топологию, где белуга (DELLE) находится внутри группы Delphinidae (морские дельфины). Но такая топология противоречит дереву на основе систематики (из практикума 1) и деревьям построенным программой FastME.
Больше доверия вызываеи дерево построенные программой FastME на основе модели MtREV.