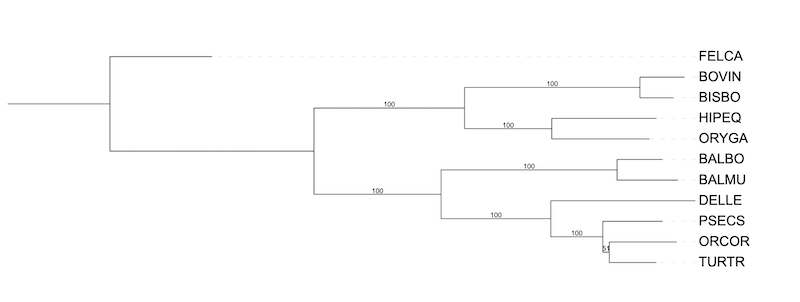
1. Реконструкция дерева по нуклеотидным последовательностям
Для 10 представителей отряда Китопарнокопытные программой FastME было построено филогенетическое дерево на основе последовательностей 12S rRNA.
Полученное дерево совпадает с построением программой FastME по последовательности цитохрома B. Так же совпадает с систематическим положение организмов.
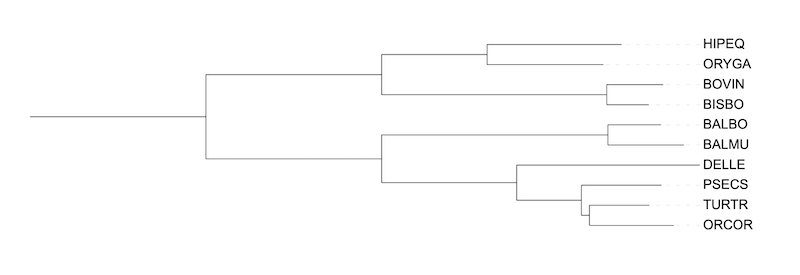
2. Укоренение во внешнюю группу
Один из подходов к укоренению деревьев -- внешняя группа. В данном случае в качестве внешней группы было решено взять котиков (Felis catus), так как они относятся к Laurasiatheria, а это таксон после которого происходит отделение ветви китопарнокопытных. Последовательность 12S rRNA была добавлена к выравниванию и было проведено укоренение дерева в ветвь, ведущую к внешней группе.
Внешняя группа была правильно позиционированна на дереве и привела к верному (на основе известной систематики) укоренению дерева и разделению таксонов.
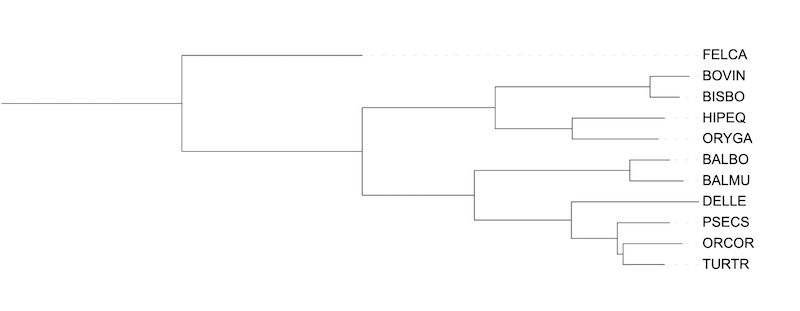
3. Бутстреп
Далее для группы китопарнокопытных с внешней группой было посчитано дерево с бутстрепом 100 (100 различных "пересборок" последовательности). Таким образом была вычислена устойчивость ветвей, т.е соответствие полученного дерева разным комбинациям столбцов выравнивания (длина как у исходного).
В полученном дереве для почти всех ветвей бутстреп 100, что говорит об их однозначности и устойчивости. Для ветви разделяющей TURTR, ORCOR от PSECS бутстреп 51. Это показывает что ветвь вероятно будет выглядить так, но это не точно. Такие результаты неплохо согласуются с неразрешенностью данной группы в случае построения дерева на основе систематических данных.