1. Составление списка гомологичных белков, включающих паралоги
Из 15 протеомов бактерий отдела Pseudomonadota были выбраны 7 протеомов:
ACICJ, BARHE, BRUSU, SACD2, ROSDO, NEIMA, THIDA
Все последовательности были собраны в 1 файл и затем на основе данных последовательностей была создана локальная база данных. Для ее создания использовалась команда makeblastdb -in all.fasta -dbtype prot
На основе полученной базы данных был запущен blastp для поиска гомологов белка CLPX_ECOLI, e-value = 0.0001
blastp -task blastp -query clpx_ecoli.fasta -db all.fasta -out res_blast.out -evalue 0.0001
В результате был получен список находок, содержайщий гомологичные белки
2. Реконструкция и визуализация
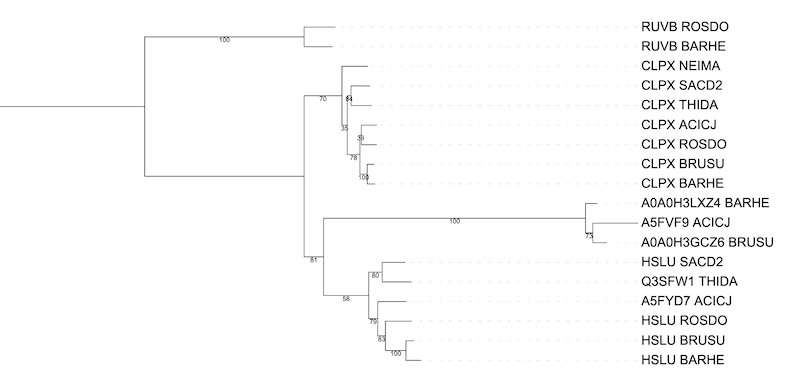
Полученные последовательности белков были собраны в fasta файл, выровнены программой muscle. Затем программой FastME было реконструировано дерево бутстреп 100, модель MtREV.
Полученное дерево было визуализированно с помощью программы iTOL, укоренение в среднюю точку.
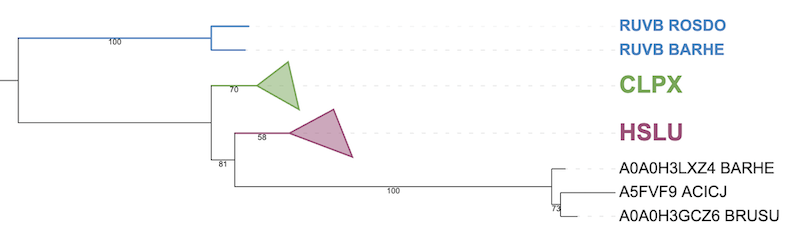
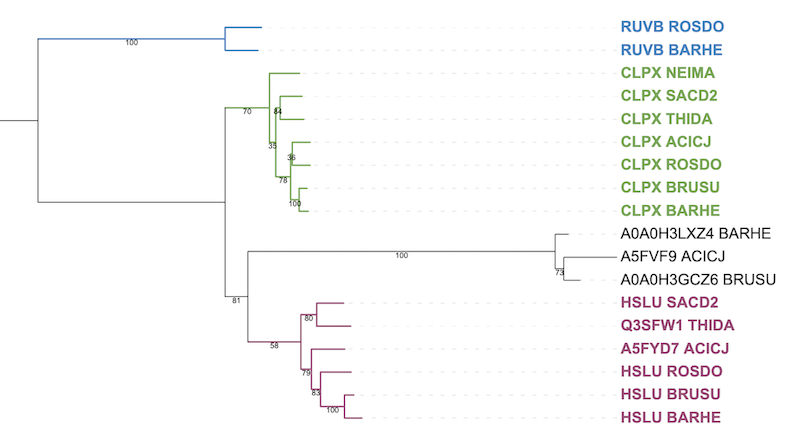
Цветами (рис 2) были визуализированы группы ортологов
Ортологи: CLPX_SACD2 и CLPX_BARHE (и другие парные выборки, зеленый цвет на картинке), HSLU_ROSDO и HSLU_BRUSU (сиреневый цвет)
Паралоги(в одном организме, разные функции): CLPX_SACD2 и HSLU_SACD2, CLPX_ROSDO и HSLU_ROSDO
Затем все ортологические группы, содержащие более трёх последовательностей, были "схлопнуты"
Группа CLPX содержит все найденные ортологи (7 штук). Группа HSLU содержит 6 ортологов (всего было исследовано 7 организмов и для бактерии с мнемоникой NEIMA не было найдено ортологичного белка)
HSLU соответсвует изестной филогении, CLPX частично несоответсвует. Группа NEIMA сестринская для THIDA, а в наше случае она сестринская для всех бактерий. Правильнее была бы кластеризация ((NEIMA, THIDA),SACD2) и (((BARHE, BRUSU), ROSDO), ACICJ). Можно заметить, что неверно собранные ветви имеют назкую бутстреп поддержку.