GO анализ
На основе предоставленных генов (ACICJ, BARHE, BRUSU, SACD2, ROSDO, NEIMA, THIDA) был проведен GO анализ (онтология - bp, fisher test, поправка на множественное сравнение - BH). В результате было получено следующее обогащение терминами (рис. 1)
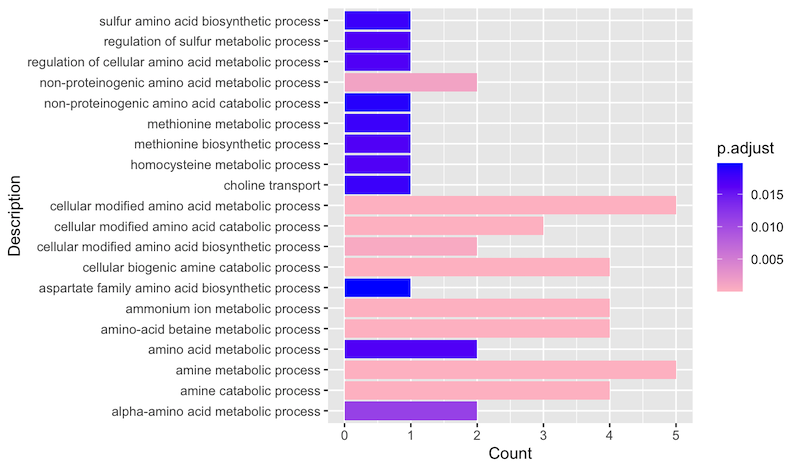
Наблюдается значительное обогащение терминами в метаболических путях аминокислот. В частности, имеется широкая представленность катаболического пути связанного с утилизацией аминогруппы. Таким образом можно заключить что данные гены отвечают за некоторый метаболический путь. Далее будет рассмотрены подробности этого процесса.
STRING
Была запущена программа STRING для 6 генов и 5 из них кластеризовались в 1 группу (рис 2)
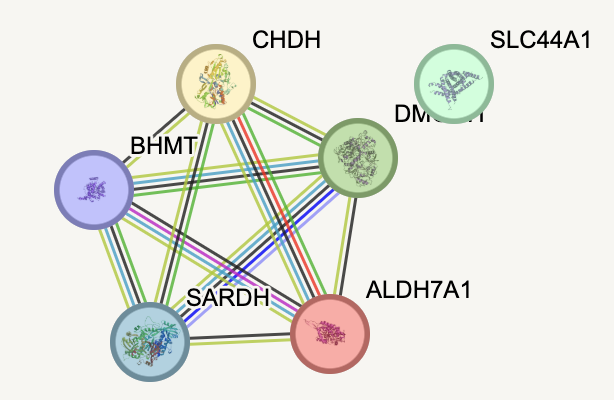
В описании анализа предоставляются ссылки на сторонние ресурсы. Таким образом было выяснено что экспрессия данных генов локализована в печени (база данных tissues). Так же все 6 генов задействованы в катаболизме холина (ссылка на картинку в высоком качестве) (база данных reactome, рис 3).
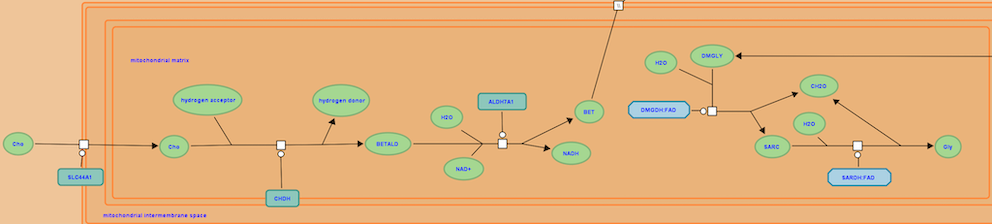
Из предложенного метаболического пути можно выяснить некоторые функции белков, кодируемых предоставленными генами. Например, SLC44A1 кодирует мембранный транспортер, находящийся в мембране митохондрии. Так же мы наблюдаем, что катаболизм холина происходит в разных компартментах клетки: цитоплазма (1 белок) и митохондрии (4 белка). Возвращаясь к 2 кластерам из STRING можно заключить, что анализ объединил между собой непосредственно гены проводящие реакции по превращению холина. Отделенный узел SLC44A1 является геном мембранного переносчика и непосредственно не учавствует в биохимических превращениях и возможно способен транспортировать и другие вещества.