Практикум №4
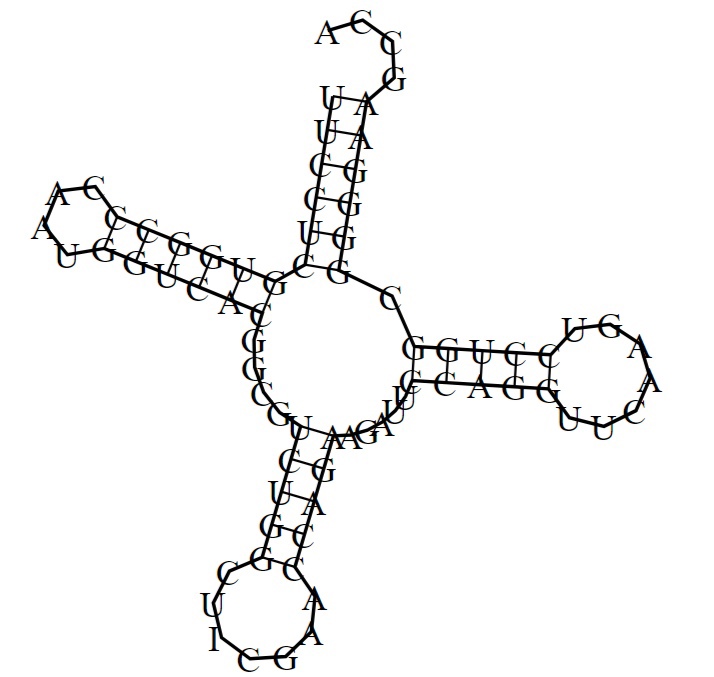
Предсказание вторичной структуры тРНК
С помощью программы einverted из EMBOSS были предсказаны инвентированные повторы тРНК.Использованная команда:
einverted -sequence 1f7u.seq -gap 10 -threshold 10 -match 2 -mismatch -3 -outseq 1f7uoutseq -outfile 1f7uoutfile
Полученный результат:
|
|
| Участок структуры | Позиции в структуре (по результатам find_pair) | Результаты предсказания с помощью einverted | Результаты предсказания по алгоритму Зукера |
|---|---|---|---|
| Акцепторный стебель | 1...7-72...66 | --- | 1...6-66...71 |
| D-стебель | 10...13-25...22 | --- | 7...12-22...17 |
| Антикодоновый стебель | 26...31-44...39 | 27...31-39...43 | 27...31-39...43 |
| T-стебель | 49...53-61...65 | 49...53-61...65 | 49...53-61...65 |
| Общее число канонических пар нуклеотидов | 21 | 10 | 20 |
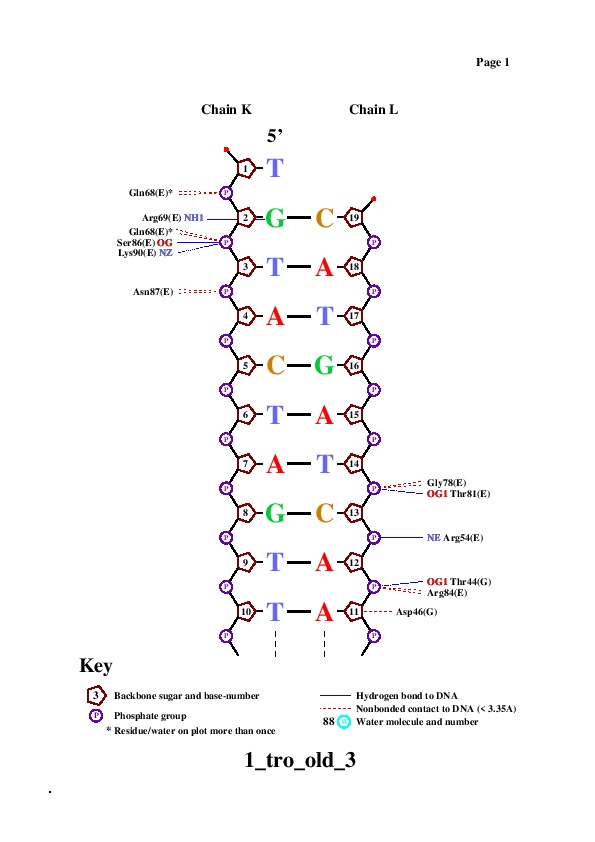
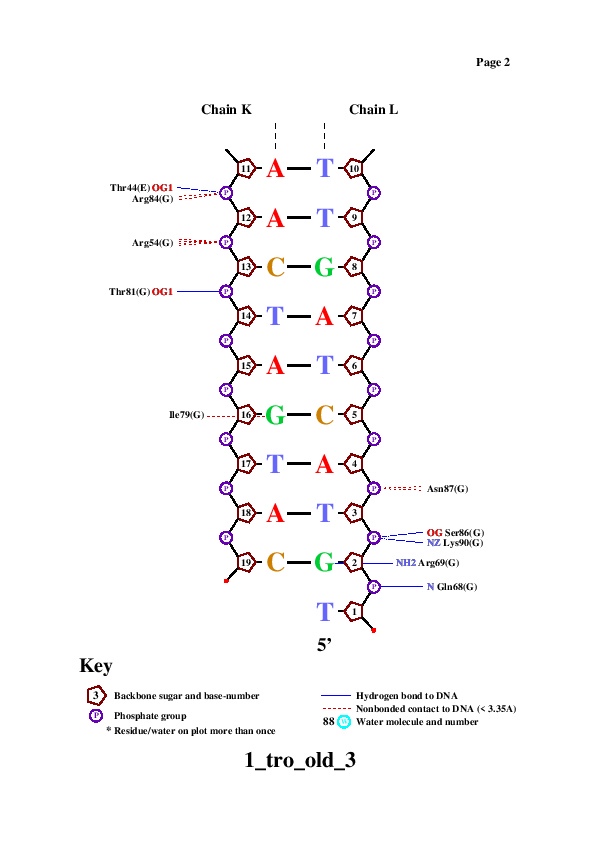
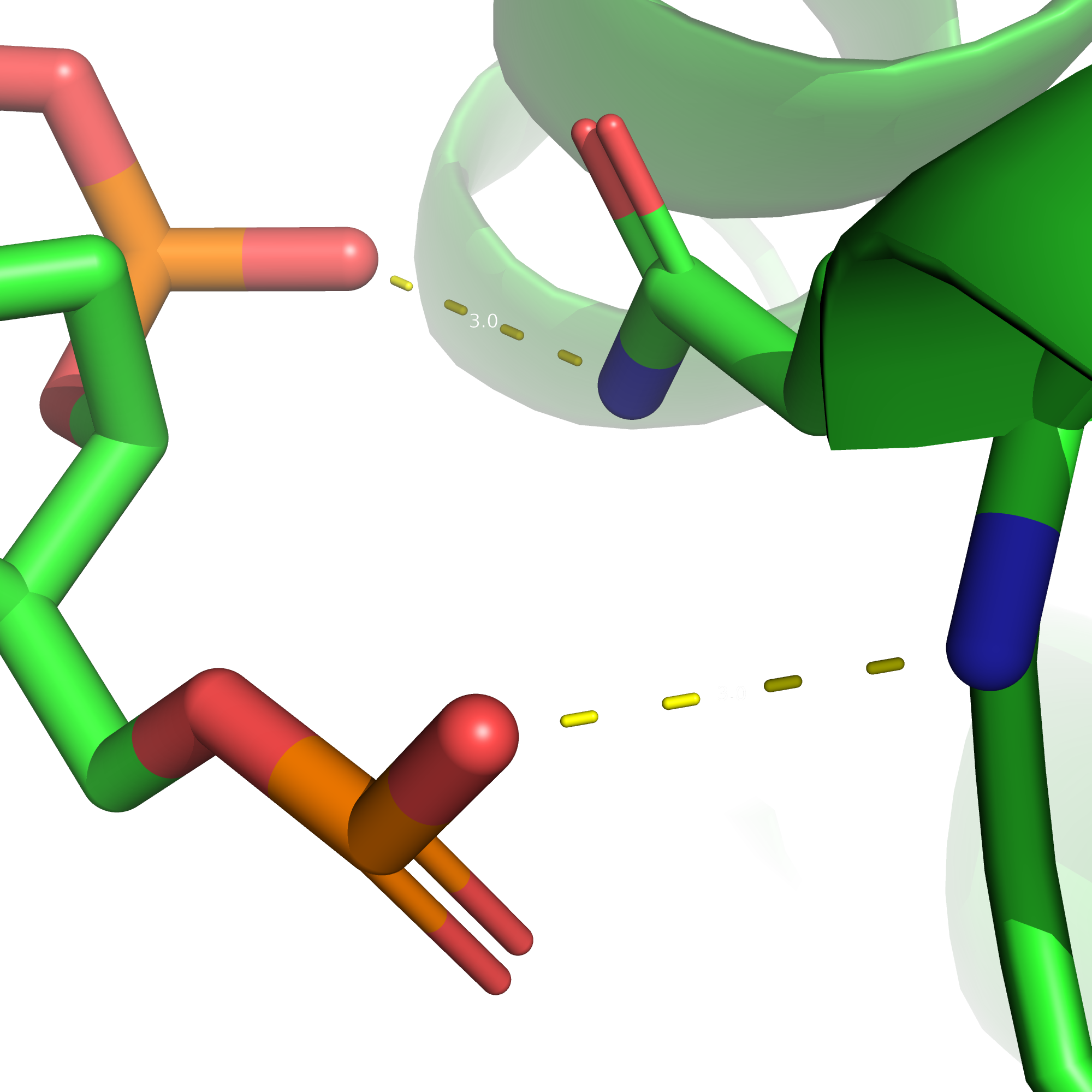
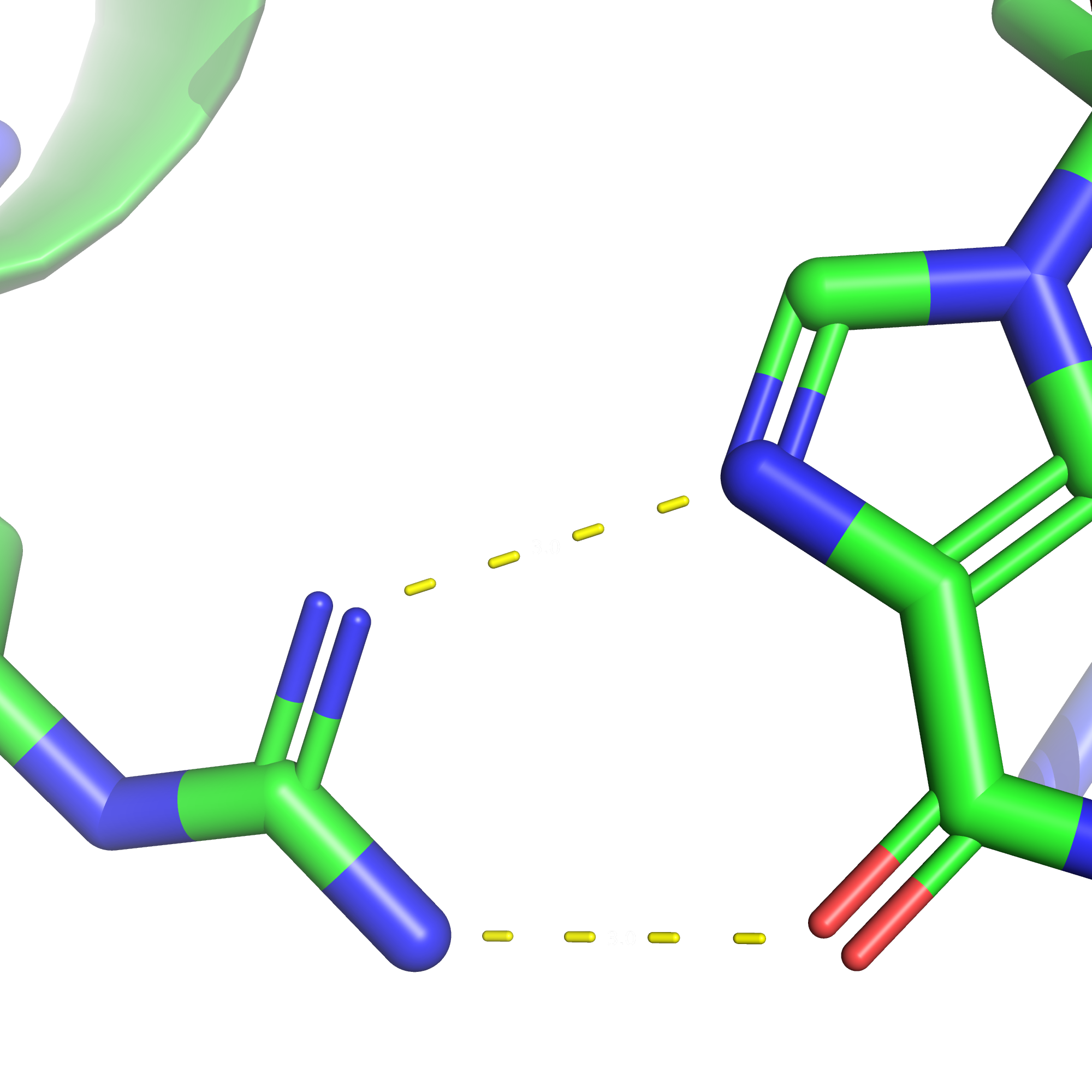
Поиск ДНК-белковых контактов в заданной структуре
Задание выполнялось для структуры 1tro (Protenin-NA complex). Чтобы получить визуализацию множества атомов в PyMol использовал скрипт.Полученная анимация:
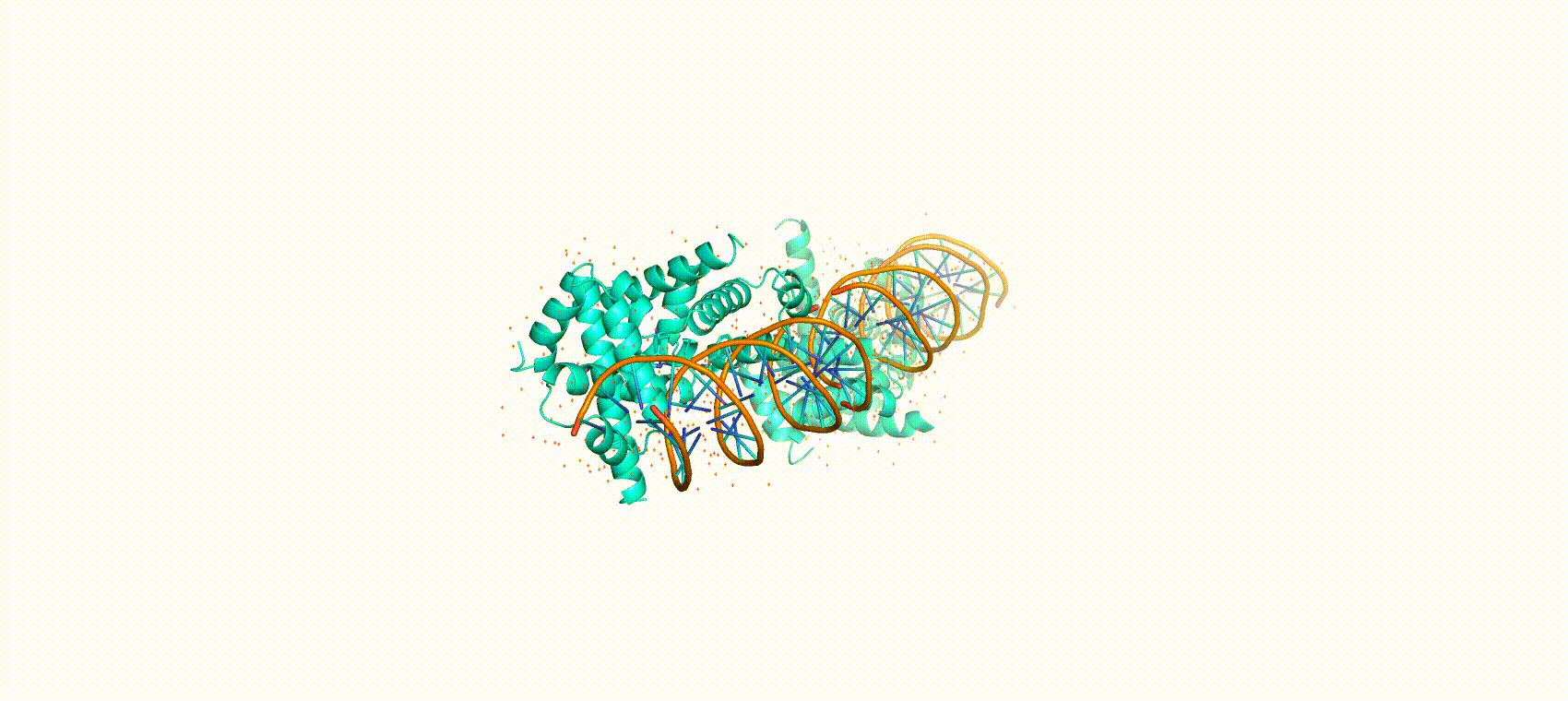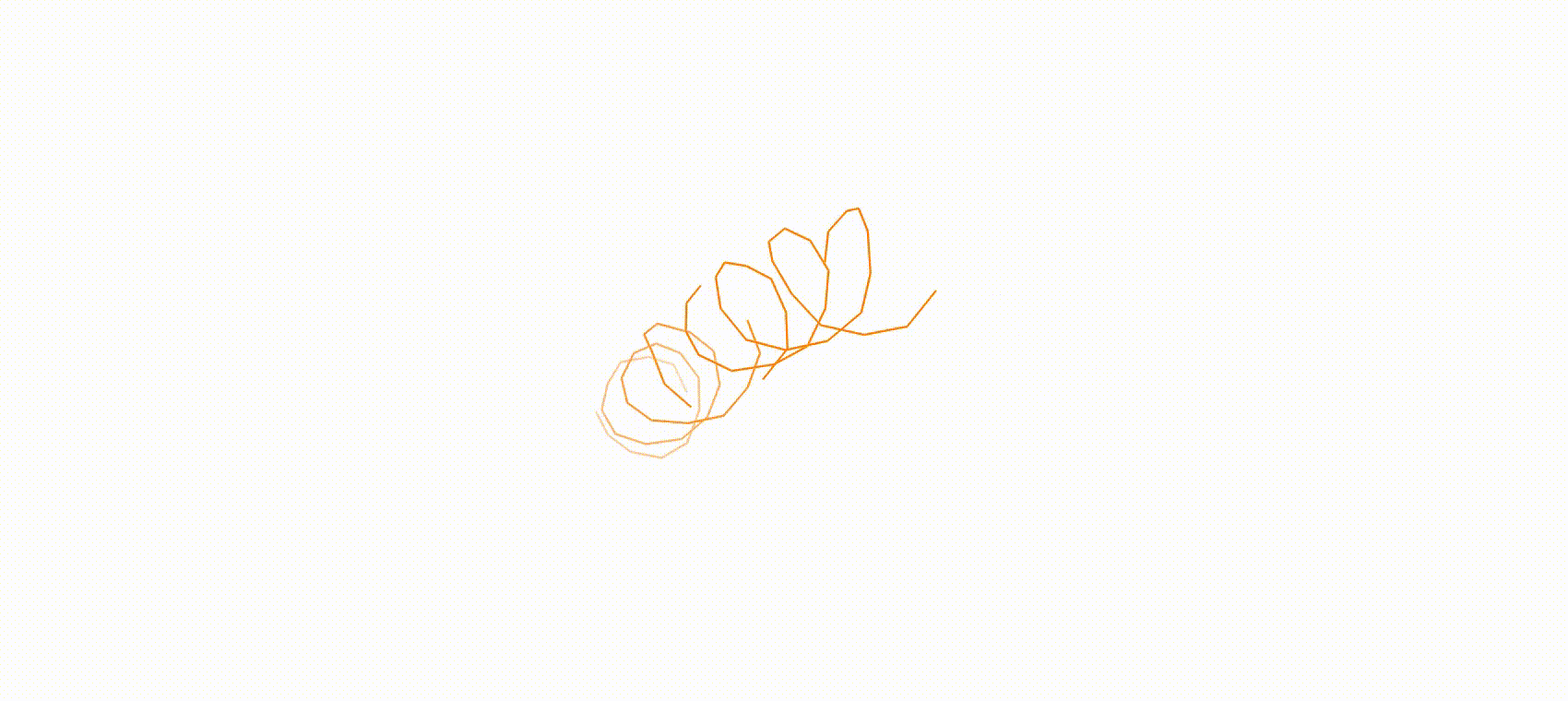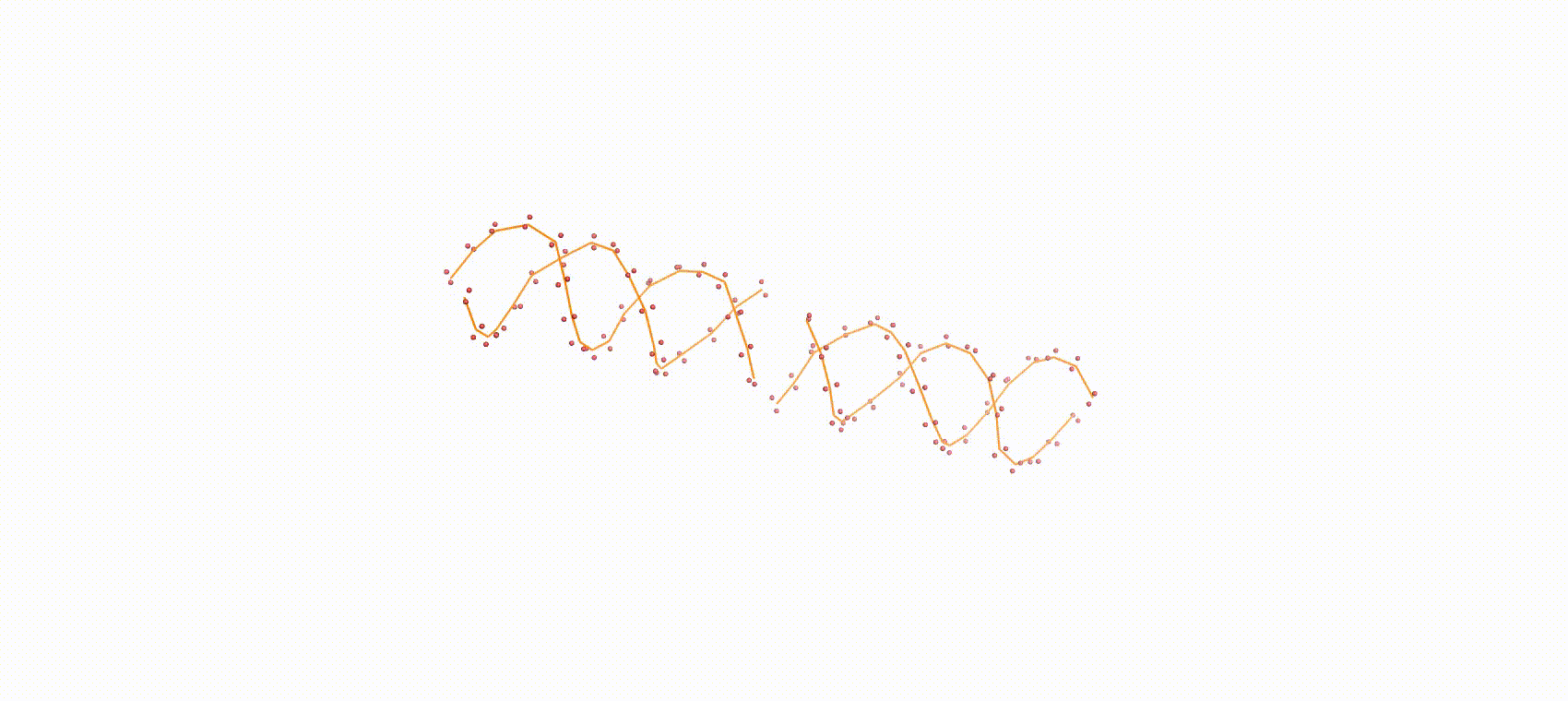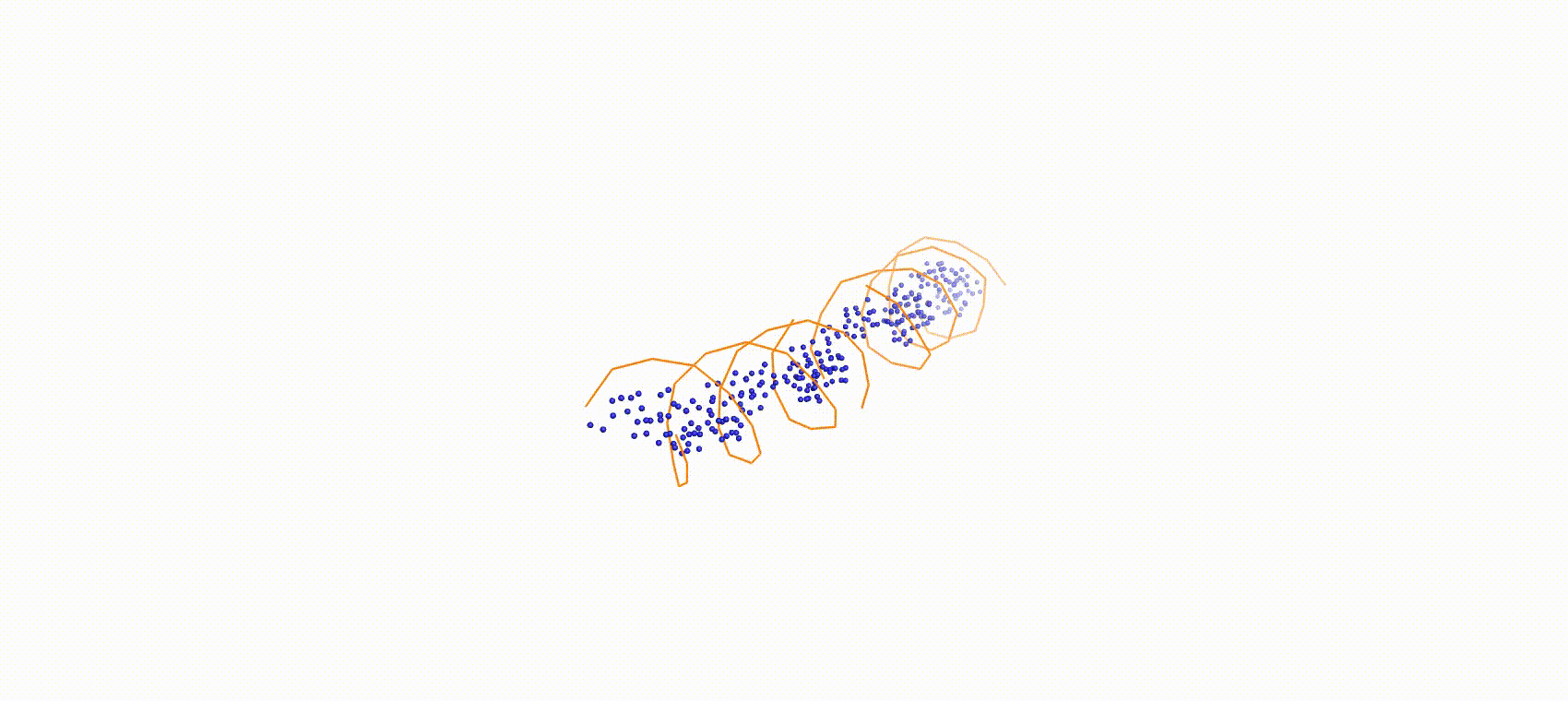
Таблица ДНК-белковых взаимодействий:
| Контакты атомов белка с | Полярные | Неполярные | Всего |
|---|---|---|---|
| остатками 2'-дезоксирибозы | 8 | 39 | 47 |
| остатками фосфорной кислоты | 88 | 19 | 107 |
| остатками азотистых оснований со стороны большой бороздки | 21 | 20 | 41 |
| остатками азотистых оснований со стороны малой бороздки | 0 | 4 | 4 |
С помощью nucplot получил схему контактов: