Семестр 2. Практикум 11. Гомология и выравнивание. Домены. JalView
Содержание
1. Выбор семейства белковых доменов
Из базы Pfam выбрано семейство белковых доменов со следующими характеристиками:
- AC:
PF00018 - ID:
SH3_1 - Summary name: SH3 domain
- #seed: 55 | #structures: 563 | #species: 1443
Домен удовлетворяет условиям задания: более 20 последовательностей в seed-выравнивании и не менее 3 структур.
2. Описание семейства доменов
Таблица 1. Формальные характеристики семейства PF00018
| Параметр | Информация | Комментарии |
|---|---|---|
| AC pfam | PF00018 | |
| ID pfam | SH3_1 | |
| #SEED | 55 | |
| #All | 176 301 (Pfam 38.1) | Proteins - All на InterPro |
| #SW | 585 | Proteins - Reviewed |
| #architectures | 4 795 | Domain architectures |
| #3D | 563 | Structures |
| #Eukaryota | 214 924 (3 684 вида) | Taxonomy |
| #Archaea | — | |
| #Bacteria | 67 (59 видов) | |
| #Viruses | 30 (19 видов) |
2.1. Функция и структура домена
SH3 (Src homology 3) — небольшой домен (~60 а.к.), впервые описанный в цитоплазматической тирозинкиназе Src (P12931). Домены SH3 характерны для белков, участвующих в передаче сигнала и организации цитоскелета. Структурно домен представляет собой частично открытую бета-бочку. SH3 домены, как правило, узнают пролин-богатые мотивы (PxxP) в белках-партнёрах, обеспечивая специфические белок-белковые взаимодействия в сигнальных каскадах.
2.2. Таксономическое распространение
Домен SH3_1 встречается преимущественно у эукариот: 214 924 белка в 3 684 видах. У бактерий представлен незначительно — 67 белков в 59 видах, у вирусов — 30 белков в 19 видах. У архей домен не обнаружен. Таким образом, SH3 — типично эукариотический домен.
Таксономическое распределение белков домена PF00018 с разной глубиной представлено на рисунках ниже.
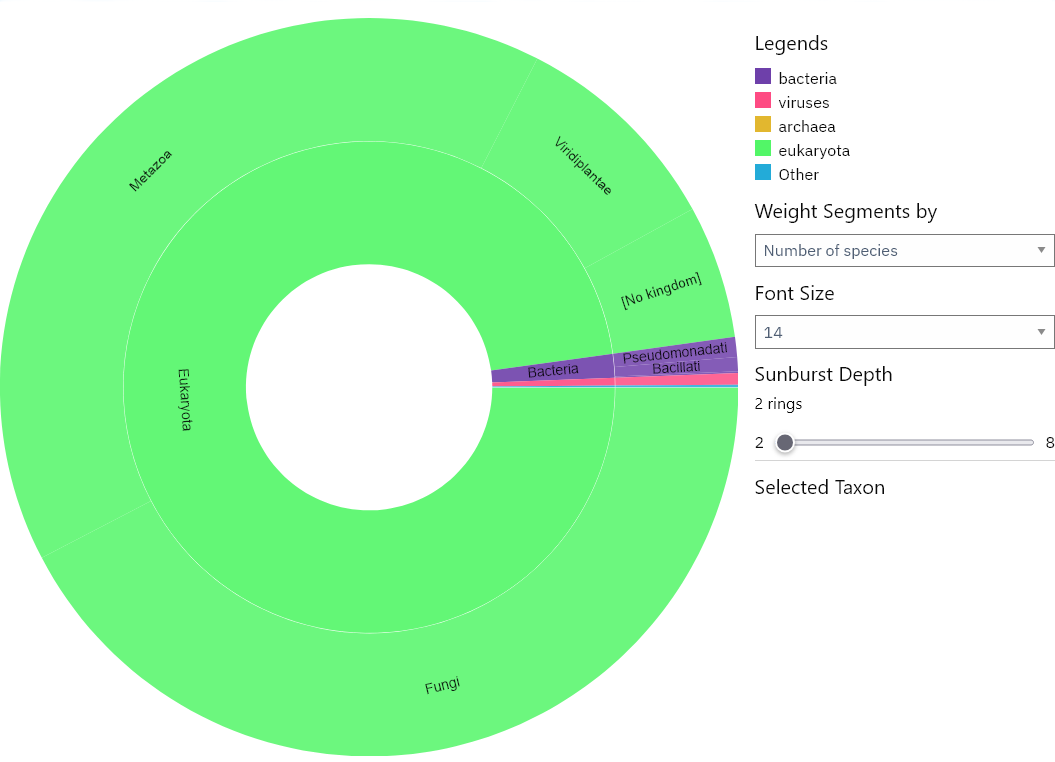
Рисунок 1а. Глубина - 2.
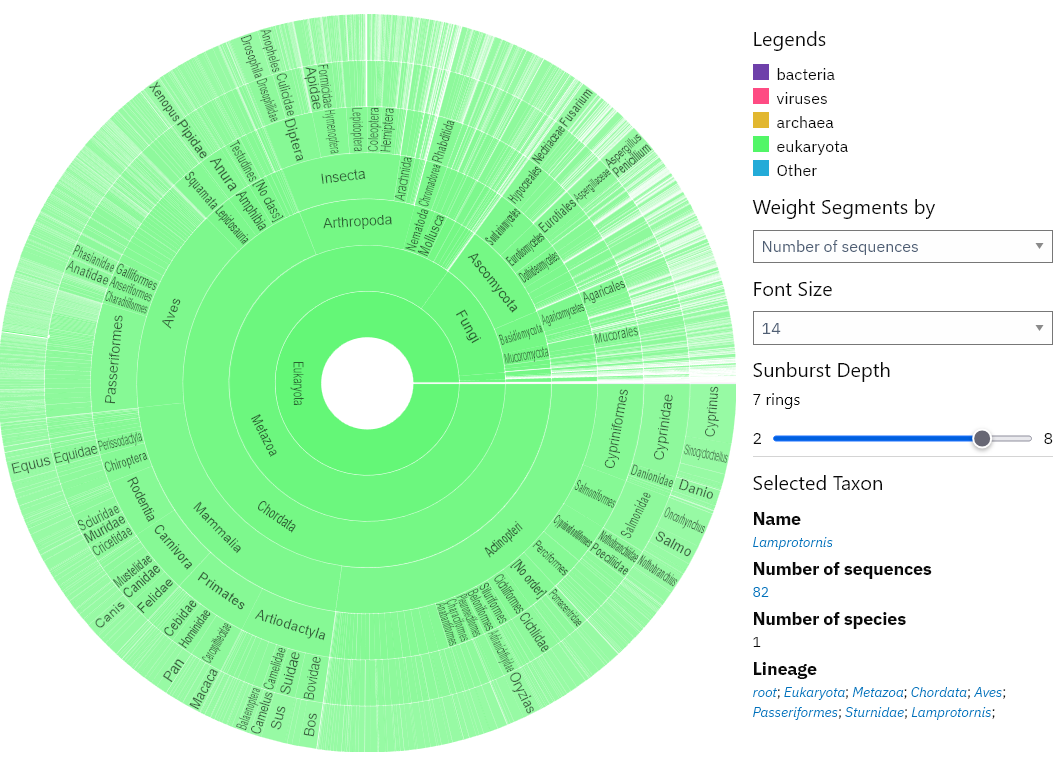
Рисунок 1б. Глубина - 7.
2.3. Доменные архитектуры
Домен SH3_1 встречается в 4 795 различных доменных архитектурах. Наиболее распространённые из них:
SH3_1 + SH2 + PK_Tyr_Ser-Thr— 16 108 белков (пример: P10447); типичная архитектура тирозинкиназ семейства SrcSH3_1— 15 993 белка (пример: P40073); домен как единственный структурный элементBAR + SH3_1— 7 406 белков (пример: P39743); белки, связанные с изгибом мембраны и эндоцитозом
3. Анализ блоков выравнивания seed
Seed-выравнивание домена PF00018 загружено в JalView (File - Fetch sequences - PFAM Seed).
Таблица 2. Результаты анализа блоков выравнивания
| Параметр | Информация | Комментарии |
|---|---|---|
| Выравнивание seed | 55 последовательностей, 56 колонок | |
| МДБ-all (колонки) | 13–28 | Col 37 (W, 100%) — абсолютно консервативная во всём выравнивании, но находится вне блока; блок 37–43 короче |
| Абсолютно консервативные колонки во всём выравнивании | 37: W (100%, 55/55, 0 гэпов) | Виден при Clustal + By conservation |
| Функционально консервативные колонки в МДБ-all | 15:[DE] (89%), 22:[DE] (84%) | Группа кислых а.к. |
| МДБ-notAll (колонки, последовательности) | 1–10, последовательности 1–54 | Q6FWR1_CANGA/526-572 исключена — имеет гэп в col 1 |
| 100% консервативные колонки в МДБ-notAll | 2:A (48/54, 89%), 4:[FY] (47/54, 87%), 6:[FY] (53/54, 98%) | |
| Недостоверный участок (колонки) | 33–35 | Col 34 имеет букву только у 1 из 55 последовательностей (BOI2_YEAST), col 33 — только у 4 |
3.1. Максимальный достоверный блок, включающий все последовательности (МДБ-all)
Блок определён на колонках 13–28 (длина 16 позиций). В этом участке все 55 последовательностей представлены буквами — гэпов нет. Блок соответствует консервативному мотиву петли между первым и вторым бета-тяжами SH3 домена, включающей функционально важный участок связывания лиганда.
Консервативные позиции внутри блока:
- Col 15: [DE] — E у 35, D у 14 из 55 последовательностей (89%); функционально консервативна (группа кислых а.к.)
- Col 22: [DE] — D у 30, E у 16 из 55 (84%); функционально консервативна
Блок максимален: расширение влево (col 12: 91% гэпов) или вправо (col 29: 4 гэпа, неконсервативна) снижает его достоверность. Добавление любой последовательности невозможно — все 55 уже включены.
Абсолютно консервативная позиция во всём выравнивании — col 37: W (триптофан, 100%, все 55 последовательностей, 0 гэпов). Она входит в блок 37–43, который короче МДБ-all. Триптофан col 37 — ключевой остаток активного сайта SH3, участвующий в связывании пролин-богатых лигандов; хорошо виден при раскраске Color - Clustal + By conservation.
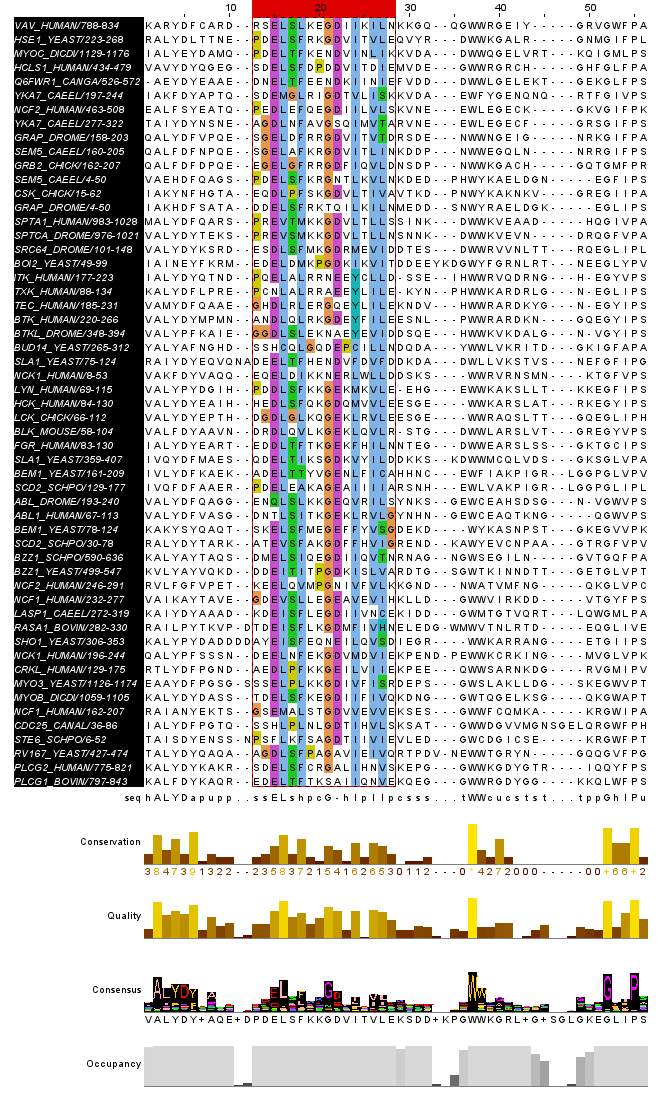
Рисунок 2. Вид «МДБ-all». Колонки 15 и 22 соответствуют консервативной группе [DE].
3.2. Максимальный достоверный блок, включающий не все последовательности (МДБ-notAll)
Блок определён на колонках 1–10, подмножество из 54 последовательностей (последовательности 1–54; исключена Q6FWR1_CANGA/526-572, имеющая гэп в колонке 1). В этих 10 колонках у 54 последовательностей нет ни одного гэпа.
Консервативные позиции внутри блока (среди 54 последовательностей):
- Col 2: A — A у 48 из 54 (89%); почти абсолютная консервация
- Col 4: [FY] — Y у 38, F у 9 из 54 (87%); функционально консервативна (группа ароматических а.к.)
- Col 6: [FY] — Y у 31, F у 22 из 54 (98%); практически абсолютная консервация [FY]
Этот блок соответствует N-концевой части домена SH3 — первому бета-тяжу и предшествующей петле с характерным мотивом xALYDY.
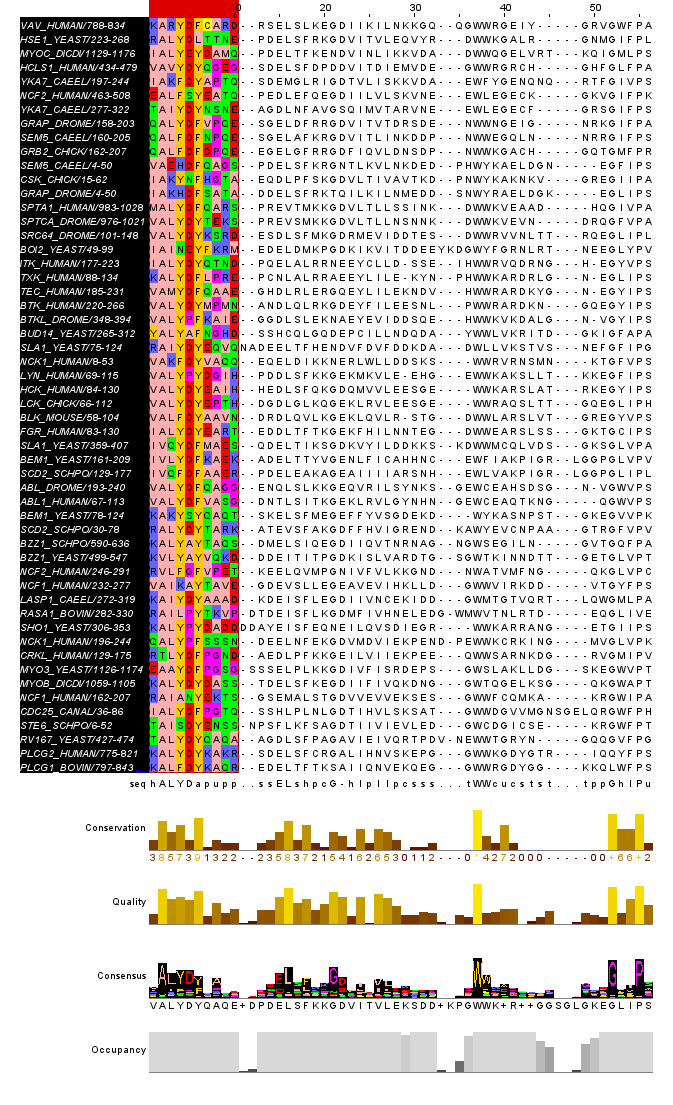
Рисунок 3. Вид «МДБ-notAll».
3.3. Участок выравнивания, не отражающий ход эволюции
Колонки 33–35 не содержат ни одного достоверного подблока даже для пары последовательностей:
- Col 33: буква только у 4 из 55 последовательностей (51 гэп, 93%)
- Col 34: буква только у 1 из 55 последовательностей (54 гэпа, 98%) — единственная буква у
BOI2_YEAST/49-99 - Col 35: буква у 16 из 55 (39 гэпов), при этом никакой консервации среди присутствующих букв нет

Рисунок 4. Вид «Недостоверный»: во всех строках — гэпы, буквы присутствуют лишь у единичных последовательностей.
На этом участке каждая последовательность имеет уникальную вставку (или её нет совсем). Нет оснований считать, что выравнивание здесь отражает эволюционное родство — скорее всего, это случайное выравнивание независимых петель переменной длины между бета-тяжами.
Проект JalView
4. Карта локального сходства двух белков с SH3-доменом
Таблица 3. Выбранные белки и их доменные архитектуры
| Параметр | Информация | Комментарии |
|---|---|---|
| Доменная архитектура 1 | SH3_1 + SH2 + PK_Tyr_Ser-Thr | |
| Белок с архитектурой 1 | P10447 — тирозинкиназа Src (репрезентативный белок) | |
| Доменная архитектура 2 | BAR + SH3_1 | |
| Белок с архитектурой 2 | P39743 — белок эндоцитоза (репрезентативный белок) |
Карта локального сходства (dotplot) построена с помощью NCBI BLASTp (Align two or more sequences - Dot Plot).
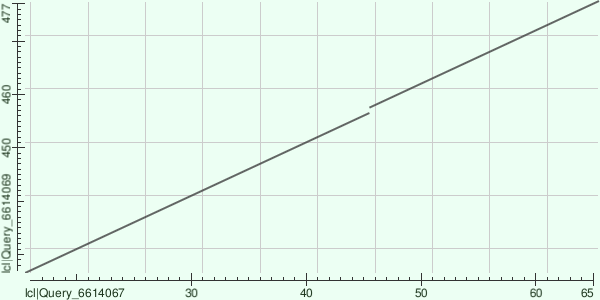
Рисунок 5. Карта локального сходства (dotplot) белков P10447 и P39743. Единственная диагональ соответствует общему SH3-домену.
На карте обнаруживается единственная диагональ, что означает одну область локального сходства между двумя белками. Это и есть общий SH3-домен: именно он гомологичен в обеих последовательностях, тогда как остальные домены — SH2 и тирозинкиназный у P10447, BAR у P39743 — друг другу не гомологичны и на карте не отображаются.
В диагонали наблюдается разрыв — нормальная эволюционная вариация внутри доменного семейства.
Таким образом, несмотря на принципиально разный белковый контекст (сигнальная киназа vs. белок регуляции кривизны мембраны), SH3-домены обоих белков сохраняют гомологию, что подтверждает общее эволюционное происхождение домена вне зависимости от архитектуры содержащего его белка.