Гомология и выравнивание. Домены. JalView
ВЫБОР СЕМЕЙСТВА БЕЛКОВЫХ ДОМЕНОВ
| Характеристика | Информация |
|---|---|
| AC pfam | PF00007 |
| ID pfam | Cystine-knot domain |
| #SEED | 24 |
| #All | 12k |
| #SW | 139 |
| #architectures | 85 |
| #3D | 30 |
| Taxonomy | |
| #eukaryota | 12210 |
| #archaea | 0 |
| #bacteria | 1 |
Домен имеет тенденцию к ассоциации с цистеин-содержащим доменом CCN3 Nov like TSP1 domain (TSP1_CCN), обеспечивающим дисульфид-опосредованное связывание, в приблизительно половине случаев, причем TSP1_CCN располагается в таких белках c N-конца относительно домена цистинового узла.
Сам Cystine-knot domain содержится во внеклеточных белках, димеризующихся посредством образования дисульфидных связей. В зависимости от топологии дисульфидных мостиков существуют разные типы цистиновых узлов, однако все их объединяет формирование ротаксан-подобной структуры благодаря формированию из двух дисульфидных связей петли, через которую проходит третья связь. Такая структура консервативна и имеет форму "гантели", проходящей через "кольцо", что делает ее так называемой кинетической ловушкой - концы "гантели" больше внутреннего диаметра "кольца", что предовращает диссоциацию данного комплекса и обеспечивает стабилизацию белковой структуры.
Цистиновый узел преимущественно представлен в белках эукариот (за одним исключением для бактерии Kangiella spongicola), причем наиболее часто у многоклеточных (за также одним исключением в виде представителя Лабиринтуломицетов Mucochytrium quahogii).
ВЫРАВНИВАНИЕ БЕЛКОВЫХ ДОМЕНОВ
| Информация | |
|---|---|
| Выравнивание seed | 24 последовательности, 112 колонок |
| МДБ-all | Колонки 82-90 |
| 100% консервативные колонки в МДБ-all | Абсолютно консервативные: 88:C, 90:C. Функционально консервативные: 85:[AI] |
| МДБ-notAll | 52-90 колонки, 1-7 последовательности (вырезаны в отдельное окно JalView) |
| 100% консервативные колонки в МДБ-notAll | Абсолютно консервативные: 54:Q, 57:C, 58:T, 59:Y, 64:Y, 66:T, 70:P, 72:C, 78:P, 82:Y, 83:P, 84:V, 85:A, 86:L, 87:S, 88:C, 90:C. Функционально консервативные: 67:[IVF], 69:[LFI], 80:[TS] |
| Недостоверный блок | 41-52 колонки |
Гиперссылка на файл с проектом Jalview.
КАРТА ЛОКАЛЬНОГО СХОДСТВА
| Информация | |
|---|---|
| Доменная архитектура 1 | PF00219 - PF00093 - PF19035 - PF00007 |
| Белок с архитектурой 1 | P18406 |
| Доменная архитектура 2 | PF00093 - PF19035 - PF00007 |
| Белок с архитектурой 2 | A7LCR5 |
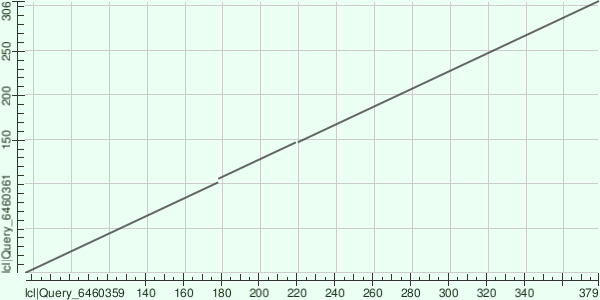
Основываясь на полученной карте локального сходства, можно заключить, что последовательности белков с выбранными доменными архитектурами практически идентичны, за исключением двух небольших участков инсерций или делеций в одной из последовательностей. Дополнительный анализ выравнивания подтверждает эту информацию: в районе 180 позиции во второй последовательности обнаруживаются 4 гэпа подряд, а в районе 150 позиции первой последовательности также присутствует один гэп (что соотносится с более и менее крупным разрывом на карте). Иллюстрации доменов в Pfam Architectures также подтверждают это выравнивание: исследуемые доменные архитектуры отличаются лишь одним небольшим белковым мотивом VWC (von Willebrand factor type C domain).