Семестр 4, практикум 4
Назад на учебную страницу Птицыной ЕленыТрансмембранные белки
Выбор белка
Перед крыльцом дачи и перед моим окном сейчас растёт голубая ёлочка, и еще я очень люблю Голосеменные растения, сосновыми и еловыми лесами покрыты все окрестности. Поэтому в Google Scholar был введен запрос "Picea Transmembrane protein". Первая статья Oliviusson P., Salaj J., Hakman I. Expression pattern of transcripts encoding water channel-like proteins in Norway spruce (Picea abies) //Plant Molecular Biology. – 2001. – Т. 46. – №. 3. – С. 289-299. была посвящена аквапоринам Picea abies. В ней авторы, в частности, идентифицировали аквапорин-подобную cDNA из корней двухнедельных сеянцев и обнаружили, что её продукт принадлежит TIP-подгруппе (tonoplast intrinsic protein) семейства MIP-белков (major intrinsic protein). Филогенетический анализ MIP-семейства показал, что её подгруппы разделились и развились примерно 330 миллионов лет назад - как раз тогда, когда разделились Покрытосеменные и Голосеменные.
B ncbi была найдена аминокислотная последовательность белка Picea mariana probable aquaporin (Sb01) mRNA, complete cds (GenBank: AF051202.1). Естественный ареал Picea mariana (Рис. 1) лежит в Северной Америке, с 1700 года она выращивается в Европе как декоративное растение, в России - с середины XIX века. Picea mariana может достигать 30 м в высоту, а в культуре встречается и маленький подвид - Picea mariana Nana в 50 см.

Предсказание трансмембранных участков
Предсказание трансмембранных участков белка была выполнена с помощью сервиса TMHMM. В окно была вставлена аминокислотная последовательность. Результат (Рис. 2):
# WEBSEQUENCE Length: 282 # WEBSEQUENCE Number of predicted TMHs: 6 # WEBSEQUENCE Exp number of AAs in TMHs: 133.17865 # WEBSEQUENCE Exp number, first 60 AAs: 21.29332 # WEBSEQUENCE Total prob of N-in: 0.11799 # WEBSEQUENCE POSSIBLE N-term signal sequence WEBSEQUENCE TMHMM2.0 outside 1 35 WEBSEQUENCE TMHMM2.0 TMhelix 36 58 WEBSEQUENCE TMHMM2.0 inside 59 78 WEBSEQUENCE TMHMM2.0 TMhelix 79 101 WEBSEQUENCE TMHMM2.0 outside 102 115 WEBSEQUENCE TMHMM2.0 TMhelix 116 138 WEBSEQUENCE TMHMM2.0 inside 139 158 WEBSEQUENCE TMHMM2.0 TMhelix 159 181 WEBSEQUENCE TMHMM2.0 outside 182 200 WEBSEQUENCE TMHMM2.0 TMhelix 201 223 WEBSEQUENCE TMHMM2.0 inside 224 242 WEBSEQUENCE TMHMM2.0 TMhelix 243 265 WEBSEQUENCE TMHMM2.0 outside 266 282
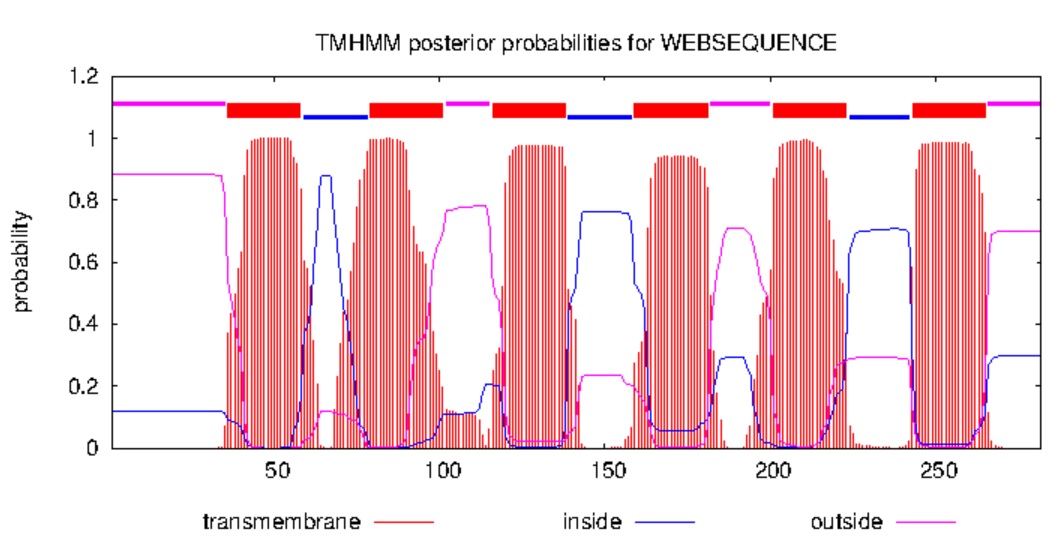
Белок пересекает мембрану 6 раз. Предсказания внутриклеточных и внеклеточных участков несколько перекрываются, но если обращать внимание только на самые вероятные участки, у белка 4 внутриклеточных участка и 3 внеклеточных.
Визуализация расположения в мембране
К сожалению, в банках не нашлось визуализации расположения в мембране этого аквапорина. Поэтому был взят другой растительный аквапорин .
Выбор белка
Теперь мы выбрали произвольный растительный аквапорин, содержащийся в базе RCSB PDB. Это AtPIP2;4, то есть Probable aquaporin PIP2-4 из Arabidopsis thaliana. В ncbi была найдена его аминокислотная последовательность.
Предсказание трансмембранных участков
Предсказание трансмембранных участков цепи A белка PIP2-4 была выполнена с помощью сервиса TMHMM. В окно была вставлена аминокислотная последовательность. Результат (Рис. 3):
# WEBSEQUENCE Length: 259 # WEBSEQUENCE Number of predicted TMHs: 6 # WEBSEQUENCE Exp number of AAs in TMHs: 131.73376 # WEBSEQUENCE Exp number, first 60 AAs: 33.45319 # WEBSEQUENCE Total prob of N-in: 0.98768 # WEBSEQUENCE POSSIBLE N-term signal sequence WEBSEQUENCE TMHMM2.0 inside 1 11 WEBSEQUENCE TMHMM2.0 TMhelix 12 34 WEBSEQUENCE TMHMM2.0 outside 35 48 WEBSEQUENCE TMHMM2.0 TMhelix 49 71 WEBSEQUENCE TMHMM2.0 inside 72 97 WEBSEQUENCE TMHMM2.0 TMhelix 98 120 WEBSEQUENCE TMHMM2.0 outside 121 139 WEBSEQUENCE TMHMM2.0 TMhelix 140 159 WEBSEQUENCE TMHMM2.0 inside 160 171 WEBSEQUENCE TMHMM2.0 TMhelix 172 194 WEBSEQUENCE TMHMM2.0 outside 195 219 WEBSEQUENCE TMHMM2.0 TMhelix 220 242 WEBSEQUENCE TMHMM2.0 inside 243 259
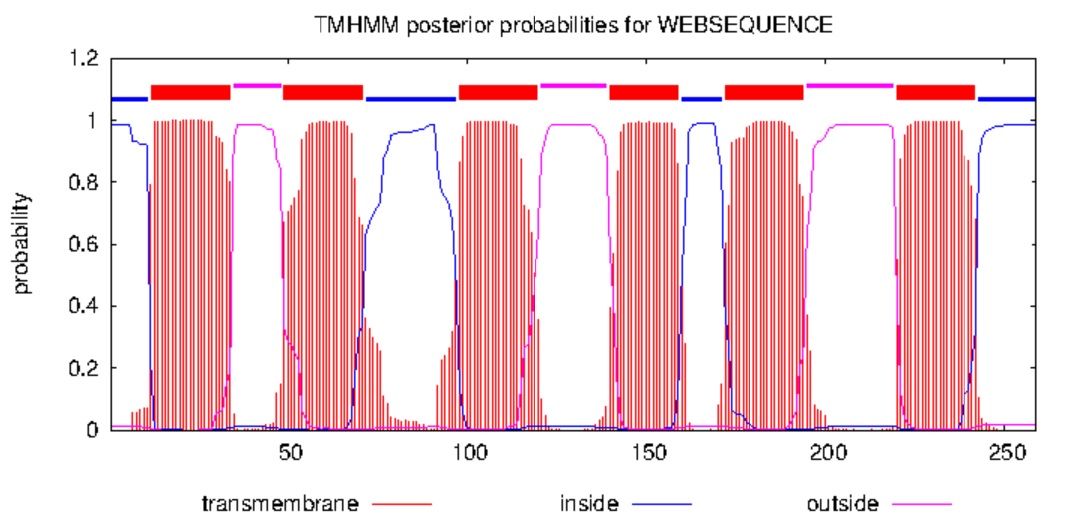
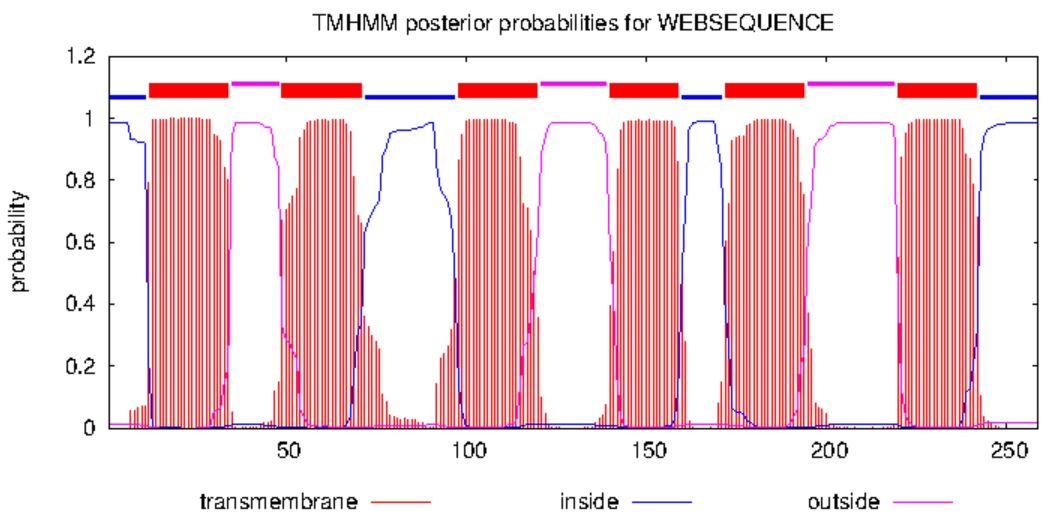
Цепь А пересекает мембрану 6 раз. Предсказания внутриклеточных и внеклеточных участков не перекрываются, есть 4 внутриклеточных участка и 3 внеклеточных. Для цепи B наблюдалась та же структура (Рис. 4).
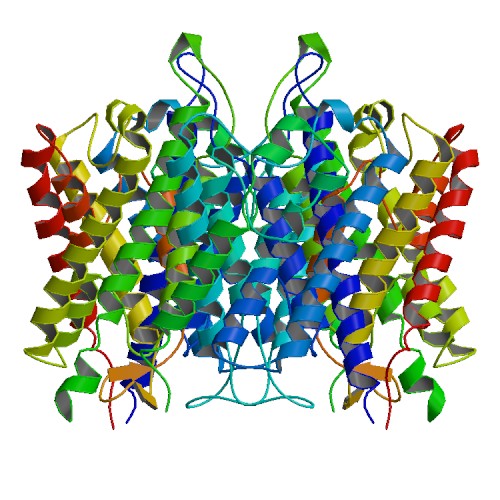
Визуализация расположения в мембране
В базе RCSB PDB была найдена визуализация расположения белка в мембране (Рис. 5).