Метаболические пути.
Цель работы - блабла
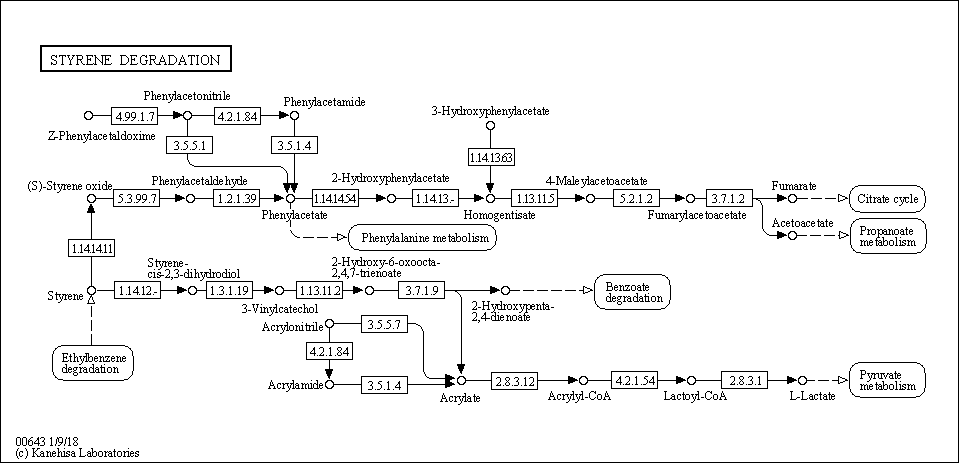
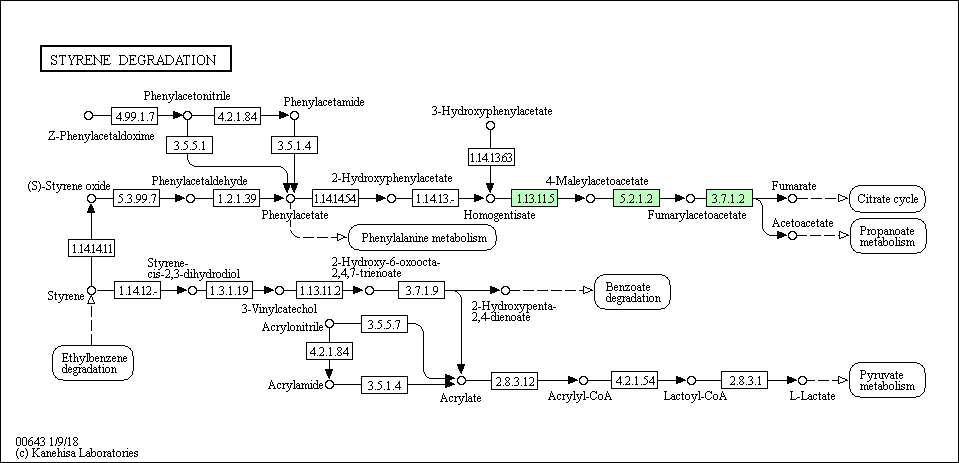
Номер моего метаболического пути - 00643 - styrene degradation (разложение стирола).
1. Картинка референсного пути
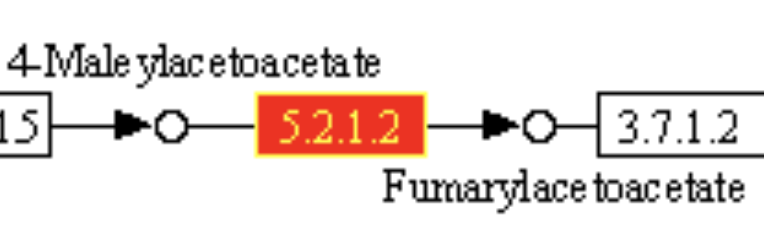
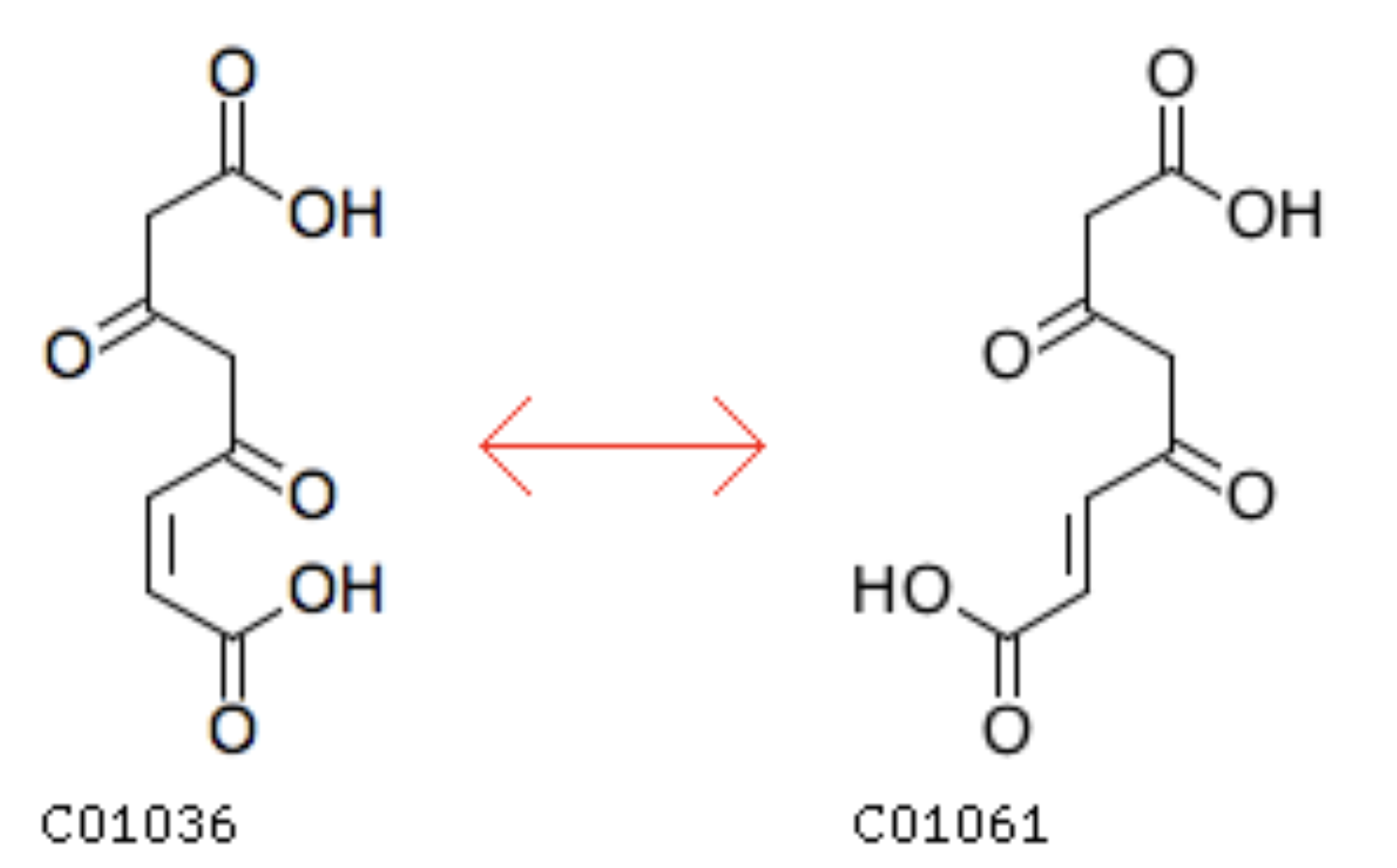
Формула реакции
5. Функции фермента, исходя из номера (5.2.1.2), согласно Brite hierarchy:
1) КЛАСС: 5 stands for Isomerases (изомеразы) - катализирует изомерные превращения;
2) ПОДКЛАСС: 2 stands for cis-trans-Isomerases (цис-транс-изомеразы) - катализирует превращения между цис- и транс- формами;
3) ПОД-ПОДКЛАСС: 1 stands for cis-trans Isomerases (only sub-subclass identified to date) (цис-транс-изомеразы - на данный момент известен лишь один под-подкласс)
4) НОМЕР ФЕРМЕНТА В ПОД-ПОДКЛАССЕ: 2 stands for maleylacetoacetate isomerase (малеилацетоацетат изомераза) - бывают разные, различаются по тому, с каким субстратом работают. этой изомеразе довелось иметь второй номер. штош, хорошо
6. 2 разных организма, их метаболические пути:
Rhizobium etli CFN 42
Vibrio vulnificus CMCP6
7. Для Vibrio vulnificus CMCP6:
число метаболических путей: 115;
число генов:
- кодирующих белки: 4433;
- рнковых: 139.
8. (*) Для двух выбранных организмов укажите число общих метаболических путей. Выполние задание с помощью KEGG API. Опишите ваши действия
сначала я перешла на сайт KEGG API
среди описанных там операций выбрала list, она позволяет получить список идентификаторов записи и связанного определения (мы хотим искать метаболические пути)
среди дб выбрала pathways
из этого лего собрала нечто такое "http://rest.kegg.jp/list/pathway/place_for_the_organism"
дальше было #@$$^%$!
пробежавшись по сайту и не найдя нормального объяснения применения там логических операций я как истинный биоинформатек написала код
скачать код
этот код делает следующее:
парсит странички с метаболическими путями моих 2х организмов
и затем сравнивает получившиеся списки путей
и на основании этого составляет список общих
9. (*) Возьмите список ID из прошлого задания, посмотрите обогащение KEGG путями (STRING)
