Для поика структурных гомологов использовался сервер PDBeFold.
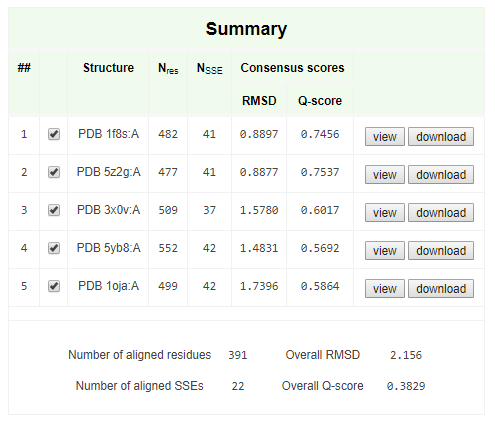
Я осуществил поиск для фермента LAAO (PDB 1f8s) по цепи А (всё равно эти цепи одинаковы), параметры поиска заданы по умолчанию. Для дальнейшей работы необходимо выбрать несколько структур с RMSD между 0,8 и 2,5 и длиной выравнивания более 50% от длины.
Были отобраны следующие гомологи: 5z2g:А (RSMD=0.56), 5yb8:A (RMSD=1.94), 1oja:A (RMSD=2.17), 3x0v:A (RMSD=1.81)

Файл с выбранными последовательностями
Файл с множественным выравниванием
Файл с совмещёнными структурами (PDB-версия)
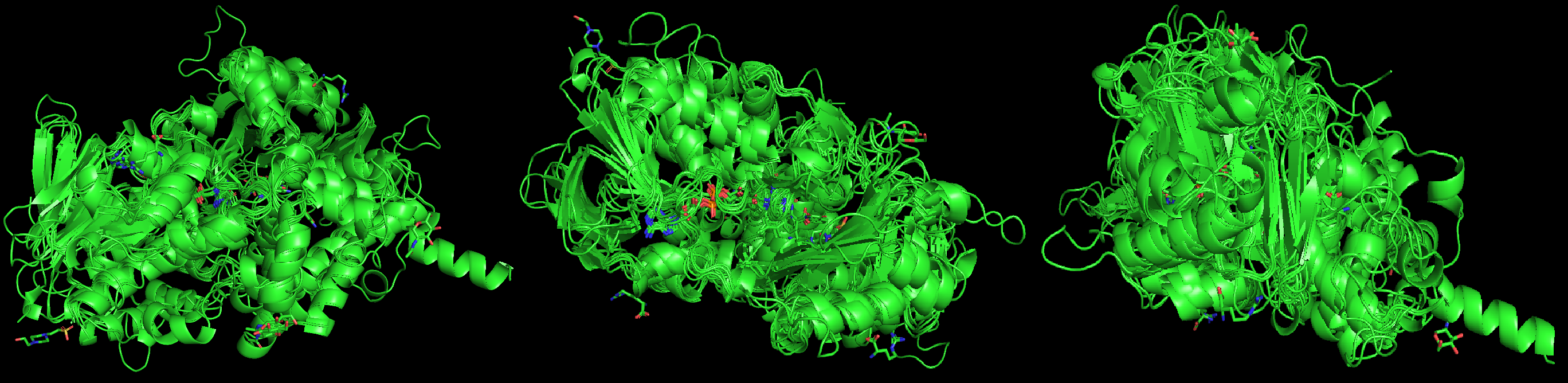
Картинка совмещения структурных гомологов LAAO (1f8r). Хорошо видно, что ход полипептидной цепи в пространстве совпадает, то есть топологии сходны. Также видно соответствие всех петель в структурах.
Ниже представлены картинки выравниваний: первая - визуализация структурного выравнивания, вторая - множественное выравнивание Muscle.


Для удобства визуализации я расположил их друг под другом.
Выравнивание последовательностей меньше структурного выравнивания. В остальном оба выравнивания похожи.
Отличия есть и довольно много (нет смысла перечислять их все), но большая часть связана с маленькими невыровненными буквами в первом выравнивании. Учитывая наличие таких невыровненных позиций, структурное выранивание является менее точным, чем выравнивание последовательностей.
Также можно отметить, что все найденные несоответствия наблюдаются именно в неструктурированных участках (или иногда захватывают граничные остатки элементов вторичной структуры) и отсутствуют в спиралях или бета-тяжах.
© Борисов Евгений 2018