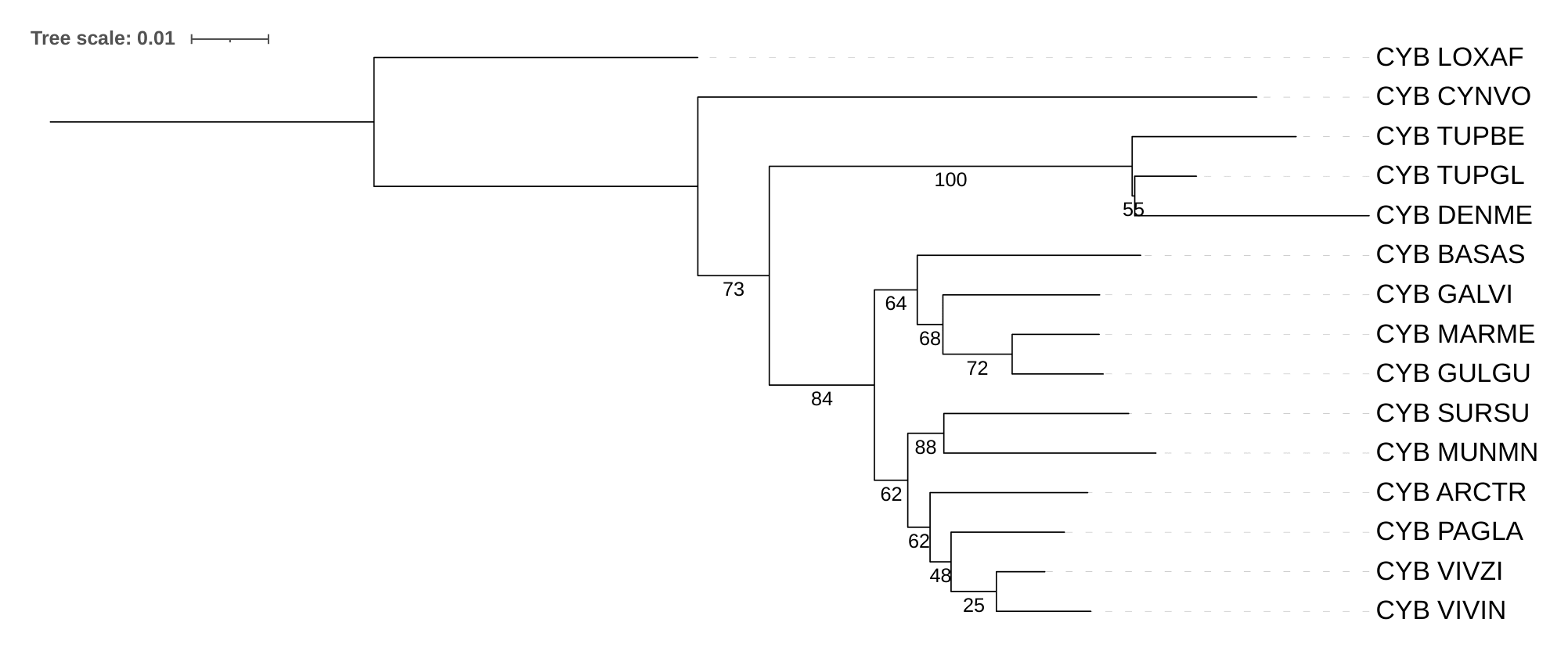
Практикум 3. Реконструкция и сравнение деревьев. Бутстреп
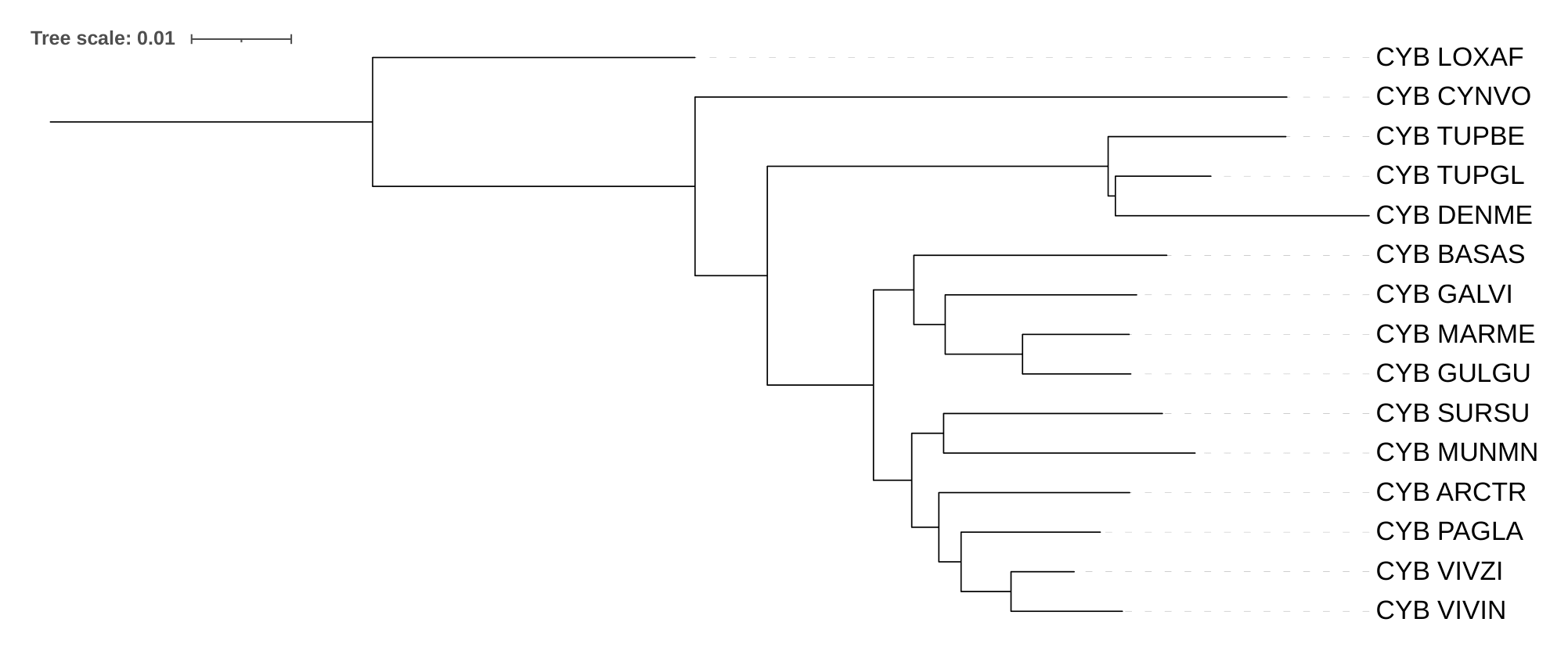
Для дальнейшего удобства я привожу два дерева (рис 1), дерево видов и дерево, построенное по белковым последовательностям цитохромов B.
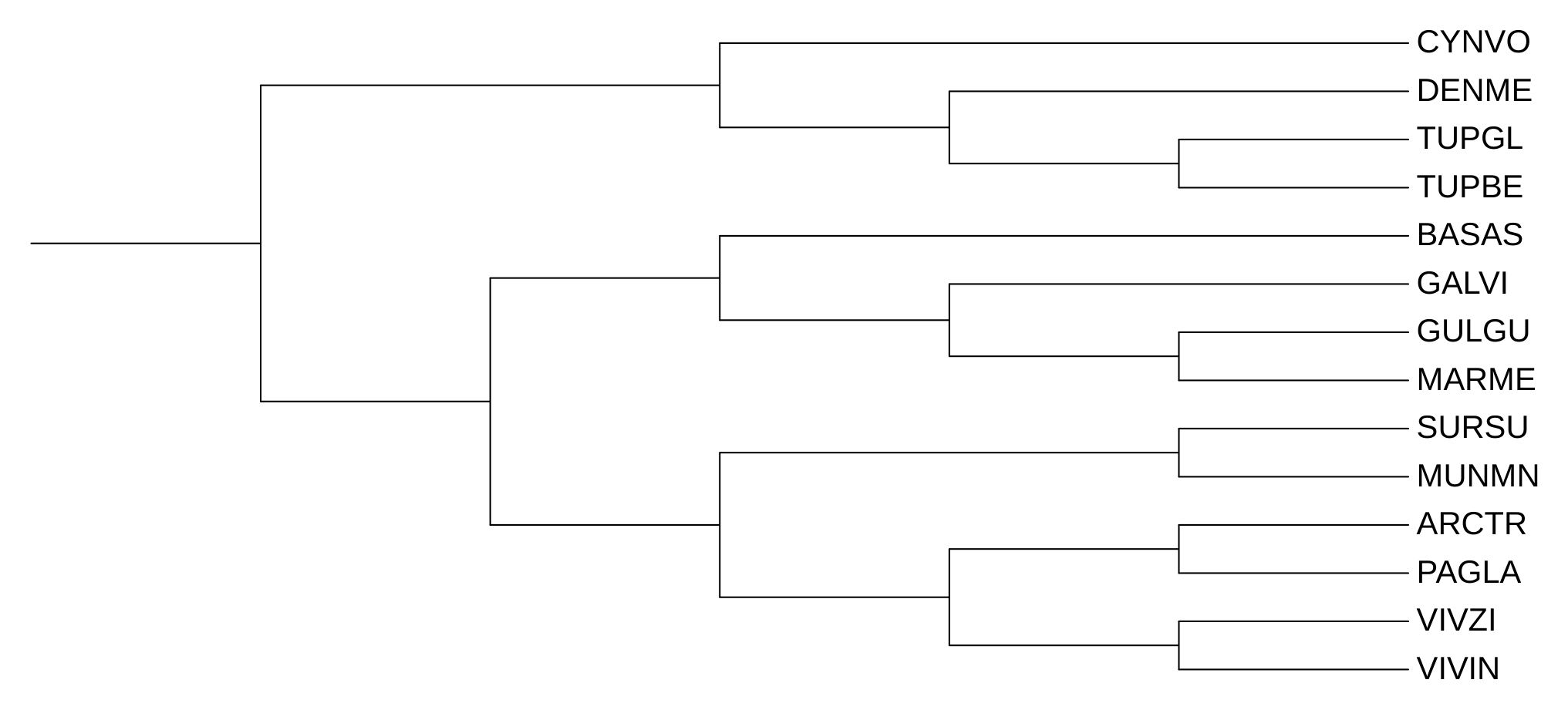
Реконструкция дерева по нуклеотидным последовательностям
Для реконструкции дерева по нуклеотидным последовательностям были выбраны последовательности 12S rRNA выбранных видов (рис 2).
К сожалению, для Martes melampus не был найден митохондриальный геном, поэтому был взят геном Martes martes (MARMT на дереве).
Анологичная ситуация для Dendrogale melanura, была взята последовательность, принадлежащая Dendrogale murina (DENMU на дереве).
А также, не аннотирован митохондриальный геном Cynocephalus volans, а геномы других видов не представленны в этом роду, поэтому был пропущен этот вид.
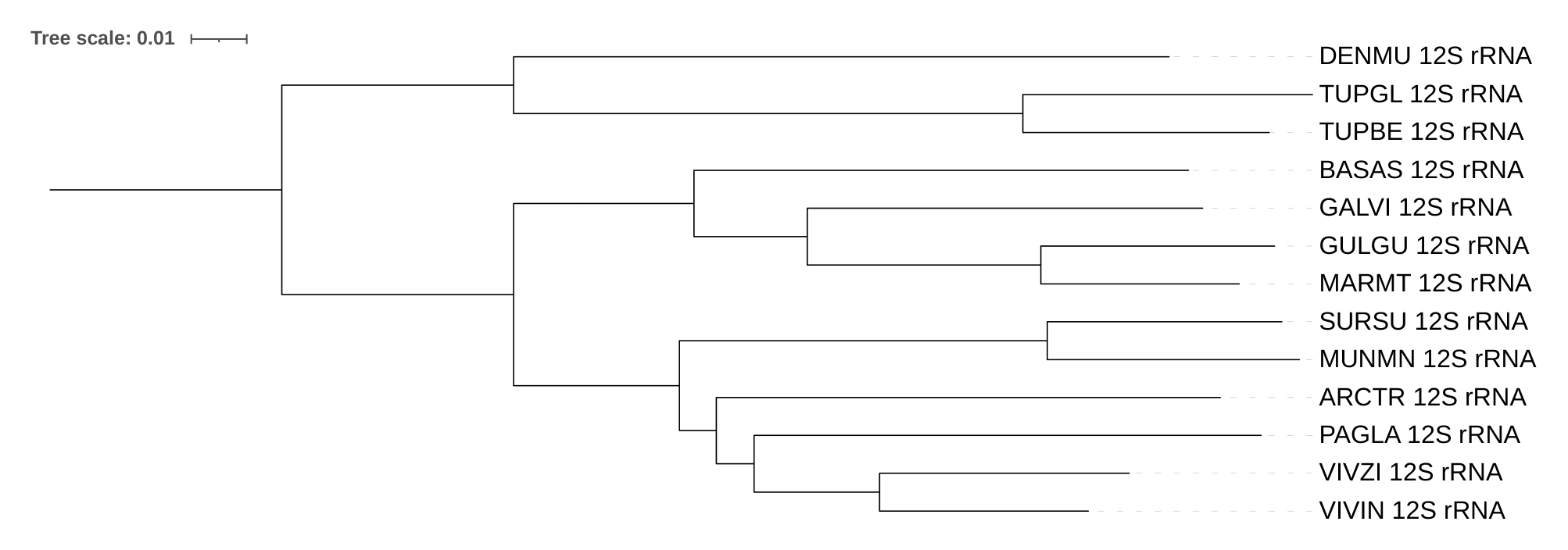
Дерево 12S рРНК по топологии идентично дереву видов (за отсутсвием названного уже вида Cynocephalus volans), за исключением того, что Arctogalidia trivirgata (ARCTR) является сестринским ко всем остальным рассматриваемым Виверровым (Viverricula indica (VIVIN), Viverra zibetha (VIVZI), Paguma larvata (PAGLA)), а не сестринской ветвью к Paguma larvata (PAGLA), также как и в случае с цитохромами.
Укоренение во внешнюю группу
Младший таксон, к которому принадлежат все выбранные виды, это Boreoeutheria, дочернему таксону Eutheria,
следовательно, в качестве аутгруппы возьмем, допустим, Loxodonta africana (LOXAF),
который принадлежит Afrotheria, еще одной группе из Eutheria.
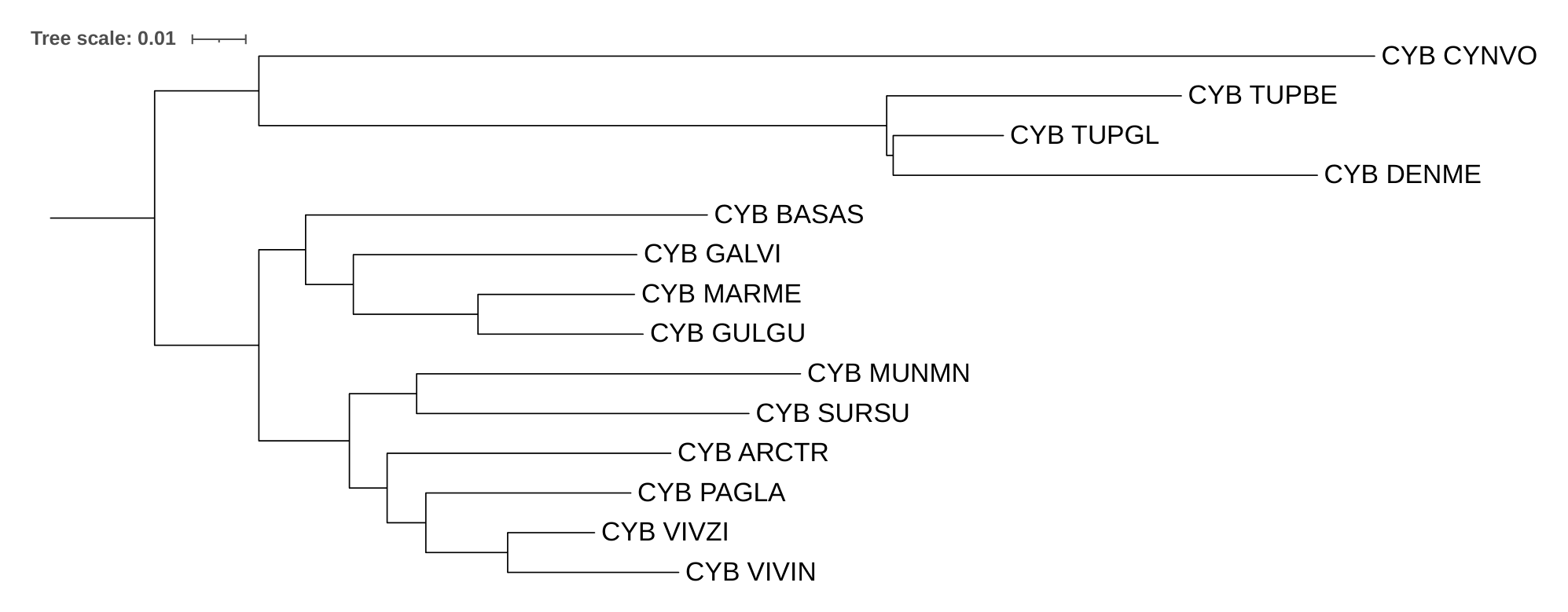
Полученное дерево с аутгруппой изменило свою топологию (рис. 3).
Теперь Cynocephalus volans является сестринской кладой ко всем рассматриваемым видам (за исключением аутгруппы, естественно),
до укоренения во внешнюю группу этот вид был сестринским к кладе из рассматриваемых Tupaiidae
(Tupaia belangeri (TUPBE), Tupaia glis (TUPGL), Dendrogale melanura (DENME)).
Бутстреп
Интересно, что неправильно реконструированные ветви имеют высокую бутсрэп-поддержку (рис. 4), возможно, из-за высокой консервативности цитохрома B и малого времени дивергенции бутстрэп-поддержка показывает не совсем точные результаты.