Предсказание вторичной структуры заданной тРНК и анализ НК-белкового комплекса.
Задание 1.
Нам нужно проанализировать предсказания вторичной структуры тРНК 3 разными программами. Анализировать мы будем на примере структуры тРНК с pdbid 1ffy. В предыдущем практикуме мы уже предсказывали структуру при помощи программу find_pair из пакета 3DNA.
Для начала поработаем с программой einverted из пакета EMBOSS.
echo GGGCUUGUAGCUCAGGUGGUUAGAGCGCACCCCUGAUAAGGGUGAGGUCGGUGGUUCAAGUCCACUCAGGCCCAC > rna.seq
einverted -sequence rna.seq -gap 12 -threshold 10 -match 3 -mismatch -3 -outfile einverted.out -outseq seqout
Выходной файл: einverted.out.
Теперь попробуем предсказать вторичную структуру тРНК при помощи программы ViennaRNA по Алгоритму Зукера.
Самая оптимальная вторичная структура тРНК, очевидно, не соответствует действительности - рисунок 1. Поэтому была выбрана единственная, наиболее похожая на классические структуры тРНК - рисунок 2.
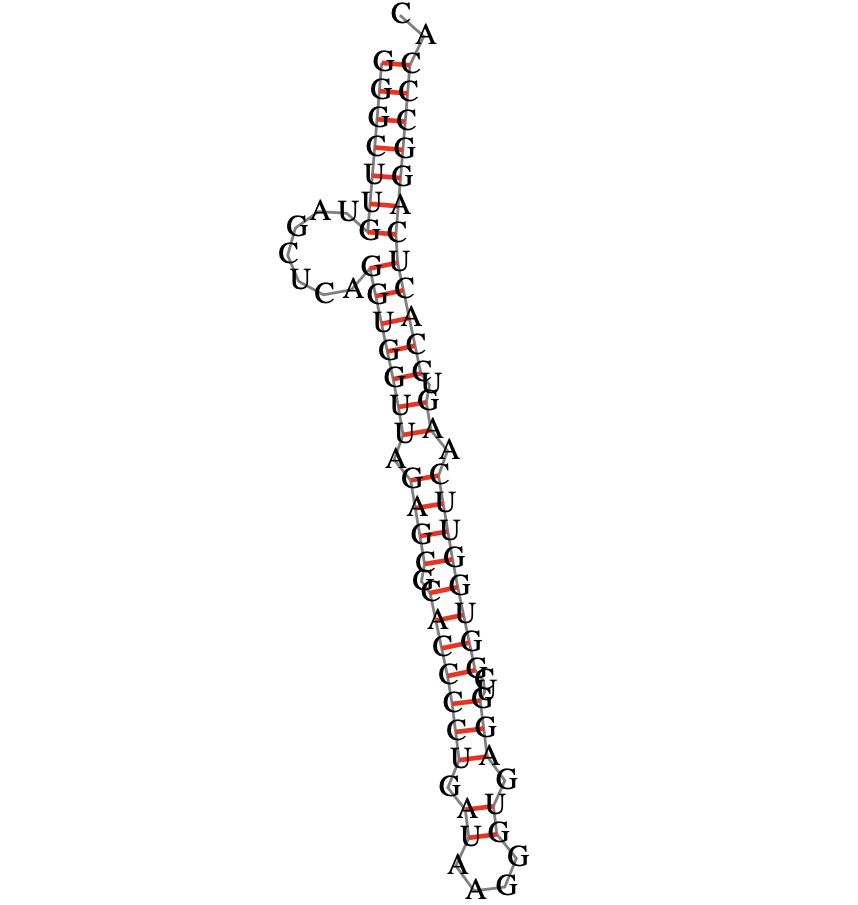
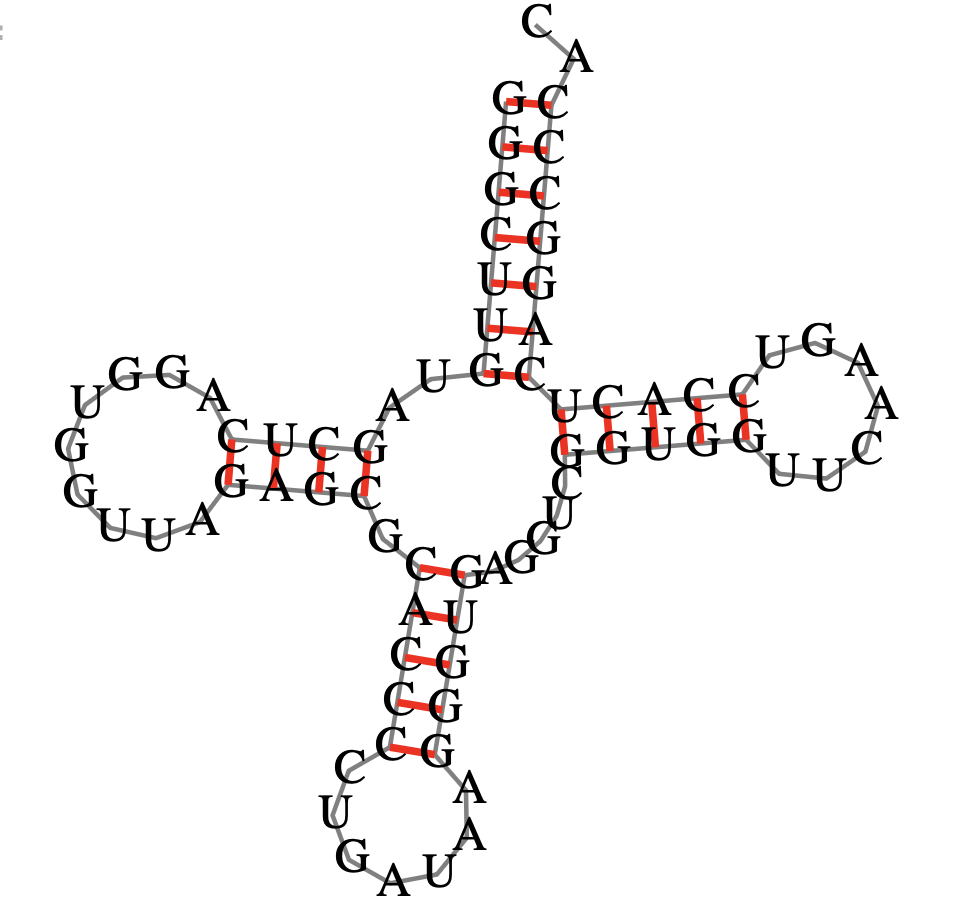
Сравним анализ трех различных программ - результаты приведены в таблице 1.
| Позиции в структуре (по результатам find_pair) | Результаты предсказания с помощью einverted | Результаты предсказания по алгоритму Зукера | |
|---|---|---|---|
| Акцепторный стебель | 1..7 - 72..66 | 1..7 - 63..57 | 1..7 - 73..67 |
| D-стебель | 10..13 - 25..22 | - | 10..13 - 26..23 |
| T-стебель | 49..54 - 65..61,58 | - | 66..62 - 50..54 |
| Антикодоновый стебель | 36,38..44 - 33..26 | 23..32 - 49..40 | 28..32 - 44..40 |
| Общее число канонических пар нуклеотидов | 23 | 14 | 21 |
Задание 2.
Упражнение 1.
В данном задании мы будем работать со структурой с pdbid 1r4o. Ниже приведен скрипт, показывающий все состоянии, требуемые в задании.
Скрипт pymol.
fetch 1r4o
hide everything
show cartoon, all
util.chainbow all
bg white
orient
time.sleep(1)
hide everything
select dna, polymer.nucleic
show lines, dna
orient dna
time.sleep(1)
select set1, (name O3'+O4'+O5')
show spheres, set1
set sphere_scale, 0.5, set1
color red, set1
orient set1
time.sleep(1)
hide spheres, set1
select set2, (name OP1+OP2)
show spheres, set2
set sphere_scale, 0.5, set2
color red, set2
orient set2
time.sleep(1)
hide spheres, set2
select set3, (symbol N and polymer.nucleic)
show spheres, set3
set sphere_scale, 0.5, set3
color blue, set3
orient set3
time.sleep(1)
Упражнение 2.
Tеперь нам нужно описать ДНК-белковые контакты в данной структуре. Будем считать полярными атомы кислорода и азота, а неполярными атомы углерода, фосфора и серы. Полярным контактом - ситуация, в которой расстояние между полярным атомом белка и полярным атомом ДНК меньше 3.5Å. Аналогично, неполярным контактом будем считать пару неполярных атомов на расстоянии меньше 4.5Å.
| Контакты атомов белка | Полярные | Неполярные | Неполярные |
|---|---|---|---|
| Отстатки 2'-дезоксирибозы | 1 | 20 | 21 |
| Остатки фосфорной кислоты | 13 | 16 | 29 |
| Азотистые основания со стороны большой бороздки | 4 | 9 | 13 |
| Азотистые основания со стороны малой бороздки | 0 | 1 | 1 |
Упражнения 3,4.
Теперь нам нужно воспользоваться программой nucplot для получения схемы ДНК-белковых контактов. Она работает только со старым форматов pdb поэтому:
remediator --old 1R4O.pdb > 1R4O_old.pdb
После этого можно уже воспользоваться nucplot:
nucplot 1R4O_old.pdb
В итоге мы получаем файл со взаимодействиями:
nucplot.pdf.


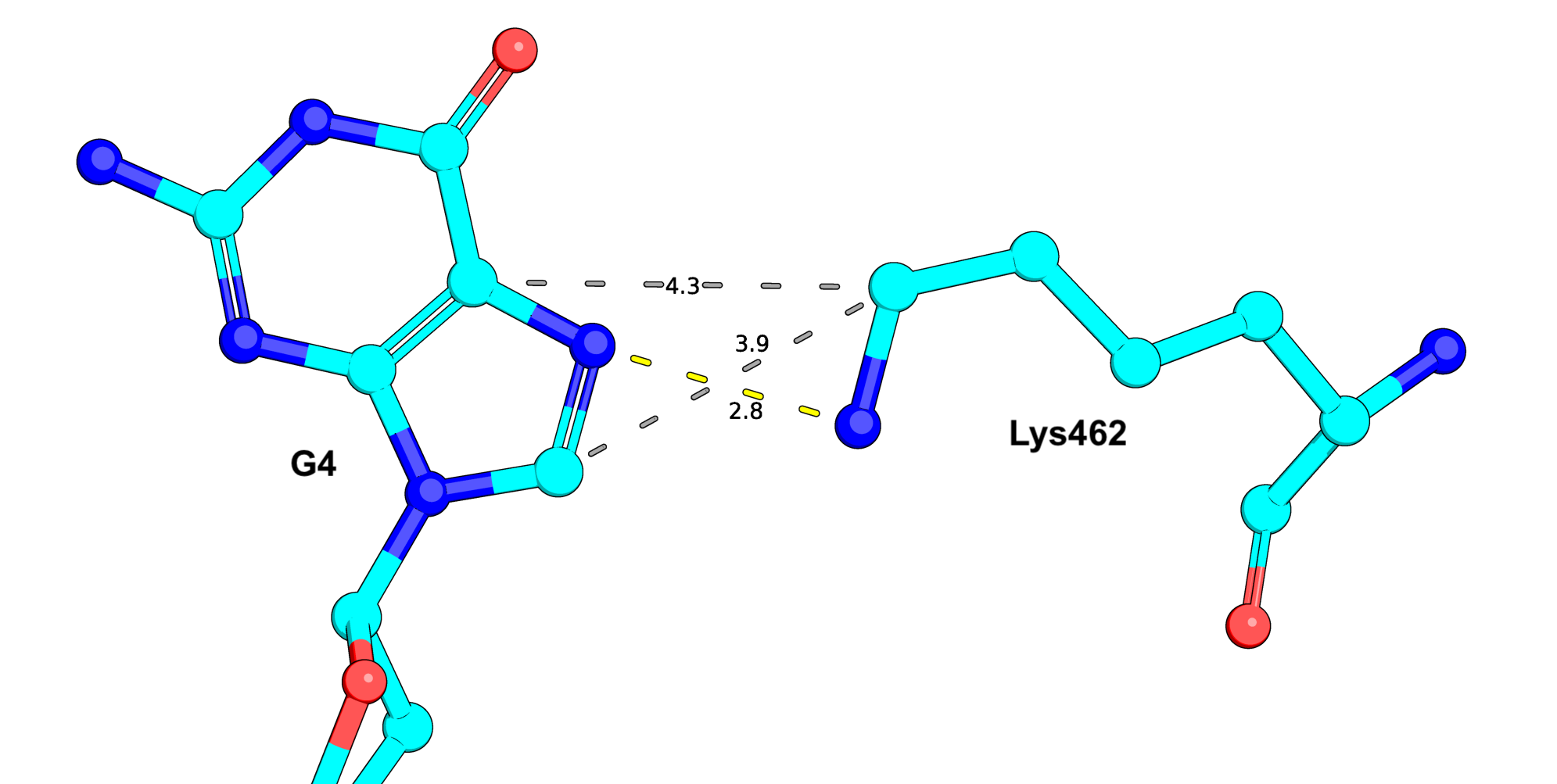
Согласно анализу программы nucplot наибольшее количество связей в этом
ДНК-белковом взаимодействии у Lys461 с гуанином 4 - рисунок 5. Однако из рисунка видно, что
2 из трех связи - неполярные связи углерода с углеродом, которые в реальности вряд ли оказывают
какое-то влияние в реальности.
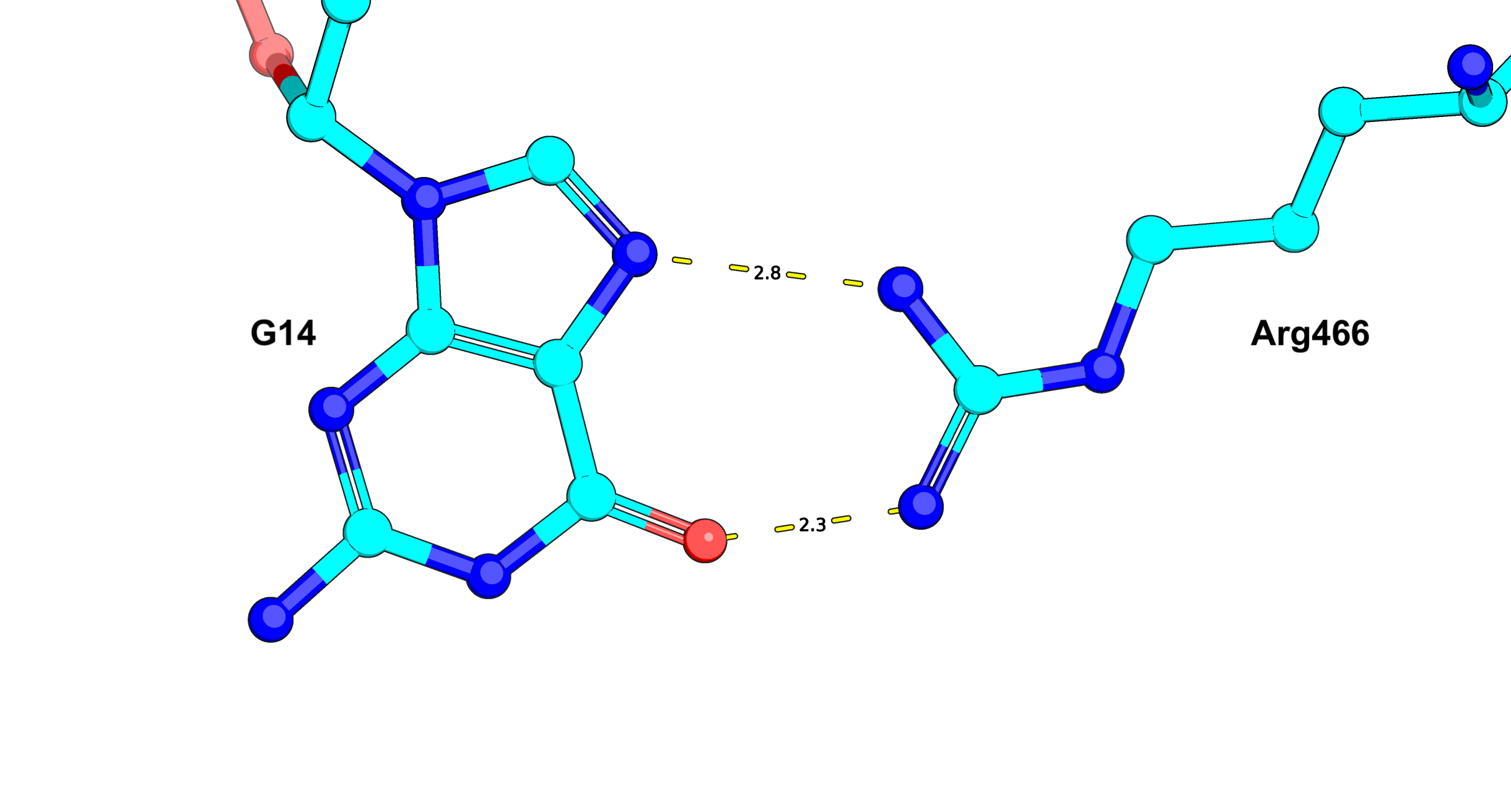
На мой взгляд, важное взаимодействие у Arg466 с гуанином 14 - рисунок 6. Мое суждение связано с тем,
что в данном взаимодействии образуются 2 водородные связи, которые не вызывают никаких сомнений
в своей реальности.