Дерево Chondrichthyes
(Хрящевые рыбы).
Таксономическое дерево класса Chondrichthyes(Хрящевые рыбы).
На рисунке 1 изображено таксономическое дерево класса хрящевые рыбы.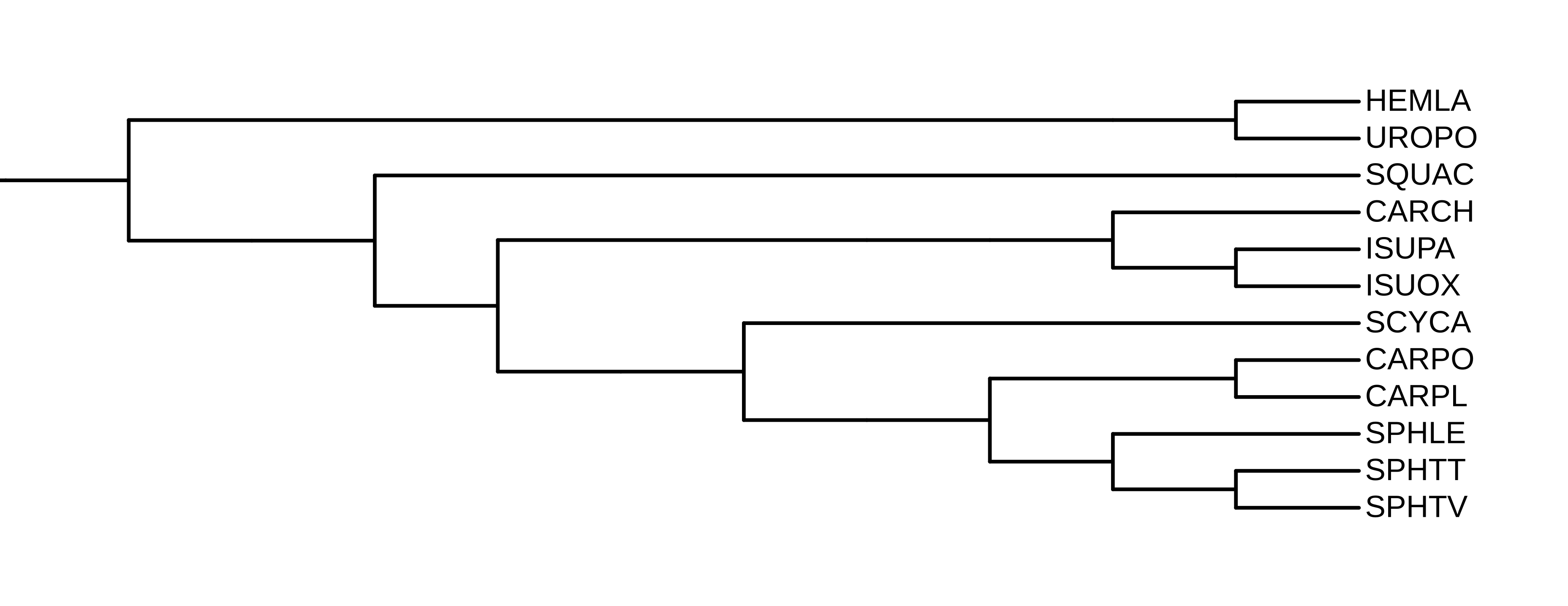
Построение деревьев класса Chondrichthyes(Хрящевые рыбы) на основе последовательной 12S митохондриальной рРНК.
Для начала были получены 7 последовательностей митохондриальной рРНК из
базы данных nucleotide ncbi для класса Chondrichthyes.
Было найдено ограниченное количество последовательностей: например,
(HEMLA,UROPO) - Скаты, не были найдены. Поэтому, чтобы это клада хрящевых рыб
был представлена хоть кем-то, я добавил к 7 найденным
последовательностям, последовательность 12S митохондриальной rRNA
ската Raja clavata (Морская лисица), с мнемоникой
RAJCL.
Полученное дерево представлено на рисунке 2.
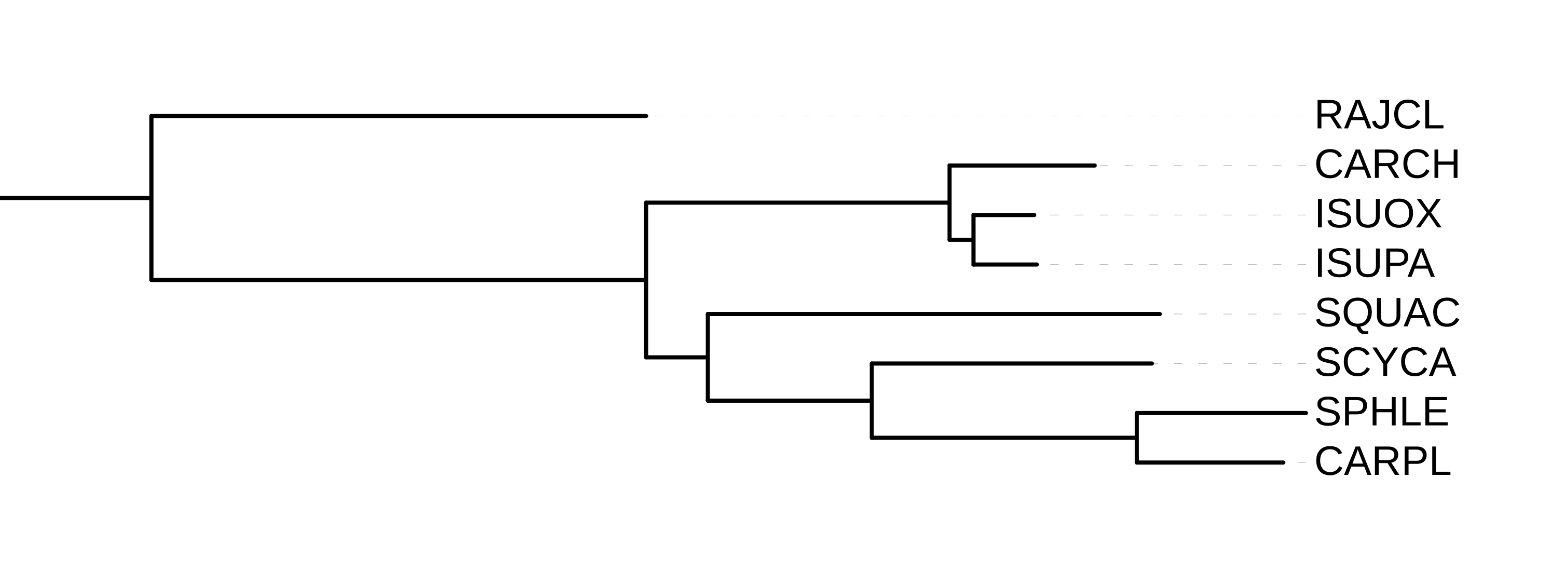
Как виднно из рисунка, топология очень похожа на топологию таксономического дерево.
Но, как и в предыдущем практикуме, когда мы строили деревья по аминокислотным последовательностям
белка цитохрома B, SQUAC (Squalus acanthias, Обыкновенный катран) все еще попадает
в "не свой" надотряд - Galeomorphii.
Также отмечу, что как и ожидалось, скат морская лисица (RAJCL) отходит от дерева хрящевых рыб
раньше остальных.
Построение дерева класса Chondrichthyes(Хрящевые рыбы) с внешней группой.
В качестве внешней группы была выбрана Латимерия (Latimeria menadoensis) -
мнемоника LATME.
На рисунке 3 изображено дерево с латимерией, укорененное по Латимерии.

Как мы видим из рисунка, латимерия далека от всех хрящевых рыб.
Но гораздо важнее отметить, что катран (SQUAC) во всех предыдущих построениях деревьев
не выделялся в отдельный надкласс Squalomorphii, а находился внутри
надкласса Galeomorphii.
А теперь, после добавления внешней группы, он расположился согласно таксономии.
Соответственно, после этого "исправления", дерево полностью соответствует таксономическому
дереву.
Бутстреп
При помощи программы Fastme было построено дерево, и были для него посчитатны 100 бутстрэп реплик:
fastme -i MitRNAOutGroup.phy -dK -b 100 -o MitRNAOutGroupB.nwk
Полученное дерево изображено на рисунке 4.
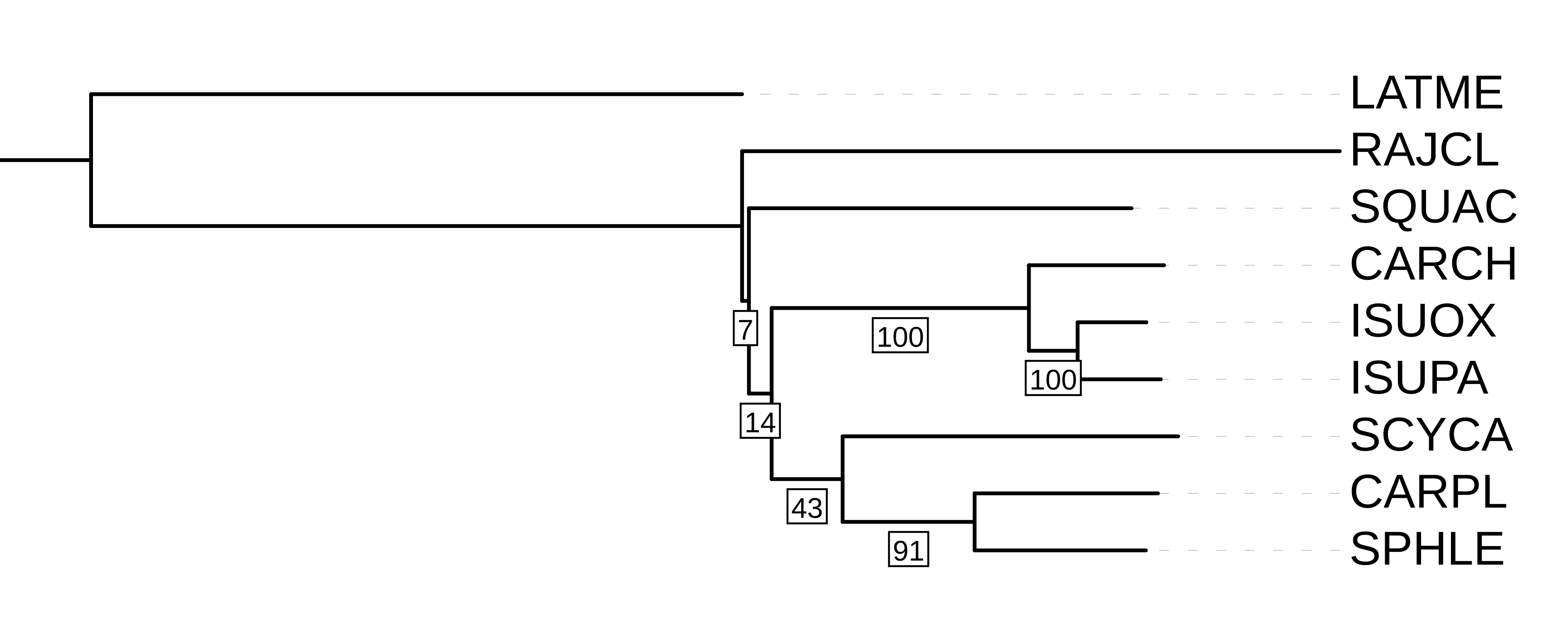
Как и в последнем случае, когда мы строили дерево с помощью программы IQtree и с внешней
группой, дерево получилось топологически идентично таксономическому дереву.
Можно задать вопрос - говорит ли низкое значение бутстрепа о недостоверности ветви?
Смотря на полученное дерево, можно сказать, что скорее нет, чем да.
Можно считать, что мы достоверно знаем, что скаты отделились от основной линии хрящевых
рыб 180 млн лет назад - однако мы видим, что
разделение на скатов и остальных хрящевых рыб имеет наименьший бутстреп из имеющихся (7/100).
Поэтому можно сказать, что низкий бутстреп не является показателем недостоверности ветви.
Саму недостоверность можно связать именно с тем, что скаты отделились очень давно: новые случайные
мутации могли привести ко вторичной схожести.