| Командна | Результаты |
java -jar /nfs/srv/databases/ngs/suvorova/trimmomatic/trimmomatic-0.30.jar SE -phred33 SRR4240360.fastq 13pr_trim_1.fastq ILLUMINACLIP:illumina_adapters.fasta:2:7:7 |
Input Reads: 8254632 Surviving: 8212774 (99,49%) Dropped: 41858 (0,51%) |
java -jar /nfs/srv/databases/ngs/suvorova/trimmomatic/trimmomatic-0.30.jar SE -phred33 13pr_trim_1.fastq 13pr_trim_2.fastq TRAILING:20 ILLUMINACLIP:illumina_adapters.fasta:2:7:7 |
Input Reads: 8212774 Surviving: 8140976 (99,13%) Dropped: 71798 (0,87%) |
java -jar /nfs/srv/databases/ngs/suvorova/trimmomatic/trimmomatic-0.30.jar SE -phred33 13pr_trim_2.fastq 13pr_trim_3.fastq MINLEN:32 |
Input Reads: 8140976 Surviving: 7915474 (97,23%) Dropped: 225502 (2,77%) |
Velveth:
velveth 13pr_velveth 31 -short -fastq 13pr_trim_3.fastq
velveth 13pr_velveth
Анализ сборки проводим на основе stats.txt
N50 = 43070
| Номер | Длина | Покрытие |
| 1 | 113474 | 33.525460 |
| 5 | 83603 | 33.646065 |
| 4 | 64155 | 35.847323 |
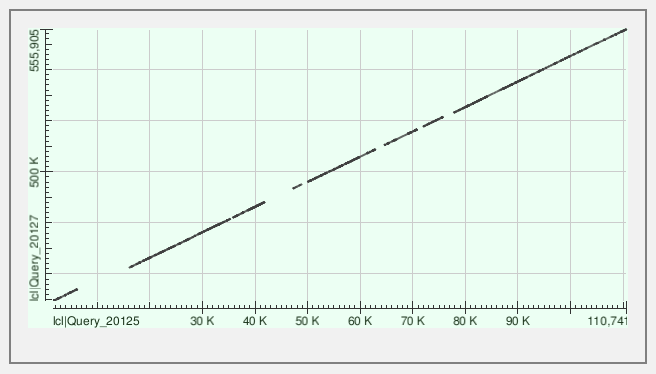
Контиг №1

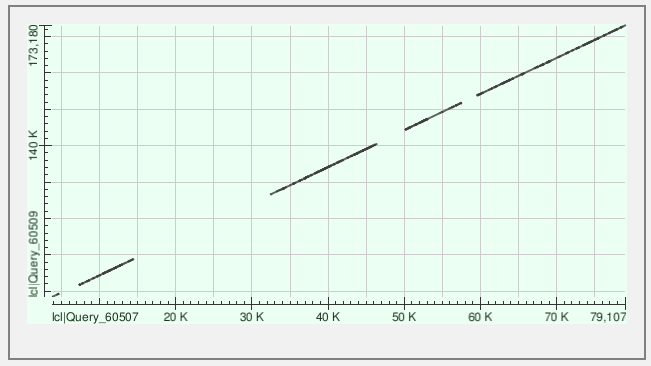
Контиг №5
Контиг №4
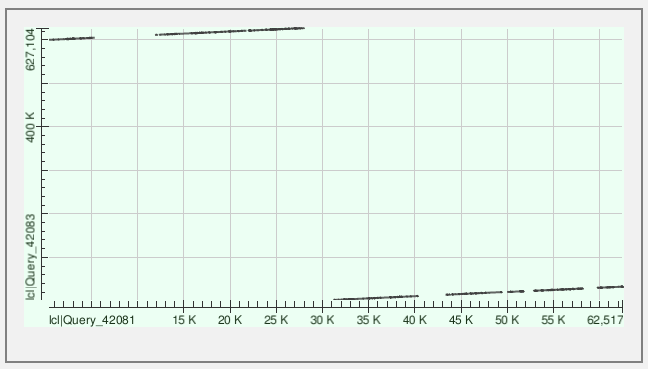
Kонтиги занимают значительную часть генома; контиг №4 прошёл через нулевую координату (хромосома кольцевая, поэтому контиг снова лёг на геном)