На страницу четвертого семестра
Аннотация базы данных SDAP
Ключевые слова: аллерген, эпитоп.
SDAP — ВЕБ-сервер, объединяющий базу данных по протеинам-аллергенам (куда входят: имя, источник,
последовательность, структура, эпитопы а так же сопутствующие ссылки на такие структурные банки
данных, как SwissProt, PIR, NCBI, PDB) с различными биоинформатическими ресурсами, позволяющими
изучать структуру и прочие особенности белков-аллерегенов. Биоинформатические ресурсы помимо
стандартных инструментов представлены собственным SDAP-алгоритмом для поиска консервативных а.о.
На данный момент база содержит 737 аллергенов и изоаллергенов, 829 белковых последовательностей, и 22 IgE и IgG эпитопа.
Главным сервером, на котором находится база, является сервер Медицинского Отдела Университета Техаса, США.
Организаторами базы являются:
- Ovidiu Ivanciuc, PhD — глава группы
- Werner Braun, PhD
- Catherine H. Schein, PhD
- Randall M. Goldblum, MD
- Edward G. Brooks, MD
- Terumi Midoro-Horiuti, MD, PhD
База составляется экспертами на основе списка аллергенов, предсоставленного веб-сервером Международного
Союза Иммунологических Обществ (International Union of Immunological Societies, IUIS), с добавлением
соответствующей литературной информации и информации о структурах из банков данных SwissProt, PIR, NCBI,
PDB.
Стартовая страница, по моему мнению, весьма удобна для пользователя. Главную страницу можно разделить
на две части: слева находятся ссылки на ресурсы Университета, ссылки на популярные биоинформатические
ресурсы, в т.ч. на различные классификации протеинов, а так же ссылки на ресурсы данной базы. Левая
часть доступна с любой страницы базы, что дает возможность получить доступ к любой другой странице или
ресурсу с любой страницы базы. Что очень важно, в этой части есть ссылки на FAQ (часто задаваемые
вопросы) и руководство по использованию базы ("мануал"). Так же можно посмотреть информацию о базе: обзор, общую информацию, информацию о текущей версии,
информацию о создателях
и публикациях.
Собственно на главной странице есть ссылка на мануал. Есть так же ссылки на списки аллергенов, в т. ч.
в алфавитном порядке. Предоставлена возможность сравнения двух последовательностей с помощью подсчета
E1-E5 Property-Based Peptide Similarity Index:
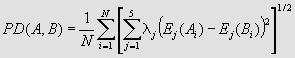
Есть ссылки на отдельные списки аллергенов с эпитопами и аллергены с PDB-структурами, что, наверное
будет полезно специалистам. Вообще на главной странице базы предоставлены много различных возможностей
для поиска аллергенов — полный список, алфавитный список, список по эпитопам и PDB — среди упомянутых,
так же список аллерегенов по классификации PFAM. Есть возможность поиска в базе по предоставленной
fasta-последовательности с помощью алгоритма PD sequence similarity index, или возможен поиск по
fasta-последовательности с помощью алгоритма FASTA 3.5.
Сейчас в базе 886 записей об аллергенах. Много это или мало? Наверное, достаточно. Но аллергенов в
природе определенно больше. Тем не менее, база выглядит весьма заоелненной. Могу для сравнения привести
результат запроса: Query
"([uniprot-Description:*allergen*] | [uniprot-Keywords:*allergen*]) "
found 1473 entries.
Так, работать еще можно, но многое уже сделано.
Перед характеристикой поисковых инструментов базы имеет смысл описать формат документа базы.
Из документа можно получить название аллергена, научное и общеупотребительное название вида - источника, тип аллергена,
описание, узнать, относится ли аллерген к списку IUIS
Например:
Dac
g 1 — название аллергена
Остальные поля:
Species - Scientific Name — Dactylis glomerata
Species - Common Name — orchard grass
Allergen Type — grass Poales
Allergen Description — AgDg1
Class — IUIS
При переходе по ссылке в имени аллрегена можно получить дополнительную информацию - ссылки на статьи в
PubMed, ссылки на соответствующую информацию в PFAM, SwissProt и т. д.
Так выглядит результат поиска:
|
Allergen
|
Species - Scientific Name
|
Species - Common Name
|
Allergen Type
|
Allergen Description
|
Class
|
|
Pan
s 1
|
Panulirus stimpsoni
|
spiny lobster
|
foods
|
tropomyosin
|
non-IUIS
|
|
Par
j 1
|
Parietaria judaica
|
|
weed Rosales
|
lipid
transfer protein; homolog: pathogenesis related protein PR14
|
IUIS
|
А так может выглядеть документ, относящийся к определенному аллергену:
Теперь о результатах тестирования различных поисковых и других инструментов базы:
| Тип поискового сервиса | Результат | Примечания |
| Алфавитный список с возможностью поиска по первой букве | Список аллергенов, чьи названия начинаются на некоторую букву, например D | Соответствующие ссылки даны на главной странице. Имена аллергенов, по которым и идет поиск, даются по биологическому названию источника. |
| Список аллергенов с имеющейся записью PDB | Выводит список аллергенов с имеющейся записью PDB | В документе есть дополнительная секция — ссылка на ресурс PDB, некоторая информация, так же ссылки на онлайн-инструменты для просмотра PDB — например WebMol. При прохождении по ссылке попадаем на соотвествующую страницу PDB RCSB |
| Список аллергенов с имеющейся 3D-моделью | Выводит список аллергенов с имеющейся 3D-моделью | Пока в этом списке один аллерген — Jun a 3
Ссылка на пресловутую 3D-модель не работает, однако можно посмотреть с помощью WebMol. Чем этот сервис отличается от представления информации об аллергенах, имеющих PDB-кристалл, не совсем понятно.
|
| Список аллерегенов с эпитопами | Выводит список аллерегенов с эпитопами | В документе появляется новая секция — эпитопы данного аллергена. Можно получить последовательности эпитопов, выполнить поиск по последовательности в банке данных PIR (странно, что не в Uniprot или хотя бы в Swissprot), можно поискать точное совпадение в базе SDAP или поискать похожие с помощью алгоритма PD (см. ниже) |
| Список семейств PFAM, содержащих аллергены | Выводит список этих семейств | Плучаем по две ссылки на каждой строке результата, одна — на список аллергенов в этом семействе, другая — непосредственно на документ PFAM. |
| Классификация PFAM для аллергенов | Выводит список семейств с перечнем аллергенов в каждом семействе | Вариант предыдущего сервиса, принципиально от него не отличается |
| Список аллергенов SDAP | Обычный алфавитный список | В случае если ничего, кроме первой буквы имени, об аллерегене неизвестно, хотя даже в таком случае имеет смысл воспользоваться поиском по первой букве |
| Список аллергенов с последовательностями в SDAP | Выводит список аллергенов, где каждому соответствует идентификатор последовательности | Идентификаторы обычно представляют собой 7-8 значное число, иногда на первом месте стоит буква О. Зачем они нужны, не совсем ясно. Данный список ненамного короче полного (на 32 хита) |
| Поиск по виду аллергена | Можно получить все альбумины, вицилины, и т.д | Фактически, выдает список всех аллергенов, в поле Description для которых есть данный термин. Например, поиск по термину Albumin даст все альбумины и 2S альбумины, парвальбумины и т. д., а поиск по термину 2S albumin — только 2S альбумины, что будет вложенным множеством по отношению к предыдущему поиску. |
В целом данную группу сервисов можно оценить высоко. Все списки проверены и работают, практически все предоставляют какой-то специфический тип информации, т.е. почти каждый список характеризует какой-то класс объектов.
Есть, конечно и недочеты, они в основном перечисленны в примечаниях: использование банка данных PIR, неразвитый (будем надеяться — временно) список по 3D-модели, фактическое дублирование списка по первой букве полным списком, определенно менее удобным в использовании (всего хитов на данный момент 886) и списком с последовательностями.
В целом достаточно разветвленная система списков может позволить найти нужный аллерген очень быстро.
Теперь о собственно поисковых инструментах:
| Тип поискового сервиса | Алгоритм | Запрос | Результат | Примечания |
| Поиск по названию, имени, источнику, etc | | Search Field: Source — common name
Search Term: lobster | Найдено два аллергена, оба из лобстера (что неудивительно) | Возможность искать по одному из 5ти полей: название, источник (научное название), источник (общеупотребительное название), описание, все поля.
Отдельно реализована возможность поиска среди пищевых аллергенов |
| FASTA-поиск в базе SDAP | FASTA 3.45 | EFQTAQHLRILA
CQQWLGGGKQAXQS
GTSGPSWTLD — последовательность из аллергена Sin a 1, слегка измененная | Выдает таблицу, аналогичную таблице, выдаваемой программой BLAST. В данном случае E score составил 5.1e-09, bit score составил 49.6 | Простой вариант поиска, в котором пользователь вводит последовательность и некоторое имя для нее. |
| FAO-WHO-поиск аллергена | FASTA 3.45, больше дополнительных параметров |
RIPGQRKEFQQAQH
LRAIPLQWLHKQAMQ
SGSGPSPQGPQQRPP
LLQQCCNQEEPLCVCPTL
KGASKAVRQQLEQQGQQGP
HVISADSRIYQTAGGGGC
NIPQVSVCP
FKKTMPGPS — последовательность из аллергена Sin a 1, слегка измененная. Дополнительные параметры:
- FASTA alignments for an 80 amino acids sliding window, sequence identity cutoff: 35
- То же самое, но Sequence identity cutoff: 65
Последовательность: EFQTAQHLRILACQQW
LGGGKQAXQS
GTSGPSWTLD
- Exact match for contiguous amino acids, 6 аминокислот
- То же самое, но 10 подряд идущих аминокислот
|
- Построил 38 выравниваний данной последовательности с последовательностью аллергена аллергена Sin a 1, для каждого было определено значение Identity
- Построил так же 38 выравниваний, значения Identitiy в среднем несколько ниже.
- Выдает точные соответствия блоков из 6 аминокислот. Если соответствия нет, пишет: No match found in SDAP for: <блок>. В данном случае программа выдала два соответствия с другим аллергеном — Bra j 1, и множество соответствий с исходным аллергеном
- Соответствий не найдено
|
Выбор дополнительных параметров основан на Правилах отнесения вещества к группе аллергенов.
В соответствии с этими правилами, вещество можно отнести к аллерегену, если
а) Сходство для окна из 80 а.о. более 35%
б) Есть полностью соответствующие блоки по 6 а.о.
На основании этого выбираются дополнительные параметры для поиска.
Первый тип поиска — поиск по последовательности, аналогичный предыдущему.
Второй — поиск по окну, применим для больших последовательностей (не меньше 80 а.о.).
Третий — поиск по совпадению блоков а.о. — применим так же в случае последовательностей меньше 80 а.о.
Необходимо отметить, что такая гибкая система поиска позволяет найти аллерген в любом случае.
Предложенные значения по умолчанию следует в большинстве случаев оставлять без изменения
|
| Сравнение двух пользовательских последовательностей | PD index |
Seq1: EFQTAQH
LRILACQQWL
GGGKQAXQ
SGTSGPSWTLD
Seq2: EFQQAQHLR
ACQQWLHKQ
AMQSGSGPS
PQGPQQRPPLL
QQCCNELHQ
EEPLCVCP
| Выдает похожие последовательности из базы ALL_SEQ, минимальное значение PD и соответствующую ему последовательность:
Minimum PD=12.76 EFQQAQHLR
ACQQWLHK
QAMQSGSGPS
PQGPQQRPP
|
База последовательностей автоматически генерируется из данных NCBI из последовательностей, аннотации которых содержат слово "alleregen" |
В целом база производит приятное впечатление. Качественные и разветвленные системы поиска, интеграция базы с другими, более общими базами, понятный и простой интерфейс могут помочь в исследовании аллергенов.
Конечно, пока возможности базы не очень широки, но уже достаточно серьезны.
К сожалению, неизвестно, поддерживается ли база сейчас. Заявлено, что апдейт базы происходит раз в три месяца, между тем последний апдейт произошел 25 января 2005 года.
Следует надеяться, что это временные трудности.
Оценка, поставленная мной за базу по пятибальной шкале — "четыре с плюсом".
©
Галкин Иван, 2006