Выравнивание последовательностей цитохромов В животных, выбранных в практикуме, было выполнено на kodomo. Все команды практикума выполнены в директории term4/practice2.
muscle -align cyb.fasta -output cyb-alignment.fasta
Выравнивание последовательностей цитохромов В животных, выбранных в практикуме, было выполнено на kodomo.
muscle -align cyb.fasta -output cyb-alignment.fasta
Скрипт для перевода в формат phylip-relaxed лежит в файле convert_to_phylip.py. С помощью команд fastme (модели p-distance, затем MtREV) и IQ-Tree реконструируем деревья.
fastme -i cyb.phy -pp-distance -o cyb_pdistance.treefile
fastme -i cyb.phy -pMtREV -o cyb_mtrev.treefile
iqtree -s cyb.phy
Полученные реконструкции были загружены в iTOL и получены изображения
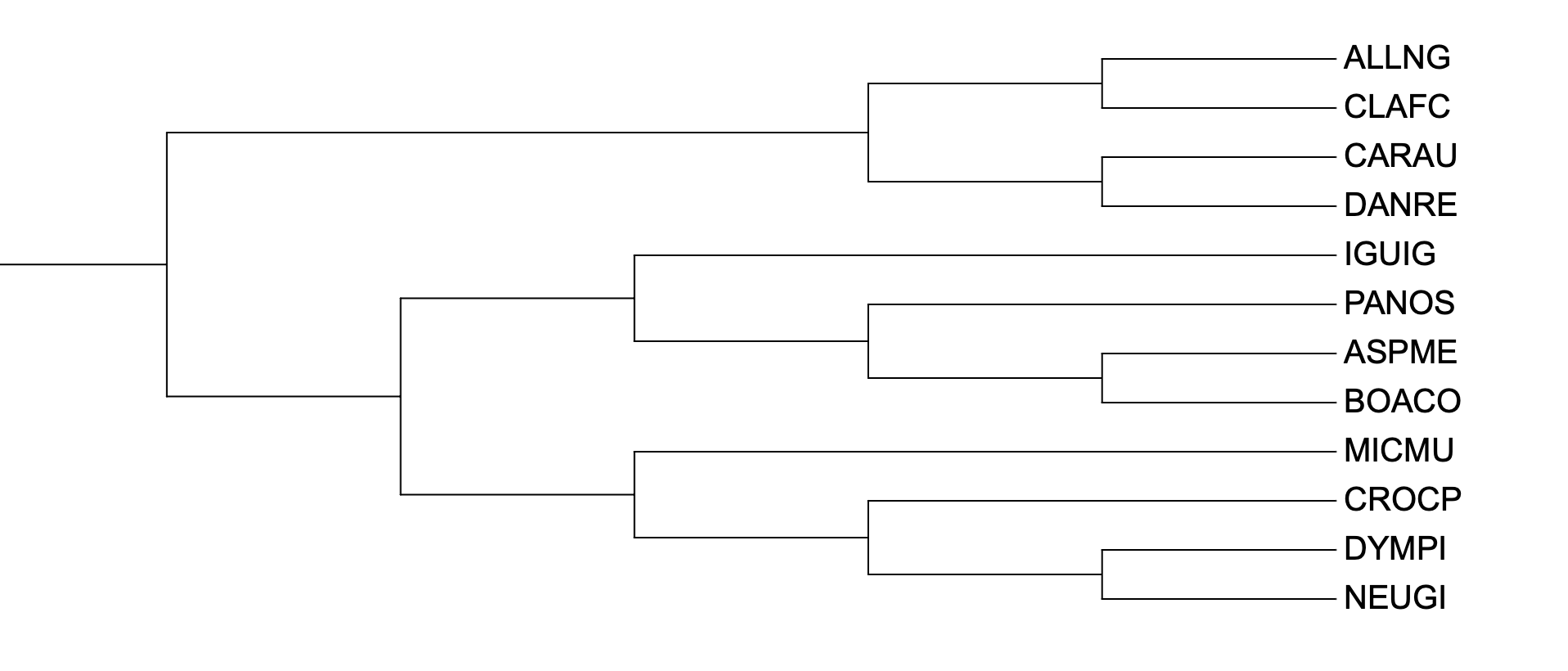

Реконструкция по CYB (fastme, p-distance) полностью воспроизводит топологию дерева видов. Ошибок реконструкции не обнаружено.

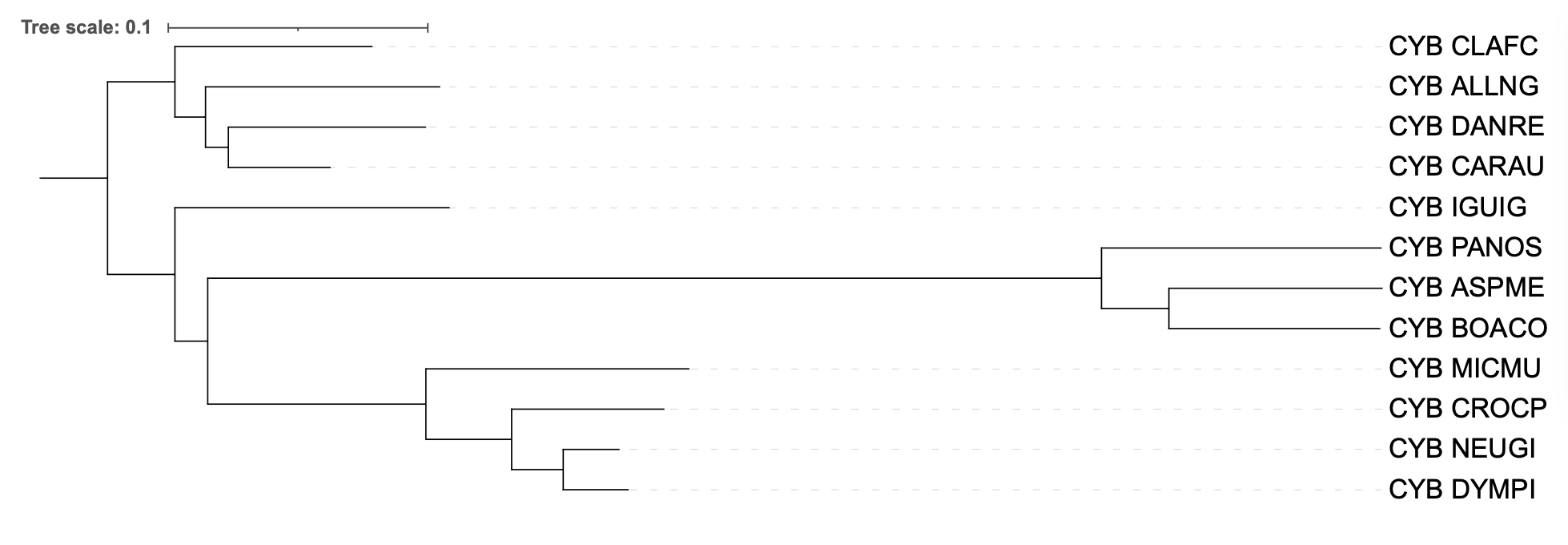
Топология полностью совпадает с деревом видов.

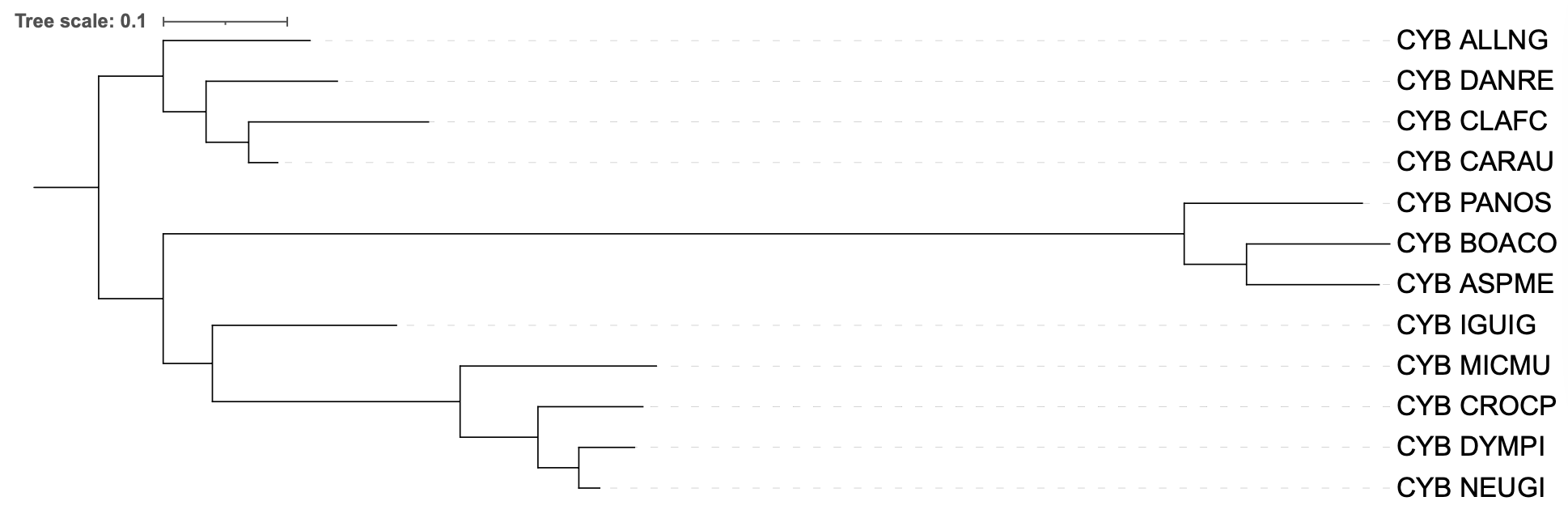
Можно заметить, что в дереве видов присутсвуют две клады (ALLNG, CLAFC) и (CARAU, DANRE), кооторые отсутсвуют в дереве реконструированном с помощью iqtree. Вместо них в iqtree присутсвуют (ALLNG, DANRE) и (CLAFC, CARAU).