Для выбранных животных в Практикуме 1было реконструировано дерево по последовательностям малой РНК митохондриальных рибосом (12S rRNA). Для пяти видов не был найден митохондриальный геном, поэтому для них были подобраны максимально родственные, у которых он имеется, чтобы структура видового дерева не была нарушена. Замены (таксономическое название + мнемоника):
Pantherophis obsoletus (PANOS) -> Pantherophis slowinskii (9SAUR)
Aspidites melanocephalus (ASPME) -> Python bivittatus (PYTBI)
Crocidura caspica (CROCP) -> Crocidura leucodon (CROLE)
Dymecodon pilirostris (DYMPI) -> Scaptonyx fusicaudus (SCAFU)
Neurotrichus gibbsii (NEUGI) -> Mogera wogura (MOGWO)
Последовательности были выровнены на kodomo (musle), переведены в формат phy и реконструированы программой FastME с использованием модели p-distance. С помощью ITOL получено изображение дерева.

Топология дерева, реконструированного по 12S rRNA, полностью соответствует видовому дереву и построенному по последовательностям цитохромов B с помощью fastme. Различия с деревом построенным с помощью iqtree описаны в практикуме 2.
В качестве внешней группы была взята минога Petromyzon marinus (PETMA)
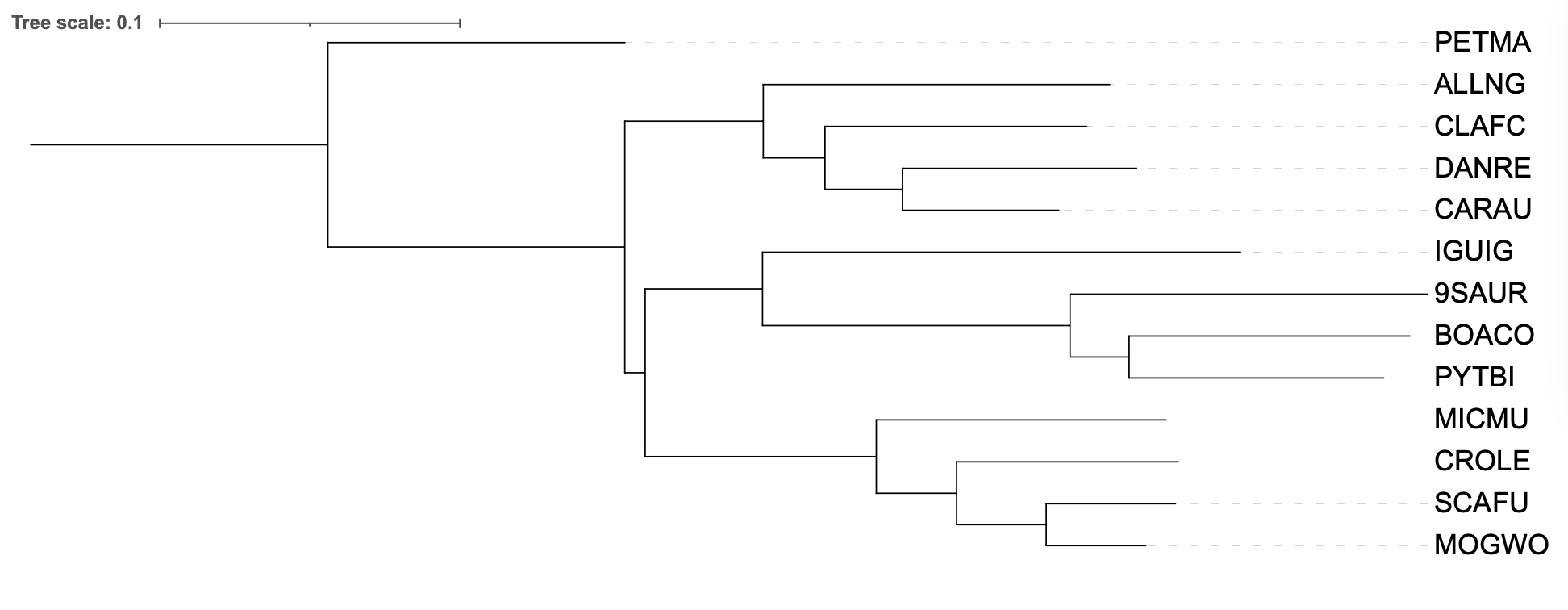
При добавлении внешней группы Petromyzon marinus (PETMA) и укоренении по ней топология взаимоотношений между основными группами организмов сохранилась.
Была повторена филогенетическая реконструкция из второго пункта программой fastme, использовав 100 реплик бутстрепа.
fastme -i 12S_rRNA_alignment_2.phy -pp-distance -o 12S_rRNA_pdistance_2_Bootstraps.treefile -d -b 100
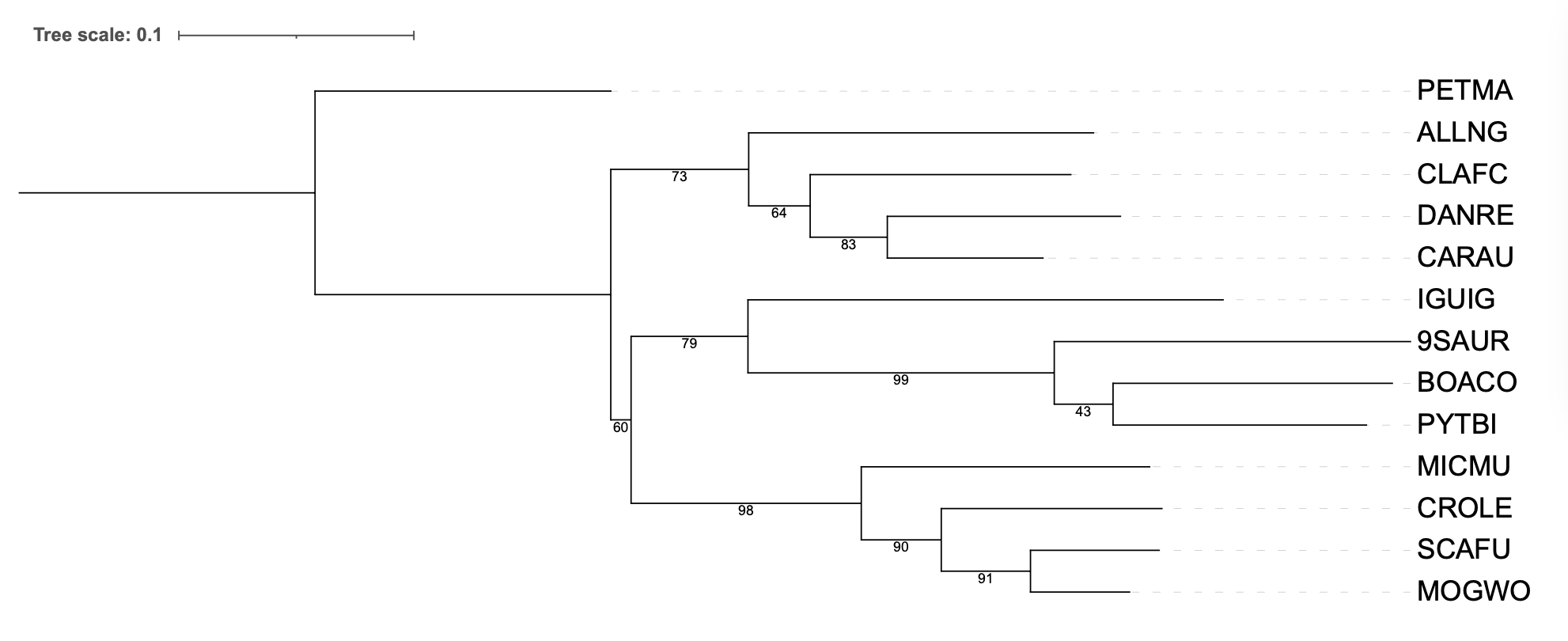
Ветвь, объединяющая BOACO и PYTBI, имеет наименьшую поддержку — 43%. Это означает, что в 57% бутстреп-реплик данная группировка не воспроизвелась, и топология в этой части дерева является статистически недостоверной. Вероятно, ген 12S rRNA не содержит достаточной филогенетической информации для надежного разделения удавов и питонов — двух древних линий змей. Остальные ветви дерева имеют высокие поддержки (60-100%), что подтверждает общую стабильность реконструкции.