Филогенетическая реконструкция
В предыдущем практикуме мы строили филогенетическое дерево, заранее обладая информацией о направлении хода эволюции. Теперь посмотрим как с построением деревьев справятся автоматические программы, анализирующие последовательности цитохромов B, выровненные друг с другом.
На Kodomo c помощью muscle было проведено множественное выравнивание последовательностей цитохрома B в кладе Toxicofera.
Деревья строились двумя программами на kodomo: fastme (с оценкой расстояний по MtREV и p-distance) и iqtree. Результаты работы программ доступны здесь: fastme (p-distance / MtREV) + iqtree
Визуализировались графы в iTol.
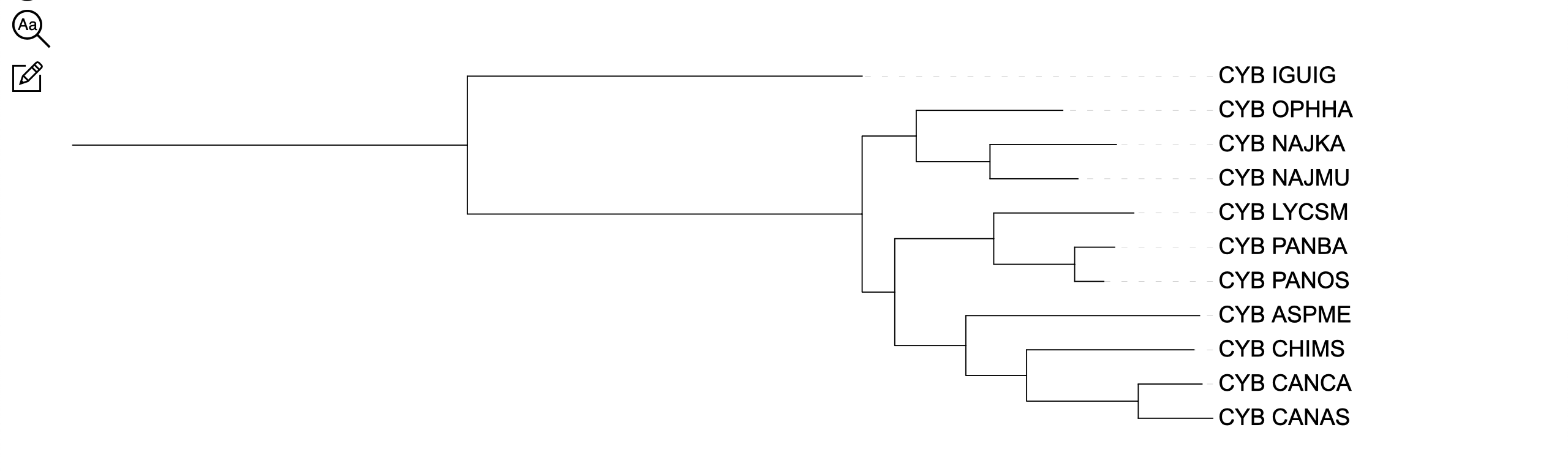
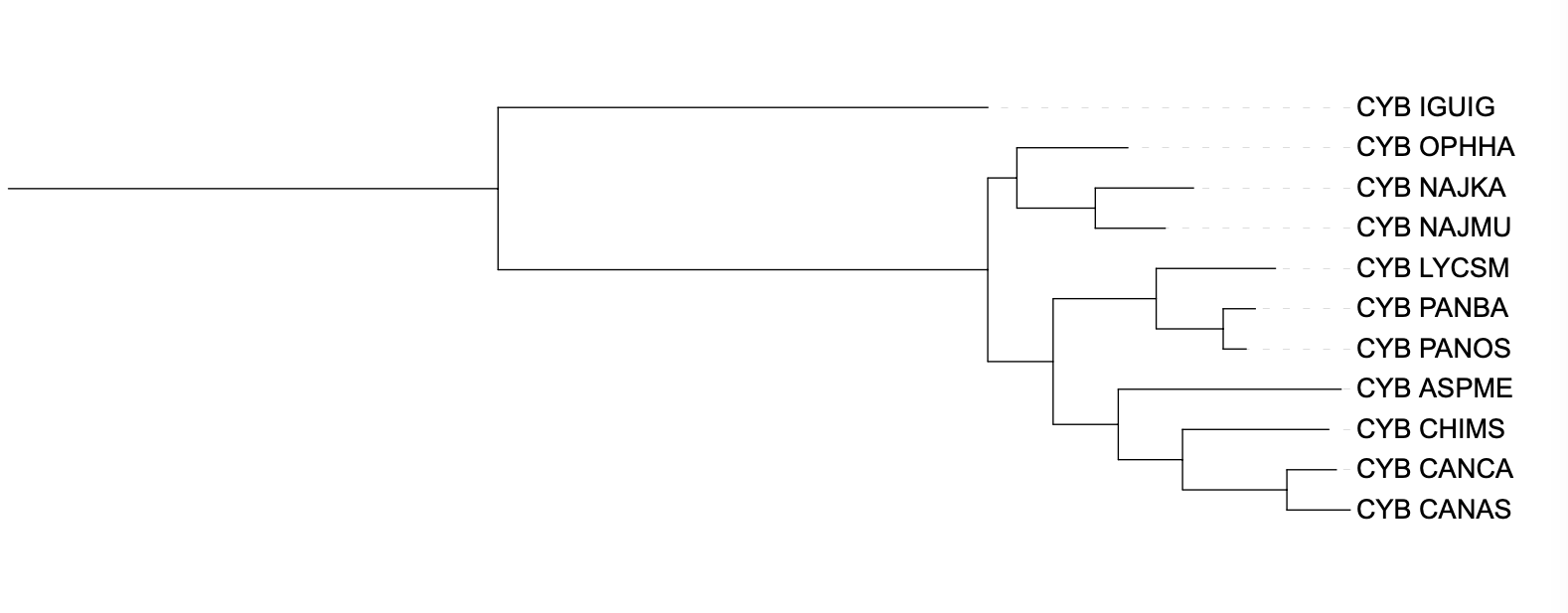
Результаты работы программ можно увидеть на рисунках 1-3. Как видно, дерево, получившееся в программе fastme (алгоритмы по p-distance и MtREV дали одинаковые результаты) не получилось эволюционно верным. Верно сгруппированы были представители Colubrinae, Boinae, Elapinae, а также Aspidites melanocephalus. Однако Iguana iguana была внесена не в ту кладу, а
Colubroidea разделены: часть (PANBA, PANOS, LYCSM) исходят из одного узла с Henophidia, другая часть (OPHHA, NAJMU, NAJKA) вынесена как параллельная ветвь.
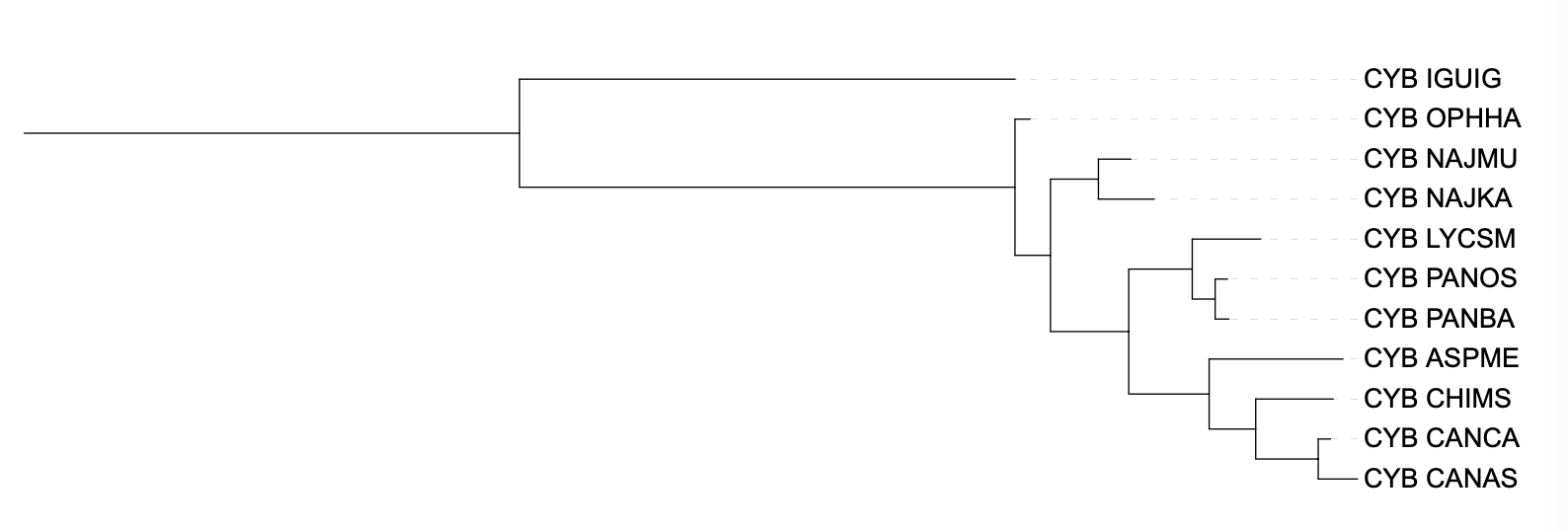
Дерево, получившееся на выходе программы iqtree, содержит ещё больше ошибок. Colubroidea (PANBA, PANOS, LYCSM) и Henophidia лежат на двух ветвях, исходящих изо одного узла, причем в этот узел приходит ветвь, параллельная с двумя другими Colubroidea (NAJMU, NAJKA). Ophiophagus hannah не связана с остальными Colubroidea, она лежит на ветви параллельной ветви с игуаной. Дерево содержит неразрешенную часть, выходящую из корня: параллельные ветви с Iguana iguana, Ophiophagus hannah и третья с остальными организмами.
Как мы видим, алгоритмы программ зачастую допускают ошибки при построении отражающих ход эволюции деревьев. Так происходит потому, что оценить ход эволюции по одному белку часто бывает невозможно: происходят случайные замены, необходимо учитывать вероятности повторных замен и брать поправку на то, что в разных позициях вероятности замен неодинаковы. При работе с вероятностями нельзя ожижать точного результата, поэтому файл, полученный на выходе таких программ, должен быть перепроверен с учетом знаний по филогенетики организмов.


