Совмещение структур
1. Нахождение структурных гомологов.
Для выполнения задания использовались ранее выбранная структура белка (см.
практикум 1) 5T30 и сервис
PDBeFold.
При поиске по цепи А были отобраны 3 следующие структуры: MnSOD из Chaetomium thermophilum 4BR6; SOD2 из Saccharomyces cerevisiae, камбиальная SOD из пропионобактерии 1AR4.
При поиске по цепи А были отобраны 3 следующие структуры: MnSOD из Chaetomium thermophilum 4BR6; SOD2 из Saccharomyces cerevisiae, камбиальная SOD из пропионобактерии 1AR4.
Рисунок 1. Выбранные последовательности для выравнивания (выдача PDBeFold для 5T30).
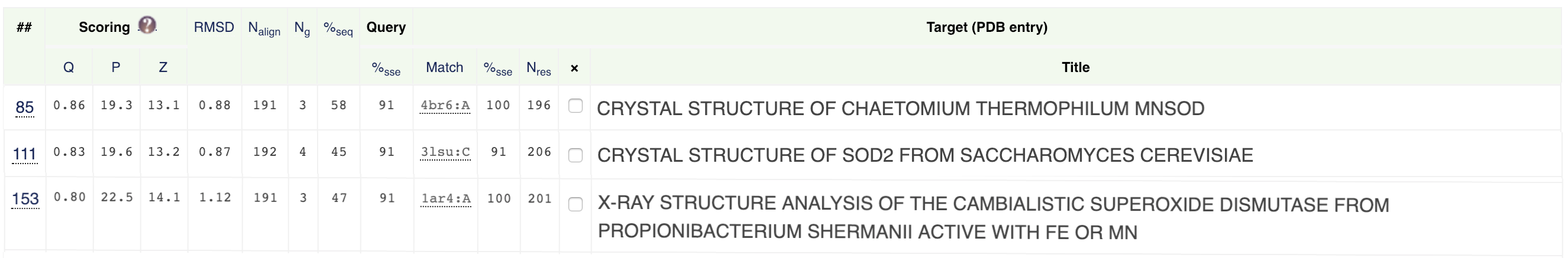
Рисунок 2.1 Визуализация структурного выравнивания с 5T30.
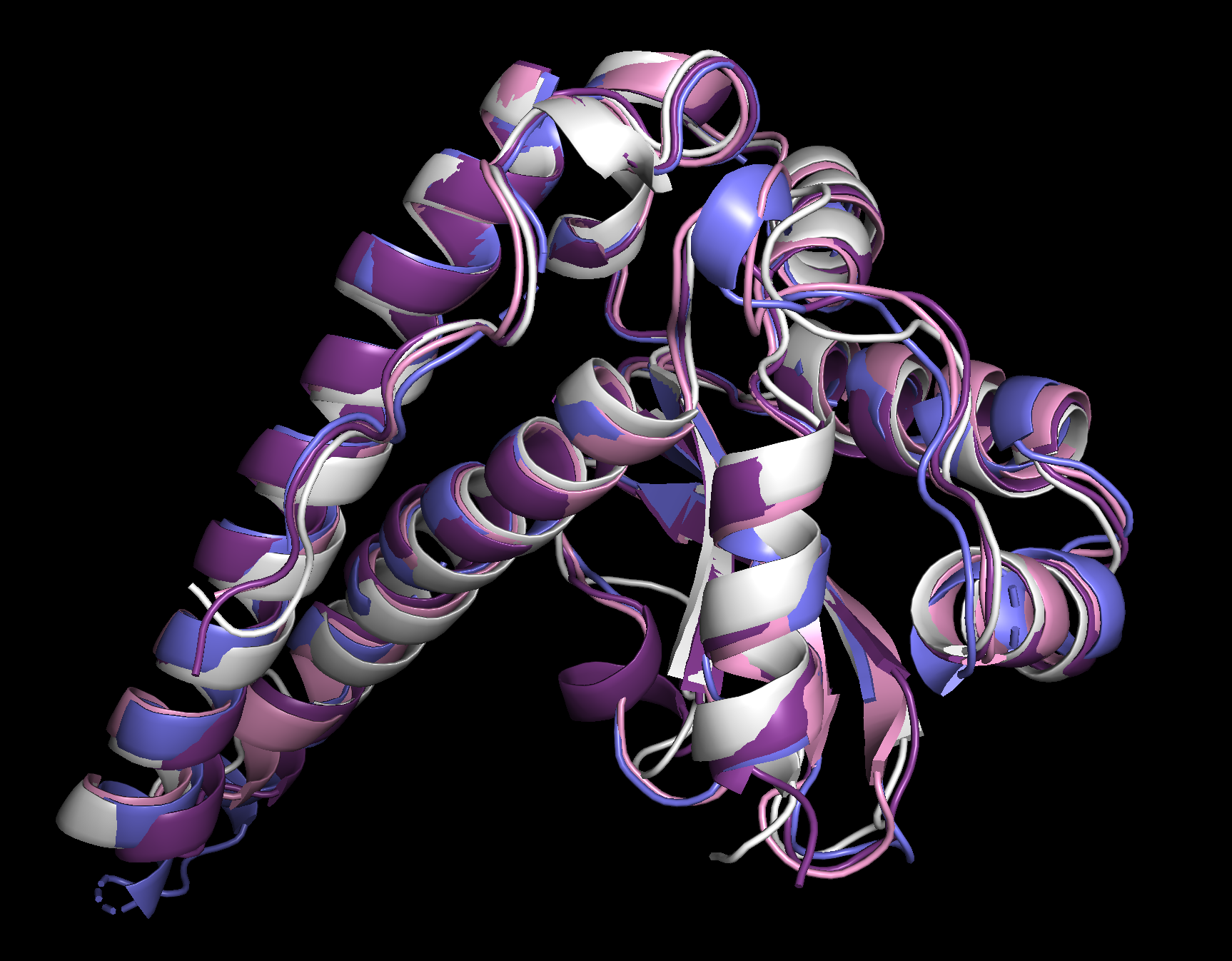
Рисунок 2.2 Визуализация структурного выравнивания с 5T30.
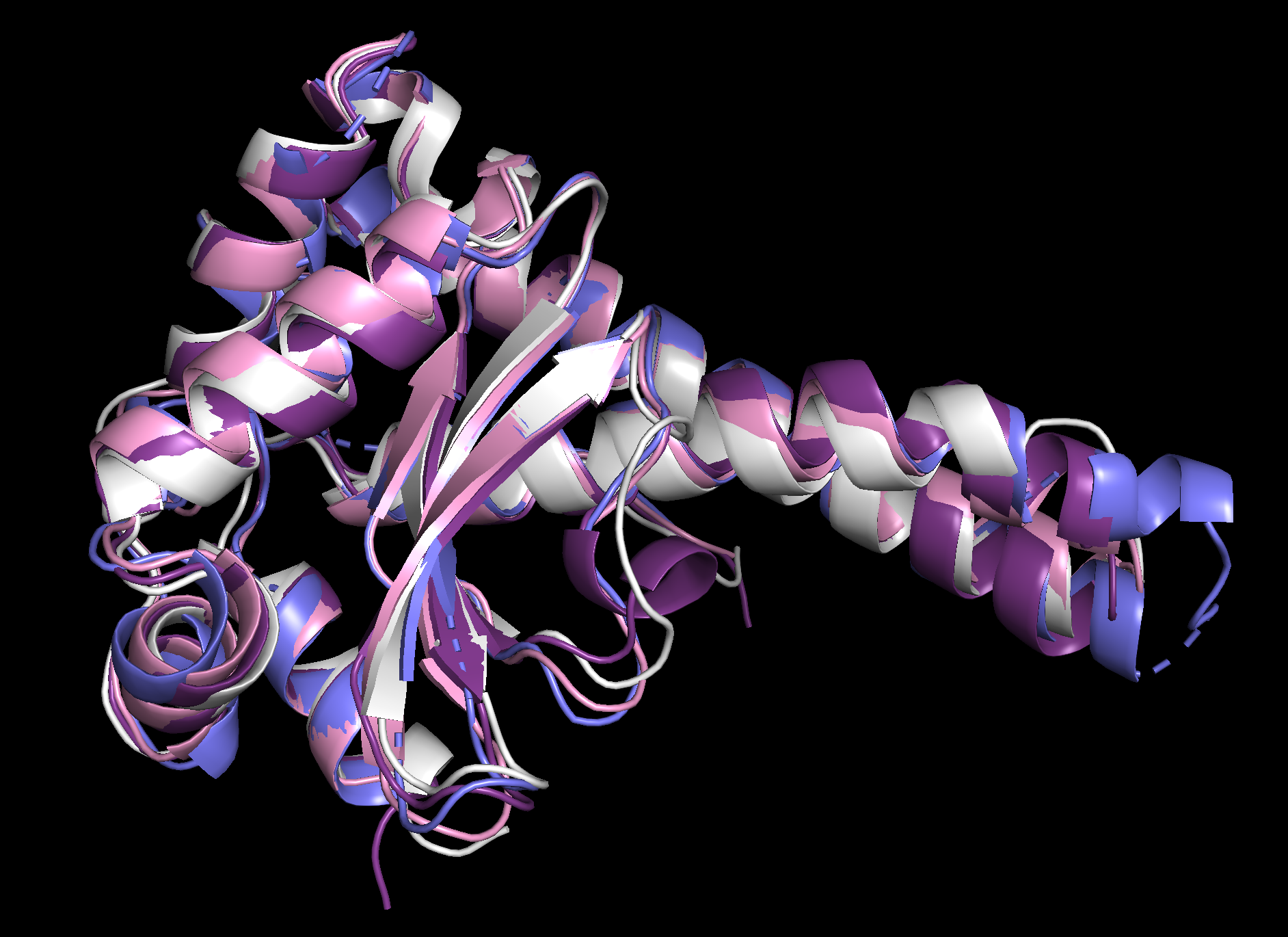
Рисунок 3. Результаты совмещения PDBeFold.
На рис. 1 представлены параметры найденных гомологов. Далее, вышеуказанный сервис был использован
для проведения множественного структурного выравнивания, результаты которого можно видеть на рис. 2.1, 2.2, 3.
Здесь белок 5T30 представлен цветом темно-фиолетовым, 4BR6 - розовым, 3LSU - серо-голубым, 1AR4 - белым. Мы видим, что
структуры достаточно хорошо накладываются друг на друга (за исключением, возможно, петель как наиболее подвижных
участков).
Полученный файл с множественным структурным выравниванием был проанализирован в JalView. Для проведения сравнения с выравниванием последовательностей в том же JalView был использован алгоритм Muscle с дефолтными параметрами. На рис. 4 можно видеть результаты сравнения двух выравниваний.
2. Сравнение выравниваний.
Полученный файл с множественным структурным выравниванием был проанализирован в JalView. Для проведения сравнения с выравниванием последовательностей в том же JalView был использован алгоритм Muscle с дефолтными параметрами. На рис. 4 можно видеть результаты сравнения двух выравниваний.
Рисунок 4. Совмещение структур (сверху) vs. выравнивание последовательностей (снизу).
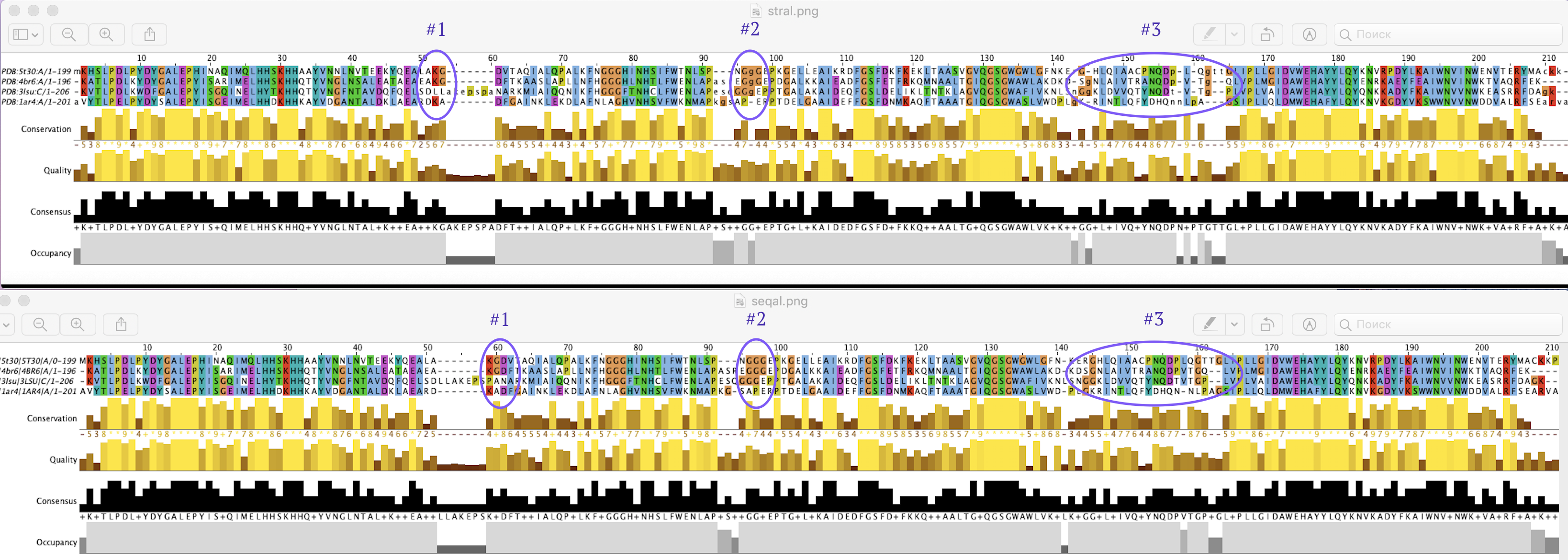
Следует отметить, что выравнивания практически идентичны, есть только 3 участка (отмечены на рис. 4),
которые немного отличаются, при этом они соотвествуют линкерным последователностям. Я сакцентирую внимание на 1-ом
таком участке, поскольку в совмещении последовательностей на участках 2, 3 выравнивания нет (отсутствуют т.н.
вертикальные блоки).
Рисунок 5. Спорный участок #1 в выравниваниях.
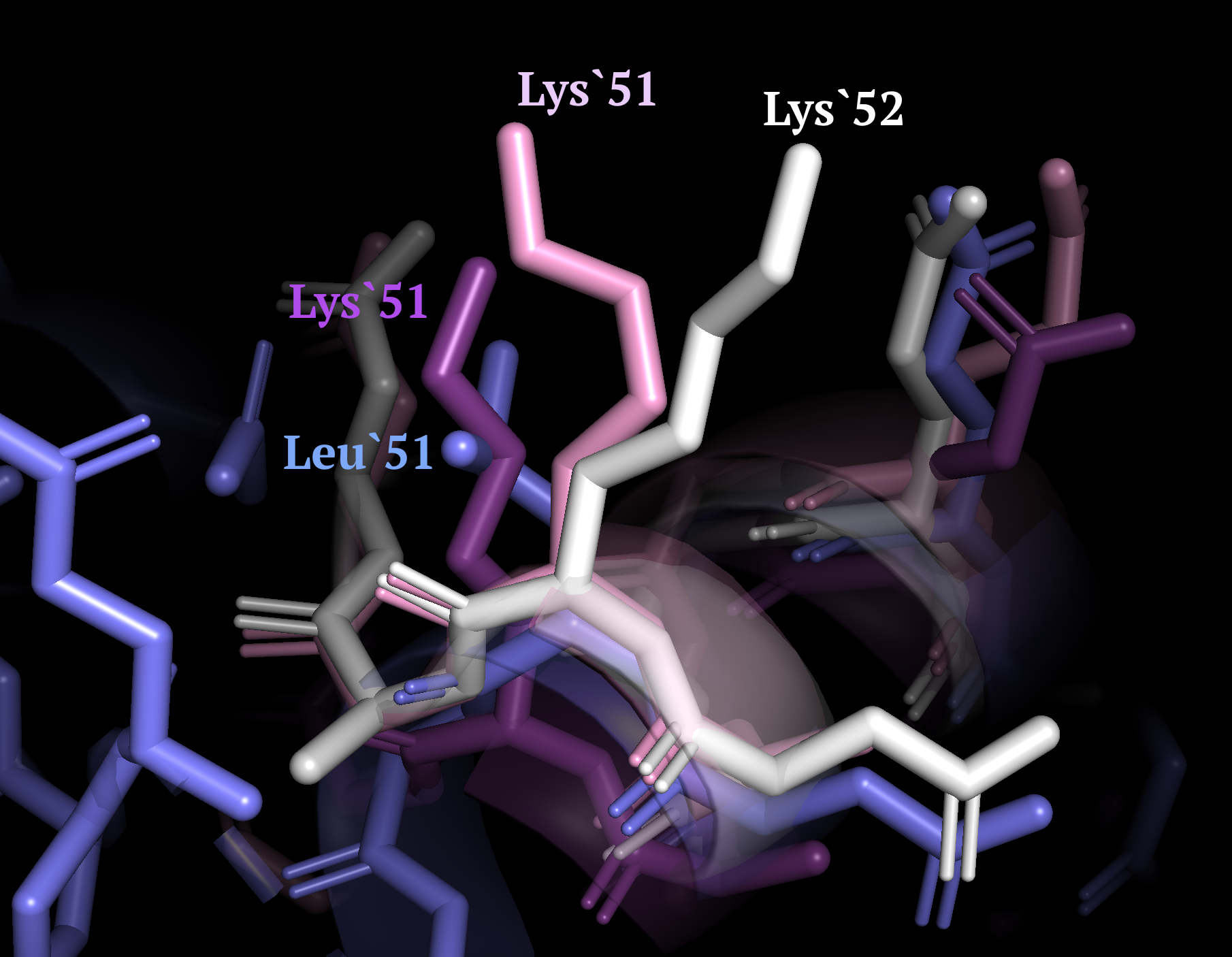
При близком рассмотрении данного участка в PyMOL (рис. 5) можно видеть, что 3 Lys (из 5T30, 4BR6 и 1AR4)
достаточно хорошо накладывается на структуру Leu из последовательности 3LSU. Таким образом, можно сделать вывод,
что структурное выравнивание для данной группы белков лучше описывает их 3D-сходство.