Практикум 6. Секвенирование по Сэнгеру.
Задание 1
В рамках данного разадния с помощью программы Ugene были проанализированы результаты секвенирования прямой и обратной последовательностей ДНК (проект с выравниванием; итоговые последовательности: консенсус).
Рассмотрим несколько интересных участков из этих последовательностей.
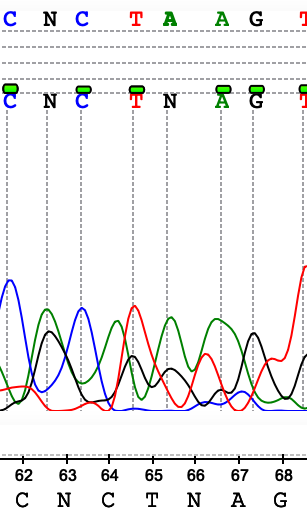
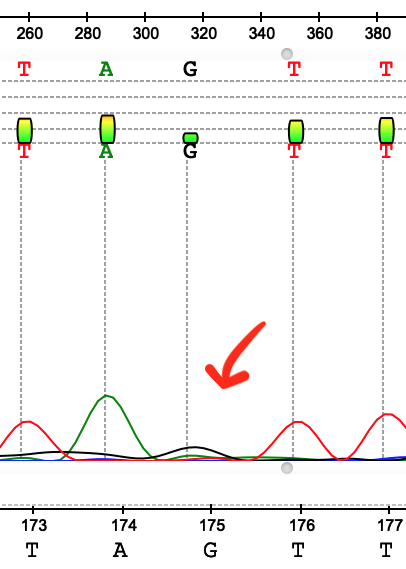
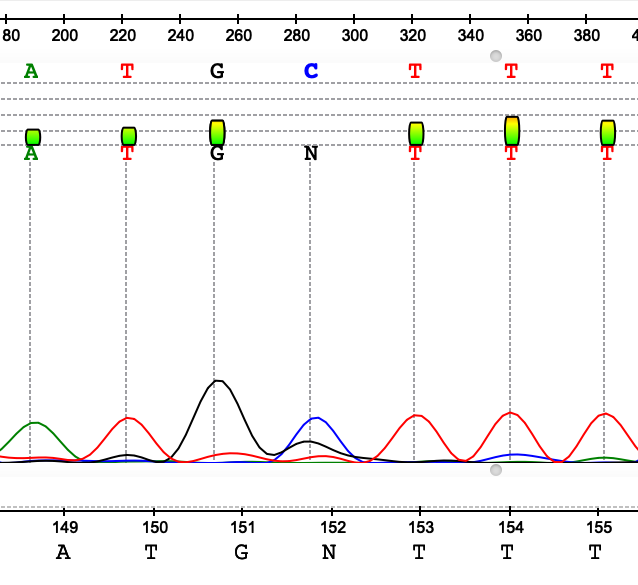
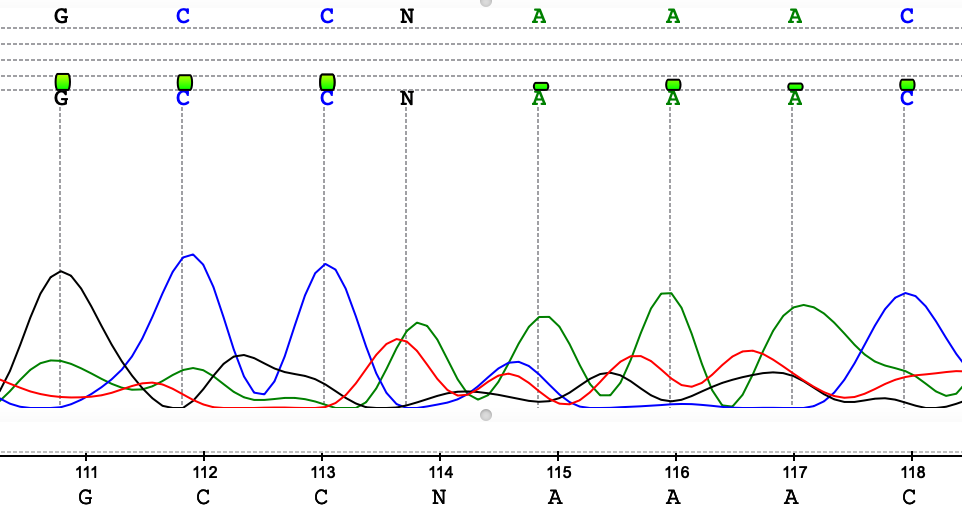
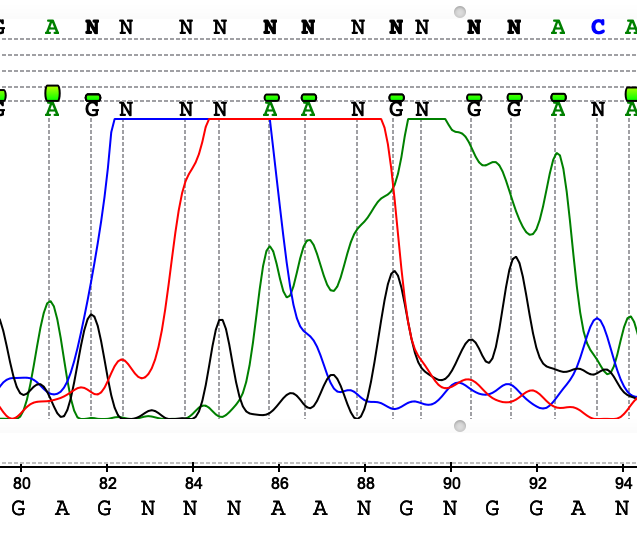
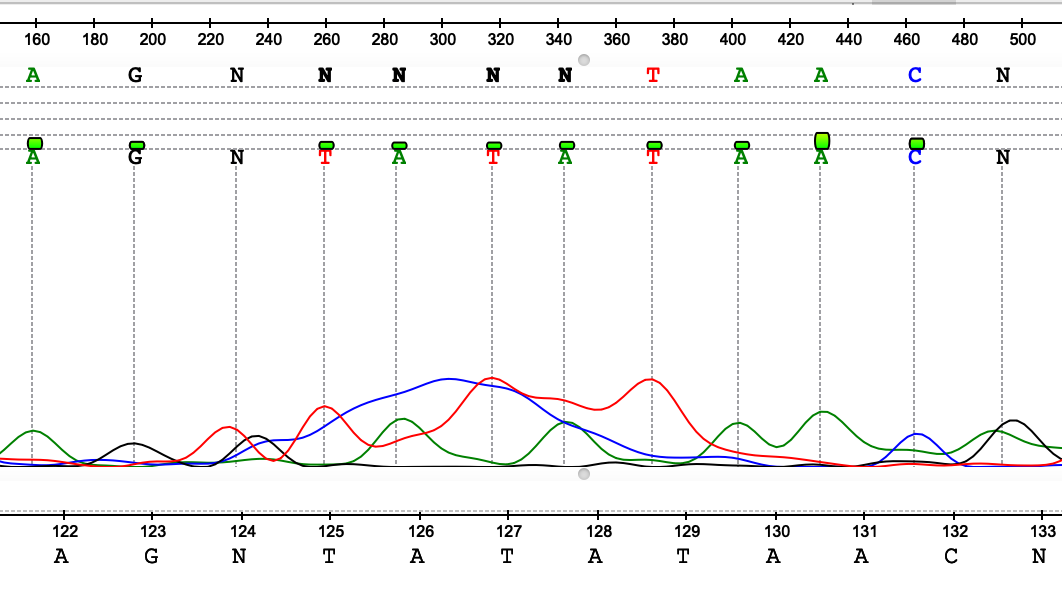
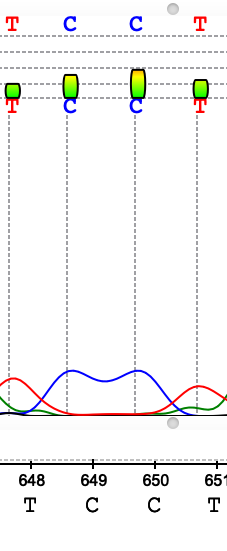
На рисунках 1-7 представлены различные ошибки/ухудшения качества сигнала, проявившиеся на данной хроматограмме. В целом можно сказать, что число подобных артефактов в последовательности небольшое, основная часть хроматограммы представлена четко выраженными пиками с незначительным фоновым шумом у "подошвы". Если посмотреть на отношение длины выделенного консенсуса к исходной длине последовательностей, мы получим соотношение 564/717, т е около 79% от числа исходной массы нуклеотидов оказались в итоге опрелены. Тем не менее, ближе к концу качество анализа плавно уменьшается, пики начинают сливаться в "седла" и другие многопиковые элементы.
Задание 2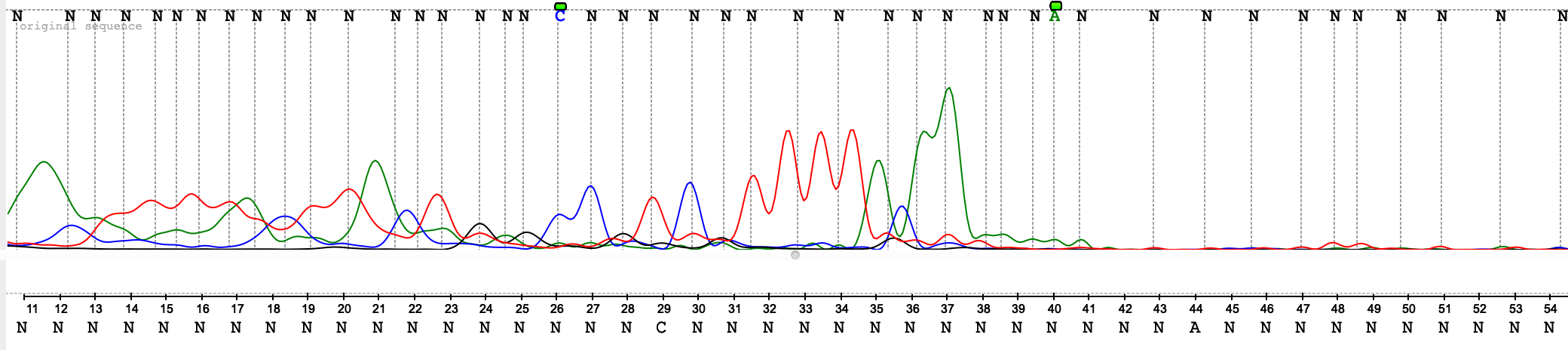
На рисунке 8 изображен фрагмент "плохой" хроматограммы. В левой части оказались густо представлены слитые, размытые, но мощные пики, справа - едва заметные колебания на уровне фонового шума. Даже алгоритм не смог определить вероятную нуклеотидную последовательность. Все это говорит нам о возможных проблемах с пробой или используемым оборудованием.
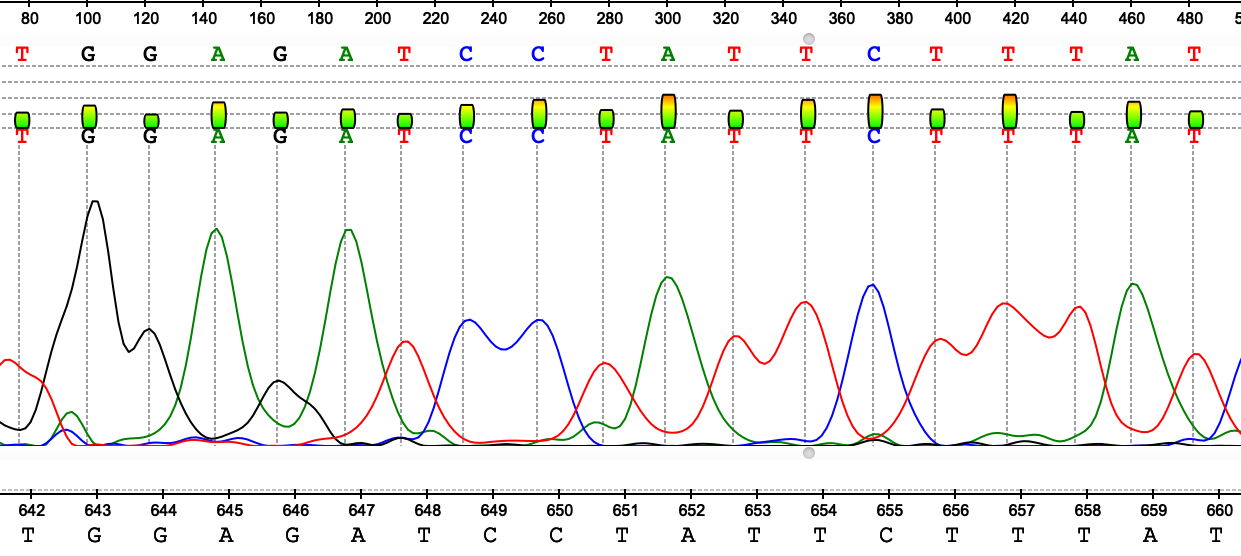
На рисунке 9 мы видим закономерное снижение качества сигнала, характерное для конца последовательности. Чаще всего оно связано с более низким числом "покрытий", как следствие, более слабым и невнятным сигналом.