Мини-обзор генома Pseudoalteromonas rhizosphaerae
Школяр Илья Александрович
АННОТАЦИЯ
Данная работа является анализом генома бактерии Pseudoalteromonas rhizosphaerae, с использованием методов программирования на языке Python и функционала электронных таблиц, а также функционала BASH в Linux. Целью исследования является определение ключевых генетических характеристик Pseudoalteromonas rhizosphaerae и понимание её адаптивных механизмов на уровне генома. Такой подход позволит открыть перспективы для научного и практически применимого использования бактерии в биотехнологиях.
1. ВВЕДЕНИЕ
Таксономическая принадлежность рассматриваемой бактерии (см. S1 сопроводительных материалов):
cellular organisms; Bacteria; Pseudomonadota; Gammaproteobacteria; Alteromonadales; Pseudoalteromonadaceae; Pseudoalteromonas; Pseudoalteromonas rhizosphaerae
Pseudoalteromonas — это бактерии, обитающие в морских и прибрежных экосистемах, которые играет важную роль в поддержании экологического равновесия и разложении органического вещества.
Исследование генома Pseudoalteromonas rhizosphaerae представляет значительный интерес благодаря своей уникальной генетической конфигурации, которая отличает его от других представителей рода Pseudoalteromonas. Процесс картирования генома позволяет идентифицировать ключевые генетические маркеры и уникальные гены, которые определяют особенности данного вида. Эти гены играют критическую роль в адаптации и выживании в специфических морских условиях, что демонстрирует высокий уровень эволюционной гибкости вида[1].
2. МАТЕРИАЛЫ И МЕТОДЫ
Геномы бактерий были взяты с сайта (см. S2, S3, S4 и S5 сопроводительных материалов). Гистограммы длин белков и GC% состава, а также подсчёт генов белков и различных типов РНК были сделаны с помощью Google Sheets (см. S6 сопроводительных материалов). В bash был написан скрипт для получения местонахождения последовательностей нуклеотидов, кодирующих 16S rRNA (см. S7 сопроводительных материалов). В Python был написан код, который вытаскивает их из файла с геномом (см. S8 сопроводительных материалов).
3. РЕЗУЛЬТАТЫ
3.1 Гистограмма длин белков
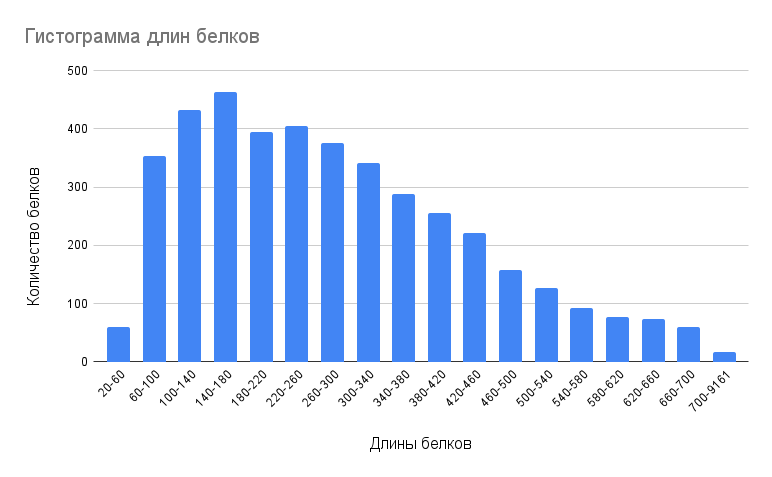
Как видно из рисунка 1, основные длины белков находятся в диапазоне между 140 и 180 аминокислот.
3.2 GC Состав последовательностей белков бактерии Pseudoalteromonas rhizosphaerae
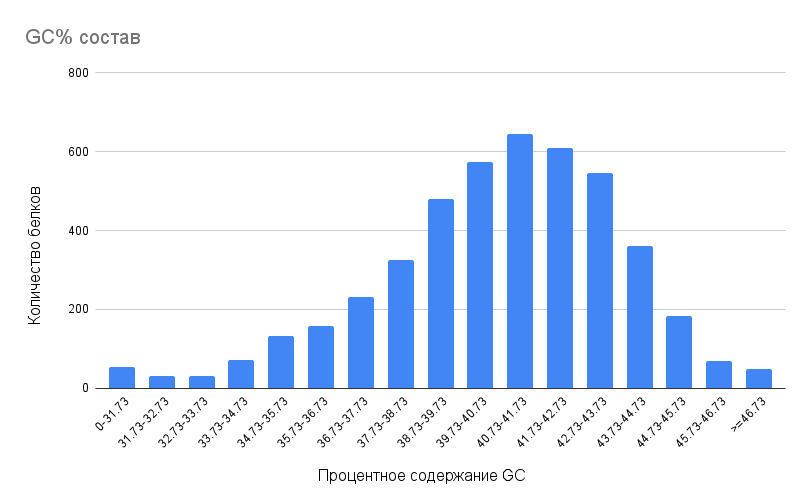
Как видно из рисунка 2, большая часть последовательностей белков имеет в своём составе 40.73-41.73% нуклеотидов GC
3.3 Число генов белков и генов разных типов РНК
Полученные данные могут демонстрировать, как много различных аминокислот включено в белки бактерии. По этим данным можно сделать предположение, что лейцин, валин и лизин наиболее распространённые аминокислоты в составе белков данной бактерии, а триптофан и гистидин наоборот - наименее распространёнными.
Таблица 1. Число генов белков бактерии Pseudoalteromonas rhizosphaerae
| генов CDS в хромосоме | генов CDS в плазмидах | |
| Число генов | 4534 | 22 |
Таблица 2. Число генов разных типов РНК бактерии Pseudoalteromonas rhizosphaerae
| tRNA | rRNA | ncRNA | tmRNA | |
| Число генов | 103 | 28 | 4 | 1 |
Таблица 3. Число генов тмРНК, некодирующей РНК, разных типов рРНК и тРНК бактерии Pseudoalteromonas rhizosphaerae
| tRNA-Ile | tRNA-Ala | tRNA-Ser | tRNA-Gly | tRNA-Thr | tRNA-Trp | |
| Число генов | 3 | 4 | 7 | 7 | 4 | 2 |
| tRNA-Phe | tRNA-Pro | tRNA-Arg | tRNA-Leu | tRNA-Tyr | tRNA-Val | |
| Число генов | 3 | 4 | 7 | 9 | 3 | 9 |
| tRNA-Met | tRNA-Glu | tRNA-Asn | tRNA-Asp | tRNA-Lys | tRNA-Cys | |
| Число генов | 6 | 6 | 4 | 7 | 9 | 2 |
| tRNA-Met | tRNA-Gln | tRNA-His | tRNA-Phe | tRNA-OTHER | 6S RNA | |
| Число генов | 6 | 4 | 2 | 3 | 1 | 1 |
| 23S ribosomal RNA | transfer-messenger RNA | signal recognition particle sRNA small type | RNase P RNA component class A | 5S ribosomal RNA | 16S ribosomal RNA | |
| Число генов | 9 | 1 | 2 | 1 | 10 | 9 |
3.4 Филогенетический анализ 16S rRNA
Для сравнения мной были выбраны геномы бактерий Pseudoalteromonas viridis, Pseudoalteromonas tetraodonis и Pseudoalteromonas aliena чтобы попробовать узнать, насколько они генетически близки и построить филогенетическое дерево. Последовательность 16S рРНК представлена девятью гипервариабельными участками и разделяющими их консервативными последовательностями. Такая особенность первичной структуры позволяет проводить филогенетический анализ, чем пользуются многие учёные[2]. Мной был написан скрипт bash, с помощью которого из feature table бактерии можно узнать где находятся кодирующие последовательности с учётом направления цепи. С помощью программы, написанной в Python, из fasta файла я смог достать конкретные последовательности генома. С помощью сервиса mafft (см. S9 сопроводительных материалов) было произведено выравнивание данных последовательностей и построено филогенетическое дерево, с помощью сервиса iTOL (см. S10 сопроводительных материалов) оно было визуализировано.

Благодаря данному анализу удалось узнать, что Pseudoalteromonas rhizosphaerae генетически близка Pseudoalteromonas tetraodonis. Если продолжить его и для остальных видов данного рода, получиться составить полное и достаточно точное филогенетическое дерево.
4. СОПРОВОДИТЕЛЬНЫЕ МАТЕРИАЛЫ
S2 Геном бактерии Pseudoalteromonas rhizosphaerae
S3 Геном бактерии Pseudoalteromonas viridis
S4 Геном бактерии Pseudoalteromonas tetraodonis
S5 Геном бактерии Pseudoalteromonas aliena
S6 Гистограмма белков и GC% состав генома
S8 Программа для получения определённого сегмента генетического кода
5. СПИСОК ЛИТЕРАТУРЫ
[1] Navarro-Torre S., Carro L., Rodríguez-Llorente I. D., Pajuelo E., Caviedes M. Á., Igual J. M., Klenk H.-P., Montero-Calasanz M. del C. Pseudoalteromonas rhizosphaerae sp. nov., a novel plant growth-promoting bacterium with potential use in phytoremediation // Int. J. Syst. Evol. Microbiol. — 2020. — Т. 70. — С. 3287–3294.
[2] Weisburg W. G., Barns S. M., Pelletier D. A., Lane D. J. 16S ribosomal DNA amplification for phylogenetic study. // Journal Of Bacteriology. — 1991. — January (vol. 173, no. 2). — P. 697—703.