Был составлен список идентификаторов цитохромов В выбранных животных. С помощью средств EMBOSS был создан файл с последовательностями этих белков. После выровняли белки программой mafft и с помощью библиотеки BioPython перевели этот файл в формат, который воспринимается программой FastMЕ (а именно phylip-relaxed). Далее была проведена реконструкция, используя в качестве модели сначала MtREV, затем p-distance. В самом конце я реконструировала дерево программой IQ-Tree. Команды, которые использовались для выполнения действий выше:
seqret @list.txt my_sequences.fastamafft my_sequences.fasta > aln.fastafastme -i aln_phy.phy -o MtREV_cyb.phy -pMfastme -i aln_phy.phy -o p-distance_cyb.phy -ppiqtree -s aln_phy.phy



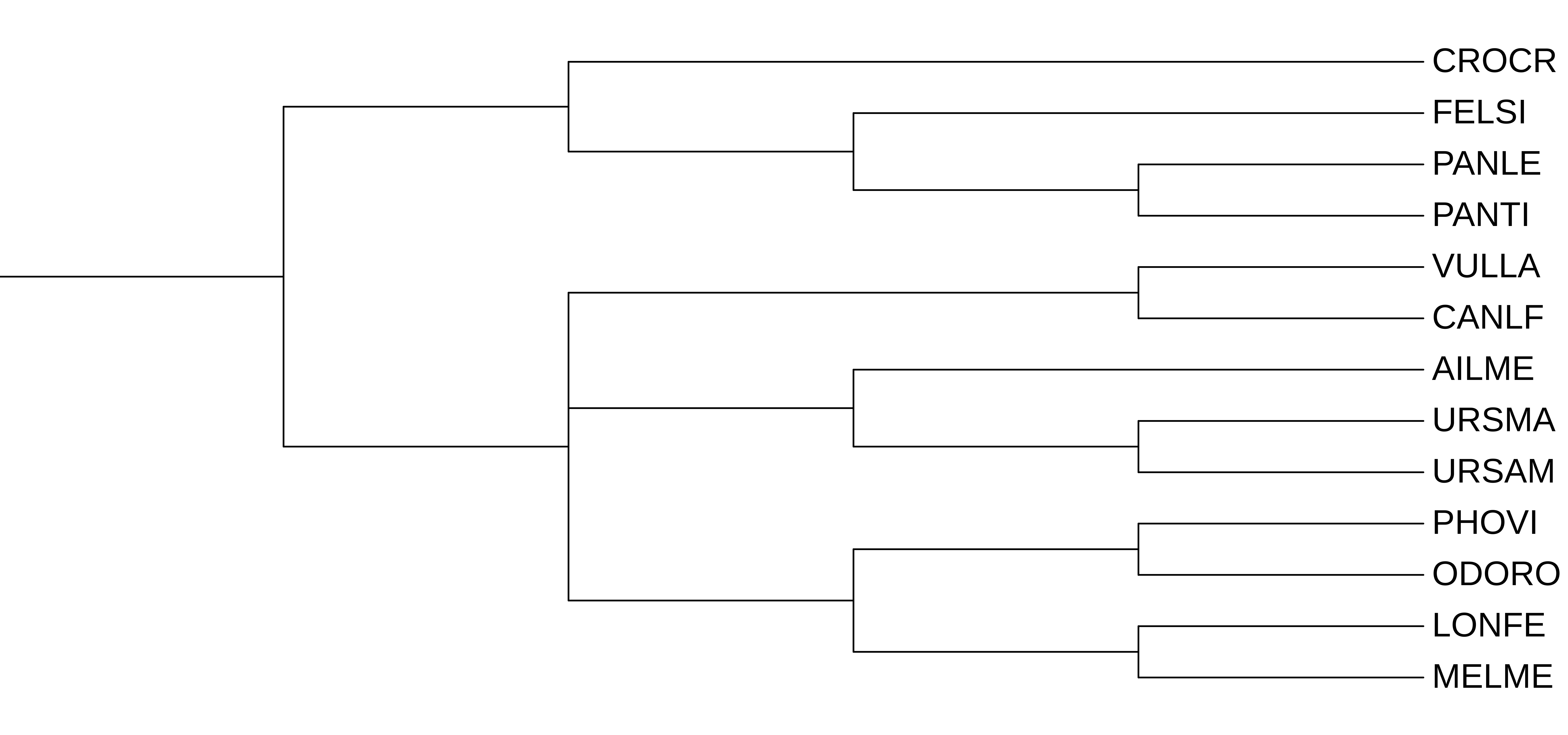
Исходное таксономическое дерево изначально было неразрешённым, программы с разрешением справились. Дерево, построеннное методом максимального правдоподобия (IQ-Tree) отличается от двух других деревьев (MTrev и p-distance): ветвь с Ursus (URSAM и URSMA) располагается более базально, чем ветвь Ailuropoda. Т.е. по сравнению с дистанционными методами, порядок другой. В остальном, все ветви, которые были разрешены на дереве, реконструированном по белкам, идентичны.