Практикум 7. Трансмембранные белки
Задачей данного практикума является сравнение предсказаний трансмембранных участков белка двумя методами: с помощью базы данных OPM (Orientation of Proteins in the Membrane) и сервиса DeepTMHMM.
В качестве исследуемого обьекта был предложен белок с PDB ID 6zhg. Данный белок является кальций-зависимой АТФазой бактерии Listeria monocytogenes serovar 1/2a (strain ATCC BAA-679 / EGD-e). Данный белок локализуется на плазматической мембране и, будучи АТФазой, использует энергию гидролиза АТФ для перекачки ионов кальция против градиента концентрации наружу (в периплазму). Uniprot AC — Q8Y8Q5.
Сначала проанализируем информацию о трансмембранных участках белка 6zhg в базе данных OPM. Координаты трансмембранных участков белка, приведенные в OPM: 1(57-75), 2(76-92), 3(240-264), 4(273-297), 5(680-701), 6(709-727), 7(756-776), 8(782-803), 9(819-840),10(850-874). Как можно заметить, в базе данных OPM находятся 10 предсказанных трансмембранных участков, являющиеся альфа-спиралями. Рисунок исследуемого белка представлен на рис. 1.
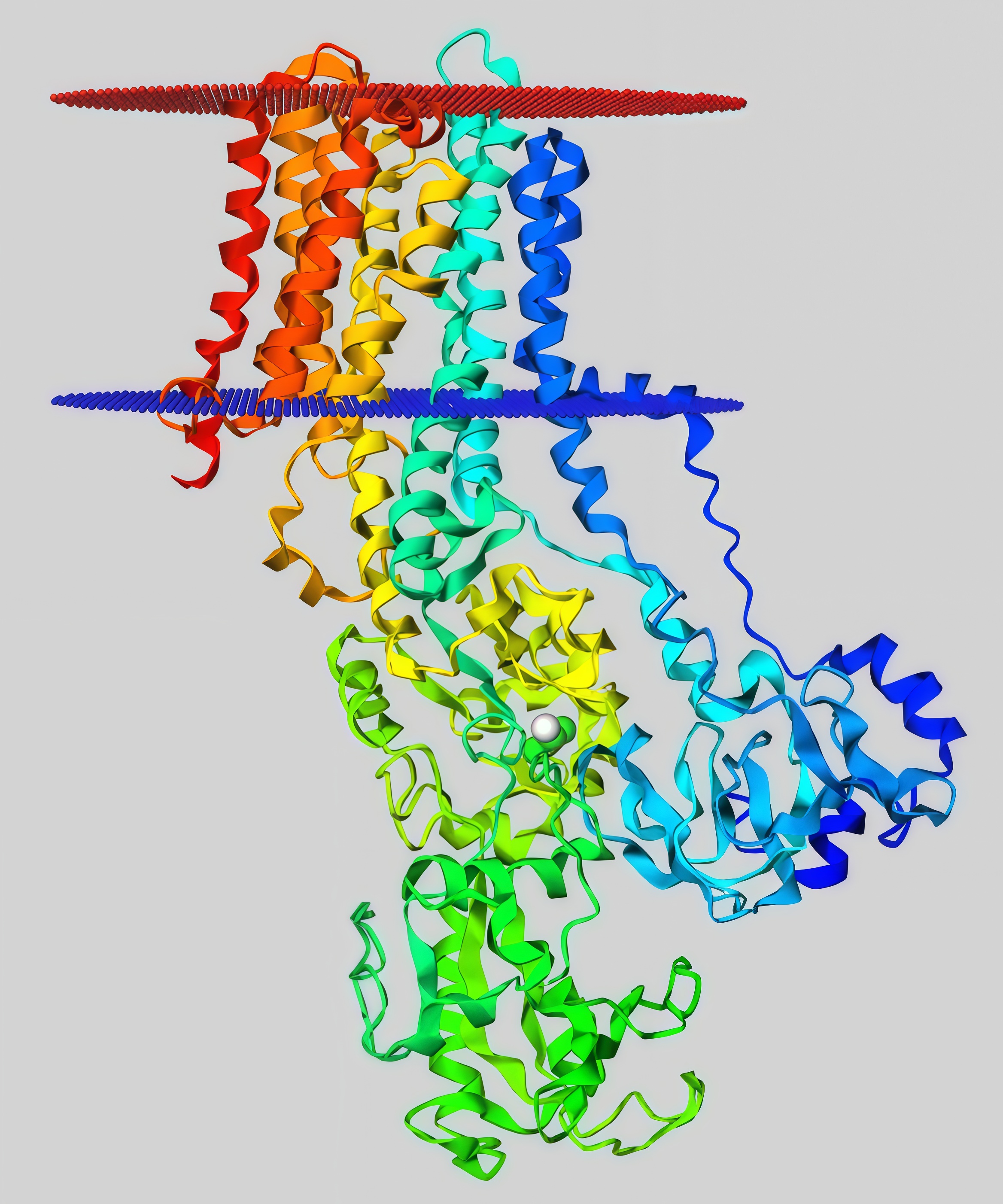
Далее проанализируем структуру белка с помощью сервиса DeepTMHMM. Последовательность белка былв а взята с UniProt. Результат выдачи программы изображен на рис. 2.
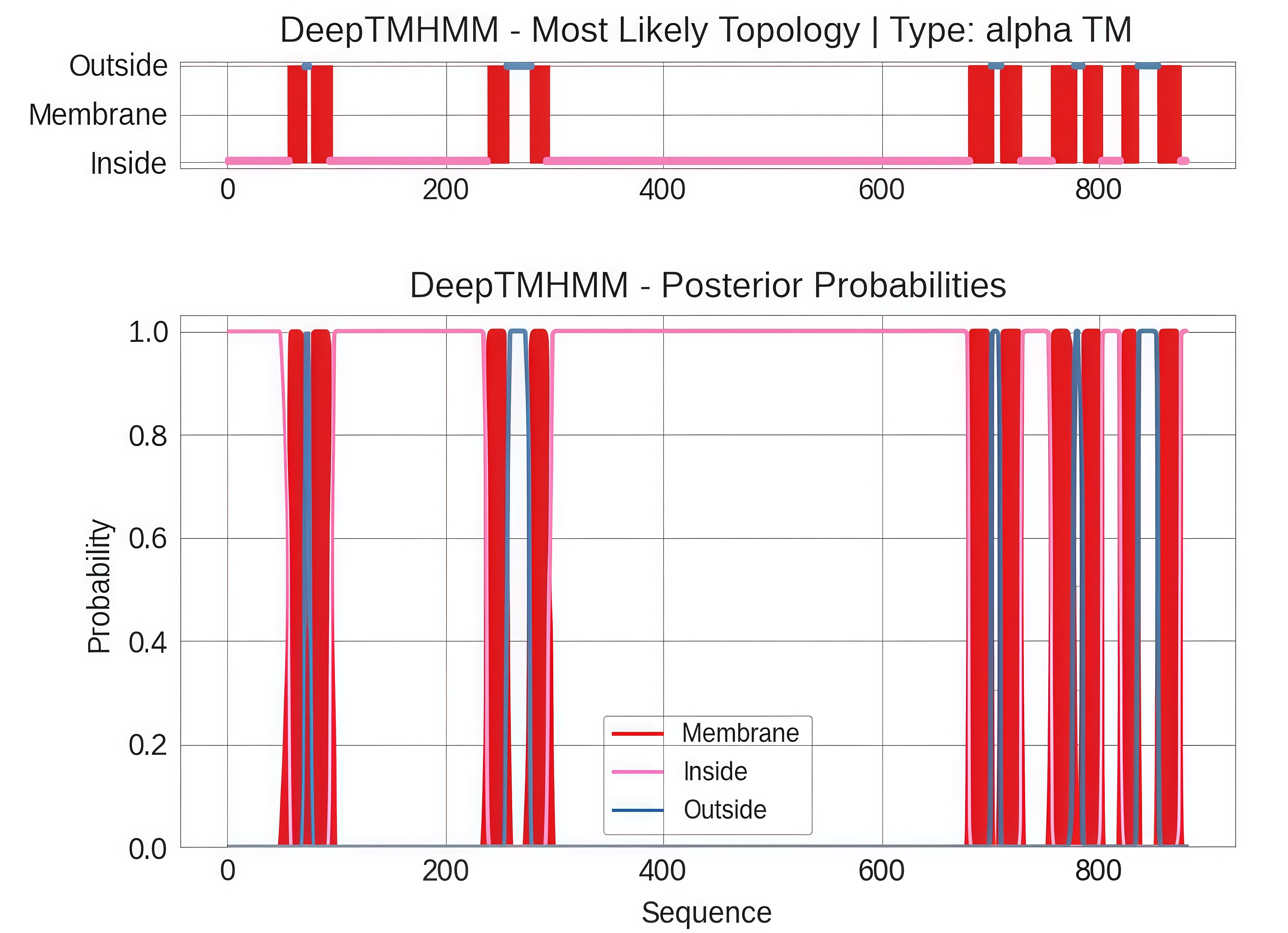
Проанализируем результаты предсказаний этих двух сервисов. В таблице 1 представлены полученные данные предсказанных трансмембранных участков.
| Трансмембранный участок | OPM | DeepTMHMM |
|---|---|---|
| 1 | 57-75 | 57-72 |
| 2 | 76-92 | 77-95 |
| 3 | 240-264 | 239-257 |
| 4 | 273-297 | 279-294 |
| 5 | 680-701 | 681-701 |
| 6 | 709-727 | 710-728 |
| 7 | 756-776 | 757-777 |
| 8 | 782-803 | 785-802 |
| 9 | 819-840 | 820-835 |
| 10 | 850-874 | 854-874 |
Если посмотреть на таблицу, видно, что результаты двух методов очень похожи. Оба предсказали одинаковое количество трансмембранных спиралей — десять. Ни одну из спиралей ни один метод не пропустил.
Границы спиралей немного отличаются — в среднем на 2–4 аминокислоты, но это небольшая разница. В целом участки, которые оба метода считают трансмембранными, перекрываются. Можно сказать, что результаты хорошо согласуются друг с другом и значимых расхождений нет.